预约演示
更新于:2026-04-05

Nanjing Tuge Medical Technology Co., Ltd.
更新于:2026-04-05
概览
关联
100 项与 南京图格医疗科技有限公司 相关的临床结果
登录后查看更多信息
0 项与 南京图格医疗科技有限公司 相关的专利(医药)
登录后查看更多信息
9
项与 南京图格医疗科技有限公司 相关的新闻(医药)2026-03-19
免费医学论文下载-乳腺细胞中GRHL2的机制性解离及PR转录共调控
玛琳·T·阿茨,安娜·诺丁,克劳迪奥·坎图,安东尼乌斯·L·范·博克斯特尔,蕾妮·范·阿梅隆根
发布日期:2026年3月17日
摘要
基因表达由复杂的转录网络控制,其中转录因子及其对应的增强子整合发育和环境信号。孕酮受体(PR)是一种激素激活的转录因子,对乳房发育和生理至关重要,但它如何与染色质及谱系特异性辅因子相互作用尚不清楚。通过无偏的方法,我们鉴定了上皮转录因子颗粒头样2(GRHL2)是激素响应性乳腺癌细胞PR活性的关键共调控因子。我们表明GRHL2与PR的相互作用与孕激素无关。在孕激素刺激下,GRHL2和PR都会被招募到目标基因的远端增强子元件。此外,结合GRHL2和PR的元件通过染色质环路进行空间连接,调控共享靶点。这些发现揭示了一种此前未被发现的机制,即GRHL2和PR通过染色质结合和三维基因组结构修饰协调基因调控,使GRHL2成为类固醇激素受体功能的关键调节因子。
作者简介
基因表达受到调控网络的严格控制,其中转录因子整合了发育和环境信号。激素是这类信号中的重要类别。在乳腺组织中,孕酮激素对正常发育和功能至关重要。孕酮结合其受体——孕酮受体,这是一种调节孕酮响应基因活性的DNA结合蛋白。然而,孕酮受体是否以及如何与谱系特异性辅因子协同调控基因表达,至今仍未完全明了。本研究中,我们确认GRHL2是激素响应型乳腺癌细胞孕酮受体的关键共调控因子。我们发现,这两种蛋白即使在没有激素刺激的情况下也会相互作用。在孕酮暴露时,这两种蛋白都会被招募到调控共享目标基因的调控区。重要的是,我们证明这些调控区域通过长距离DNA环路物理连接,实现基因表达协调。我们的发现共同为激素驱动的基因调控提供了新的见解,并强调GRHL2是乳腺细胞中孕酮受体功能的重要贡献者。
数据
Table 1Fig 1Fig 2Fig 3Fig 4Fig 5Fig 6Table 1Fig 1Fig 2Fig 3
引用: Aarts MT, Nordin A, Cantù C, van Boxtel AL, van Amerongen R (2026) 乳腺细胞中GRHL2的机理性解离及PR转录共调控。PLoS Genet 22(3): e1012088。 https://doi.org/10.1371/journal.pgen.1012088
编辑: 莫妮卡·P·科莱亚科沃,美国哈佛医学院
收到: 2025年12月10日;接受: 2026年3月9日;发布日期: 2026年3月17日
版权所有: © 2026 Aarts 等。这是一篇开放获取文章,根据知识共享署名许可协议(Creative CC Attribution License)发布,允许在任何媒介中不受限制地使用、分发和复制,前提是必须注明原作者和来源。
数据可用性: 所有相关数据均包含在手稿及其支持信息文件中。原始数据可通过开放科学框架获取,时间为 https://osf.io/9uqsw。
资金来源: RvA感谢荷兰科学研究组织(OCENW)的资助。KLEIN.169 + NWO ALW VIDI 864.13.002。CC感谢Cancerfonden(21 1572 Pj和24 3487 Pj 01 H)、瑞典研究理事会、Vetenskapsrådet(2021–03075和2023-01898)、Additional Ventures(SVRF2021-1048003)、林雪平大学、Joanna Cocozzas基金会的支持。CC是Wallenberg分子医学(WCMM)和SciLifeLab的会士,并获得Knut和Alice Wallenberg基金会的慷慨资助。MTA感谢对Claudio Cantù实验室进行CUT&RUN实验的研究访问的资金支持,资金来自Landelijk Netwerk voor Vrouwelijke Hoogleraren(LNVH,2024/2025年女性生物学进步基金)和Genootschap ter bevordering van Natuur-, Genees- en Heelkunde。资助方在研究设计、数据收集与分析、发表决策或手稿准备中没有参与。
利益冲突: 作者们宣称不存在竞争利益。
简介
基因表达受到复杂的转录网络严格调控,其中DNA结合转录因子(TFs)起着核心作用。这些网络通过整合细胞内在的发育线索和外在环境信号,决定基因何时何地表达[1]。TFs结合调控DNA元件中不同的基序,调节转录输出[2–4]。TFs不单独作用,而是以组合组装形式工作,并加入额外的转录因子、辅因子和染色质重塑因子。这种分层调控结构确保不同基因表达项目以细胞类型和情境特异性方式执行,使得专门化的细胞身份在整个发育过程中出现,并在成年组织中得到忠实维护[5,6]。
类固醇激素受体是一类独特的转录因子,其特点是作为配体激活受体和基因表达的直接调节者。与许多具有固定性DNA结合活性的转录因子不同,类固醇受体功能由特定激素的存在外在调控。配体结合后,这些受体在细胞核中积累,并动态地与染色质上的激素反应元件结合,调控转录程序[7]。
这一类受体包括雌激素受体(ER),它具有独特的DNA结合基序,以及3-酮类固醇受体,它们共享共识序列:孕酮受体(PR)、矿物皮质激素受体(MR)、糖皮质激素受体(GR)和雄激素受体(AR)。ER和PR由卵巢激素激活,是产后乳腺组织发育的关键调控因子[8–10]。在该组织中,它们几乎完全在一类腔内细胞中表达,称为成熟腔内细胞或激素感知细胞。鉴于ER在激素依赖性乳腺癌中的作用(及其靶向性),大多数注意力都集中在解决ER的信号机制上。PR信号的分子机制尚不完全明了,但它调控了多条细胞内在和副分泌信号通路。这些通路促进局部增殖和基底膜重构[11],进而支持妊娠期间导管的生长、侧支和肺泡生成[10]。因此,PR对乳腺发育和生理至关重要,抗孕激素也被积极从乳腺癌预防和治疗的角度探讨[12]。
类固醇受体如ER和PR并非孤立作用,而是在涉及额外相关蛋白的复杂调控网络中发挥作用。其中,先锋因子(一类能够调节染色质可及性)的转录因子[13],越来越被认可为类固醇受体活性的关键协调控因子,尤其是在激素依赖性癌症中[14]。例如,ER与FOXA1和GATA3等先驱因子合作,促进其目标基因的转录激活[15–20]。相比之下,公关在类似互动中的程度仍不十分理解。Grainyhead-like 2(GRHL2)最近被认为是激素受体阳性癌症(包括乳腺癌)中的潜在先驱因子[21]。然而,迄今为止几乎所有研究都聚焦于GRHL2在内质网和雌激素信号传导中的作用,其在PR和孕激素介导调控中的作用尚未深入探讨[22–26]。
本研究中,我们鉴定并剖析PR与GRHL2(GRHL蛋白家族成员)之间的功能转录相互作用。该家族包括三种进化保守的先驱转录因子(GRHL1、GRHL2和GRHL3),在上皮细胞中发挥重要作用[27,28]。它们共享高度保守的DNA结合结构域,并表现出显著的结构同源性[29,30]。尽管有这些相似之处,GRHL家族成员展现出独特的时空表达模式,并执行独特的上皮转录程序,支撑其特定的生物功能。
本文结合基因组学、转录组学和蛋白质组学方法,首次对人类乳腺癌细胞中PR和GRHL2的协调转录活性进行了机理性剖析。我们表明PR和GRHL2可以独立于孕酮相互作用,并且在孕酮刺激下常常共占增强子元素。此外,GRHL2 是调控一组 PR 靶基因所必需的。染色质环路分析进一步揭示了共享(即同一DNA元素)和不同(即线性分离的DNA元素)PR和GRHL2结合事件如何在三维染色质空间中长距离收敛,调控共同靶点。我们的发现共同揭示了由GRHL2和三维基因组结构塑造的新PR基因调控层。
选举结果
GRHL2与PR以孕酮无关的方式物理相互作用
为了在无偏载人机中鉴定GRHL2的核相互作用体,我们在T47DS细胞中进行了内源蛋白(RIME)快速免疫沉淀质谱(RIME)[31](图1A)。在剥离血清、非激素刺激条件下,我们鉴定出2352个GRHL2相关蛋白,包括若干此前报道的核相互作用物,如FOXA1 [18]、KMT2C/D (MLL3/4) [32]、GRHL1 [27,33](图1B)。在这2352个相互作用体中,共有103个被标记为转录因子或染色质关联/修饰蛋白,基于Panther分类系统[34]。我们通过MaxQuant蛋白识别分数对这些蛋白质进行了排名,以识别并突出高置信度候选者(图1C)。有趣的是,得分最高的几个相互作用体,如CTBP1、MTA2、SMARCC2、SMARCD2、CHD3和PHF6,都参与染色质可及性和重塑,这符合GRHL2作为染色质可及性先驱因子和调节因子的既定功能[28](见图1C)。
缩略图 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图1。 对GRHL2相关蛋白的RIME分析显示,GRHL2-PR的相互作用与孕酮无关。
A)内源性蛋白快速免疫沉淀质谱(RIME)[31]方案的示意概述,该方案用于识别激素耗竭和孕激素处理条件下的GRHL2相互作用体。B)火山图,展示激素耗竭条件下GRHL2 RIME与IgG对照组的结果。每个灰色点代表质谱中识别的单一蛋白质。灰色虚线表示Log2FC(-3,3)和-Log10(p值)截止值(0.05)。共有2352种蛋白质符合这些标准,因此被鉴定为GRHL2相互作用物。红色高亮点为一些此前报道的GRHL2互助体示例[18,27,32,33,35]。C)根据Panther分类系统,呈现103个GRHL2相互作用体,作为转录因子或染色质关联/修饰蛋白过滤的词云[34]。蛋白质名称的大小和颜色代表基于MaxQuant蛋白识别得分(Andromeda分数和)对已识别相互作用的置信度,反映了蛋白质检测的相对置信度。D)在激素耗竭及PR激动剂R5020刺激条件下4小时1 nM相互作用的共免疫沉淀法西墨迹验证。西部印迹显示GRHL2和PR,A和B异构体,输入蛋白和免疫沉淀样本。E)火山图,展示GRHL2 RIME在激素耗竭与4小时1 nM R5020治疗条件下的结果。每个灰色点代表质谱中识别的单一蛋白质。灰色虚线表示Log2FC(-3,3)和-Log10(p值)截断值(0.01)。只有2个蛋白(1个缺失,1个增加)符合这些标准,并被鉴定为高置信度的孕酮依赖性GRHL2相互作用物。蓝色高亮点表示失去GRHL2的蛋白质,红色高亮点表示获得GRHL2结合的蛋白质。
https://doi.org/10.1371/journal.pgen.1012088.g001
出乎意料的是,PR成为这些剥离血清条件下最强健的GRHL2相互作用体之一,表明两者之间存在激素独立关联(见图1B-C)。我们通过在激素剥离载体处理和激素剥离的R5020(PR激动剂)处理的T47DS细胞中共同免疫沉淀验证了该相互作用,确认GRHL2–PR相互作用未受孕激素刺激影响(见图1D)。有趣的是,我们发现GRHL2主要结合PR的全长且转录活性的同工型PR-B,但不结合PR-A(见图1D)。
由于GRHL2-PR相互作用不依赖于孕酮的存在,我们想知道孕酮是否以及如何改变GRHL2的相互作用组。因此,我们在合成孕激素R5020处理4小时后,也在T47DS细胞中进行了GRHL2 RIME检测(见图1E)。与未治疗状态的比较显示,仅有少量相互作用受影响。仅有一种蛋白TAB2在孕激素刺激下与GRHL2的相互作用丧失。相反,同样只有一种蛋白CCNB1仅在激素存在时被招募(见图1E)。这些差异性相互作用蛋白未被归类为转录因子或染色质调控因子,迄今文献中尚无与孕酮或PR直接相关性的报道,尽管两者都被认为与乳腺癌有关[36,37]。由于GRHL2-PR相互作用本身尚未被功能性表征,我们后续分析将重点放在这一潜在的转录伙伴关系上。
GRHL2和PR DNA结合的全局定位揭示了增强子位点的共占性
为确定GRHL2与PR的相互作用是否发生在共享基因组位点,我们重新分析了T47D细胞中两份此前已发布的CHIP-seq数据集,分别针对GRHL2[23]和PR[38]。值得注意的是,GRHL2数据集是在剥离血清条件下生成的,因此代表了雌激素和孕激素耗尽条件下GRHL2的结合。PR数据集同样在剥离血清条件下生成,但这里细胞同时被1 nM R5020刺激。在本次分析中,我们识别出46,746个PR峰和28,925个GRHL2峰。其中6,335个位点重叠,占PR的13.5%,GRHL2结合事件总数的21.9%(见图2A)。图2B展示了这样一个GRHL2-PR共享区域的例子。通过热图可视化PR和GRHL2结合在仅PR、仅GRHL2和GRHL2-PR重叠位点的结合,显示最强的PR和GRHL2信号集中在重叠区域,尽管部分GRHL2信号也在最强PR峰被检测到,反之亦然(见图2C-D)。GRHL2和PR信号在定义的重叠峰之外共存的观察表明,它们的功能协作很可能超出了我们分析中严格阈值化的位点(图2C-D)。对PR和GRHL2 ChIP-seq峰的基因组注释显示,PR(~66%)和GRHL2(~57%)位点,包括重叠的PR-GRHL2(~61%)位点,都位于远端基因间或内含子区域的增强子处(见图2E)。值得注意的是,GRHL2-PR重叠区域对应于R5020刺激条件下由H3K27ac标记的活性增强子(见图2F)。GRHL2峰比含PR峰更频繁地位于转录起始位点(TSS)以内(约占所有GRHL2峰的25%,GRHL2-PR共享位点的~17%)<(见图2E)。此外,根据ATAC-seq(图2G)确定,GRHL2–PR重叠区域比仅PR或仅GRHL2的染色质更常与可及染色质相关(图2G)。一致地,siRNA介导的GRHL2敲低改变了GRHL2–PR共享位点的染色质可及性,表明GRHL2有助于维持这些区域的可及性(见图2G)。基序分析确认PR和GRHL2基序在单独峰和重叠峰中均有强烈富集(S1A图)。此外,PR或GRHL2结合区以及GRHL2-PR重叠区被富集为FOXA1基序。此外,TEAD基序在GRHL2结合区(包括GRHL2-PR重叠位点)中特异性富集。这表明FOXA1和TEAD在乳腺组织中作用于与GRHL2和PR相似的调控区域(S1A见图)。
缩略图 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图2。 GRHL2和PR在基因组中共同结合调控区域。
A)维恩图,显示未处理的GRHL2[23]芯片序列与1 nM R5020刺激PR[38]ChIP-seq峰的重叠。如果峰重叠至少1个碱基对,则视为重叠。B)两个PR峰和GRHL2峰重叠的代表性例子。数据在IGV浏览器中进行可视化[39]。NT = 未治疗。C)热图显示未处理的GRHL2结合ChIP-seq信号[23]和1 nM R5020在仅PR、仅GRHL2和GRHL2-PR共占的基因组区域刺激PR[38]。D)信号强度图,显示GRHL2[23]和1 nM R5020在仅PR、仅GRHL2和GRHL2-PR共占基因组位点的累计ChIP-seq信号[38]。E)所有PR、所有GRHL2或GRHL2-PR共享峰的基因组注释,均由ChIPseeker进行[40,41]。位点被注释为5'UTR、先驱子、第一外显子、其他外显子、第一内含子、其他内含子、3'UTR内含子、远端基因间区及下游。推动器区域分为三个子类别,定义为:< TSS的1 kb、1-2 kb的TSS或2-3 kb。F)信号强度图,显示H3K27ac在仅PR、仅GRHL2和GRHL2-PR共占基因组位点30分钟内,R5020刺激T47D细胞的累计ChIP-seq信号[42]。G)信号强度图,显示siControl和siGRHL2 T47D细胞在仅PR、仅GRHL2和GRHL2-PR共占基因组位点的累计未处理ATAC信号[43]。
https://doi.org/10.1371/journal.pgen.1012088.g002
接着我们询问孕酮是否以及如何调节GRHL2染色质结合。为深入了解此类结合动态,我们在激素缺乏T47DS细胞中,在未刺激和孕激素刺激条件下对GRHL2和PR进行了CUT&RUN分析。在无激素刺激且血清剥离条件下,我们鉴定出7,039个GRHL2峰,而在4小时R5020处理后识别出5,520个GRHL2峰(见图3A)。其中只有713个地点重叠。此外,R5020刺激下GRHL2信号显著增强,表明GRHL2染色质结合在R5020刺激下既重新分布又增强(见图3A)。这种效应不太可能仅仅通过GRHL2蛋白水平的增加来完全解释,因为4小时的R5020处理仅略微提升了GRHL2蛋白水平,最多增加了20%(且统计学上无显著意义)(S2A-B图)。对于PR,我们在R5020刺激4小时后识别出3033个峰值。重叠GRHL2和PR峰显示,GRHL2和PR结合位点仅在R5020处理条件下重叠(158位点,图3B,S1B-S1C)。 对这些位点的基序分析确认了PR和GRHL2基序的富集,如预期(图3C)。鉴于PR和GRHL2在孕酮存在和缺失时均生化相互作用(图1),这表明PR的活化促进GRHL2对孕酮反应性染色质元件的招募。
缩略图 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图3。 CUT&RUN揭示黄体酮刺激后的GRHL2重分布。
A)显示CUT&RUN GRHL2信号在未处理且4小时1 nM R5020刺激条件下的状态,分布于激素耗竭状态(GRHL2缺失)、激素枯竭和R5020刺激条件下结合GRHL2(GRHL2保守)或GRHL2结合于R5020刺激条件下(GRHL2增益)的站点。B)热图显示GRHL2在未处理且4小时1 nM刺激条件下的CUT&RUN信号,以及仅PR时GRHL2和4小时1 nM R5020刺激条件下的PR信号,GRHL2在R5020刺激条件下结合,GRHL2在R5020刺激与PR共占CUT&RUN峰值时表现。C)通过HOMER基序分析确定,所有未处理的GRHL2峰、所有R5020处理的GRHL2峰、所有R5020处理的PR CUT&RUN峰,以及所有GRHL2处理后的R5020和PR共占CUT&RUN峰中富集的前5个转录因子基序[44]。
https://doi.org/10.1371/journal.pgen.1012088.g003
将我们的CUT&RUN信号绘制在图2中识别的GRHL2结合峰和GRHL2-PR共享ChIP-seq峰上,也证实了这些位置GRHL2结合依赖性的增加(S1D图)。在未处理条件下观测到的CUT&RUN GRHL2信号虽然强度有所降低,但也与GRHL2结合和GRHL2–PR共享的ChIP-seq峰有大量重叠。值得注意的是,我们在R5020刺激条件下的PR切断和运行信号不仅在PR束缚和GRHL2-PR共享ChIP-seq峰处富集,也在仅GRHL2的ChIP-seq峰处得到浓缩。这些综合观察表明,出于某种原因,T47DS中R5020刺激的GRHL2切断与运行状态与此前报告的T47D未刺激GRHL2 ChIP-seq数据相呼应。
综合来看,PR和GRHL2可以独立结合DNA,但也可能在增强子区域重叠。此外,在孕激素刺激下,GRHL2染色质结合会被强化和重新分布。这支持了PR和GRHL2协同协同进行激素依赖转录调控的模型。
GRHL2和PR共同调控参与乳腺发育的部分基因
接下来,我们试图识别由GRHL2和PR调控的转录程序。为此,我们通过稳定的shRNA介导敲低GRHL2(S2A-B图)生成了T47DS细胞,并对野生型和GRHL2敲低T47DS细胞进行了RNA测序,分别用R5020进行4小时或R502024小时处理。主成分分析(PCA)显示,97%的基因表达变异由R5020刺激(PC1)或GRHL2敲低(PC2)解释,证实了对实验条件的强健转录反应(S2C见图)。为识别直接且持续的GRHL2与PR共调基因,我们基于三项标准进行了严格筛选:1)R5020处理4小时后基因表达差异,2)R5020处理24小时后基因表达差异显著,3)GRHL2耗竭后R5020转录反应显著改变(见图4A)).应用这些标准,我们识别出298个同时受PR和GRHL2调控的基因(见图4B)。基因本体富集分析识别出参与信号转导和细胞过程的基因,以及包括腺体发育在内的若干发育过程(见图4C)。我们验证了qRT-PCR对选定目标基因(包括GRHL2本身、IGFBP5和TGFB2)的表达变化(见图4D)。这些结果共同揭示了大量基因由GRHL2和PR共同调控,证实了它们在激素响应型乳腺癌细胞中的共调作用。
缩略图 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图4。 GRHL2和PR共同调控参与乳腺发育的靶基因。
A)野生型(WT)T47DS细胞及shRNA介导的GRHL2基因降(shGRHL2)T47DS细胞,在1 nM R5020刺激24小时后,体体RNA测序过程的概览,以及选择GRHL2和PR共调基因的标准。B)对WT和shGRHL2 T47DS细胞的体量RNA测序数据进行热图,该细胞被1 nM R5020刺激,持续4小时或24小时。热图显示了根据(A)中列出的标准选择的298个基因的无监督聚类和表达变化。表达式值以n=3次重复时的z分数表示。NT = 未治疗的剥离血清状态,T = 处理过的状态。C)点阵图,显示对298个选定的GRHL2和PR共调基因进行Go项富集分析。富集分析和图生成使用Clusterprofiler完成[49]。D)qRT-PCR数据条形图,显示WT或shGRHL2 T47DS细胞中,1 nM R5020处理4小时后GRHL2、IGFBP5和TGFB2的平均相对表达。参考基因:YWHAZ。数据点:n=2/3个生物复制体的个别值,以平均重叠变化为对照标准化。P值采用双因子方差分析计算,随后进行未校正费舍尔最低显著差异检验。
https://doi.org/10.1371/journal.pgen.1012088.g004
我们进行了首次探索性分析,以评估由GRHL2和PR共调控的298个基因的潜在临床相关性。为此,通过cBioPortal下载了METABRIC(乳腺癌分子分类国际联盟)队列的临床和转录组数据,该队列包含1980个原发性乳腺肿瘤[45–48]。其中940个肿瘤被归类为PR阴性,1,040个被归类为PR阳性。事实上,分配的PR状态与PGR mRNA表达水平对应(S3A见图)。值得注意的是,PR阴性和PR阳性肿瘤之间的GRHL2表达无差异(S3B图)。
随后,我们计算了GRHL2/PR综合特征评分,并根据中位数将肿瘤分为高特征组和低特征组。Kaplan–Meier分析显示,高特征表达患者的总体生存率显著降低(见S3C图),并经多变量Cox回归(调整年龄和肿瘤分期)证实了这一关联(HR = 1.055,95% CI 1.030–1.080,p = 1.1 × 10 ⁻ ⁵)。 反直觉的是,PR阳性肿瘤的特征评分显著低于PR阴性肿瘤(S3D图)。由于低签名评分与生存率提升相关,我们使用多变量Cox模型及交互项测试了签名的预后影响是否因PR状态而异。相互作用无显著性(HR = 1.038,95% CI 0.976–1.103,p = 0.24),表明较高的特征表达与PR阳性和PR阴性肿瘤的较差结局相关。 由此我们初步得出结论,虽然GRHL2/PR特征与较差预后有关,但这与PR状态无关。然而,重要的是要注意,本分析属于探索性质。原发肿瘤的功能性PR信号难以直接评估,细胞系模型可能无法完全重现肿瘤生物学。因此,还需要进一步验证和分层分析,以进一步评估乳腺癌患者PR/GRHL2评分的预后价值。
染色质环连接GRHL2和PR位点与远端目标基因
尽管我们对三维基因组组织的理解取得了重大进展,但功能上将增强子与其目标基因连接仍具挑战性[50]。在大多数研究中,增强子被分配到最近的基因,尽管实际上33–73%的增强子并不一定调控其最近的基因[51–53]。这很重要,因为PR以及许多其他转录因子经常与距离其真实相关TSSs在30 kb到1 Mb之间的远端增强子结合[54,55]。高分辨率染色质构象捕捉技术——如Hi-C、5C、ChIA-PET和HiChIP——能够识别对转录调控至关重要的长程染色质相互作用[50]。
基于此,我们试图物理连接基因组中的GRHL2和PR位点(由ChIP-seq,见图2)与它们调控的基因(由RNA-seq识别,见图4)。我们推断,如果GRHL2或PR位点参与特定基因的调控,它应当环路到该基因的TSSs。为验证该假设,我们使用了之前发表的PR HiChIP数据集,该数据集使用T47D细胞获得[38]。HiChIP是Hi-C的延伸,通过富集由感兴趣的转录因子或组蛋白修饰结合的DNA相互作用,捕捉蛋白质特异性染色质环。每个染色质环包含两个锚点,分别位于两端,代表通过三维染色质环路被带到接近的相互作用DNA区域。PR HiChIP在R5020刺激30分钟后,捕获了7,076个无刺激PR染色质环,以及9,591个在一个或两个锚点处发生PR染色质环(图5A)。其中仅有987个环重叠,显示PR介导染色质在R5020刺激后30分钟内发生显著重连(图5A)。
缩略图 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图5。 对HiChIP、ChIP-seq和RNA-seq的整合分析揭示了功能性的GRHL2–PR环。
A)维恩图,显示未处理(T0)条件下PR HiChIP环路与30分钟10 nM R5020处理状态(T30)之间的重叠情况。数据重绘(即Zaurin等人[38]B)的被调用环数,甜甜圈图显示了GRHL2和PR调控基因的转录起始位点(TSS)比例,这些位置与先前发表的PR HiChIP锚点重叠[38]。在通过RNA-seq识别的298个GRHL2和PR调控基因中,有79个基因具有与HiChIP锚点重叠的TSS。剩余219个基因的TSS与HiChIP锚点不重叠。C)通过染色质环路可视化GRHL2和PR峰如何汇聚ARF6基因启动子,显示PR ChIP-seq [38]峰、GRHL2 ChIP-se序列[23]峰和PR HiChIP环[38],直接锚定于GRHL2/PR调控的TSS。锚点按GRHL2和PR占用率着色,如右下角图例所示,没有GRHL2、PR ChIP-seq信号或带注释TSS的锚点被定义为“其他”。基因TSS用灰色条高亮显示。数据在IGV浏览器中进行可视化[39]。D)甜甜圈图,展示了HiChIP[38]锚点占用率,分类为与GRHL2峰值、PR峰值、TSS或这三者的组合重叠。包含的292个锚点(146个环中每个两个)与79个GRHL2的TSS和PR调控基因相关,这些基因与HiChIP[38]锚点重叠。E) 定义为与GRHL2、PR、GRHL2 + PR ChIP-seq峰或其他在146个选定HiChIP [38]环路对对面锚点重叠的锚点频率的可视化表示。这121个环路被选中至少有一个锚点具有PR ChIP-seq峰值。线条的颜色和粗细代表出现频率。
https://doi.org/10.1371/journal.pgen.1012088.g005
接下来,我们将PR HiChIP数据与GRHL2及PR ChIP-seq和RNA-seq数据整合。这里,我们使用了之前发布的 ChIP-seq 数据,而非新生成的 CUT&RUN 数据集,因为 HiChIP 在方法论上与 ChIP 更为相似,因此更有可能有效整合。首先,我们从RNA-seq分析中提取了全部298个GRHL2-PR共调控基因,评估其TSS是否与至少一个HiChIP环的锚点重叠。通过该方法,我们鉴定出79个基因在转录上受GRHL2和PR调控,且在其TSS附近或附近也拥有PR HiChIP环锚点(图5B)。我们共识别出146条直接连接79个GRHL2和PR调控基因的环路(图5B-5C)。这些环路长度可达500kb,大多数跨度为50–100kb(S4A见图)。随后我们想知道GRHL2和PR是否能在这146个环的锚点被探测到。因此,我们对GRHL2和PR ChIP-seq数据进行了比对,以评估它们在每个锚点的占用情况。对于所有146个环路,我们根据是否存在GRHL2和/或PR ChIP-seq峰和/或TSS对相关的292个锚点进行了分类(见图5C,5D)。 在注释锚点中,26%在GRHL2和PR之间共享(~相较整个ChIP-seq数据集富集为两倍,见图2B),其中14%位于或接近TSS。
另有29%仅含有PR峰,其中15%位于或靠近TSS,11%仅含有GRHL2峰,其中2%位于或接近TSS(见图5D)。值得注意的是,21%的环锚属于“其他”类别,意味着它们缺少GRHL2、PR或TSS注释(见图5D)。我们假设这些锚点可能被参与GRHL2和PR靶基因联合调控的其他转录调控因子占据。为探讨这一可能性,我们专门在这些位点进行了基序富集分析(S4B图)。该分析未发现此前与乳房有特异关联的转录因子。然而,我们观察到STAT3的显著富集,这一因子在GRHL2 RIME中也被观察到(图1C),表明STAT因子可能参与GRHL2和PR发挥功能的三维调控情境(S4B图)。
为进一步探讨GRHL2与PR在基因调控中的协同功能,我们分析了它们在PR HiChIP环对向锚点的占有情况(见图5E)。这里,我们只包含了至少在两个锚点中有一个有PR ChIP-seq峰值的环路,因此总共选择了121个环路。其中,~56%至少含有一个锚点同时含有GRHL2和PR ChIP-seq峰,表明GRHL2-PR介导基因调控最常见的方式可能是GRHL2和PR与至少一个调控元件的共结合(见图5E)。尽管如此,GRHL2与PR占有的其他组合也被观察到,表明不同结合GRHL2和PR的元件可以通过三维染色质结构趋同,共同调控基因表达(见图5E,S4C)。 此外,一些PR、GRHL2或GRHL2-PR重叠的峰不仅与基因启动子建立了直接连接,还与额外的GRHL2和PR(以及其他转录因子)结合位点相互作用(S4C见图)。
GRHL2和PR转录共调的整合模型
CTCF和内腭介导的环路已被广泛认可为促进长程增强子-启动子相互作用的关键机制[56]。在我们的RIME中,我们发现GRHL2与多个Cohesin复合组分及相关调控因子相关(S5A图)。此外,公开的CTCF [42]和RAD21 [42]在未处理和30分钟R5020处理条件下的ChIP-seq数据集显示,虽然CTCF结合相对稳定,但RAD21与染色质结合在R5020处理后高度富集(S5B-C 图)。由于TAD边界在R5020存在与否下相对稳定[57],我们假设部分GRHL2/PR/TSS相互作用由CTCF/Cohesin介导的环路介导,从而在GRHL2–PR增强子与其靶启动子之间的空间接近度中起作用。我们推测,在孕酮存在的情况下,RAD21/Cohesin复合物可能与GRHL2一起被招募到染色质中。
综合所有数据,我们提出了一个由GRHL2和PR共调控基因的模型,在缺乏激素刺激的情况下,GRHL2和PR已存在于细胞核内,并能够物理相互作用(见图6,左侧)。在此条件下,PR基本不结合其基因组靶位点,而GRHL2则与不一定与GRHL2和PR共调控靶基因相关的区域结合,然而,它很可能已经动态且在更低水平上与共享的GRHL2/PR位点结合(图6,左侧)。大多数由任一或两项因子结合的基因组靶点和调控元件尚未接近其各自目标基因的启动子(见图6,左侧)。在孕酮存在或实验环境中,R5020刺激时,核内GRHL2和PR的水平会微妙上升,转录活性PR被招募到GRHL2/PR共享且仅PR结合位点。同时,在孕激素刺激下,GRHL2染色质结合会被强化和重组。
缩略图 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图6。 一个展示GRHL2–PR共调控目标基因转录调控的模型。
GRHL2和PR在特定共调控目标基因的调控机制模型。在缺乏激素(左图)的情况下,GRHL2和PR形成一个复合体,GRHL2动态结合于与GRHL2-PR目标基因无关的区域,同时在更低水平下,PR大多不结合染色质。因此,GRHL2和PR不与其靶引导子相互作用。孕酮刺激(右侧)会触发GRHL2和PR被增强子招募,并形成CTCF/内聚蛋白依赖性和独立染色质环路,将由GRHL2、PR或辅因子共结合或单独结合的远端元件与其目标基因连接起来。
https://doi.org/10.1371/journal.pgen.1012088.g006
除了相互结合外,GRHL2和PR还与多种协同因子结合。这导致局部GRHL2和PR浓度极高,这得益于CTCF/Cohesin依赖性和-非依赖性环路,将远端增强子与靶向启动子连接(图6,右)。虽然超过一半的PR环增强子至少在一个锚点上被GRHL2和PR共结合,但不同的GRHL2或PR结合元素也会在启动子上收敛(见图6右侧)。此外,多个增强子位点——由GRHL2和/或PR及其他转录辅因子结合——通过直接或间接环路与基因启动子紧密结合,从而高效转录参与孕激素驱动乳腺组织发育和生理的基因(图6,右侧)。
讨论
本研究为先驱转录因子GRHL2与类固醇激素受体PR协调转录调控提供了机制框架。通过整合T47D和T47DS细胞在未刺激和R5020刺激条件下的蛋白质组学、转录组学和基因组分析,我们提出了一个GRHL2和PR共调控靶基因的模型,在缺乏激素的情况下,GRHL2和PR形成一个预组装的核复合体,并与其他染色质修饰因子相关(见图1A-D和图6, 左)。在孕酮刺激下,GRHL2和PR在特定增强子处富集,启动激素依赖性的染色质环路,使远端调控元件(或由GRHL2和PR共结合,或由任一因子单独结合)与其目标基因启动子接触,激活对乳腺发育和生理至关重要的转录程序(图6,右侧)).因此,虽然整体核GRHL2蛋白相互作用组在激素刺激下未发生重大变化(见图1E),但这些发现揭示了一种动态的激素响应调控结构,使乳腺细胞基因表达能够精确时空调控。
利用RIME和共免疫沉淀法,我们鉴定PR在血清脱离条件下是GRHL2的孕酮非依赖性相互作用物。虽然RIME涉及有利于染色质相关蛋白的核富集步骤,但免疫沉淀作用于核裂解液,因此同时捕获染色质结合和可溶性核复合物。因此,在没有配体的情况下观察到的PR–GRHL2相互作用,很可能反映了未稳定结合染色质的核复合物。这与已知配体对稳定PR-DNA结合的要求一致。我们提出PR和GRHL2可能在核质内形成预先存在的复合物,这些复合物在配体刺激下能迅速与染色质结合。与此观点一致,R5020处理后GRHL2结合增强并重新分布,表明预形成的PR–GRHL2复合物可能促进GRHL2快速招募到孕激素响应的基因组区。
GRHL2-PR的相互作用也出现在一项对MCF7和T47D细胞进行PR RIME的研究中[35],但这里显示为孕激素依赖性。尽管两项研究均检测到PR与GRHL2之间的相互作用,但我们的发现在激素依赖性上存在差异。最可能的解释是穆罕默德等人。[35]采用了一种未治疗的状态,涉及含有内源性雌激素和孕酮的全血清培养基,并能模拟生理激素刺激。相比之下,我们的非刺激样本是在剥离血清条件下获得的。此前研究显示,GRHL2可与其他激素受体结合,即内质网[23,25,58]和AR[59]。具体来说,GRHL2增强了内质网和抗逆体依赖的结合及转录活性[25,59]。在前列腺癌细胞中,GRHL2本身是一个AR靶基因[59],类似于我们观察到GRHL2在乳腺癌细胞中是PR靶点[60]。由于GRHL2在雌激素、雄激素和孕酮信号通路中发挥作用,在多个激素受体同时表达和活跃的细胞中,GRHL2的结合可能具有动态分布。控制这种分布的机制尚不清楚。值得注意的是,我们发现在T47DS细胞中,且在缺乏雌激素和孕酮的情况下,GRHL2优先与PR结合,且这种相互作用在孕激素刺激下得以维持或可能增强。结合上述研究观察,我们假设在雌激素存在下,无论是单独存在还是与低水平孕酮同时存在,GRHL2可能更倾向于与内质网结合而非PR。这共同引发了关于GRHL2的DNA结合活性和相互作用组在激素波动条件下如何调控,以及这种调节如何促进激素响应细胞的转录程序的重要问题。
本研究仅简要探讨了哪些额外的转录因子可能参与GRHL2–PR介导的基因调控。尽管如此,我们在PR-、GRHL2-和GRHL2-共享结合位点的RIME和基序分析中,仍鉴定出若干转录因子及其家族。例如,FOXA1在GRHL2、PR和GRHL2–PR共享区域的全基因组分析中,成为富集最强的基序之一(S1A图),同时也是我们PR CUT&RUN数据中富集基序中的典型,这与其在成熟腔体内的核心作用一致[43,61–63]。有趣的是,FOXA1的耗竭被报道会增加增强子位点的PR结合[64],表明FOXA1在某些情况下可能与PR竞争增强子占有率。综合来看,这些观察表明,虽然GRHL2和FOXA1在某些环境下可能合作,但GRHL2与PR的协调活性很可能在很大程度上独立于FOXA1发生。同样,在我们的RIME分析中检测到了GATA3和TRPS1,且在ChIP-seq数据中,GATA基序在仅PR、仅GRHL2和GRHL2–PR共享区域中得到丰富。鉴于GATA3与内质网表达和功能相关[19,20],它可能在协调内质网/PR活性方面扮演类似GRHL2的角色。最后,STAT1、STAT3和STAT6被鉴定为GRHL2的相互作用体,且在ChIP-seq数据中,STAT结合基序在仅PRs、仅GRHL2及GRHL2-PR重叠位点富集。IL/STAT 信号此前已被关联于内质网和 PR 通路[65,66],但据我们所知,本研究是首个将 GRHL2 与 STAT 信号联系起来的证据,值得进一步探讨其潜在的功能相互作用。
我们的CUT&RUN分析显示,当孕酮存在时,GRHL2染色质结合会重新分布并增加。此前未曾报道,但这与GRHL2作为直接PR靶点[60]以及先前研究显示雌激素治疗能促进全基因组GRHL2结合增加[58]相符。有趣的是,我们发现R5020处理后检测到的GRHL2 CUT&RUN峰(未治疗条件下检测不到)与非激素刺激条件下ChIP-seq识别的GRHL2位点重叠(S1D见图)。这种差异可能由原始ChIP-seq实验中残留的激素活性或方法学差异解释:与ChIP-seq不同,CUT&RUN不涉及交联,因此更可能捕获稳定的DNA-蛋白质相互作用。短暂、较弱或间接的相互作用,如动态转录因子如GRHL2和PR,可能只有在稳定(如激素治疗)后才能通过CUT&RUN检测到,而ChIP-seq则可能更容易捕捉这些相互作用。这些方法学和生物学差异也可能解释为何我们的CUT&RUN数据中识别出的GRHL2和PR峰数量比重新分析的ChIP-seq数据集少近两个数量级(见图3B与图2B)。
归根结底,确定单个增强子的精确功能并准确将其与目标基因连接仍具挑战性。这一困难主要源于增强子的位置,它们通常距离其调控的基因相当远,同时它们能够绕过附近和夹杂的基因。尽管如此,绘制增强子与靶基因关系对于理解增强子在正常生物学和疾病中的功能至关重要。在缺乏单独实验验证的情况下,基于染色质构象的方法目前是预测增强子-启动子相互作用的最有效方法。因此,我们利用PR HiChIP数据将GRHL2和/或PR位点与其目标基因连接起来。虽然这种方法比将峰值分配到最近基因更能提供更高的目标分配置信度,但也存在局限性。值得注意的是,我们使用的PR HiChIP数据集是在孕激素刺激后的早期时间点(即30分钟)生成的。虽然这使得最早的GRHL2–PR共调靶点被识别,但额外的时间点将捕捉更广泛的相互作用动态范围,增加可分配靶点数量,并为PR介导的增强子-启动子环路的时间动态提供见解。此外,由于该数据集以PR为中心,它无法捕捉那些不直接涉及PR但可能收敛于相同启动子的GRHL2介导染色质环。因此,我们可能低估了GRHL2调控影响的范围以及GRHL2–PR共调控靶基因的整体分布。然而,分开PR和GRHL2 HiChIP数据集也不理想,因为它们无法直接检测PR和GRHL2重叠锚点。遗憾的是,目前尚未开发出测量两种转录因子蛋白质导向基因组结构的方法。
总之,本研究通过整合基因组学、转录组学和蛋白质组学数据,拓展了我们对乳腺上皮中孕酮信号调控景观的认识。我们发现了GRHL2与PR之间此前未被发现的合作关系,通过动态染色质结合和三维基因组组织协调激素响应基因表达。我们的模型假设,在缺乏激素的情况下,GRHL2和PR会形成复合物,但在这种条件下,它们并不能稳定地结合染色质。孕激素刺激招募GRHL2-PR复合物到增强子,随后形成染色质环,将远端元素与目标基因启动子连接起来。GRHL2、PR或辅因子的共结合或个体结合随后激活关键转录程序。该模型为理解GRHL2–PR介导的基因调控提供了广泛的框架。然而,我们发现每个目标基因最终都由一组独特的远端元素单独或联合结合,这些因子由GRHL2、PR及其他转录因子结合,这些因子环路到其启动子。我们的综合分析强调了这些调控相互作用的复杂性和基因特异性,展示了仅仅两个转录因子相互作用即可产生的复杂性。
研究的局限性
虽然我们的多组学方法提供了激素无关性物理相互作用的证据,支持GRHL2和PR在孕激素刺激下的协调增强子占有,但仍需承认若干局限性。首先,尽管我们展示了PR与GRHL2的共居、染色质环路以及协调转录调控,但GRHL2调节PR依赖增强子活性的具体分子机制仍未解决。特别是GRHL2究竟主要作为先驱因子、共调控因子的支架,还是参与环状形成的结构成分,以及GRHL2是否影响PR结合动力学,需要进一步的机制分析。其次,大部分分析是在T47D(S)细胞中进行的,这些细胞过度表达PR。尽管该细胞系是极少数对PR反应的细胞系之一,能够受控地探究GRHL2/PR的交叉调控,但它并未反映内源性化学计量或生理调控。因此,进一步验证我们在其他细胞系和乳腺(癌症)模型中的发现,对于评估所提出调控机制的普遍性和生物学相关性将非常重要。第三,由于目前只有一种功能良好的GRHL2抗体可用,该抗体被用于所有实验,包括RIME、Western blots和CUT&RUN分析,以及我们重新分析的之前生成的ChIP-seq数据集。尽管经过精心筛选并广泛使用,我们未能通过替代的GRHL2抗体确认数据,也无法正式排除与GRHL1的交叉反应性。最后,仅在mRNA水平评估了GRHL2/PR共调控基因的功能验证。虽然转录组变化稳健且可重复,但由于技术限制,包括缺乏合适的抗体,无法对关键靶点如IGFBP5和TGFB2进行蛋白质级验证。因此,转录变化在蛋白质丰度和下游细胞表型变化中的影响程度仍有待确定。
材料与方法
细胞培养
人类T47DS乳腺癌细胞(由荷兰乌得勒支胡布雷希特研究所Stieneke van den Brink博士慷慨捐赠)和HEK293TN细胞(System Biosciences,#LV900A-1)常规培养在含有GlutaMAX(Gibco,#11584516)的Dulbecco改良鹰培养基(DMEM),并补充10%胎儿牛血清(FBS)(Thermo Fisher Scientific,#11573397)。细胞每3-4天以1:10比例分割,并常规检测支原体。处理后,T47DS细胞在含GlutaMAX(Gibco,#11584516)的DMEM中培养,辅以5%活性炭剥离胎牛血清(Thermo Fisher Scientific,#A3382101)24小时,随后在指示时间内刺激1 nM R5020(Perkin Elmer,#NLP004005MG),同样在剥离血清条件下进行。
T47DS GRHL2 敲击线的生成
为产生慢病毒,5× 10⁶ HEK293TN细胞种子于10厘米的培养皿中。次日,细胞被转染3微克包装载体pCMVDR8.2(Addgene,#8455)、3微克RSV-rev(Addgene,#12253)、3微克VSV-G(Addgene,#12259)和8微克pLKO.1 GRHL2 shRNA载体(RNAi联盟,TRCN0000015812;阿姆斯特丹联合卫理公会Peter Stroeken慷慨赠送)。24小时后,培养基进行更新。转染后48小时采集病毒上清液,通过0.45微米滤纸过滤,并以1:2比例稀释。T47DS细胞在聚苯(1:2,000;默克米利普尔,#TR-1003-G)存在下被病毒上清液感染。孵育24小时后,细胞被切割并用普罗霉素(1 μg/mL,Thermo Fisher Scientific,#A1113803)选拔,以产生稳定的GRHL2敲低系。
内源性蛋白快速IP-质谱(RIME)
RIME分析按照Mohammed等人之前描述的方式进行[31]。简要,6x107每种条件下,T47DS 通过向培养基中加入甲醛(Thermo Fisher Scientific, #28908)至最终浓度为1%,交联8分钟。反应通过将甘氨酸加入至最终浓度0.1 M来淬火。细胞被用冰冷的PBS洗涤两次,辅以蛋白酶抑制剂(Sigma-Aldrich,#P8340,1:500),并通过刮除板块收集。随后通过离心法将细胞沉淀为2,000克,浸泡3分钟,浸泡在4°C,并使用溶解缓冲液LB1(50 mM HEPES-KOH,pH 7.5,140 mM NaCl,1 mM EDTA,10%(vol/vol)甘油,0.5%(vol/vol)天然-40,0.25%(vol/vol)Triton X-100)。随后在4°C旋转5分钟时,再次对LB2进行裂解(10 mM Tris-HCL(pH 8.0)、200 mM NaCl、1 mM EDTA和0.5 mM EGTA)。 随后将样品重新悬浮于LB3中(10 mM 三盐酸(pH 8.0)、100 mM NaCl、1 mM EDTA、0.5 mM EGTA、0.1%(重量/体积)脱氧胆酸钠和0.5%(体积/体积)N-月烯酸盐),并分成三根独立的Eppendorf管,在Bioruptor pico中进行超声波处理。(Diagenode)在4°C下使用30秒的开关循环,持续10个周期。再次将超声波样本合并,加入Triton X-100至最终1%体积,并通过离心清除裂解液。与此同时,Dynabeads(蛋白A、Invitrogen、#10001D)在含有5 mg/ml BSA的PBS中洗涤了四次。在室温下,将5 μg GRHL2抗体(Sigma Aldrich,#HPA004820)和IgG(Santa Cruz,#sc-2027X,作为阴性对照)结合在PBS/BSA溶液中,在室温下共轭1小时。通过超声核裂解液与抗体共轭的珠子混合,并在4°C下旋转培养过夜。次日,用RIPA缓冲液(50 mM HEPES(pH 7.6)、1 mM EDTA、0.7%(重量/体积)脱氧胆酸钠、1%(体积/体积)NP-40和0.5百万LiCl)洗涤,共洗涤十次。对于每个实验条件,三个独立处理的样本被并行处理,代表用于评估可重复性的重复样本。
此后,阿姆斯特丹大学斯瓦默丹生命科学研究所生物分子质谱实验室负责处理和分析。简而言之,输入样本的处理方式如Hughes等人[67]所述。蛋白质浓度通过Pierce BCA蛋白质检测法(Thermo Fisher Scientific, #23227)定量,按照制造商的方案进行,所有样品均一次性还原并烷基化。根据Mohammed等人[31],拉下样品被珠状消化。肽样品使用Ultimate 3000 RSLCnano UHPLC系统(德国格默林根Thermo Fisher Scientific)与TIMS-TOF Pro质谱仪(德国不来梅布鲁克)进行分析。原始数据使用MaxQuant(版本2.6.2.0)处理,胰蛋白酶/P被指定为消化酶,允许最多遗漏两个切割。半胱氨酸的氨甲酰甲基化被设定为固定修饰,甲硫氨酸的氧化则为可变修饰。光谱与人类单蛋白蛋白组数据库进行了检索。MaxQuant IBAQ输出值用于Perseus(版本2.1.3.0)进行下游分析。潜在污染物、仅通过携带一个或多个修饰氨基酸的肽鉴定的蛋白质,以及从诱饵序列中识别出的蛋白质被过滤掉。取值采用Log2变换,且每个实验组缺失一个值的行被丢弃。其他NaN值被从正态分布中替换,三次技术重复实验利用两样本学生t检验和基于置换的假发现率(FDR)修正以识别多重测试中不同条件间表达的蛋白质。采用了FDR<0.05的显著阈值。诱饵蛋白GRHL2具有2折叠富集为3.3且为-Log10(padj)2.2。原始和处理后的RIME数据通过以下渠道公开:https://osf.io/9uqsw/。
共免疫沉淀
在T47DS细胞中共免疫沉淀GRHL2,利用约3个×10⁸细胞完成。细胞在皿上直接用含有蛋白酶抑制剂(Sigma-Aldrich,#P8340,1:500)清洗一次,然后通过刮擦采集。颗粒化细胞被重新悬浮在溶解缓冲液中(50 mM 三盐酸(pH 7.40)、5 mM EDTA、0.25% Triton X-100、10% 甘油、100 mM NaCl)中,并在4°C下培养30分钟,并轻柔旋转。裂解液通过离心法在2000×克、4°C下20分钟清除。 上清液的一小块被保留为整个裂解液控制的输入。剩余裂解液在4°C下与5 μg GRHL2抗体(Sigma-Aldrich,#HPA004820)轮流孵育。次日早晨,加入50微升预平衡的Dynabeads蛋白A(Invitrogen,#10001D),并在4°C下旋转样品1小时。 珠子用裂解缓冲液洗涤三次,结合蛋白通过在洗脱缓冲液中煮沸(50%裂解缓冲液,50%Laemmli缓冲液;Sigma-Aldrich,#38733)在95°C下持续5分钟。随后通过西部印迹分析了洗脱后的蛋白质。
西部污点
西方印迹法如前所述进行[68]。简而言之,一半的免疫沉淀或输入样本被装入10%的SDS-PAG凝胶上。蛋白质通过转印涡轮转移系统(Bio-Rad)转移到0.2微米的硝化纤维素膜上,并用1:1稀释的TBS和Odyssey阻断缓冲液封闭(LI-COR Biosciences, #927–50100)。膜在4°C下过夜孵育,稀释原级抗体于阻断缓冲液中,补充0.1% Tween-20:抗PR(1:1,000,Thermo Fisher Scientific,#MA5–16393,识别PR-A和PR-B)和抗GRHL2(1:2,000,Sigma-Aldrich,#HPA004820)。次日,膜在补充0.1% Tween-20的TBS中洗涤,并在RT下与稀释1:20,000的次级抗体及0.1% Tween-20在TBS中孵育1小时:IRDye 680LT(LI-COR,#926–68022)或IRDye 800CW(LI-COR,#926–32211)。信号检测使用奥德赛Fc成像系统(LI-COR生物科学)完成。
RNA分离、文库制备及RNA测序分析
RNA的分离、处理和RNA测序分析均如前所述[69]。总之,70万个T47DS WT或GRHL2敲低细胞(稳定shRNA)被植入含有DMEM + GlutaMAX(Gibco,#11584516)的6孔板中,并辅以5%含炭的胎牛血清(Thermo Fisher Scientific,#A3382101 年)。电镀后24小时,培养基进行更新,细胞再用1 nM R5020或乙醇(载体对照)处理24小时。按照制造商说明,使用RNeasy Mini Kit(Qiagen,编号#74104)并进行柱上DNA酶消化(Qiagen,RNase-Free DNase Set,编号#79254)进行RNA分离。
为文库制备,使用NEBNext Poly(A)mRNA磁分离模块(新英格兰生物实验室)对1微克总RNA进行了poly(A)选择。RNA测序文库使用NEBNext Ultra II定向RNA文库制备套件和NEBNext多重寡核(Dual Index 引物对;新英格兰生物实验室),遵循制造商的规范。使用配备安捷伦D1000屏幕磁带的2200 TapeStation系统(安捷伦科技)评估了图书馆规模分布。定量工作使用NEBNext库定量套件,在QuantStudio 3实时PCR系统(Thermo Fisher Scientific)上完成。库通过NextSeq 500/550高输出套件v2.5(75周期)在NextSeq 550系统(Illumina)上进行序列(75位元对应单端)。所有图书馆的准备和测序均由阿姆斯特丹大学斯瓦默丹生命科学研究所(Swammerdam Institute for Life Sciences)荷兰基因组服务与支持提供者MAD负责。
原始的FASTQ文件在银河服务器上处理。质量控制使用MultiQC [70]进行,随后用Trimmomatic[71]通过策划的适配器列表对过度代表序列进行裁剪。通过HISAT2对截断读序列比对到人类参考基因组(GRCh38.p14)[72]。映射质量通过SAMtools统计评估,并用MultiQC总结。读取计数使用HTSeq计数[73]获得,并在RStudio(版本2023.06.1)中使用DESeq2进行差异基因表达分析[74]。这些数据已以编号GSE291778存放于NCBI GEO。通过 https://osf.io/9uqsw/ 以下网站,298个GRHL2和PR共调控基因,以及79个由GRHL2和PR转录调控且在其TSS附近拥有PR HiChIP环锚点的基因的Log2fold变异列表。通过Clusterprofiler R包的enrichGO()函数对选定的PR和GRHL2调控基因进行Go项富集[49]。
RNA分离与qRT-PCR
RNA分离和qRT-PCR的操作如前所述[68]。简而言之,按照制造商的方案,使用TRIzol试剂(Invitrogen,#15596018)从T47DS细胞中提取了总RNA。分离的RNA被RQ1 DNase(Promega,#M6101)处理以去除基因组DNA污染。cDNA合成采用SuperScript IV逆转录酶(Invitrogen,#18090200)和随机六聚体(Invitrogen,#N8080127),并加入了RiboLock RNase抑制剂(ThermoFisher,#EO0328)。所得的cDNA样本在qRT-PCR前被稀释了10倍。定量实时PCR使用5台HOT FIREPol EvaGreen qPCR Mix Plus(ROX)(Solis Biodyne,#08-24-00008)在QuantStudio 3实时PCR系统上完成。引物序列列于表1。相对表达水平采用ΔΔCt方法计算,并归一化至YWHAZ[75]及未处理对照样本。
缩略图 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
表1。 用于qRT-PCR的引物。
https://doi.org/10.1371/journal.pgen.1012088.t001
CUT&RUN 低容积尿素(LoV-U)
CUT&RUN LoV-U 的执行方式如 Zambanini 等人所述。[76],并进行了以下修改。每个样本约采集50万个T47DS细胞,使用0.25%胰蛋白酶,并在核提取缓冲液中洗涤三次细胞(20 mM HEPES-KOH(pH 8.2)、10 mM KCl、0.5 mM spermidine、0.05% IGEPAL、20% 甘油和罗氏完全蛋白酶抑制剂无EDTA)中分离细胞核。核颗粒被速冻在异丙基腔室中,并以–80°C储存,等待进一步加工。核被解冻,在核提取缓冲液中洗涤一次,随后结合于平衡的磁性ConA琼脂糖珠(抗体在线,#ABIN6952467)。培养后,核珠复合物在洗涤缓冲液(20 mM HEPES(pH 7.5)、150 mM NaCl、0.5 mM spermidine和罗氏完全蛋白酶抑制剂 EDTA-Free,0.025% 地微素)中洗涤5分钟,然后转移到PCR管中。加入抗体(抗PR(1:100,细胞信号,#8757S)、抗GRHL2抗体(1:100,Sigma-Aldrich,#HPA004820)或兔IgG同型对照(1:100,Invitrogen,#100500C))加入洗涤缓冲液中,并在4°C旋转器上隔夜孵育。次日,样品用洗涤液洗涤五次,然后重新悬浮于pAG-MN缓冲液(含120 ng/样品pAG-MN)中,并在旋转器上以4°C培养30分钟。经过五次洗涤后,消化启动,将珠子重新悬浮在补充2 mM CaCl₂的洗涤缓冲液中,并在室温下培养5分钟,随后在4°C下再培养25分钟。 通过添加250 mM EDTA/EGTA混合物,该反应被阻止。通过加入5 M NaCl并在37°C下孵育30分钟,开始释放片段。收集上清液后,将小珠重新悬浮于1个×尿素缓冲液中(100 mM NaCl,2 mM EDTA,2 mM EGTA,0.5% IGEPAL,8.5M 尿素),进行第二次释放步骤。在室温下30分钟后,尿素释放液与初始上清液结合。样品先用SDS和蛋白酶K处理,随后进行酚:氯仿:异戊醇萃取和乙醇沉淀。文库在Illumina NextSeq 550平台上采用36碱基对序端读段测序,深度为每样本500万至1500万次。
CUT&RUN 数据分析
读取质量通过fastQC评估[77]。读取序列通过bbmap bbdud [78]裁剪,以去除适配器和多重[AT]、[G]和[C]重复序列。读段与hg38基因组配对,配对了蝴蝶结2[79],选项为:–local –very-sensitive local – no-unal –no-mixed -no-discordant –phred33 –dovetail -I 0 -X 500。使用Samtools套件[80]来移除重复和错误配对的读取。Bedtools [81] 用于从 bam 文件中移除映射到 CUT&RUN hg38 嫌疑人列表 [82] 的读取。床图是利用Bedtools genomecov的配对端模式创建的。峰值通过MACS2[83]进行调用,针对窄峰的IgG对照,选项为-f BAMPE和-p 1e-3。CUT&RUN数据已以GSE307203号存入NCBI GEO。
ChIP-seq数据集的再分析
来自PR [38]的原始ChIP-seq数据文件(Control;SRX11374768,并处理了1 nM R5020;SRX11374766)和GRHL2[23](两个复制体;SRX5350536,SRX5350537)数据集从SRA服务器下载。读取质量使用fastqc[77](版本0.11.9)评估,随后用Trimmomatic修剪过代表序列适配器和PCR引物[84]。修剪后,读组与hg38基因组与蝴蝶结[79]比对,选项为:局部、极敏感、局部、无一元、无混合、无不和谐、燕尾榫、-I、0、-X500。Samtools [80] 用于将 sam 文件转换为 bam 文件,修复配对错误的配对,并删除重复文件。Bedtools [81] 用于移除映射到 hg38 黑名单区域的读段[85]。可用片段的最终读取计数是从过滤和去重的 bam 文件中确定的。床图是用Bedtools genomecov的配对端模式创建的。在 IGV 中观察到床抓 [39]。为了峰值调用、可视化和信号图,复制的bam文件与SAMtools合并为单一文件。峰值通过MACS2[83]调用,狭窄峰值则有-f BAMPE和-p 1e-3。deepTools [86] 用于将 bam 文件转换为规范化的 BigWig 文件(bamCoverage 使用 -RPGC 选项和 -e 扩展读取至片段长度)。大人物被用IGV形象化;图中显示的轨迹是两个生物复制(GRHL2)或单次复制(PR)合并,归一化为每个基因组覆盖的读段数,并按因子进行尺度化。
下游分析
对于ChIP-seq和CUT&RUN信号强度,均使用deepTools生成了热图和信号剖面[86]。峰值重叠使用床工具计算[81],要求至少1碱基对重叠。维恩图使用Venndiagram R软件包创建,基因组注释则使用ChIPseeker [40,41] R软件包完成。使用HOMER[44]进行了基序丰富分析,选项为-size 200和-mask。处理了来自R5020刺激T47D细胞的PR HiChIP数据(Zaurin等人)。[38],GEO注册号:GSM5425945)以.bedpe格式下载,并与549个通过RNA-seq调控的PR和GRHL2基因的TSS区域重叠[81]。选择含有HiChIP锚点的TSS区域进行进一步分析。从ChIPatlas检索了R5020刺激的H3K27ac [42](SRX22674023)、RAD21[42](SRX22674036)和CTCF [42](SRX22674025)的峰值调用ChIP-seq数据集,以及siControl(SRX23397061)和siGRHL2(SRX23397063)的ATAC-seq数据集[43][43]。
临床数据分析
原发性乳腺肿瘤的基因表达和临床数据通过cBioPortal从METABRIC(乳腺癌分子分类国际联盟)队列获取 [45–48]。去除了无基因注释的探针,对于具有多个探针的基因,保留了样本间变异最大的探针。合并了样本和患者层面的临床数据。仅纳入了同时具有临床和表达数据的肿瘤,最终数据集为1,980名患者,用于生存分析。由GRHL2和PR共调控的298个基因(如图4所示)合并为基因签名,使用Hacksig [88]R软件包计算每个肿瘤特征的综合特征评分。上调和下调基因分别评分并合并得出总特征评分。评分在患者间标准化(z评分),高特征组和低特征组以中位数为界限定义。PGR GRHL2的表达水平从表达矩阵中提取用于下游分析,并绘制箱形图比较PR阳性和PR阴性肿瘤间的基因和特征表达。统计显著性通过Wilcoxon秩和检验进行评估。存活数据使用Survival [89,90]和Survminer [91] R软件进行分析。在全队列中,针对高特征与低特征肿瘤生成了Kaplan–Meier生存曲线。存活差异通过对数秩检验进行评估。使用多变量Cox比例风险回归模型评估GRHL2/PR特征评分与总体生存期之间的关联,并调整诊断年龄和肿瘤分期。还测试了交互模型,以评估特征在PR阳性和PR阴性肿瘤间的预后影响是否存在差异。
支持信息
通过CUT&RUN识别的R5020诱导GRHL2结合位点与GRHL2 ChIP-seq序列匹配。
显示1/5:pgen.1012088.s001.tif
跳转到图分享导航
抱歉我们无法加载您的数据。
1 / 5
下载
图格分享
第一季 图。 通过CUT&RUN识别的R5020诱导GRHL2结合位点与GRHL2 ChIP-seq序列匹配。
A)通过HOMER基序分析确定的所有1 nM R5020刺激PR峰、所有未处理的GRHL2峰或GRHL2-PR共享峰中,前五个被确定富集的转录因子基序[44]。B)维恩图,显示4小时1纳米R5050刺激的GRHL2与PR切割与运行峰值的重叠。如果峰重叠至少1个碱基对,则视为重叠。C)两个PR和GRHL2重叠的CUT&RUN峰的代表性例子。数据在IGV浏览器中进行可视化[39]。NT = 未治疗。D)热图显示PR R5020处理后与GRHL2在未处理及4小时1 nM刺激条件下,PR R5020与GRHL2在仅PR、仅GRHL2和GRHL2-PR共享ChIP-seq峰的CUT&RUN信号。
https://doi.org/10.1371/journal.pgen.1012088.s001
(TIF)
第二季 图。 验证直接GRHL2-PR靶基因。
A)对野生型(WT)和shRNA介导的GRHL2敲低(shGRHL2)T47DS细胞进行Western blot,刺激1 nM R5020,持续4小时。展示了三个独立的生物复制体。ACTIN被用作加载控制。B)条形图,显示(A)中西部印迹中GRHL2蛋白在ACTIN上的相对表达。个体数值在未处理的WT(对照)上进行归一化。数据点:n=3个生物复制的个体值,表现为均值折叠变化,归一化为对照。P值采用双因子方差分析计算,随后进行未纠正费舍尔最低显著差异检验。C)对未处理(NT)或用1 nM R5020刺激24小时的WT和shGRHL2 T47DS细胞中,所有在整体RNA序列中表达的基因进行主成分分析(PCA)。每个点代表一个复制品;每个组包含 n = 3 个复制体。
https://doi.org/10.1371/journal.pgen.1012088.s002
(TIF)
第三季 图。 高GRHL2/PR调控的基因表达与乳腺癌患者的总体生存率降低有关。
A-B)箱型图显示了PGR (A) 和GRHL2 (B) mRNA表达(log2归一化)在METABRIC队列中按PR状态分层分布。单个肿瘤以抖动点表示。C)基于中位GRHL2/PR特征评分,将METABRIC肿瘤分层为高特征组和低特征组进行Kaplan–Meier分析。高特征表达(红色)患者整体生存率显著较低表现(蓝色)差(对数秩检验,P < 0.001)。D)显示METABRIC队列中GRHL2/PR特征评分按PR状态分层分布的箱型图。单个肿瘤以抖动点表示。
https://doi.org/10.1371/journal.pgen.1012088.s003
(TIF)
第四季,图。 GRHL2或PR结合增强子可以通过三维染色质环路收敛,共同调控基因表达。
A)146个PR HiChIP[38]环的环径分布密度图,这些环直接连接由RNA-seq确定的GRHL2/PR调控TSS。环路大小以千基(kb)表示。B)选择被认定为富集于不存在GRHL2峰、PR峰或调控TSS锚点的转录因子基序,被定义为“其他”。使用HOMER进行了基序富集分析[44]。C)可视化显示单个非重叠的GRHL2和PR峰,以及通过染色质环路收敛到一个PR峰的ARID5B启动子,显示PR ChIP-seq [38]峰、GRHL2 ChIP-seq [23]峰和PR HiChIP环[38]。灰色条线突出显示ARID5B TSS。橙色条纹突出了PR和GRHL2的各个峰值。数据在IGV浏览器中进行可视化[39]。
https://doi.org/10.1371/journal.pgen.1012088.s004
(TIF)
S5图。 GRHL2与内聚复合体成员相互作用。
A)火山图,展示激素耗竭条件下GRHL2 RIME与IgG对照组的结果。每个灰点表示质谱中识别的单一蛋白质。灰色虚线表示Log2FC(-3,3)和-Log10(p值)截断值(0.05)2,325个通过这些标准的蛋白质,被鉴定为GRHL2相互作用物。红色高亮点表示已知的内聚蛋白亚基,即与GRHL2显著相互作用的负荷和释放因子。B-C)维恩图显示T47D细胞中未处理与30分钟R5020处理的CTCFChIP-seq峰[42](B)或未处理与30分钟R5020处理的RAD21 ChIP-seq峰[42](C)之间的重叠情况。对ChIP-Atlas数据(即称为峰值)的重新分析。如果峰重叠至少1个碱基对,则视为重叠。
https://doi.org/10.1371/journal.pgen.1012088.s005
(TIF)
致谢
我们感谢阿姆斯特丹大学斯瓦默丹生命科学研究所生物分子质谱实验室的Gertjan Kramer及其他成员在质谱分析方面的支持。我们还感谢Selina van Leeuwen及MAD:荷兰基因组学服务与支持机构、阿姆斯特丹大学斯瓦默丹生命科学研究所的其他成员,提供测序服务。感谢发育、干细胞与癌症生物学(DSCCB)组的同事以及斯瓦默丹生命科学研究所细胞与系统生物学主题的其他同事,在项目期间给予了富有成效的讨论和反馈。我们要感谢坎图实验室所有成员在我们CUT&RUN实验中的指导。我们特别感谢我们的实习硕士生Jeltje Rommens,他在识别GRHL2和PR调控基因方面提供了初步分析和工作流程设置。
参考文献
1.克莱姆SL、希波尼Z、格林利夫WJ。染色质可及性与调控表观基因组。国家牧师热内。2019;20(4):207–20.PMID:30675018
查看文章PubMed/NCBI谷歌学术
2.Ravasi T、Suzuki H、Cannistraci CV、片山S、Bajic VB、Tan K等。小鼠与人类组合转录调控图谱。细胞。2010;140(5):744–52.PMID:20211142
查看文章PubMed/NCBI谷歌学术
3.费多罗娃 E, Zink D. 核结构与基因调控。生物物理学报。2008;1783(11):2174–84.PMID:18718493
查看文章PubMed/NCBI谷歌学术
4.巴尔德瓦杰·N,扬·K-K,格斯坦·MB。对多样调控网络的层级分析显示,中层协作的趋势一致。美国国家科学院院刊 2010年;107(15):6841–6.PMID:20351254
查看文章PubMed/NCBI谷歌学术
5.金J、崔M、金J-R、珍熙、金VN、赵K-H。人类基因调控网络中转录因子的共调控机制。核酸研究 2012;40(18):8849–61.PMID:22798495
查看文章PubMed/NCBI谷歌学术
6.诺丁·A、赞巴尼尼·G、埃纳尔·约纳森·M、韦斯·T、范德格里夫特Y、帕杰拉·P等。构建小鼠发育过程中转录因子结合图谱,识别出流行的调控区域。发展。2025;152(6):d ev204311。PMID:40013513
查看文章PubMed/NCBI谷歌学术
7.更富勒。类固醇受体超家族:多样性机制。FASEB期刊。1991.
查看文章谷歌学术
8.Frigo DE, Bondesson M, Williams C. 核受体:从分子机制到治疗。生物化学论文。2021;65(6):847–56.PMID:34825698
查看文章PubMed/NCBI谷歌学术
9.布里斯肯 C,帕克 S,瓦斯 T,莱登 JP,奥马利 BW,温伯格 RA。乳腺发育中上皮孕酮受体在旁分泌的作用。美国国家科学院院刊,1998年;95(9):5076–81.PMID:9560231
查看文章PubMed/NCBI谷歌学术
10.Brisken C, Scabia V. 孕酮90年:正常乳腺中的孕酮受体信号及其对癌症的影响。J Mol 内分泌醇。2020;65(1):T81–94。PMID:32508307
查看文章PubMed/NCBI谷歌学术
11.阿塔卡·D、奥阿德·P、康斯坦丁·C、拉斯洛·C、贝勒特·M、沙姆塞丁·M等。分泌蛋白酶Adamts18将激素作用与乳腺干细胞生态位的激活联系起来。国家公社。2020;11(1):1571.PMID:32218432
查看文章PubMed/NCBI谷歌学术
12.巴特利特近端锋,埃文斯·I,琼斯·A,巴雷特·JE,哈兰·S,赖塞尔·D等。抗孕激素能减少年轻健康女性乳腺组织中的表观遗传场癌变。基因组医学 2022;14(1):64.PMID:35701800
查看文章PubMed/NCBI谷歌学术
13.扎雷特,堪萨斯州,卡罗尔,JS。先驱转录因子:建立基因表达能力。基因发育 2011;25(21):2227–41.PMID:22056668
查看文章PubMed/NCBI谷歌学术
14.约兹维克,卡罗尔,JS。先驱因素在激素依赖性癌症中存在。纳特·雷夫·癌症。2012;12(6):381–5.PMID:22555282
查看文章PubMed/NCBI谷歌学术
15.乌尔塔多·A,霍尔姆斯·KA,罗斯-因尼斯·CS,施密特·D,卡罗尔·JS。FOXA1是雌激素受体功能和内分泌反应的关键决定因素。纳特·热内。2011;43(1):27–33.PMID:21151129
查看文章PubMed/NCBI谷歌学术
16.卡罗尔·JS、刘XS、布罗茨基AS、李W、迈耶CA、萨里·AJ等。雌激素受体结合的染色体全域定位显示,需要叉头蛋白FoxA1进行长期调控。Cell。2005;122(1):33–43.PMID:16009131
查看文章PubMed/NCBI谷歌学术
17.穆罕默德·H、德桑托斯·C、塞兰杜尔·AA、阿里·HR、布朗·GD、阿特金斯·A等。内源性纯化揭示了GREB1作为关键的雌激素受体调控因子。细胞报告 2013;3(2):342–9.PMID:23403292
查看文章PubMed/NCBI谷歌学术
18.约兹维克·KM,切尔努欣I,塞兰杜尔AA,纳加拉詹·S,卡罗尔·JS。FOXA1通过招募甲基转移酶MLL3,将H3K4单基化导向增强子。细胞报告 2016;17(10):2715–23.PMID:27926873
查看文章PubMed/NCBI谷歌学术
19.Eeckhoute J, Keeton EK, Lupien M, Krum SA, Carroll JS, Brown M. 正向交叉调控环将GATA-3与乳腺癌中雌激素受体α表达联系起来。癌症研究 2007年;67(13):6477–83.PMID:17616709
查看文章PubMed/NCBI谷歌学术
20.马丁·EM,奥兰多KA,横堀K,韦德宾夕法尼亚。雌激素受体/GATA3/FOXA1转录网络:乳腺癌的经验教训。Curr Opin Struct Biol. 2021;71:65–70.PMID:34225008
查看文章PubMed/NCBI谷歌学术
21.里斯·RM,哈里森 MM,阿拉里德·ET。《颗粒头样蛋白2:激素依赖性癌症与表观遗传学的新兴作用》。内分泌学。2019;160(5):1275–88.PMID:30958537
查看文章PubMed/NCBI谷歌学术
22.郑C、高艾伦、刘T、Solodin NM、Meyer MB、Salem K等。GRHL2升高赋予ER阳性乳腺癌细胞的可塑性。癌症(巴塞尔)。2024;16(16):2906.PMID:39199676
查看文章PubMed/NCBI谷歌学术
23.Chi D、Singhal H、Li L、Xiao T、Liu W、Pun M 等。雌激素受体信号在乳腺肿瘤发生过程中被重新编程。2019年美国国家科学院院刊;116(23):11437–43.PMID:31110002
查看文章PubMed/NCBI谷歌学术
24.Wang Z、Coban B、Wu H、Chouaref J、Daxinger L、Paulsen MT 等。腔腔乳腺癌中由GRHL2控制的基因表达网络。细胞通讯信号。2023;21(1):15.PMID:36691073
查看文章PubMed/NCBI谷歌学术
25.里斯·RM,赫尔泽·KT,艾伦·KO,郑C,索洛丁·N,阿拉里德·ET。GRHL2增强磷酸化雌激素受体(ER)染色质的结合,并调控ER介导的转录激活和抑制。分子细胞生物学,2022年;42(10):e0019122。PMID:36036613
查看文章PubMed/NCBI谷歌学术
26.科切·KJ、贾斯珀·JS、德索特尔斯·TK、埃弗雷特·L、沃德尔·S、韦斯特林·T等。谱系决定因子GRHL2与FOXA1合作,建立内分泌耐药性乳腺癌的靶向通路。细胞代表 2019;29(4):889-903。第10页。PMID:31644911
查看文章PubMed/NCBI谷歌学术
27.威拉诺夫斯基·T,塔克菲尔德·A,切鲁蒂·L,奥康奈尔·S,圣R,帕雷克·V等。一个高度保守的哺乳动物发育转录因子家族,与果蝇颗粒头蝇相关。机甲开发 2002;114(1–2):37–50.PMID:12175488
查看文章PubMed/NCBI谷歌学术
28.雅各布斯法官、阿特金斯·M、戴维·K、伊姆里乔娃·H、罗曼内利·L、克里斯蒂安斯·V等。转录因子颗粒头通过置换核小体,启动上皮增强子以实现时空激活。纳特·热内。2018;50(7):1011–20.PMID:29867222
查看文章PubMed/NCBI谷歌学术
29.明Q、罗斯克Y、舒茨A、瓦伦丁K、Ibraimi I、施密特-奥特KM等。Grainyhead/CP2转录因子家族基因调控的结构基础。核酸研究 2018;46(4):2082–95.PMID:29309642
查看文章PubMed/NCBI谷歌学术
30.文卡特桑 K,麦克马纳斯 HR,梅洛 CC,史密斯 TF,汉森 U。古代复制转录因子家族成员之间的功能保守性,LSF/格雷尼头。核酸研究,2003年;31(15):4304–16.PMID:12888489
查看文章PubMed/NCBI谷歌学术
31.Mohammed H, Taylor C, Brown GD, Papachristou EK, Carroll JS, D'Santos CS. 内源性蛋白快速免疫沉淀质谱(RIME)用于染色质复合物分析。纳特·普罗托克。2016;11(2):316–26.PMID:26797456
查看文章PubMed/NCBI谷歌学术
32.麦克福恩一世、威尔逊·H、塞尔斯·拉、莱顿一世、塞雷布里斯基一世、布莱克利·RC等。Grainyhead-like-2通过与表观遗传修饰因子的相互作用赋予NK敏感性。Mol免疫。2019;105:137–49.PMID:30508726
查看文章PubMed/NCBI谷歌学术
33.拉马穆尔蒂·L、巴伯·V、塔克菲尔德·A、克劳斯顿·D、托普汉姆·D、坎宁安·JM等。针对CP2基因的靶向破坏,CP2基因是NTF家族的转录因子成员。《生物化学杂志》2001年;276(11):7836–42.PMID:10995745
查看文章PubMed/NCBI谷歌学术
34.Thomas PD、Ebert D、Muruganujan A、Mushayahama T、Albou L-P、Mi H. PANTHER:让基因组尺度的系统发生学对所有人开放。《蛋白质科学》2022年;31(1):8–22.PMID:34717010
查看文章PubMed/NCBI谷歌学术
35.穆罕默德·H,拉塞尔·IA,斯塔克·R,鲁埃达·奥姆,希基·TE,塔鲁利·乔治亚州等。孕酮受体调节乳腺癌中的ERα作用。自然。2015;523(7560):313–7.PMID:26153859
查看文章PubMed/NCBI谷歌学术
36.汉夫·D、法辛·P、加斯·P、马蒂亚斯·W·贝克曼、哈克·CC、海因德尔·F等。CCND1扩增对激素受体阳性、HER2阴性乳腺癌患者的预后影响——临床和病理标志物的相关性。乳腺癌治疗。2025;210(1):125–34.PMID:39586971
查看文章PubMed/NCBI谷歌学术
37.雷内里·S、阿加蒂·S、米亚诺·V、萨尼·M、贝尔奇亚拉·P、里奇·L等。Tab2的一种新功能结构域,参与乳腺癌细胞中雌激素受体α的相互作用。PLoS One。2016;11(12):e0168639。PMID:27992601
查看文章PubMed/NCBI谷歌学术
38.扎乌林·R、费拉里·R、纳赫特·AS、卡博内尔·J、勒·迪利·F、丰特-马图·J等。一组可及增强剂使乳腺癌细胞能够对生理孕素浓度做出初步反应。核酸研究 2021;49(22):12716–31.PMID:34850111
查看文章PubMed/NCBI谷歌学术
39.罗宾逊·JT,索瓦尔兹多蒂尔·H,温克勒·W,古特曼·M,兰德·ES,盖茨·G等。整合基因组学查看器。纳特生物技术。2011;29(1):24–6.PMID:21221095
查看文章PubMed/NCBI谷歌学术
40.Wang Q、Li M、Wu T、Zhan L、Li L、Chen M 等。通过 ChIPseek 探索表观基因组数据集。柯尔·普罗托克。2022;2(10):e585。PMID:36286622
查看文章PubMed/NCBI谷歌学术
41.余G,王L-G,何Q-Y。ChIPseeker:一款用于 ChIP 峰值标注、比较和可视化的 R/Bioconductor 软件包。生物信息学。2015;31(14):2382–3.PMID:25765347
查看文章PubMed/NCBI谷歌学术
42.Ramírez-Cuéllar J, Ferrari R, Sanz RT, Valverde-Santiago M, García-García J, Nacht AS 等。LATS1 控制 3D 培养乳腺癌细胞的 CTCF 染色质占有及激素反应。EMBO J. 2024; 43(9):1770–98. PMID:38565950
查看文章PubMed/NCBI谷歌学术
43.Yang L, Kumegawa K, Saeki S, Nakadai T, Maruyama R. 通过染色质可及性剖析,识别乳腺癌细胞系中谱系特异性表观遗传调控因子FOXA1和GRHL2。癌症基因 Ther. 2024; 31(5):736–45. PMID:38429368
查看文章PubMed/NCBI谷歌学术
44.Heinz S、Benner C、Spann N、Bertolino E、Lin YC、Laslo P 等。谱系决定转录因子的简单组合为巨噬细胞和B细胞身份所需的顺调调元素。Mol细胞。 2010; 38(4):576–89. PMID:20513432
查看文章PubMed/NCBI谷歌学术
45.de Bruijn I、Kundra R、Mastrogiacomo B、Tran TN、Sikina L、Mazor T 等。AACR Project GENIE 生物制药协作项目中纵向基因组和临床数据的分析与可视化,载于 cBioPortal。癌症研究 2023; 83(23):3861–7. PMID:37668528
查看文章PubMed/NCBI谷歌学术
46.柯蒂斯·C、沙阿警长、秦S-F、图拉什维利·G、鲁埃达·OM、邓宁·MJ等。2000个乳腺肿瘤的基因组和转录组结构揭示了新的亚群。自然。2012;486(7403):346–52.PMID:22522925
查看文章PubMed/NCBI谷歌学术
47.道森 S-J,鲁埃达 OM,阿帕里西奥 S,卡尔达斯 C.一种新的基因组驱动综合乳腺癌综合分类及其影响。EMBO J. 2013;32(5):617–28.PMID:23395906
查看文章PubMed/NCBI谷歌学术
48.佩雷拉·B、秦S-F、鲁埃达·OM、沃兰·H-KM、普罗文扎诺·E、巴德韦尔·HA等。2433例乳腺癌的体细胞突变谱进一步完善了其基因组和转录组图谱。国家公社。2016;7:11479.PMID:27161491
查看文章PubMed/NCBI谷歌学术
49.徐S、胡娥、蔡毅、谢子、罗晓、展L等。使用 clusterProfiler 来刻画多组学数据。纳特·普罗托克。2024;19(11):3292–320.PMID:39019974
查看文章PubMed/NCBI谷歌学术
50.姚·L,伯曼·BP,法纳姆PJ。揭开增强子的秘密使命:将远端调控元件与目标基因连接。2015年生物化学分子生物学评论;50(6):550–73.PMID:26446758
查看文章PubMed/NCBI谷歌学术
51.桑亚尔·A,拉乔伊·BR,贾因·G,德克尔·J。基因启动子的远程相互作用景观。自然。2012;489(7414):109–13.PMID:22955621
查看文章PubMed/NCBI谷歌学术
52.李G、阮X、奥尔巴赫RK、桑杜KS、郑M、王P等。广泛的启动子中心染色质相互作用为转录调控提供了拓扑基础。Cell。2012;148(1–2):84–98.PMID:22265404
查看文章PubMed/NCBI谷歌学术
53.米夫苏德·B、塔瓦雷斯-卡德特·F、杨·AN、舒格·R、舍恩费尔德·S、费雷拉·L等。利用高分辨率捕捉Hi-C绘制人体细胞中远程启动子接触图。纳特·热内。2015;47(6):598–606.PMID:25938943
查看文章PubMed/NCBI谷歌学术
54.Tettey TT、Rinaldi L、Hager GL。激素依赖性癌症中的远程基因调控。纳特·雷夫·癌症。2023;23(10):657–72.PMID:37537310
查看文章PubMed/NCBI谷歌学术
55.金F、李Y、迪克森JR、塞尔瓦拉杰S、叶Z、李AY等。人体细胞三维染色质相互作用组的高分辨率图谱。自然。2013;503(7475):290–4.PMID:24141950
查看文章PubMed/NCBI谷歌学术
56.Handoko L, Xu H, Li G, Ngan CY, Chew E, Schnapp M 等。CTCF 介导的功能性染色质相互作用组在多能细胞中。纳特·热内。2011;43(7):630–8.PMID:21685913
查看文章PubMed/NCBI谷歌学术
57.勒迪利 F、鲍 D、波尔 A、维森特 GP、塞拉 F、索罗内拉斯 D 等。染色质拓扑结构域的不同结构转变与激素诱导的基因调控协调相关。基因开发 2014;28(19):2151–62.PMID:25274727
查看文章PubMed/NCBI谷歌学术
58.Holding AN、Giorgi FM、Donnelly A、Cullen AE、Nagarajan S、Selth LA 等。VULCAN 将 ChIP-seq 与患者来源的共表达网络整合,以识别 GRHL2 作为乳腺癌增强子 ERa 的关键共调控因子。基因组生物学,2019年;20(1):91.PMID:31084623
查看文章PubMed/NCBI谷歌学术
59.Paltoglou S、Das R、Townley SL、Hickey TE、Tarulli GA、Coutinho I 等。新型雄激素受体协调剂 GRHL2 在前列腺癌中同时发挥致癌和抗转移功能。癌症研究 2017;77(13):3417–30.PMID:28473532
查看文章PubMed/NCBI谷歌学术
60.Grift YB van de、Aarts MT、Wiese KE、Heijmans N、Hooijkaas IB、Pritchard CE 等。GRHL和PGR通过3D循环控制乳房腺中WNT4表达,这些增强子是保守且物种特异性增强子的[互联网]。2025年[引用于2025年6月6日];2025.04.11.648333。可从以下网站获取:https://www.biorxiv.org/content/10.1101/2025.04.11.648333v1
61.Bernardo GM、Bebek G、Ginther CL、Sizemore ST、Lozada KL、Miedler JD 等。FOXA1抑制基底乳腺癌细胞的分子表型。癌基因。2013;32(5):554–63.PMID:22391567
查看文章PubMed/NCBI谷歌学术
62.Bernardo GM、Lozada KL、Miedler JD、Harburg G、Hewitt SC、Mosley JD 等。FOXA1是ERalpha表达和乳腺导管形态发生的重要决定因子。发展。2010;137(12):2045–54.PMID:20501593
查看文章PubMed/NCBI谷歌学术
63.刘毅、赵毅、斯凯里·B、王X、科林-卡辛C、拉迪斯基·DC等。Foxa1对乳管形成至关重要。创世纪。2016;54(5):277–85.PMID:26919034
查看文章PubMed/NCBI谷歌学术
64.塞巴洛斯-查韦斯中场,苏布蒂尔-罗德里格斯中场,贾诺普卢 EG,索罗内拉斯后卫,巴斯克斯-查韦斯 E,维森特 GP 等。染色质重塑剂CHD8是激活孕酮受体依赖增强子所必需的。《公共图书馆》Genet。2015;11(4):e1005174。PMID:25894978
查看文章PubMed/NCBI谷歌学术
65.Siersbæk R、Scabia V、Nagarajan S、Chernukhin I、Papachristou EK、Broome R 等。IL6/STAT3信号诱导雌激素受体α增强子驱动乳腺癌转移。癌症细胞。2020;38(3):412-423.e9。PMID:32679107
查看文章PubMed/NCBI谷歌学术
66.Gooch JL, Christy B, Yee D. STAT6介导人类乳腺癌细胞中白介介素-4增生抑制。肿瘤。2002;4(4):324–31.PMID:12082548
查看文章PubMed/NCBI谷歌学术
67.Hughes CS,Foehr S,Garfield DA,Furlong EE,Steinmetz LM,Krijgsveld J。利用顺磁珠技术进行超灵敏蛋白质组分析。分子系统生物学,2014年;10(10):757.PMID:25358341
查看文章PubMed/NCBI谷歌学术
68.Aarts MT,Wagner M,van der Wal T,van Boxtel AL,van Amerongen R.一个用于研究孕酮受体信号传导的分子工具箱。《乳腺生物肿瘤杂志》。2023;28(1):24.PMID:38019315
查看文章PubMed/NCBI谷歌学术
69.van de Grift YB、Aarts MT、Wiese KE、Heijmans N、Hooijkaas IB、Pritchard CE 等人。GRHL和PGR通过3D循环控制保守且物种特异性增强子在乳腺中的WNT4表达。bioRxiv。2025.
查看文章谷歌学术
70.Ewels P、Magnusson M、Lundin S、Käller M. 多质量检测:在一份报告中总结多个工具和样本的分析结果。生物信息学。2016;32(19):3047–8.PMID:27312411
查看文章PubMed/NCBI谷歌学术
71.Trimmomatic:用于Illumina序列数据的灵活剪裁器 |生物信息学 |牛津学术 [互联网]。[引自2024年11月26日];可从以下网站获取:https://academic.oup.com/bioinformatics/article/30/15/2114/2390096
72.Kim D、Paggi JM、Park C、Bennett C、Salzberg SL。基于图表的基因组比对与基因分型,利用HISAT2和HISAT基因型进行。纳特生物技术。2019;37(8):907–15.PMID:31375807
查看文章PubMed/NCBI谷歌学术
73.Anders S, Pyl PT, Huber W. HTSeq——一个用于处理高通量测序数据的Python框架。生物信息学。2015;31(2):166–9.PMID:25260700
查看文章PubMed/NCBI谷歌学术
74.Love MI, Huber W, Anders S. 利用DESeq2对RNA-seq数据的折叠变化和扩散进行调节估计。基因组生物学,2014年;15(12):550.PMID:25516281
查看文章PubMed/NCBI谷歌学术
75.Chua SL、参见 Too WC、Khoo BY、Few LL。UBC 和 YWHAZ 是使用 MCF7、HCT116 和 HepG2 细胞系进行基因表达准确规范化的合适参考基因。细胞技术。2011;63(6):645–54.PMID:21850463
查看文章PubMed/NCBI谷歌学术
76.赞巴尼尼·G,诺尔丁·A,约纳森·M,帕杰拉·P,坎图·C。一种针对转录辅因子优化的新型CUT&RUN低容积尿素(LoV-U)协议揭示了Wnt/β-catenin组织特异性基因组靶点。发展。2022;149(23):d ev201124。PMID:36355069
查看文章PubMed/NCBI谷歌学术
77.de Sena Brandine G, Smith AD. Falco:用于测序数据质量控制的高速快速QC仿真。F1000Res。2019;8:1874.PMID:33552473
查看文章PubMed/NCBI谷歌学术
78.布什内尔B、鲁德J、辛格E。BBMerge——通过重叠准确的双枪判读并线。PLoS One。2017;12(10):e0185056。PMID:29073143
查看文章PubMed/NCBI谷歌学术
79.Langmead B,Salzberg SL。与蝴蝶结2的快速间隙读比对。自然方法。2012;9(4):357–9.PMID:22388286
查看文章PubMed/NCBI谷歌学术
80.李H、汉德萨克B、怀索克A、芬奈尔T、阮J、霍默N等。序列比对/图谱格式和SAM工具。生物信息学。2009;25(16):2078–9.PMID:19505943
查看文章PubMed/NCBI谷歌学术
81.阿肯色州昆兰,霍尔内科。BEDTools:一套灵活的工具组合,用于比较基因组特征。生物信息学。2010;26(6):841–2.PMID:20110278
查看文章PubMed/NCBI谷歌学术
82.诺尔丁·A,赞巴尼尼·G,帕杰拉·P,坎图·C。CUT&RUN怀疑基因组中存在问题区域。《基因组生物学》2023年;24(1):185.PMID:37563719
查看文章PubMed/NCBI谷歌学术
83.张毅、刘T、迈耶CA、Eeckhoute J、约翰逊DS、伯恩斯坦BE等。基于模型的ChIP-Seq(MACS)分析。基因组生物学,2008年;9(9):R137。PMID:18798982
查看文章PubMed/NCBI谷歌学术
84.Bolger AM, Lohse M, Usadel B. Trimmomatic:用于Illumina序列数据的柔性剪裁器。生物信息学。2014;30(15):2114–20.PMID:24695404
查看文章PubMed/NCBI谷歌学术
85.Amemiya HM,Kundaje A,Boyle AP。《ENCODE黑名单:基因组问题区域的识别》。科学报告 2019;9(1):9354.PMID:31249361
查看文章PubMed/NCBI谷歌学术
86.Ramírez F、Dündar F、Diehl S、Grüning BA、Manke T. deepTools:一个用于探索深度测序数据的灵活平台。核酸研究,2014年;42(网页服务器问题):W187-91。PMID:24799436
查看文章PubMed/NCBI谷歌学术
87.Zou Z, Ohta T, Oki S. ChIP-Atlas 3.0:一套数据挖掘套件,用于探索染色体结构及大规模调节组数据。核酸研究 2024;52(W1):W45–53。PMID:38749504
查看文章PubMed/NCBI谷歌学术
88.Carenzo A、Pistore F、Serafini MS、Lenoci D、Licata AG、De Cecco L. hacksig:一个统一且整洁的R框架,用于轻松计算基因表达签名评分。生物信息学。2022;38(10):2940–2.PMID:35561166
查看文章PubMed/NCBI谷歌学术
89.Therneau M, Grambsch PM。《生存数据建模:扩展Cox模型》。
90.瑟诺·T。R语言中的生存分析包[互联网]。2026;可从以下网站获取:https://CRAN.R-project.org/package=survival
91.Kassambara A、Kosinski M、Biecek P. survminer:使用ggplot2绘制生存曲线 [互联网]。2025;可从以下网站获取:https://CRAN.R-project.org/package=survminer
引进/卖出
2025-11-22
开发针对G蛋白偶联受体并表现出逻辑门控信号的双位纳米抗体配体偶联
希瓦尼·萨奇德夫,斯瓦纳利·罗伊,罗斯·W·切洛哈
抽象
G蛋白偶联受体(GPCRs)是最大的一类嵌入质膜的信号蛋白家族。这些受体参与了多种生理过程,使其成为药物开发的理想靶点。双中心配体由靶向受体直立位点的药效团和结合到独立位点的相关部分组成,具有显著潜力处理GPCR功能。本文报告了新型双中心偶联物的合成与评估,该结合体由小分子药效团激活与抗体片段(纳米抗体,Nbs)相关联的腺苷A2A受体(A2AR)。该方法利用Nbs与工程A2AR变体非直构位点的高亲和力和特异性结合,提供双中心Nb配体偶联,激发强烈且持久的信号反应。我们进一步证明,这类双中心共轭物可以通过跨越两个不同的受体原体来诱导激活。这一特性使受体对能够选择性地定向到任一受体之上,作为一种“逻辑门控”活性的形式。我们通过展示双位共轭在靶向多对共表达受体(包括不同类别的GPCR单体)中的活性,展示了其广泛适用性。此外,我们证明了这种双重靶向策略启动的信号反应与单价配体诱导的信号反应不同。利用Nb配体偶联物靶向受体对的能力,提供了一种强大的策略,具有细胞类型选择性信号传导的潜力,并对GPCR药物发现更广泛具有启示意义。
数字
介绍
G蛋白偶联受体(GPCRs)是哺乳动物细胞表面蛋白中最大的家族,是成熟的药物靶点,约占目前上市治疗药物的35%[1]。其广泛分布和多样的功能特性使GPCR成为药物开发的理想候选产品。GPCRs由多种配体激活,配体范围从小分子到肽和蛋白质。GPCR激动剂结合到受体的正体位点。该结合事件诱导构象变化,进而激活异三聚体G蛋白及下游细胞内信号级联反应。迄今为止,大多数GPCR药物发现工作都集中在靶向正构位点。此类位点在GPCR亚型中高度保守,这对识别高度特异性配体存在挑战。受体直立囊外的结合位点,也称为变构结合位点,可能在GPCR亚型之间表现出更多差异,并为生成高度特异性的结合剂提供了更好的前景[2]。然而,变构位点的结合常常无法诱导所需的信号反应。解决这一问题的一种方法是关注双位配体——即由直构和变构药基组成的分子,通过化学连接实现两个结合位点的靶向[3]。尽管双中心化合物有潜力实现选择性,但对其合理设计具有挑战性,尤其是对于通常缺乏高度明确次级结合位点的A类GPCRs。
A类,即视紫红质家族的GPCRs,是GPCR中最大的亚组,并且已被广泛研究。大多数A类GPCRs的特征是有一小块碎片暴露在细胞外空间,尽管也有许多例外[4]。其中一个代表性成员是A2A腺苷受体(A2AR),是药物开发的重要靶点。基于结构的分子结合、理性药物设计、药物化学研究和高通量筛选等方面的努力,扩展了A2AR配体的基因库[5]。这些努力催生了具有多样药理特性的新化合物;然而,仍然迫切需要新方法为配体提供所需的特异性。
特异性挑战因单个GPCRs(如A2AR)在不同组织中的表达而加剧。在一种组织中激活GPCR可能导致与在不同组织或细胞类型中激活时不同的生理反应。A2AR广泛表达于大脑、心脏、胃、膀胱、肝脏、免疫细胞和脂肪组织等组织中[6]。GPCR功能中与疾病相关的变化可能仅发生在特定的细胞亚群中。调节这些广泛表达受体功能以用于治疗的努力,可能会因药物作用在其他组织中的作用而变得复杂,导致靶点在靶点、组织外的不良副作用。解决此类并发症的一种方法是开发具有组织特异性作用的配体[7]。仅在表达两个不同靶点时发挥作用的配体,类似于“AND”逻辑门的作用,有望仅在两个靶点均表达的细胞上引发生物反应。逻辑门控活性通过使配体活性条件条件于第二标记在目标解剖部位优先表达,从而仅针对特定组织中广泛表达的受体(如A2AR)提供了可能。尽管这种方法很有吸引力,但具有逻辑门控活性的配体设计仍然具有挑战性[8,9]。
抗体及相关生物制剂因其高亲和力及能结合受体表面的能力,为GPCR药物发现提供了独特可能性[10,11]。纳米抗体(Nbs)源自骆驼科动物中仅重链抗体,因其体积小(12–15 kDa)、模块化技术支持多聚化以及高抗原结合亲和力,具有优于其他方式的优势[11–13]。此类单域抗体片段有时能结合传统单克隆抗体难以处理的GPCR表位[11]。这些特性使Nb成为组装多特异构造的理想构件。我们团队以往的研究表明,将Nbs与生物活性GPCR配体结合,这两种配体结合同一受体,提供了具有特殊且有用特性的双位共轭[14–19]。然而,这些以往的研究仅限于由肽配体结合的GPCR靶点。这些配体以逻辑门控方式作用的能力也尚未被评估。
本文介绍了一种新的半合成化学生物学方法,提供小分子-Nb偶联物,其中Nb结合系绳连接靠近作用位点的小分子激动剂,促进靶向受体激活。这些工程化的双中心小分子-Nb偶联物表现出高度有效力的A2AR激活能力,完全依赖于Nb与其细胞表面表位靶的结合。我们进一步阐述该平台,证明Nb配体共轭物可以以逻辑门控方式作用。通过将GPCR配体与靶向不同受体的Nb连接,我们产生了仅在两个靶点在单一细胞群体中共表达时表现出活性的轭射体。当配体或Nb靶单独表达时,这些轭联物不表现出活性,明确显示逻辑门控行为。该方法为组织特异性药理学提供了一条路径,对GPCR药物发现和副作用较少的疗法具有重要意义。
结果
我们团队过去针对细胞表面受体的研究主要集中于构建由Nb和中大型肽GPCR配体组成的轭联物[14–19]。在此背景下,基于结构和结构-活性关系研究,选择连接子与肽配体连接位点。连接点安装在肽末端(N或C-),位于配体与受体直立位点最紧密结合的部分远端。大多数小分子GPCR配体不具备如此明显的连接子安装位点。为克服这一挑战,我们设计了基于A2AR结构、结合腺苷类似物和激动CGS21680剂(CGS)的结构的小分子配体-Nb共轭物[20]。CGS结合A2AR的直立位点,同时将羧酸基团投射到受体的胞外前庭(见图1)。这一特性为连接子的附着提供了良好的手柄,从而构建CGS共轭物而不破坏配体激动剂特性。以往研究表明,在该位点功能化的CGS类似物仍保持强健的激动剂活性[21,22]。我们通过短聚乙二醇(PEG)将叠氮化基团连接到CGS上3)链条(S1文本中的图1和图A)。值得注意的是,这种方法能够在不改变CGS药管核心结构的情况下制备双中心共轭。
thumbnail 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图1。 工程双中心配体和受体的组成。
A)合成由Nbs和小分子G蛋白偶联受体配体(CGS)组成的轭轭物合成方案。材料与方法以及S1正文中的图A和图B提供了小分子和共轭物的详细合成方法和表征。B)受体构造的示意图。(左)未改造A2AR与CGS复合体结构(PDB: 4UG2)。(中间)表位标记(BC2、6E、ALFA)被基因移植到A2AR的N端(细胞外部分),以实现Nb识别。(正确)ALFA表位标签和Nb6E被基因植入A2AR的N端。通过Colabfold,利用Alphafold2生成了A2AR受体变异的模型(参见材料与方法)。
https://doi.org/10.1371/journal.pbio.3003424.g001
目前尚无报告有Nbs能结合A2AR的细胞外面。为便于评估靶向A2AR的CGS-Nb偶联物,我们将标记序列植入A2AR的远端N端(细胞外部分)。这些标签序列通过受体表达质粒的工程引入,由识别14mer表位标签的Nb组成(Nb)6E见图1B,右侧)[18]或串联表位标签(BC2、6E和ALFA),被其他Nb识别(图1B,中间)。这两个构造都包含ALFA表位标签[23],即Nb阿 尔 法.植入的标签作为高亲和力锚定位点,作用于任一表位标签结合的Nb(例如Nb)阿 尔 法与A2AR-Nb结合6E-ALFA 或 A2AR-BC2-6E-ALFA)或表位肽(例如 6E 肽与 A2AR-Nb 结合)6E-ALFA)。我们假设Nb-tag相互作用会促进高亲和力配体结合,从而提高受体直体位点配体的局部浓度。这些Nb标签对此前已被鉴定,包括GPCR工程工作的背景下[14–19]。这些Nb标签相互作用的亲和力很高,K为D数值范围从纳摩尔(6E标签,BC2标签)到皮科莫尔(ALFA标签)[18,23–25]。
我们生成了嵌合配体,既结合受体直排位点,也结合高亲和力非直立(标签)结合位点;这是我们实验室此前建立的方法[14–19]。注释(注释)6E铌阿 尔 法,以及负对照NbGFP) [26],其C末端具备sortase A识别基序(LPETG),在大肠杆菌中重组表达(见S1文本图A)。Nb C末端通过三甘氨酸功能化二苄基环辛(DBCO)探针进行位点特异性修饰,采用分选[27]。通过压力促进的叠氮化物-烔烔环加成(“点击”)反应,通过一种叠氮化物标记的CGS-叠氮化物和DBCO标记的Nbs(见S1文本中的图1和图A)共轭。我们还基于先前发表的方法(见S1文本中的图B)合成了一组肽基共轭物,其中CGS的类似物与6E表位标签肽相连[18]。通过质谱分析确认了各双中心CGS-Nb和CGS肽偶联物的身份(见S1文本中的表A和B)。对CGS-Nb的评估6E通过酶联免疫吸附测定(ELISA)与表位(6E标签)结合,发现其具有高亲和力的靶标结合能力,亲和力与Nb非常相似6E(见S1文本中的图C)这一观察表明,本研究所采用的配体连接方式并未对Nbs对表位的亲和力产生负面影响。
我们通过测量细胞内环腺苷单磷酸(cAMP)的产生情况,评估了工程受体的功能及半合成结合物诱导其激活的能力,cAMP是GPCR介导Gα的常见读数s信号。我们的检测方法采用了基于HEK293的细胞系,稳定表达感兴趣的单个A2AR受体变异,同时结合基于荧光素酶的生物传感器,实时监测受体信号传导和cAMP生成[28,29]。这些细胞系均表现出CGS的荧光团共轭染色(CGS-AZ647),其中A2AR-BC2-6E-ALFA或A2AR-Nb6E-ALFA染成最高水平(见S1文本中的图D)。我们比较了CGS与CGS-6E、CGS-Nb的激动剂特性6E,CGS-Nb阿 尔 法,以及CGS-NbGFP在表达A2AR、A2AR-BC2-6E-ALFA或A2AR-Nb的细胞系中6E-阿 尔 法。CGS治疗显示cAMP在所有受体变体中均具有浓度依赖性诱导,验证了工程受体的功能性(见图2)。将工程化的Nb和肽CGS偶联物应用于无表位标签的野生型A2AR活性较小。这一发现与先前研究一致,即不与目标受体结合的Nbs与亲和力较低的配体的联锁会显著降低激动剂活性[14,17]。表达A2AR-BC2-6E-ALFA的细胞暴露于特定CGS-Nb结合物(CGS-Nb)6E以及CGS-Nb阿 尔 法) 导致cAMP的完全活化,其效能是CGS本身的25倍(见图2B)。CGS与阴对照Nb(CGS-Nb)的共轭GFP) [26],该表位识别不存在的表位(绿色荧光蛋白,GFP),使该共轭物在该受体处基本失活(见图2)。
thumbnail 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图2。 工程配体信号活性评估。
Nb配体共轭激活G的活性α-介导的cAMP反应在稳定表达(A, B) A2AR, (C, D) A2AR-BC2-6E-ALFA或 (E, F) A2AR-Nb 的细胞中进行评估6E-阿 尔 法。(A,C,E)配体诱导cAMP生成的代表性浓度-反应曲线。Y轴指配体添加后约12分钟记录到的cAMP峰值响应信号。反应通过每秒发光计数(cps)来量化。(B、D、F)配体诱导cAMP反应在配体添加及配体洗刷后进行的代表性动力学测量。配体添加(12 m,“配体上”)后,多余/未结合配体被移除,向细胞添加新培养基,并测量反应30分钟(“配体脱离”)。汇总和量化描述冲刷期内浓度依赖信号(曲线下面积测量,AUC)的数据见S1正文图F。数据对应于单次实验中均值±S.D.,该实验包含两次技术重复。使用三参数逻辑S形形模型生成了浓度-响应曲线。表1展示了包含3-5个生物复制的统计数据。底层数据可在S1数据中找到。
https://doi.org/10.1371/journal.pbio.3003424.g002
thumbnail 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
表1。 配体在A2AR及变体上诱导cAMP反应的活性总结。
https://doi.org/10.1371/journal.pbio.3003424.t001
在表达A2AR-Nb的细胞上也进行了类似实验6E-ALFA [18]。这里是CGS-6E和CGS-Nb阿 尔 法与CGS相比,其效力提升了30倍。相比之下,CGS-Nb6E由于该受体变异体缺少6E标签(见图2C),该变体已不再活跃。我们还将增强型GFP变体的受体构建体插入受体外胞域(A2AR-GFP)。“负对照”CGS-NbGFP共轭配体的效果优于该受体测试的其他配体,而在所有缺乏GFP的A2AR变体上则无活性(见S1文本中的图E)。这些发现证实共轭活性依赖于Nb表位相互作用,可能通过配体系留机制起作用。
配体诱导信号反应的持续时间会影响整体生物反应的强度[30]。为了确定小分子激动剂在作用位点上的Nb介导连接是否会影响信号传递持续时间,我们测量了在广泛洗刷后较长时间内的cAMP反应。简而言之,表达感兴趣受体的细胞系被刺激一段规定时间,在此期间cAMP产生达到峰值,之后激动剂被洗净。CGS诱导的cAMP反应在冲刷后持续时间相对较短,这与之前的观察结果一致(见图2)[18]。相比之下,活性CGS-Nb偶联物诱导的cAMP反应比CGS更为持久(见图2)。我们通过测量冲洗后曲线下面积(AUC)来量化信号持续时间,结果显示共轭配体与非共轭配体在作用持续时间上存在显著差异(见S1文本中的图F)。这一趋势表明,Nb对标签的亲和力可能促进了洗刷后信号的持续传递。
引入了替代工具和检测格式,进一步探讨双中心共轭的活性。基于生物发光共振能量转移(BRET)的G蛋白激活测定平台被改编用于测量A2AR的激活[31]。该方法通过测量G蛋白生物传感器的易位(GPCR激活中的近端事件)来评估配体活性,从而最大限度地减少测量下游第二信使产生方法(如cAMP)固有的信号放大效应。该BRET检测方法也应用于同一A2AR-Nb6E-用于上述cAMP实验的ALFA细胞系。使用该BRET测定法,CGS的效力与先前报告的数值[31]及测试的两种共轭物(CGS-6E和CGS-Nb)相近阿 尔 法)的效力显著更高,与cAMP测定结果一致(见S1文本中的图G)。配体诱导的BRET信号变化在整个测定过程中持续(30米),表明G蛋白激活持续受到刺激(见S1文本中的图G)。未来研究将受益于扩展BRET生物传感器测定方法,如TRUPATH或旁观者BRET,以报告配体冲刷后G蛋白激活的动态[31,32]。
评估GPCR激动剂的另一个常见问题是使用转染外源构造体的细胞系以驱动高水平受体表达。此类细胞系能提供高信噪比分析读数,但有时无法在更生理的环境中预测配体的作用。为探究该变量,我们生成了表达较低A2AR-Nb水平的细胞系6E- ALFA采用极限稀释和克隆选择。两种A2AR-Nb的表达水平6EALFA细胞系采用流式细胞术分析(见S1文本图H)[18]。高密度A2AR-Nb6E-ALFA细胞系在示踪肽下呈现强烈染色,而受体密度较低的细胞则显著(~200倍)降低。这促使我们评估受体表达较低细胞中的激动剂活性。在所有测试的共轭粒子中,CGS-Nb阿 尔 法激活的受体具有最高的效力和效力,而天然激动剂CGS和CGS-6E仅在高浓度时表现出活性(见S1文本中的图H)。这一观察表明,Nb小分子配体偶联物是受体水平较低的应用的有前景候选物,如体内常见的观察。
我们还试图测试工程化双中心配体通过双位点(标签和直立结合)机制与受体的相互作用程度(见图3A)。为评估在受体直立位点或Nb表位结合位点持续作用的重要性,我们在冲洗阶段开始时引入了竞争者(见图3B)。我们添加了游离6E肽以竞争CGS-Nb之间的相互作用6E以及A2AR-BC2-6E-ALFA(图3C)。6E竞争肽的加入导致CGS-Nb的cAMP信号迅速减弱6E通过AUC测量量化(见S1文本中的图I)。相比之下,CGS和CGS-Nb都没有阿 尔 法在相同条件下测试时,信号传递的减少如预期。CGS-Nb 信号的极快丧失6E加入6E肽后,表明双中心配体在信号响应期间无法持续与6E标签结合。
thumbnail 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图3。 冲洗信号反应的机制性研究。
A)洗净竞赛测定的示意图。配体洗脱检测使用表达A2AR-BC2-6E-ALFA的细胞进行,如上所述,并在洗脱阶段加入6E肽或黄嘌呤同系(XAC)。B)在有无竞争6E肽的情况下,稳定表达A2AR-BC2-6E-ALFA的HEK293细胞中环状腺苷单磷酸(cAMP)产生的时间周期。请注意,左右两张图中显示相同的CGS信号数据,以便更清晰地可视化。曲线数据下的量化浓度-反应面积见S1文本中的图I。C)在拮抗剂存在或缺失的情况下,cAMP冲洗反应的类似数据,XAC。请注意,左右两张图中显示相同的CGS信号数据,以便更清晰地可视化。由三个独立实验得出的激动剂效力参数总结见S1文本中的图I。底层数据可在S1数据中找到。
https://doi.org/10.1371/journal.pbio.3003424.g003
这一观察促使我们思考,工程化双中心配体是否也容易受到针对A2AR正构位点的竞争者影响。我们评估了强效A2AR受体直立拮抗剂黄氨酸同源物(XAC)对配体洗离的影响[33]。在冲刷阶段加入XAC后,CGS-Nb均为CGS-Nb6E以及CGS-Nb阿 尔 法信号持续时间略有缩短,这一现象在基于AUC测量的剂量-响应图中也可见(见S1文本中的图3D和图I)。在CGS冲洗阶段加入XAC时,信号传递也出现了类似但较轻的下降。CGS-Nb观察到的信号丢失相对较快6E以及CGS-Nb阿 尔 法表明这些双位共轭可能不会持续作用于受体的直立位点,而是在结合Nb表位和受体正构位点之间切换。类似行为此前也在针对副甲状激素受体-1(PTHR1)的双中心Nb配体偶联物研究中观察到[17]。
成功开发出靶向单一受体的双位配体,促使我们探讨该平台是否可适应处理两种不同的细胞表面蛋白(杂源共轭蛋白)。我们设想了这样一种情景:共轭物的Nb会结合到一个靶点,而连接的配体会激活在同一细胞上共表达的GPCR。我们假设异源共轭的活性取决于被Nb结合对象和配体靶向GPCR的细胞表达。这种双重依赖性将使得能够开发出表现出“AND”逻辑门控行为的共轭基因,即仅在共表达两个靶点的细胞中诱导生物反应。
我们首先将该方法应用于从不同受体类别中选取的两种不同GPCRs。A2AR属于A类GPCR,而PTHR1属于B类,其特征是参与配体识别和受体激活的大型胞外结构域[34]。我们基于上述方法,基于先前鉴定的PTHR1结合Nb(Nb)的连接合成了一组新的轭物PTHR1) [14,17]与CGS合作。CGS-Nb的生物活性PTHR1结合物通过与表达PTHR1和/或A2AR的细胞进行检测。果然,CGS-NbPTHR1仅对表达A2AR或PTHR1的细胞则不活跃(图4A和4B)。相比之下,两种受体的共表达导致CGS-Nb的生物活性强劲PTHR1 (图4C)。我们假设PTHR1和A2AR水平的绝对值和相对值变化可能导致对异异共轭反应的差异。为应对这一可能性,我们评估了CGS-NbPTHR1在受体表达水平不同、由质粒转染诱导的细胞中(图4D—4G)。CGS-NbPTHR1当使用等量质粒进行细胞转染时,诱导了强健的cAMP反应(见图4C)。还测试了质粒比例高达10:1(按w比)的比例(见图4H和S1文本表D)。采用编码A2AR:PTHR1质粒的10:1比例,CGS-NbPTHR1尽管与CGS相比,其效力仍能有效刺激cAMP反应(见图4G)。相反,当编码PTHR1的质粒水平比A2AR质粒高出10倍时,CGS-NbPTHR1显示出超过单用CGS的cAMP诱导效力(见图4D)。这些观察表明,Nb配体共轭的活性与Nb结合靶标表达水平相关。此外,Nb靶的高表达水平使异构Nb配体偶联体在相同情境下表现出超过单一配体反应的生物学活性。这些发现说明了受体共表达的原理,作为限制异源Nb配体共轭活性的手段(见图4I)。
thumbnail 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图4。 通过利用工程化双位配体靶向G蛋白偶联受体对,进行逻辑门控激活信号传导。
A–G)在与不同数量编码甲状腺激素受体-1(PTHR1)和/或A2A腺苷受体(A2AR)的质粒共转染细胞中,诱导环腺苷单磷酸(cAMP)反应的代表性浓度-反应曲线。面板A–G中的数据对应于单一代表性实验中技术重复品的平均±标准差。H)热图,描绘配体在转染不同量A2AR和PTHR1编码质粒细胞时诱导的最大cAMP反应。对应的数值数据见S1文本中的表D。I)拟议的双位配体受体依赖性活性机制。本面板中使用的PTHR1和A2AR结构均使用Alphafold2生成(参见材料与方法)。底层数据可在S1数据中找到。
https://doi.org/10.1371/journal.pbio.3003424.g004
为评估基于异源Nb配体共轭方法的适应性,我们还测量了CGS-Nb的活性PTHR1在稳定表达PTHR1的HEK293细胞系中(HEK-PTHR1,而非上述的瞬时转染)[29],随后短暂转染A2AR-Nb。6E- ALFA(见S1文本中的图J)。非共轭配体(PTH1–34,PTH1–11以及CGS被纳入对照组,以验证受体表达和功能。与上述结果一致,CGS-NbPTHR1诱导了共表达PTHR1和A2AR-Nb细胞中cAMP生成的浓度依赖性增加6E-阿 尔 法。该共轭在未表达A2AR变异的细胞中不活跃(见S1文本中的图J)。以往针对PTHR1的Nb配体偶联物研究显示,cAMP信号高度选择性激活,且未同时诱导β-停止素招募(偏倚激动剂)[17]。其他研究表明,与大多数GPCRs不同,A2AR的激活不会刺激心脏停止蛋白招募[31]。因此,未对针对这对受体的结合物进行β停止蛋白招募分析。
我们还测试了一种异构Nb配体共轭的配置,其中Nb结合和靶向配体基的方向性相反。这里有一个弱活性的PTHR1配体(PTH)1–11)与Nb有关联阿 尔 法.选择PTH的原因1–11基于Nb配体共轭的先前判例[14]。The PTH1–11-铌阿 尔 法共轭物的cAMP诱导效力相较PTH提高了20倍1–11在共表达PTHR1和A2AR-Nb的细胞中6E- ALFA(见S1文本中的图J)。相比之下,缺乏A2AR-Nb的细胞6E-ALFA对PTH几乎没有反应1–11-铌阿 尔 法,展示了信号传递时两个靶标共表达的需求。这些发现证实了异构CGS-Nb共轭在多种条件下的活性。
尽管以往研究表明,Nb配体和PTHR1均靶向的Nb配体偶联物无法诱导受体内化,但目前尚不清楚共靶向A2AR和PTHR1的Nb配体偶联物是否会有不同的行为。为探究这一问题,我们进行了基于细胞的ELISA检测受体在受体激动剂处理后细胞表面的消失情况(见S1文本中的图K)。只有典型的PTHR1激动剂PTH1–34刺激了细胞表面PTHR1水平的下降。相比之下,PTH都不是1–11-铌阿 尔 法也不是CGS-NbPTHR1降低了细胞表面检测到的PTHR1水平。这一观察可能与之前的结论有关,即PTH的1–11-Nb共轭未能诱导β心跳停止招募[17]。同样重要的是,A2AR的激活不会显著激活β-抑制素或受体内化[31,35]。先前研究表明,针对CXCR7的双价共轭物(GPCR)可诱导靶向内化[36],表明进一步研究将有助于揭示双价共轭在何情况下刺激靶点下调。
还测试了异源Nb配体共轭策略的进一步变体。我们构建了一个结合体,其中CGS与一种Nb结合,该Nb结合细胞表面蛋白复合体——Class I主要组织相容性复合体(MHC-I)[37],该复合体在大多数细胞中自然表达较高水平。CGS-Nb 的应用MHC-I与表达A2AR变体的细胞共轭,导致cAMP的产生可忽略不计(见S1文本中的L图)。我们通过流式细胞术确认了高水平的MHC-I表达和Nb与HEK细胞的结合(见S1文本中的L图)。这些发现表明,高水平表达Nb结合靶点不足以确保Nb配体偶联物的活性。
还测试了连接Nb与配体的连接子的组成和长度对生物活性的重要性。我们最初选择连接剂长度是基于我们团队之前使用CGS肽偶联物的研究,其中中长PEG连接剂有效[19]。CGS-Nb共轭结合体具有不同连接子,采用上述合成方法合成(见S1文本中的图M)。我们假设较长的联动器可能缓解距离约束,而距离约束可能对共轭活动产生负面影响。连接剂与4或24单位长的聚乙二醇(PEG)构建模块线性链一起掺入。这些偶联物在共表达PTHR1和A2AR的细胞中进行了测试。本集CGS-NbPTHR1共轭在诱导cAMP反应方面表现出类似活性(见S1文本中的图M)。包含最长连接子CGS-(PEG)的共轭24-铌PTHR1与原型CGS-Nb相比,最大响应显著减少PTHR1配体共轭(见S1文本中的图M)。这种效力下降可能与较长连接体未能保持短连接剂所带来的局部浓度增强有关。
我们还探讨了Nb配体偶联物是否可以通过连接两种在不同细胞群体中表达的受体来诱导信号传导。我们共同培养了表达PTHR1(Nb靶点)或表达A2AR(配体受体)的HEK293细胞(见S1文本中的图N)。The CGS-NbPTHR1结合物未能诱导GPCR信号的细胞间激活,表明该连接机制仅在单个细胞群体同时表达两种受体时发挥作用。
在一个独立系统中评估了依赖于两种受体共表达的受体激活的普遍性。在该新版本中,A2AR与带有N端6E标签(GLP1R-6E)的类胰高血糖素肽受体在HEK293细胞中共表达。与PTHR1类似,GLP1R是一种B类GPCR,其结合者是我们群先前表征的Nb(Nb)GLP1R) [17]。我们比较了CGS-Nb6E以及CGS-NbGLP1R与GLP1R的内源肽激动剂(GLP-pep,序列见S1文本表G)[17]。在共表达GLP1R-6E和A2AR的细胞中测试时,CGS-Nb6E以及CGS-NbGLP1R诱导的cAMP反应类似于CGS(见图5)。相比之下,这些共轭在仅表达GLP1R-6E的细胞中完全不活跃(见图5及S1文本表E),这说明了异源Nb配体共轭在逻辑门控信号传递中的适应性。
thumbnail 下载:
PPT幻灯片
巴布亚新几内亚大图
多伦多国际电影节原始图片
图5。 双位Nb配体轭轭至替代的G蛋白偶联受体对和信号通路。
A)示意图,展示生物电影Nb配体偶联激活GLP1R-A2A腺苷受体(A2AR)对的过程。B)配体诱导的环腺苷单磷酸(cAMP)在表达GLP1R-6E和/或A2AR的细胞中浓度反应评估。C)示意图显示双位共轭激活MOR-6E和PTHR1信号。注意,MOR激活诱导的细胞反应(如Γi激活、β-抑制素招募),而非A2AR激活介导。D) 配体诱导的Gαi2在表达MOR-6E和/或PTHR1的细胞中,激活(TRUPATH生物传感器,BRET)和E)β-抑制素招募(BRET)。数据点对应于代表性实验中技术重复±的平均值SD。来自三个独立实验的激动剂效力参数总结于S1文本中的表E和表F中。底层数据可在S1数据中找到。
https://doi.org/10.1371/journal.pbio.3003424.g005
上述例子涉及共靶向两个主要通过G信号的受体α其中一个受体来自B类GPCRs(PTHR1,GLP1R),另一个来自A类(A2AR)。我们想知道是否可以用类似的方法处理两种A类GPCRs,即主要通过Gα以外的通路信号的受体s(见下文)为评估第一种可能性,我们制造了由Nbs组成的结合物,这些结合物靶向具有N端(细胞外)6E标签(MOR-6E)的μ-阿片受体。我们通过MOR-6E和A2AR的(共)表达评估激活。我们首先评估了当Nb组分结合MOR-6E时,CGS-Nb偶联物是否能诱导cAMP反应。CGS-Nb6E确实在共表达MOR-6E和A2AR的细胞中,该活性对诱导cAMP反应具有活性(见S1文本中的图O),而仅表达A2AR的细胞中缺乏该活性。与上述例子相比,CGS-Nb诱导的cAMP反应的疗效更为显著6E低于仅有CGS的数字(见S1文本中的图O)。
我们实验室之前的研究表明,Nb配体共轭中,两个成分都靶向PTHR1,会强烈激活Gαs信号传递且不诱导β-抑制素2的招募,这是通路选择性信号传导的戏剧性例证[17]。通路选择性信号与PTH-Nb偶联体在两个不同受体原体间作用的能力相关。我们想知道,针对两种不同类型的受体是否也会导致通路选择性信号传导。为验证这一点,我们开发了靶向MOR-6E和PTHR1的Nb配体偶联物。值得注意的是,激活MOR或PTHR1已知会刺激β-抑制素的招募,尽管这些受体通过相反的G蛋白通路(Gα)发出信号我与Gαs分别是 。
我们产生了由Nb组成的共轭PTHR1以及MOR激动剂肽Dynorphin A(DynA8-Nb)的片段PTHR1,详见S1文本中的表G,关于DynA8序列),采用类似于合成Nb-TTH激动剂的方法[17]。DynA8-NbPTHR1与典型的MOR激动剂(DAMGO)、DynA8本身以及由DynA8与阴性对照Nb结合的结合物进行了比较,Nb结合了细胞表面缺失的表位(DynA8-Nb)。阴性).我们评估了DynA8-NbPTHR1在测量Gα的检测中i2激活[32]。DAMGO和DynA8在单表达MOR-6E的细胞以及与MOR-6E和PTHR1共转染的细胞中,在刺激Γγ方面表现出相似活性(见图5和S1文本中的表F)。相比之下,DynA8-NbPTHR1在仅表达MOR-6E的细胞中,其活性明显低于同时表达MOR-6E和PTHR1的细胞,后者其活性与DAMGO和DynA8相似(见图5和S1文本表F)。
还通过测量GPCR激活后质膜招募β-抑制蛋白的检测,评估了DynA8-Nb偶联物[31]。令人惊讶的是,DynA8-NbPTHR1在MOR-6E和PTHR1共表达时,其刺激β-抑制素2的效力比DAMGO或DynA8高出>10倍(见图5)。DynA8-NbPTHR1仅表达MOR-6E的细胞中,完全无活性以刺激停止蛋白招募(见图5及S1文本表F)。这些发现与以往仅靶向PTHR1的双中心Nb配体偶联结果形成鲜明对比,后者在β-停止蛋白2招募中表现为微乎其微[17]。
以进一步了解DynA8-Nb增强的β抑制素招募机制PTHR1相较于传统MOR配体,我们进行了额外的实验。我们通过转染改变编码MOR-6E和PTHR1的质粒水平,以诱导受体表达。随后,我们测量了这些转染细胞中DynA8-Nb偶联物的活性。相比PTHR1,使用较多MOR-6E编码质粒(MOR-6E与PTHR1的比例为3:1和10:1)导致DynA8-Nb活性减弱PTHR1相对于β-阿莱斯顿招募测定中的DAMGO(S1文本中的图P)。相比之下,使用更高水平的PTHR1编码质粒(MOR-6E与PTHR1的比率分别为1:3和1:10)则产生了DynA8-NbPTHR1相对于DAMGO表现出更高的活性(见S1文本中的图P)。这些数据表明,高水平的Nb靶表达导致Nb配体结合物的活性高。这些发现出乎意料,首次证明了Nb配体共轭两个受体能够强力刺激除Gα以外的通路信号传导s(Gα我以及β-停止),其活性仅超过母配体。
讨论
本研究开发的双位共轭物带来了两项重大进展。首先,我们描述了由A2AR小分子激动剂(CGS21680)制成的Nb配体共轭物(见图1)。这代表了过去研究的重大扩展,过去用于共轭合成的配体仅限于肽激动剂[14–17,38]。许多GPCR仅被非肽小分子激活[1],这里描述的方法应有助于开发Nb配体轭联物以靶向这些受体,如上述CGS-Nb共轭物所示。其次,我们利用双位共轭通过跨越两个受体原传体诱导激活的能力,实现对单细胞表达受体对的选择性靶向(见图4和图5)。我们表明,这类Nb配体偶联体仅在Nb和配体靶共表达时表现出活性。这种双靶点依赖信号为生成仅在特定生物生态位内活性的结合物提供了有前景的途径,同时最大限度地减少靶向、组织外的副作用[39]。A2AR在不同组织中的表达[40,41]为探讨组织限制激活广泛表达受体的后果提供了机会。例如,A2AR在大脑中激活的功能效应可能与免疫细胞激活时观察到的不同[6]。CGS-Nb偶联物表现出此类研究所需的一些特性,尽管在天然组织环境中仍需进一步探索。
这些研究的一个显著观察是,CGS-Nb偶联物在工程化A2AR中诱导的信号响应持续时间更长,相较于单独CGS(见图2和图3)。这一观察表明,双位共轭的持续激活与Nb和CGS不同结合位点有关,合作相互作用导致与受体的长期结合。目前尚不清楚单个共轭物的Nb和配体组分是否同时结合,还是一次只有一个组分能结合。对连接更长的CGS-Nb偶联结合体的研究表明同时结合是可行的,但可能不是延长信号响应的重要因素(见S1文本中的图M)。对结合受体的CGS-Nb偶联物的结构研究对于解决这些问题至关重要。长效配体对A2AR具有特别的重要性,A2AR是多种疾病的成熟治疗靶点。关于人类A2AR的研究显示,配体活性在体内与受体停留时间之间存在强烈相关性。例如,长效A2AR激动剂UK-432097在治疗肺部炎症方面的强效性表明延长驻留时间可能提升治疗效果[6,42]。本研究开发的双位靶向策略为合理设计具有良好药理特性的配体提供了一种手段。
本研究中描述的方法与以往开发能够选择性定位预先指定的GPCR组装体的分子的努力有相似之处[43]。GPCR单体如A2AR在单细胞中共表达时,常与其他GPCR在膜内二聚或寡聚化[44,45],这为开发高度特异性调节受体功能工具提供了诱人机会[46,47]。然而,设计具有GPCR二聚体或高阶寡聚体特异性的配体仍然具有挑战性。我们推断,同时利用抗体(纳米抗体)和配体结合,可以为选择性靶向GPCR异源体提供一条路径[3]。我们已经证明,这种Nb配体共轭物仅在表达两个靶点(“AND”逻辑门)的细胞上才有活性[8]。虽然这些特性可能通过传统配体设计策略实现,但Nb配体共轭的模块化可能使得更高效的扩展到新的受体对。多价共轭的原位形成提供了另一条有吸引力的前进路径[48]。
新兴证据强调GPCR组装体在介导此前分配给单个受体的生化过程中的功能性作用[46]。研究表明,GPCR组装体可由受体组成,这些受体通过相同的G蛋白通路进行信号(例如,通过Gα的A2AR-β1/β2肾上腺素能受体对)s)或通过相反的G蛋白通路(例如A2AR-D2R对,通过Gαs以及 Gα我互动)。关于GPCR组装如何整合配体刺激和环境线索以产生独特细胞反应的全面理解仍然未知。本研究了当Nb配体偶联靶向时,表达多种GPCR对(包括不同类别及不同同源G蛋白(如A2AR-PTHR1、A2AR-GLP1R、A2AR-MOR)的信号传导(见图5)。这些实验揭示了几个有趣的趋势。Nb配体添加诱导信号反应最强烈的细胞中,Nb靶向受体表达高于配体结合受体。我们还首次证明,除了Gα外,双位共轭还可以通过信号伴侣诱导信号传导s(Gα我, β-arrestin)。一个令人惊讶的观察是,一种靶向表达PTHR1和MOR的双位共軛物(DynA8-Nb)比单独的配体(DynA8)更能强健地诱导停止蛋白招募(见图5)。这些结果与以往仅针对PTHR1的双位配体偶联表现出强烈G蛋白激活且抑制素招募极少的例子形成对比[17]。这些发现提出了关于共表达GPCR对产生专门信号反应的能力的有趣问题,相较于受体单独表达的情况。这些趋势在生理学环境中尤为重要,单细胞共表达多种膜蛋白,可能扩展受体在原生细胞环境中的复杂性。
使用Nb配体偶联物进行逻辑门控受体激活,为未来研究提供了若干有吸引力的机会。例如,活化胰高血糖素家族受体(GLP1R、GIPR、GCGR)在治疗2型糖尿病和肥胖方面具有治疗效果[49];然而,这些受体在多个组织中表达[50]。组织特异性药理学对整体治疗疗效和副作用特征的贡献尚不明确。逻辑门控双位共轭物可促进基于次级细胞标记共表达的细胞类型特异性受体激活,从而实现机制性研究。我们策略的模块化和可编程特性,可能使得在体内作用部位为多种生理相关GPCRs设计配体成为可能。向生理学新领域的扩展将受益于识别与GPCR结合的Nbs的新方法[11,51–55]。还需要进一步研究设计能够跨越两个细胞(细胞间功能)来作用于异质组织中跨细胞类型的Nb配体共轭。
材料与方法
材料
指定的试剂采购自商业供应商:PTH1−34(Genscript,RP01001)、DAMGO(开门化工,编号#21553)、D-荧光素(GoldBio,LUCNA-1G)、辅腔肠素prolume purple(纳米光技术,#369-1)、CGS21680(SelleckChem,#S2153)、XAC(开曼化工,编号#23077)和THPTA(载体实验室,#CCT-1010-100)。溶剂(二甲基甲酰胺、二氯甲烷、乙腈、二乙醚和二甲基硫氧化物)及其他化学试剂(二异丙基甲基亚胺、二异丙基碳二亚胺、奥西玛、三氟乙酸、三异丙基硅烷)均从Sigma Aldrich采购。其他试剂则如相关图文和方法所述,在内部合成(或购买)。
细胞培养与分析
细胞培养、细胞转染及配体结合分析方法,均见S1文本。使用商业基因合成与克隆服务(Genscript)制备的质粒被用于转染细胞以表达感兴趣的GPCRs。
cAMP反应的测量(包括冲洗和竞争测定)
通过cAMP荧光素酶报告测定,通过Gs信号通路对受体激活进行了定量[28,29]。表达cAMP报告器和目标受体的HEK293细胞被蛋白酶化并植入白壁96孔平透明底板(Corning #3610)。在生物测定中使用前,细胞已培养至完全融合。在生物测定之前,已移除培养基,并去除无血清的一氧化碳2加入了含有0.5 mM D-荧光素的独立培养基。使用多孔板读器(Biotek Neo2板读器)监测10分钟,以建立稳定基线。CO中稀释的配体2-在井中加入独立介质,最终井容积为100微升。发光响应每2分钟测量一次,共计12分钟。峰值发光响应(通常测量于12米处)用于生成浓度-响应曲线。利用GraphPad Prism的三参数S形剂量-响应模型(对数对应反应)拟合浓度-反应曲线,生成EC50以及E麦克斯值。
为了测量cAMP冲洗反应,细胞被激动剂刺激,持续一段指定时间(通常为12米),如上所述(配体加持期)。此时,含有配体的培养基被丢弃。新指挥官2在所有孔中加入含有新鲜荧光素的独立培养基,并每2分钟测量一次发光反应,持续30分钟(配体脱离阶段)。对于竞争冲刷检测,实验方案如上所述,但竞争者是在配体脱离阶段加入的。冲刷测定的浓度-响应曲线通过量化冲刷阶段的发光动力学测量AUC生成。在冲刷阶段的每个时间点的不确定性测量数据被传播,以提供AUC测量的标准误差值,AUC在相关图表中以误差条表示。
生物发光共振能量转移(BRET)检测β-阻滞素易位和G蛋白运输(G)我特鲁帕斯和Gs解离)
表达目标受体的HEK293细胞被植入一个10厘米的培养皿中,使用约2,250,000个细胞,并在37°C下粘附并生长12小时。 随后,依附细胞被转染编码膜系结BRET受体质粒(rGFP-CAAX或rGFP-FYVE,1,008 ng)和RlucII结合的β-arrestin 2 BRET供体质粒(β-arrestin 2-RlucII,72 ng),如前所述,如前所述[17,31]。对于Gαs解离BRET测定,1008 ng rGFP-CAAX质粒和144 ng Gαs-RlucII质粒被转染[17,31]。
对于TRUPATH G我- 活化测定,1微克G。我TRUPATH质粒编码Gαi2,Gβ3,以及Gγ9用于转染[32]。转染细胞再培养20–24小时。转染后,细胞被重新悬浮在标准培养基中,并以密度为每孔70,000个的白色透明底96孔板中播种。生长24小时后,板化细胞在由Hanks缓冲盐水溶液组成的分析缓冲液中孵育5米,补充5 mM HEPES和1.3 μM Prolume Purple,随后加入连续稀释配体或纳米体-配体偶联物。BRET 信号通过 Biotek Neo2 板读器测量,并使用适当滤波器测量 400 和 510 nm 的发射。板式读数约需150秒,重复总计30–40分钟。每个时间点计算了每口井的BRET比值(515/410纳米)。通过使用GraphPad Prism量化BRET比率动力学测量的AUC生成了浓度-响应曲线。标准误数是通过传播每个时间点测量的标准差来计算的。
Alphafold赋能受体结构建模
在线工具ColabFold[56]实现了Alphafold2,用于预测带标记的受体和Nb受体复合物[57]。应用了默认的AlphaFold2设置,导致每个输入序列生成五个模型。所有图形均采用PyMOL生成顶级模型。在某些情况下,模型通过PyMOL中的“align”命令与相关的实验确定结构进行比对。
化学合成
关于肽和小分子的合成、纯化和分析的描述见S1文本的合成方法部分及S1文本中的图A和B。这些化合物的表征见S1正文中的表A和表B。
蛋白质表达与通过分选标记
关于使用Sortase A表达和纯化Nbs及其标记的详细内容见S1文本。Nb和Nb共轭物的质谱表征见S1正文表B。
统计分析
数据归一化仅在图例中明确提及时执行。重复数据以平均±标准差或平均±标准误表示,样本量为n。统计检验采用单向方差分析(ANOVA)评估统计显著性,并进行Dunnett事后更正。统计比较使用GraphPad Prism进行。
支持信息
补充数据、表格和方法。
显示1/3:pbio.3003424.s001.pdf
跳转到图分享导航
抱歉我们无法加载您的数据。
1 / 3
下载
图格分享
第一季文本。 补充数据、表格和方法。
https://doi.org/10.1371/journal.pbio.3003424.s001
(PDF)
S1数据。 用于生成主文中显示的图形的原始数据。
https://doi.org/10.1371/journal.pbio.3003424.s002
(XLSX)
S2数据。 用于生成图形的原始数据,显示在S1文本中。
https://doi.org/10.1371/journal.pbio.3003424.s003
(XLSX)
确认
我们感谢蒙特利尔大学的M. Bouvier和犹他大学的J. English提供用于基于RET的质粒,用于β-阿雷斯汀和G蛋白信号传导的基于BRT的检测。我们认可NIDDK(J. Lloyd)内部质谱核心设施,用于肽和轭物的表征。感谢S. Ferre(NIH)、K. Jacobson(NIH)和F. Ciruela(巴塞罗那大学)带来的有益讨论。
引用
1.张M、陈T、陆X、兰X、陈Z、Lu S. G蛋白偶联受体(GPCRs):结构、机制和药物发现的进展。信号转导目标。2024;9(1):88.PMID:38594257
查看文章PubMed/NCBI谷歌学术
2.斯洛斯基轻型机枪,卡隆机枪,巴拉克长枪。偏置变构调制剂:GPCR药物发现的新前沿。《趋势药学》2021年;42(4):283–99.PMID:33581873
查看文章PubMed/NCBI谷歌学术
3.萨奇德夫·S,卡巴尔特贾·CC,切洛哈右翼。利用多价偶联物靶向细胞表面蛋白的策略与化学生物学。《细胞生物学方法》2021年;166:205–22.PMID:34752333
查看文章PubMed/NCBI谷歌学术
4.周Q、杨D、吴M、郭毅、郭W、钟L等。A类GPCRs的常见激活机制。Elife。2019;8:e50279。PMID:31855179
查看文章PubMed/NCBI谷歌学术
5.Jacobson KA,Gao Z-G,Matricon P,Eddy MT,Carlsson J. 腺苷A2A受体拮抗剂:从咖啡因到选择性非黄嘌呤。《布里达尔·法拉科尔杂志》。2022;179(14):3496–511.PMID:32424811
查看文章PubMed/NCBI谷歌学术
6.雅各布森·KA,托什·DK,贾因·S,高Z-G。临床前和临床开发中的历史及当前腺苷受体激动剂。前细胞神经科学。2019;13:124.PMID:30983976
查看文章PubMed/NCBI谷歌学术
7.赵Z、Ukidve A、Kim J、Mitragotri S。组织特异性药物递送的靶向策略。细胞。2020;181(1):151–67.PMID:32243788
查看文章PubMed/NCBI谷歌学术
8.陈Z、基布勒RD、亨特A、布什F、珀尔J、贾M等。蛋白质逻辑门的新设计。科学。2020;368(6486):78–84.PMID:32241946
查看文章PubMed/NCBI谷歌学术
9.奥斯廷迪SC、里纳尔迪DA、佐姆GG、韦斯特MJ、波莱特D、阿尔-塔米米K等。逻辑门控抗体对选择性作用于共表达两种抗原的细胞。纳特生物技术。2022;40(10):1509–19.PMID:35879362
查看文章PubMed/NCBI谷歌学术
10.彼得森·SM,哈钦斯首席大法官,胡中锋,马图尔·M,萨拉梅·JW,阿克斯罗德·F等。发现并设计了G蛋白偶联受体靶向抗体。专家观点药物分析。2023;18(4):417–28.PMID:36992620
查看文章PubMed/NCBI谷歌学术
11.萨洛姆·D、吴A、刘CC、帕尔切夫斯基·K。纳米抗体对G蛋白偶联受体结构生物学的影响及其作为治疗剂的潜力。Mol Pharmacol。2024;106(4):155–63.PMID:39107078
查看文章PubMed/NCBI谷歌学术
12.切洛哈右翼,哈曼德·TJ,维涅·C,施瓦茨·图,普洛伊赫·HL。探索纳米抗体的细胞生物化学。《生物化学杂志》2020年;295(45):15307–27.PMID:32868455
查看文章PubMed/NCBI谷歌学术
13.哈默斯,SMWR,博伊尔,夏普,TH。工程激动性双特异性以研究距离对表面介导补体激活的影响。《免疫学杂志》。2024;213(2):235–43.
查看文章谷歌学术
14.切洛哈右翼、费舍尔足球协会、伍德汉姆AW、戴利E、苏明斯基N、加德拉TJ等。通过纳米体系留改进的GPCR配体。国家公社。2020;11(1):2087.PMID:32350260
查看文章PubMed/NCBI谷歌学术
15.布拉加·埃米迪奥·N,切洛哈右翼。半合成纳米抗体-配体偶联物表现出可调信号特性,并在神经激肽受体-1处增强转录输出。《蛋白质科学》2024年;33(2):e4866。PMID:38088474
查看文章PubMed/NCBI谷歌学术
16.布拉加·埃米迪奥·N,斯莫尔·BM,凯勒·阿肯色,切洛哈·右翼,温格勒·LM。纳米抗体介导的血管紧张素受体双重结合拓宽了偏置配体药理学。Mol Pharmacol。2024;105(3):260–71.PMID:38164609
查看文章PubMed/NCBI谷歌学术
17.萨奇德夫·S,克里默,文学学士,加德拉·TJ,切洛哈右翼。通过纳米抗体连接GPCR配体高度偏向的激动剂。国家公社。2024;15(1):4687.PMID:38824166
查看文章PubMed/NCBI谷歌学术
18.卡巴尔特贾·CC,萨奇德夫·S,切洛哈·右翼。纳米体-表位标签相互作用的表征及其在受体工程中的应用。ACS化学生物学,2022年;17(8):2296–303.PMID:35930411
查看文章PubMed/NCBI谷歌学术
19.卡巴尔特贾·CC,萨奇德夫·S,切洛哈·右翼。利用纳米抗体-表位标签对快速共价标记活细胞膜蛋白。生物结合化学 2022;33(10):1867–75.PMID:36107739
查看文章PubMed/NCBI谷歌学术
20.勒邦G、爱德华兹PC、莱斯利AGW、泰特CG。CGS21680与人类腺苷A2A受体结合的分子决定因素。Mol Pharmacol。2015;87(6):907–15.PMID:25762024
查看文章PubMed/NCBI谷歌学术
21.拉拉纳加-维拉A、托蒂KS、弗拉托JS、哈拉奇AJ、沃尼克E、拉奥H等人。新型阿仑膦酸CGS21680结合物可减少骨吸收,并在绝经后骨质疏松和炎症性骨溶解小鼠模型中诱导新骨形成。关节炎 RES THER。2022;24(1):265.PMID:36494860
查看文章PubMed/NCBI谷歌学术
22.雅各布森KA,潘内尔LK,吉XD,贾维斯中场,威廉姆斯中场,哈奇森AJ等。A2腺苷受体的激动剂衍生分子探针。我很懂。1989;2(4):170–8.PMID:2561548
查看文章PubMed/NCBI谷歌学术
23.Götzke H、Kilisch M、Martínez-Carranza M、Sograte-Idrissi S、Rajavel A、Schlichthaerle T 等。ALFA-tag 是一种高度多功能的工具,用于纳米抗体生物科学应用。国家公社。2019;10(1):4403.PMID:31562305
查看文章PubMed/NCBI谷歌学术
24.凌J,切洛哈右翼,麦考尔N,孙Z-YJ,瓦格纳G,普洛伊HL。一种纳米抗体能够识别E2泛素偶联酶UBC6e中14残基肽表位,从而调节其活性。Mol免疫。2019;114:513–23.PMID:31518855
查看文章PubMed/NCBI谷歌学术
25.布劳恩·MB,特兰克尔·B,科赫·PA,埃梅莱·F,韦斯·F,波茨·O等。头锁肽——一种新型高亲和力且多功能的肽结合纳米抗体,用于蛋白质组学和显微镜学。科学报告 2016;6:19211。PMID:26791954
查看文章PubMed/NCBI谷歌学术
26.基尔霍夫 A、赫尔玛 J、施密特尔斯 K、弗劳尔 C、奎 S、卡尔彻 A 等。利用纳米抗体调节活细胞中的蛋白质特性。自然分子结构生物学,2010年;17(1):133–8.PMID:20010839
查看文章PubMed/NCBI谷歌学术
27.布拉加·埃米迪奥·N,切洛哈右翼。分酶介导标记:在位点特异性蛋白功能化领域拓展前沿,开辟了新的研究方向。Curr Opin 化学生物学。2024;80:102443。PMID:38503199
查看文章PubMed/NCBI谷歌学术
28.Binkowski BF,Butler BL,Stecha PF,Eggers CT,Otto P,Zimmerman K 等。一种具有更大动态范围的发光生物传感器,用于细胞内cAMP。美国化学学会化学生物学,2011年;6(11):1193–7.PMID:21932825
查看文章PubMed/NCBI谷歌学术
29.切洛哈 RW、前田A、迪恩T、加德拉 TJ、盖尔曼SH。多肽药物的骨架修饰改变体内作用持续时间。纳特生物技术。 2014; 32(7):653–5. PMID:24929976
查看文章PubMed/NCBI谷歌学术
30.霍夫曼 C,卡斯特罗 M,林肯 A,勒尔斯 R,希尔 SJ,维舍尔 HF。配体在G蛋白偶联受体的驻留时间——为什么我们应该花时间研究它。Mol Pharmacol。 2015; 88(3):552–60. PMID:26152198
查看文章PubMed/NCBI谷歌学术
31.Avet C、Mancini A、Breton B、Le Gouill C、Hauser AS、Normand C 等。效应膜易位生物传感器揭示了100个治疗相关GPCRs的G蛋白和βarrestin偶联谱。Elife。 2022; 11:e74101。PMAD:35302493
查看文章PubMed/NCBI谷歌学术
32.Olsen RHJ、DiBerto JF、English JG、Glaudin AM、Krumm BE、Slocum ST 等。TRUPATH,一个用于探测GPCR换导体的开源生物传感器平台。自然化学生物学,2020年; 16(8):841–9. PMID:32367019
查看文章PubMed/NCBI谷歌学术
33.雅各布森·KA,乌克纳·D,柯克·KL,达利·JW。[3H]黄氨酸胺与1,3-二丙基-8-苯基黄黄同系:腺苷受体的受体拮抗剂放射配体。1986年美国国家科学院院刊;83(11):4089–93.PMID:3012550
查看文章PubMed/NCBI谷歌学术
34.切洛哈右翼,盖尔曼短腿,维拉尔达加,J-P,加德拉,TJ。PTH受体-1信号机制见解及治疗前景。内分泌自然牧师。2015;11(12):712–24.PMID:26303600
查看文章PubMed/NCBI谷歌学术
35.泽祖拉·J,弗赖斯穆斯·M。A(2A)腺苷受体:具有独特特征的GPCR?《布里达尔·法拉科尔杂志》。2008;153 Suppl 1(Suppl 1):S184–90。PMID:18246094
查看文章PubMed/NCBI谷歌学术
36.潘斯·K、格拉梅斯帕彻·JA、伯恩斯二世、萨朗桑·F、塞拉诺·J-AC、科顿·AD等。模块化细胞因子受体靶向嵌合体,用于细胞表面和细胞外蛋白的靶向降解。纳特生物技术。2023;41(2):273–81.PMID:36138170
查看文章PubMed/NCBI谷歌学术
37.多曼斯卡·K、范德哈根·S、斯里尼瓦桑·V、帕登·E、杜普·F、马尔克斯·JA等。一种被纳米体捕获的结构域交换二聚体的淀粉异源β2-微球蛋白变体的原子结构。2011年美国国家科学院院刊;108(4):1314–9.PMID:21220305
查看文章PubMed/NCBI谷歌学术
38.切洛哈右翼,费舍尔足协,加德拉TJ,普洛伊HL。通过间接抗体介导的配体连接激活G蛋白偶联受体。RSC化学生物学,2021年;2(6):1692–700.PMID:34977584
查看文章PubMed/NCBI谷歌学术
39.Simic MS、Watchmaker PB、Gupta S、Wang Y、Sagan SA、Duecker J 等。编程组织感应T细胞,将治疗药物传递到大脑。科学。2024;386(6726):eadl4237。PMID:39636984
查看文章PubMed/NCBI谷歌学术
40.彼得弗伦德 RA,麦考林 M,古塞拉 J,芬克 JS。人类A2a腺苷受体基因的表征与表达。《神经化学杂志》。1996;66(1):362–8.PMID:8522976
查看文章PubMed/NCBI谷歌学术
41.王M、李Z、宋毅、孙Q、邓L、林Z等。腺苷A2A受体的遗传标记揭示了其在脑区的异质表达。前神经神经分析。2022;16:978641.PMID:36059431
查看文章PubMed/NCBI谷歌学术
42.霍瑟尔 JD、郭 D、萨尔达 S、谢泼德 RJ、陈 H、Keur W 等。由缓慢解离动力学驱动的腺苷A2A受体激动剂持续效应的结构-活性关系。Mol Pharmacol。2017;91(1):25–38.PMID:27803241
查看文章PubMed/NCBI谷歌学术
43.Newman AH, Battiti FO, Bonifazi A. 2016 Philip S. Portoghese 药物化学讲座:设计用于G蛋白偶联受体的双价或双位分子。整体大于部分之和。医学化学杂志 2020年;63(5):1779–97.PMID:31499001
查看文章PubMed/NCBI谷歌学术
44.阮KDQ、维格斯M、塞法E、塞帕拉S、胡佛JP、肖嫩巴赫NS等。人类腺苷A2A受体的同源寡聚是由内在无序的C端驱动的。Elife。2021;10:e66662。PMID:34269678
查看文章PubMed/NCBI谷歌学术
45.Ferré S, Ciruela F, Casadó V, Pardo L. G蛋白偶联受体的寡聚化:仍然存疑吗?2020年《分子生物学研究进展》;169:297–321.PMID:31952690
查看文章PubMed/NCBI谷歌学术
46.戴尔 NC,约翰斯通 EKM,普弗莱格 KDG。GPCR异源体:其分类、功能及生理相关性的概述。前叶内分泌醇(洛桑)。2022;13:931573.PMID:36111299
查看文章PubMed/NCBI谷歌学术
47.刘武、王D、王L、胡S、江毅、王毅等。受体二聚体与偏置配体:靶向G蛋白偶联受体的新策略。药物。2025;269:108829.PMID:40023322
查看文章PubMed/NCBI谷歌学术
48.萨哈耶稣会士,切洛哈右翼。通过纳米抗体结合的化学诱导二聚化促进原位配体组装和按需激活GPCR。JACS Au。2024;4(12):4780–9.PMID:39735930
查看文章PubMed/NCBI谷歌学术
49.雅斯特雷博夫·AM,卡普兰·LM,弗里亚斯·JP,吴Q,杜Y,古尔布兹·S等。三激素受体激动剂逆肽治疗肥胖——一项二期临床试验。2023年《N Engl J Med.》;389(6):514–26.PMID:37366315
查看文章PubMed/NCBI谷歌学术
50.德鲁克DJ。胰高血糖素样肽1的作用机制及治疗应用。细胞甲基。2018;27(4):740–56.PMID:29617641
查看文章PubMed/NCBI谷歌学术
51.麦克马洪C、拜尔AS、帕斯科卢蒂R、韦格雷基M、郑S、翁JX等。酵母表面显示平台,用于快速发现构象选择性纳米体。自然结构分子生物学,2018年;25(3):289–96.PMID:29434346
查看文章PubMed/NCBI谷歌学术
52.克罗尔 PJ、范 J、杨 H、范戴克 D、安 Z、金 KB 等。利用悬浮细胞进化方法发现靶向多通跨膜蛋白的抗体。细胞代表法。2023;3(3):100429.PMID:37056366
查看文章PubMed/NCBI谷歌学术
53.施利姆根RR、彼得森FC、赫克斯R、斯米特MJ、麦考维JD、沃尔克曼BF。细胞外GPCR纳米抗体选择性和拮抗性的结构基础。国家公社。2024;15(1):4611.PMID:38816420
查看文章PubMed/NCBI谷歌学术
54.余志、库马尔·A、张X、马丁·C、范·霍尔斯贝克·K、赖亚·P等。纳米抗体拮抗剂靶向μ阿片受体的结构基础。国家公社。2024;15(1):8687.PMID:39384768
查看文章PubMed/NCBI谷歌学术
55.丰丹·T、布施·A、拉埃尔曼斯·T、德·塞斯科·S、梁永荣、雅科拉·V-P等。人类黑色素皮质素-4受体特异性直立纳米抗体激动剂的结构阐明。国家公社。2024;15(1):7029.PMID:39353917
查看文章PubMed/NCBI谷歌学术
56.Mirdita M、Schütze K、Moriwaki Y、Heo L、Ovchinnikov S、Steinegger M. ColabFold:让蛋白质折叠普及。自然方法。2022;19(6):679–82.PMID:35637307
查看文章PubMed/NCBI谷歌学术
57.萨奇德夫·S、罗伊·S、萨哈·SJ、赵G、库马里亚·R、克里默·BA等。AlphaFold建模用于阐明纳米抗体-肽表位相互作用的评估。《生物化学杂志》2025年;301(7):110268.PMID:40409557
查看文章PubMed/NCBI谷歌学术
2024-12-20
·动脉网
2024年,医疗器械行业普遍承压,但也孕育着新的发展机遇。在2024年,医疗器械行业经历了市场验证的关键时期,面对医疗设备招标采购的推迟、带量采购的常态化以及宏观经济的挑战,行业增长面临不小的压力。动脉智库观察到行业出现了三大显著变化:首先,行业增长的动能正在发生转变,成熟产品的利润空间受到挤压,这要求企业对成熟产品进行更精细化的运营管理,同时,差异化创新产品的市场渗透率正在提升,企业正积极寻求进入高增长的赛道,拥有多层次、综合解决方案的企业更能适应市场的变化。其次,行业出清的趋势正在加剧,2024年创新医疗器械企业的生存压力增大,不少企业开始探索转型之路,行业并购整合趋势也在加速。第三,从支付角度来看,医保控费成为大势所趋,集采常态化运行,成为决定企业生死存亡的关键因素。
为了深入理解国内医疗器械的发展方向,本报告将从宏观市场环境、准入改革、赛道更迭、投融资趋势、出海探索等多个维度回顾2024年医疗器械行业的发展,并展望2025年的行业趋势。总体而言,创新医疗器械领域是长坡厚雪的赛道,唯有持之以恒的耐心,方能迎来成长的硕果。
01
数说2024年医疗器械:行业承压下的机遇和挑战
2024年,国内创新医疗器械整体增长承压,但长期来看增长动力十足。国内创新医疗器械行业面临医疗反腐、集采扩面、招投标延迟和医保控费等多重挑战,导致整体增长势头受到抑制。然而,从长远来看,我国医疗器械行业仍受到三大核心动力的持续推动。首先,人口老龄化趋势不断加剧,带来了对长期医疗需求的增长;其次,国家对医疗领域的投入持续增加,医疗卫生机构数量稳步上升;最后,技术创新为行业发展注入了新活力。医学科技创新作为医疗行业新质生产力的体现,不仅是推动经济发展的关键因素,也是促进行业高质量发展的重要引擎。因此,尽管短期内行业增长可能面临波动,但长期来看,这三大驱动力将为医疗器械行业带来持续而强劲的增长潜力。
2019—2023年中国医院数量(单位:家)
数据来源:2019-2023医疗卫生统计公报
医疗设备更新换代有望拉动2025的增长,10万亿元化债政策提供资金保障。2024年底出台的政策支持地方政府化解债务风险,通过增加债务额度来支持地方化解隐性债务,这将为地方腾出更多财力以促进发展和保障民生。这将使2025年市场出现回暖,这一趋势已在2024年第四季度的招投标数据中得到体现,众成医械的统计数据显示,自11月以来,设备更新招标项目金额显著增长。
医疗设备迭代主要工作方案
数据来源:安徽省推进卫生健康领域设备迭代升级工作方案
成本管控+进入高增长赛道策略组合助力企业降低带量采购影响。降低带量采购对业绩的影响需要两方面的关键举措策略。一方面内部需要降本增效,核心举措包括成本管控、进入高增长的赛道。另一方面需要积极应对带量采购,精准报价,掌握分组优势,抓住带量采购带来渗透率提升、临床使用产品结构变化和国内企业市场份额提升等机会。
全球企业走出带量采购影响关键策略
数据来源:动脉智库
投融资数据:投融资进入下滑阶段,并购数据增长。在2024年,中国医疗投资领域依旧保持着谨慎态度,投资活动有所减少。2023年,创新医疗器械领域的融资事件共计307起;而截至2024年10月,公开的创新医疗器械融资事件为240起,显示出整体融资环境已回落至四年前的状态。导致创新医疗器械融资持续下降的原因包括退出渠道的阻碍、二级市场医疗器械估值的低迷以及募资难度的增加等多重因素。
2019-2024创新医疗器械私募数(单位:起)
数据来源:动脉智库、浩悦资本
从行业来看,创新医疗器械分布在医疗设备、高值耗材、体外诊断、上游供应链四大类别中。其中医疗设备中内窥镜、手术机器人、脑机接口、光电医美设备几大细分领域融资事件数量靠前;高值耗材中心血管、眼科、医美、微创外科融资事件排名前列;体外诊断领域中分子诊断平台(包括数字PCR、肿瘤早筛、测序服务)、气液相和质谱仪器、代谢组学、蛋白组学、空间组学等临床应用开发和服务商,以及上游、流式荧光在免疫领域应用等领域的融资事件较为频繁。此外,上游供应链赛道崛起,影像设备核心零部件、CDMO、核心上游材料都有数起融资。值得一提,GLP-1的火热带动了上游注射笔融资的火热。
2024年创新医疗细分领域融资数量 (单位:起)
数据来源:动脉智库
近期,医疗器械行业的并购活动呈现出升温趋势。推动2024年国内医疗器械并购关注度提升的因素主要包括:技术创新的驱动、市场需求的扩张、行业整合的加速以及政策环境的支持。2024年国内医疗器械二级市场发生了多起并购整合交易,包括迈瑞医疗并购惠泰医疗、中国生物制药收购科创板浩欧博控制权。我国上市医疗器械公司数量超过170家,IVD企业超过80家,二级市场并购整合空间仍然很大。政策层面多次强调并购重组的重要性,并出台相关政策深化上市企业并购重组市场化改革。可以预见,未来国内医疗器械二级市场有望通过并购重组方式优化资源配置、激发市场活力。
创新审批数据:创新彰显产业韧性。在行业发展承压之际,创新仍然是对抗内卷最好的方式。2024年国内医疗器械在创新医疗器械审批方面也有所变化。据高端医械院数据中心最新数据显示,截至2024年12月16日,共有66个产品成功进入国家级创新医疗器械审批通道。而2023年进入国家级器械优先审批通道的产品总数为67件。
从这两年的数据来看,国内企业进入国家级医疗器械优先审批通道的产品数量增长并不显著。动脉智库分析,这一现象可能源于两个方面:首先,面对市场压力,国内医疗器械企业在创新研发方面的投入有所减少;其次,经过前几年的快速发展,许多企业已经完成了产品的准备和管线布局,目前正将重点转向实现产品的大规模商业化。这表明,尽管创新步伐有所放缓,但企业正逐步从研发阶段过渡到市场推广和应用阶段。
02
年度产业之问:细分领域发展分化,发展逻辑重构
医疗器械产业以其多样化的细分市场而著称,每个细分市场都有其独特的发展路径和逻辑。本章节将深入探讨2024年创新医疗器械各主要细分领域的最新动态和未来发展趋势,揭示这些领域在技术革新、市场需求、政策导向等方面的显著变化。
我们将对创新医疗器械产业进行细致划分,主要分为四个核心板块:高值耗材、医疗设备、体外诊断、上游供应链和核心零部件。接下来,我们将深入分析这些板块内各个细分领域所经历的主要变化。
● 高值耗材
冠脉介入集采提升药球、冲击波系统渗透率。冠脉介入产业变化主要体现在持续的渗透率提升和创新医疗器械产品用量增加两方面。虽然冠脉支架集采后价格下降加快,但用量提升明显且国产替代效应明显。此外,带量采购也推动了药物球囊、冠脉冲击波治疗系统等创新产品渗透率提升,例如药物球囊渗透率从2020年的不到5%提升到2023年的18%。药物球囊放置前需要血管预处理,因此药物球囊的使用将推动血管预处理产品的增长。
冲击波球囊在处理中重度钙化病变方面显示出良好的效果和更高的安全性。它是目前唯一能够有效处理血管深层钙化病变的器械,通过精准输送声压力波到钙化部位,震裂或震松血管内的钙化斑块,恢复血管弹性,保持血流通畅,完成冠脉血管的重塑。与传统钙化处理技术相比,冲击波球囊导管不仅对浅表钙化有效,还能安全、高效、精准地破坏浅表和深层钙质,同时最大限度地减少对软组织的损伤,改善血管顺应性,为后续的球囊扩张和支架植入做好准备。因此,冲击波球囊已经成为冠脉介入领域的一个创新热点。
冠脉钙化治疗方式特点
数据来源:冠状动脉钙化治疗方式、冠状动脉钙化病变诊治中国专家共识(2021版)
冲击波球囊有源介入是高壁垒产品,国内企业已实现突破。冠脉冲击波治疗系统属于有源介入产品。虽然无源介入已经发展多年,成熟度较高,但有源产品国内技术积累相对国外较为薄弱,其中涉及关键性的技术、组件和卡脖子问题。在这一高技术壁垒领域,也有部分国内企业实现突破,国内包括赛禾医疗、蓝帆医疗、乐普医疗等企业的血管内冲击波治疗设备已获批上市。其中,赛禾医疗的冠脉冲击波治疗系统通过向冲击波导管提供脉冲式驱动电能,能向外360°全周向,间歇性地输出发散式、低强度冲击波能量,进而对钙化斑块产生压裂作用、改善血管顺应性,其学习曲线极短,使用简便、安全。
心衰和心脏辅助设备:人工心脏进医保带来重大利好,国产植入量超千例。在国内上市的多款植入式人工心脏中,结合2024中国生物医学工程大会暨创新医疗峰会中国阜外医院胡盛寿院士公布的中国开展长期LVAD植入术总体情况,以及2023年阜外医院年度发展总结报告公布的LVAD植入术情况看,2017年6月至2024年8月,国内医院共完成4款LVAD植入术1140例。核心医疗的左心室辅助装置Corheart® 6的植入量以385例位居首位;2024年1月至8月,国内医院共完成4款LVAD植入术约479例(估算),其中,Corheart® 6的植入量最多约208例,约占总植入量的43%。
全磁悬浮一体化双心室辅助系统,进入创新医疗器械绿色通道。在临床应用中,LVAD并非终末期心衰最终、最完善的解决方案。终末期心衰患者中,多达30%患者存在右心/全心衰竭,需要右心辅助/双心辅助支持;此外,目前单纯LVAD植入后发生右心衰竭的比例高达30%,显著降低LVAD患者长期生存率。全心衰患者需要双心室辅助,但现有的全人工心脏(TAH)存在发症高、泵体体积大、生存率低等问题,无法有效解决双心室衰竭的难题。
目前,全球范围内,双心辅助装置尚无产品获批,值得一提的是,2024年,核心医疗的全磁悬浮一体化双心室辅助系统DuoCor®进入创新医疗器械绿色通道,具有以下关键创新:采用1套系统实现一体化协同控制以及左右心平衡;采用集成化设计,具有轻便的外携设备,提高患者生活质量;采用全球首创的双心一体化设计,重量、体积进一步降低,且能更好地适应右心血流动力学和生理结构。DuoCor®有望为终末期双心衰竭患者带来新希望。
在中国,ICE市场以其快速的增长速度和广泛的应用范围迅速扩张。心腔内超声技术已被广泛应用于指导结构性心脏病和心律失常的介入治疗,并监测术中并发症。其应用场景包括房颤导管消融、房间隔穿刺、房间隔缺损封堵、左心耳封堵术以及二尖瓣成形术等。目前,ICE在中国主要应用于电生理领域,其中房颤治疗占据主导地位,左心耳封堵紧随其后。与美国超过90%的电生理手术中使用ICE的渗透率相比,中国ICE渗透率仅为发达国家的十分之一,显示出中国ICE市场的巨大潜力。
据调研,到2030年,中国在LAAC(左心耳封堵术)、PFO(卵圆孔未闭封堵术)、ASD/VSD(房间隔缺损/室间隔缺损封堵术)等ICE常用术式中的手术量合计将达到70万例。此外,房颤消融手术量有望超过100万例,表明未来中国ICE市场增长潜力巨大。未来,ICE应用于电生理手术仍然是主要市场,同时,随着ICE技术的不断进步,其在结构性心脏病治疗中的重要性和益处将日益凸显,ICE在该领域的应用比例将逐步增加,进一步推动ICE市场的持续扩张。
ICE企业需要增强的四大能力
数据来源:动脉智库
外周介入国内创新产品密集获批,解决复杂病变产品成布局重点。外周介入市场的竞争相对缓和,其特点在于产品种类繁多、类型多样。目前,国内企业正处于产品完善和补全的关键“爬坡”阶段。在球囊、髂静脉支架、药物涂层球囊(DCB)、刻痕球囊以及通路类产品等领域,国内企业已基本实现了产品线的全面覆盖。随着国内企业逐渐深入外周介入领域,解决外周复杂病变的产品成为国内企业下一阶段布局的重点。展望未来,抽吸系统、IVL系统、雷帕霉素DCB等产品将成为国内企业未来几年的重点布局管线。
其中,下肢血管钙化患者占外周血管钙化患者的大多数,外周钙化病变的特点是病变长度更长、狭窄程度更高,并且下肢动脉存在非支架区,后续更多联用药物球囊,下肢血管钙化相较于冠状动脉血管钙化,其钙化层更厚、钙化病变时间更长。
因此,外周冲击波球囊治疗尤其适用于下肢血管钙化病变的治疗。外周领域对于IVL的需求主要在于能否顺利通过闭塞段,能否更多的获得管腔以及能否减少补救性支架等,IVL技术在外周领域还处于起步阶段,现有的IVL手术量在千级左右,随着更多产品的获批,未来的手术量增长会比较可观。
国内IVL领先企业,如赛禾医疗的外周冲击波治疗系统已获批,该系统提供脉冲式驱动电能,可向外360°全周向、间歇性地输出发散式、低强度冲击波能量,且对管腔内膜和正常血管组织不造成损伤,有优异的人机交互功能、耐压性和手术效率。
在集采政策的影响下,外周介入市场的竞争程度加剧,拥有完整产品线或创新产品的企业更有可能在市场竞争中占据优势。在带量采购常态化背景下,单一品类的市场规模被大大压缩,产业迎来出清时刻。一个全面的产品线和综合解决方案对于市场的开拓尤为关键。正如业界共识,集采效应下,只有具备完整产品线的企业才能有效打开市场,引领行业格局的变化。其次,在常态化的带量采购背景下,同质化产品之间的竞争愈发激烈,导致利润空间不断缩小。然而,辅助类产品价格的降低也为创新产品的推广提供了更多的支付空间。在这种市场环境下,具有突破性、差异化的创新产品更易获得竞争优势。
比如,中天医疗在外周介入领域的快速发展主要得益于其创新产品和差异化优势,其分离器辅助下的外周血栓抽吸SWAM创新技术实现更高效的血栓清除;其外周完全可控带纤毛弹簧圈实现更精准可控的栓塞效果;其颈动脉支架产品采用单层微孔混合编织的创新设计,作为国产首款通过“绿色通道”。
国内神经介入企业正步入盈利期,而抢占大型中心医院的市场份额成为其发展的关键。2024年,多家领军企业在商业化方面取得了突破性进展,正式跨入盈利阶段。企业要实现持续盈利,需要依靠创新差异化产品来推动营收增长,同时还需通过成本控制和提升运营效率来增强盈利能力,及抓住集采带来的机遇,实现收入的跨越式增长。比如,中天医疗在2024年实现盈亏平衡,且完成了新一轮融资,主要归功于其卓越的综合实力,其AIS一站式创新解决方案累计服务超5万名中国病患,中天天巡®远端通路导管在京津冀“3+N”集采中A组中标。
● 医疗设备
眼科设备市场逆势增长,国产市场认可度显著提升。尽管2024年受到国内招投标流程延迟的影响,公立医院的招标采购活动有所减少,但眼科领域的终端需求仍在持续增长。增长驱动力来自三方面:①眼科专科门诊数量的增加以及民营医院的强劲需求,推动了眼科门诊对诊断设备需求的不断升级。②眼科设备需求是多层次的,产品不断升级持续推动市场增长。从眼底照相机到OCT(光学相干断层扫描),再到从普通眼底照相机到超广角共聚焦激光照相机,以及从第二、三代OCT产品到扫频OCT。③眼科高端设备国产替代。
过去,由于高端眼科设备的技术门槛较高,市场主要由少数几家进口企业垄断。然而,随着国内企业在技术积累和突破上的不懈努力,眼科终端客户对国产高端眼科设备的看法正在发生积极变化,国产品牌的市场认可度也随之提高,进一步促进了市场的繁荣。
2017—2021年国内眼科专科医院数量(单位:家)
数据来源:卫生健康统计年鉴
OCT市场国产品牌通过技术迭代确立竞争优势。在OCT领域,国内企业市场份额已经超越进口企业,之所以实现超越,关键在于OCT技术的快速迭代为国内企业提供了弯道超车的机会。OCT技术路线始终保持着高速的更新换代,与此同时,进口品牌由于面临更高的技术转型成本和较慢的转型速度,这为采用最新技术路线的国内企业提供了超越的机会。因此,采用扫频OCT的国产OCT产品在性能上超越进口产品变得更加可行。
比如,Intalight赛炜如意全眼OCT开启了“全眼OCT”新时代,在国内已有近500台落户于各地眼科医院,120台以上进驻国家或省级标杆医院,且已在美国、欧洲、南美洲、亚太等30家以上海外顶级医院及眼科机构使用,实现了出海即巅峰;其如意150单次扫描范围可达150°,将OCTA范围拓展到极致;2024年发布的如意全眼生物测量仪搭载独家第二代可视化扫频生物测量新技术,把眼轴检出率从94%提高到99%以上,可实现9mm大范围眼底成像及全角膜地形图,且可集成前节OCT。
眼底照相机国内企业份额实现突破。随着资本市场对眼科设备领域的关注和投入不断增加,国内高端眼科设备市场的参与者数量显著增长,眼底照相机的认证数量也大幅上升。眼底照相机领域尤其考验企业的长期研发能力。超广角激光相机(包括造影和照相)的年新增采购量约为600台,增速保持在15%-20%之间。超广角激光技术正逐渐成为眼底照相机的主流技术,预计到2028年,超广角激光眼底相机将全面取代传统产品。
根据中国公立医院公开可查询的中标数据显示,2023年,欧堡Davtona(P200T)型号总销售金额占比最高,达到38%;蔡司CLARUS-500 型号产品占比排名第二,销售金额市占率26.8%,微清医疗排名第三,销售金额市占率24.9%。这一排名在2024年有更新,据比地招标网统计,2024年1-6月,眼底照相机金额市占率较高的品牌中,微清医疗作为国产首位总排名第二,其眼底激光相机已完成近500家医院装机、全国眼科的重点医院实现覆盖并完成多台装机,在部分医院中标价超过同类进口产品,且已覆盖全球40多个国家和地区。
国产眼科设备正从替代进口产品向引领行业发展迈进。2024年见证了多款国产高端眼科设备的突破性上市,这些设备打破了传统产品的局限。比如,微清医疗的SKY全眼影像平台融合共焦激光及SS - OCT等技术,集超广角激光彩照、造影、自发荧光等眼底平面影像及超广、超深、前后节断层影像于一体,实现多模态实时同屏显示,还具备智能标注辅助分析及无极光学变焦功能。其一站式检查提高诊断效率、改善医患体验,让诊断更高效、全面、精准。
2024年,国内内镜市场受到医疗行业整顿和医疗设备更新项目的影响,招标采购活动持续推迟。在硬镜领域,图像质量和产品功能是市场竞争的核心。市场格局上,外资企业依靠先发优势和卓越的产品性能,主导着国内市场。其中,卡尔史托斯和奥林巴斯位居第一梯队,史赛克和德国狼牌紧随其后,位列第二梯队。与此同时,国内企业的市场份额显著增长,主要竞争者包括迈瑞医疗、欧谱曼迪、开立医疗、沈大内窥镜、天松医疗、新光维、康基医疗和图格医疗等。特别是在荧光内窥镜领域,国产设备的装机量已超过市场的一半。在软镜市场,镜体的操控性和图像质量成为竞争的关键因素。目前,外资企业仍占据较高的市场份额,而国内企业的市场占有率相对较低。国产软镜的主要参与者包括澳华内镜和开立医疗,这些企业有望在未来提升国产软镜的市场竞争力。
提供内窥镜领域的全链路解决方案成为核心竞争力。比如,海信医疗在内窥镜领域可提供全链路解决方案,解决了国产内窥镜普遍存在的产品稳定性和长期使用后的性能衰减等核心痛点问题,其内窥镜的高性能、高稳定性均达到了行业领先水平。其智能导航4K荧光内窥镜系统同时搭载了智能导航系统、智能一体化示教系统和智能AI算法优化系统,可提供术前规划,术中精准导航、直播示教、远程手术指导等,及术后效果评估的全流程解决方案,大大提高手术成功率,可满足临床诊疗、学术、教学等需求。
一次性内窥镜市场持续增长,出海表现亮眼。随着CMOS图像传感器芯片技术的高速发展,特别是国产芯片的自主可控,给内窥镜行业带来了蓬勃发展的机会,一次性电子内窥镜将成为国产医疗内窥镜厂家赶超世界名企、实现弯道超车的绝佳选择,对于防感染刚需的科室如呼吸科、消化科、妇科等有较大需求。此外,国内内窥镜成熟的产业链为一次性内窥镜出海奠定产业优势,国内一次性内窥镜出口量在25—30万支,体量仍然有较大增长空间。2024年前三季度,国内内窥镜出口增长显著,国内内窥镜出海市场大有可为。
在国内众多一次性内窥镜企业中,大规模量产能力、全科室产品布局、卓越的图像质量和先进的图像处理技术、以及设备的高度可操作性,构成了企业在激烈竞争中脱颖而出的关键竞争力,总体来看,技术实力和大规模商业化能力是一次性内窥镜企业成功的关键因素。
比如,瑞派医疗的全球化、多科室、多产品全面布局,及医用光学、影像处理、软件和算法等创新技术让其在竞争中领先,其高阶医学影像算法让新一代主机呈现超清画质影像,智能辅助诊疗技术提高病灶检出率和医生工作效率。目前,公司的肾盂镜、膀胱镜、胆道镜、宫腔镜、胃肠镜等一次性内窥镜产品已获得包括NMPA、CE、FDA在内共100余个批准,产品和服务触达北美、欧洲、中东、东南亚、南美、非洲等50多个国家和地区,服务全球2600多家医院。
2024年1-10月中国内窥镜出口前十大国家及金额(单位:万元)
数据来源:中国海关
公立综合医院采购需求疲软,康复专科医院和民营医院增长动力更强。康复设备市场中,公立综合医院数量大,仍然占据了主要市场,但是由于公立综合医院床位有限和康复专业化程度总体较低,加上2024年国内医疗设备整体招标速度放缓,公立综合医院康复设备市场需求在2024年表现疲软。与此同时,康复专科医院和民营医院对于智能化康复设备释放出强劲的增长力。康复专科医院采购体量较大,民营康复医院作为新兴市场增长较快。
国内康复专科医院2019—2021年数量 (单位:家)
数据来源:中国卫生健康统计年鉴
康复市场正朝着专业化方向升级。随着国内康复器械行业的不断进步,医院对康复设备的认识日益深入,其需求也随之向更专业的方向发展。这一趋势不仅体现在对康复器械的需求上,康复学科本身也在不断细化,涵盖了认知康复、神经康复、骨科康复、心肺康复以及心脏康复等多个专业领域。
在产品层面,国内康复医疗器械正朝着专业化和智能化的方向发展。康复机器人的智能化水平正在提升,目前市场上的康复机器人主要以固定式或半固定式为主,这些产品在自主性和灵活性方面存在一定的局限性,无法根据患者的具体情况提供个性化的反馈。外骨骼康复机器人作为辅助患者站立和行走的工具,具有步态矫正、增强助力和运动代偿等功能。
外骨骼机器人在中国已经发展了一段时期,正逐步从自动化向智能化转变,智能化的外骨骼机器人需要能够精确识别和预测人体的运动意图,并通过精确的力学反馈来辅助患者行走,在互动性和趣味性上也有所改善,让患者实现个性化、沉浸式练习,提高其依从性。除了技术上的迭代,不少企业在产品布局上也实现了多元化,从下肢到踝关节、上肢、手部、床旁等,在细分人群上也拓展至儿童。
如聚焦神经康复领域的安杰莱科技,从解决偏瘫患者运动功能障碍入手,以AI+康复的创新路径研发“智能化、主动化、个性化、系统化、精准化”的智能康复医械,满足肩、肘、腕、髋、膝、踝、手等关节的智能康复训练需求,逐步形成以神经康复为核心,肌骨康复为特色,早期床旁康复和老年康复为延伸的智能解决方案。这些产品投入临床应用,既为患者提供更优效的康复治疗,也减轻康复治疗师重复繁重的体力劳动,有效提高科室运营效率。
国内康复辅具市场发展历程
数据来源:动脉智库
治疗与生命支持设备包括麻醉机、心肺复苏、体外除颤、呼吸机、监护仪、ECMO等产品,其中大部分产品国产化进程较快,心肺复苏、体外除颤设备、呼吸机、麻醉机、血氧测量设备等设备招标采购国产设备占比已超过50%。但其中体外循环高端医疗设备有多种产品仍然依赖进口供应,包括ECMO系统、器官灌注系统等。
以器官灌注系统为例,器官灌注系统用于器官转运过程中保持器官保存,中国人体器官移植手术量目前位列全球第二,器官移植对于转运环节要求极高。目前临床中最常用的器官保存方法主要有两种:静态低温保存(static cold storage,SCS)和机械灌注保存(machine perfusion,MP)。为了应对日益严峻的供者器官短缺问题,大量边缘供者器官被应用于临床,这对传统的器官保存技术提出了更高的要求。
机械灌注保存不但可以提高器官保存的效果、延长器官保存的时限,还可为器官质量评估和损伤修复提供平台,目前已成为器官保存领域的主要发展方向。2024年8月26日,器官保存和运输公司Paragonix Technologies宣布同意被Getinge公司以4.77亿美元(约合人民币34亿元)的价格收购,这一大额并购展现了器官移植体外循环设备的市场潜力。
MP技术中,常温机械灌注(normothermic machine perfusion,NMP)是一种在常温条件下进行的机械灌注技术,灌注液一般为红细胞或血红蛋白溶液,可提供充足的氧气及代谢底物,以维持器官正常的有氧代谢,从而有效避免缺血损伤,保护器官功能。此外,在灌注期间还可对器官质量进行实时评估,并可主动修复器官损伤,从而降低器官弃用率。
器官保存方法特点
数据来源:动脉智库
在这一高精尖领域,国内企业正成为创新主力,利用全新的技术和结合临床需求的设计变革已有的NMP产品。如清瀚医疗对NMP系统有五大创新设计:①一体式推车及全景手术台设计满足临床转运/手术等不同场景需求;②采用双泵高精度灌注系统,开发搏动式离心泵以提升微血管灌注效果,同时采用恒流式离心泵稳定血液压力;③自研了全系列氧合器及针对肝脏NMP灌注的专用小预充氧合器;④实时显示血液动力学指标、血气指标、供肝代谢物等指标;⑤内嵌针对温控系统和氧供系统的智能算法,使离体肝脏器官实现最优仿生环境下的生存和修复。
● 体外诊断
2024年,中国体外诊断行业正面临显著挑战。受新冠疫情影响,国内企业大幅扩张产能,导致现有产能超出市场消化能力,价格竞争趋于激烈。同时,2024年国内试剂市场消耗量受到了非刚性医疗需求低迷、以及DRG落地执行等因素的影响。此外,2024年监管环境的变化也对行业构成压力。
2024年对体外诊断行业影响较大的政策方向
数据来源:动脉智库
流式荧光在免疫诊断中的应用备受关注,特别是一些兼备试剂上游技术和仪器平台产业化能力的企业。这一技术受到关注的原因有多方面:①其多指标联合检测优势:流式荧光技术提供了一种多指标联合检测的高效解决方案,提高了检测效率,实现了高通量检测,这是流式荧光最大的优势。②突破全自动化技术:流式荧光自动化开发解决了效率问题,可实现无人值守,为临床大规模应用提供了有力支撑。③试剂检测成本优势:相比传统化学发光检测,耗材成本大大降低,更符合国内体外诊断行业集中采购的趋势。④应用场景广泛:流式荧光技术主要应用于细胞因子、自身免疫疾病、肿瘤和感染性疾病的检测,这些领域拥有庞大的患者基数、长期的治疗方案和持续的检测需求。此外,该技术还有潜力拓展到阿尔兹海默症生物标志物检测等新兴市场。
同时,流式荧光诊断在临床应用中也遭遇了一些挑战。首要的挑战源自支付端:随着DRG/DIP付费改革的推进,对费用控制的要求愈发严格,特别是在自身抗体和过敏原检测领域,传统的多项联检模式亟需在DRG/DIP付费框架下进行相应调整,这就需要一种更灵活开放的检测平台顺应政策和市场;其次是需要国内企业投入市场教育,提升临床认可度,扩大临床应用量。
流式荧光诊断领域机遇与挑战并存,头部企业需具备三项核心能力:首先,技术研发实力是基础,企业需要掌握微球编码、多重试剂开发、光学检测、软件算法等关键技术,有利于企业形成产品核心竞争力,增大产品市场应用空间;其次,渠道能力至关重要,体外诊断产品商业化依赖于精准的市场定位和强大的渠道营销,以实现产品放量;第三,全球化能力是拓宽流式荧光产品应用空间的关键,同时有助于应对单一市场变化的风险,需要根据海外市场特点开发适配的仪器和试剂。企业间的竞争已从单一技术的竞争转变为综合实力的较量,出海成为新的竞技场,渠道资源积累、商业模式和优质产品等成为重要竞争因素。
流式荧光企业能力版图
数据来源:动脉智库
比如,胡曼智造与多家欧洲IVD企业达成长期合作、形成双向绑定的合作模式,实现产品和渠道双赢。以德国企业HUMAN为例,胡曼智造代理HUMAN的产品并负责其在国内市场的准入和营销、售后等,同时为HUMAN研发和生产产品;HUMAN利用其160多个国家的渠道资源和50多年的品牌影响力,将胡曼智造的产品成功推向国际市场。目前,胡曼智造的POCT产品线HumaFIA已成功出海,并在中东、拉美、非洲等数十个国家上市。此外,公司的多条产品线已在布局中,出海前景值得期待。
● 上游供应链及核心零部件
近年来,尽管医疗器械行业面临资本寒冬,但上游及供应链融资事件的数量却持续攀升,显示出该领域的韧性。在国内医疗器械产业链迅速崛起的背景下,加之外部环境的变化,越来越多的企业开始寻求供应链的稳定性。上游核心供应链更换客户频率较低,供应链较为稳定,也为国内上游零部件企业带来稳定预期。这为国产上游企业带来了系统性的发展机遇,并预示着高速增长的潜力。在医疗器械上游产业链中,融资主要集中在两大主题:一是上游供应链的优化与整合,二是上游核心零部件及材料的研发与创新。这两个领域的发展对于提升整个医疗器械行业的竞争力至关重要。过去,影像类核心零部件例如CT球管最受市场关注,2024年有多个其他核心零部件受到关注。
国内企业在关键零部件制造领域取得了显著进展,成功打破了国际企业长期以来的独家垄断局面。以磁悬浮电机为例,全磁悬浮电机是左心室辅助装置和ECMO等关键医疗设备的核心组件,同时在生物制药生产过程中,全磁悬浮搅拌器有助于降低生物工艺中的剪切风险,保护生物活性物质。此外,磁悬浮电机在半导体制造领域也扮演着重要角色。此前,这些关键零部件被国际企业所垄断,而磁悬浮泵等关键技术产品甚至被列入禁运名单。如今,国内已有企业在这一领域实现了技术突破,填补了市场空白。
比如,凯磁医疗已有全磁悬浮植入式左心室辅助系统(LVAD)、全磁悬浮体外人工心脏、全磁悬浮搅拌器、全磁悬浮洁净泵等产品。公司最新一代多自由度全磁悬浮平台性技术可解决其他技术路线存在的磨损、发热、污染、破坏血液等问题,实现了无接触、无摩擦、无发热、低剪切力,能保持良好的血液相容性。另外,公司的电机定子、转子、传感器、控制系统等产品已实现全流程自主设计,其全磁悬浮体内外血泵用电机可有效控制产品成本,惠及更多患者。
国内CDMO企业正迅速崛起。特别是在2024年,它们在内窥镜、微创外科、体外诊断、激光医疗、CGM等多个高增长领域崭露头角。内窥镜领域的需求增长尤为显著,一次性内窥镜的发展简化了产品结构,降低了成本控制的难度,从而催生了大量的代工需求。 体外诊断领域中,由于仪器和试剂的生产差异以及研发、生产的长周期特性,也催生了庞大的CDMO需求。 这些产品通常结构复杂,下游市场对渠道依赖性强,且对成本控制和用量有较高要求,进一步推动了CDMO需求的增长。 国内CDMO企业通过提供全流程服务,降低了行业的进入门槛,使得国内企业能够快速响应市场需求,加速产品上市,从而在激烈的市场竞争中占据优势。
国内CDMO发展历史
数据来源:动脉智库、波士顿咨询
目前,国内CDMO企业大多还处于零部件加工的阶段,能够提供从设计到生产的全流程服务的CDMO企业相对较少。这种现状表明,国内CDMO企业在提供全流程服务方面还有较大的发展空间,尤其是在提升研发设计、临床试验、注册申报以及大规模生产制造等关键能力上,但仍有佼佼者。
比如,东劢医疗提供从医疗器械的合规设计开发、工程转化、工艺输出、检验验证、质量体系、注册咨询、临床服务、小试、中试到批量委托生产等全流程服务,在医工融合产业化、进口器械国产化、存量企业集约化上均具优势,公司积累了产学研优质资源,提供技术引进、生产优化及注册申报等服务,可实现快速、低成本注册,其生产基地配套大型生产设备和高精密检验设备,可承载多模块、多领域、多品种医疗器械,实现大批量生产。
结合本章行业创新逻辑分析、企业实践举措,本次白皮书推选出了年度二十大创新优秀案例,并将在后续章节中对其中部分案例进行详细解读。
以上为报告主要内容节选,扫描二维码可获取报告完整版
报告目录
前言
CHAPTER1 数说2024
1.1宏观环境去芜存菁,行业拐点将至
1.2带量采购提质扩面,走出集采影响
1.3手术量持续增长,医疗需求强劲
1.4投融资数据:投融资进入下滑阶段,并购数据增长
1.5出海数据:出海已经成为必由之路
1.6创新审批数据:创新彰显产业韧性
CHAPTER 2 年度产业之问
2.1高值耗材
2.2医疗设备
2.3体外诊断
2.4上游供应链及核心零部件
CHAPTER 3 医疗器械及供应链创新案例解读
3.1凯磁医疗——全磁悬浮电机技术的引领者
3.2安杰莱科技——专注于脑科学应用的智能康复医疗器械
3.3海信医疗——医学影像设备及智慧医疗解决方案提供商
3.4核心医疗——为全球心衰患者提供全面解决方案
3.5赛禾医疗——中国泛血管有源介入诊疗方案的提供商和先行者
3.6中天医疗——为临床提供泛血管介入治疗一站式创新解决方案
3.7东劢医疗——为全球医疗器械产品提供全生命服务周期解决方案
3.8 胡曼智造——以流式荧光技术为核心,提供整体诊断解决方案
3.9 Intalight赛炜——与全球眼科界相识于顶峰
3.10微清医疗——开启全眼、真同步影像时代,引领眼科诊疗新纪元
3.11清瀚医疗——提供微循环+肺循环+体循环+循环动力解决方案
3.12 瑞派医疗——提供一次性内窥镜微创诊疗解决方案
*封面图片来源:神笔PRO
如果您认同文章中的观点、信息,或想进一步讨论,请与我们联系;也可加入动脉网行业社群,结交更多志同道合的好友。
近
期
推
荐
声明:动脉网所刊载内容之知识产权为动脉网及相关权利人专属所有或持有。未经许可,禁止进行转载、摘编、复制及建立镜像等任何使用。
动脉网,未来医疗服务平台
带量采购核酸药物并购
100 项与 南京图格医疗科技有限公司 相关的药物交易
登录后查看更多信息
100 项与 南京图格医疗科技有限公司 相关的转化医学
登录后查看更多信息
组织架构
使用我们的机构树数据加速您的研究。
登录
或

管线布局
2026年04月12日管线快照
无数据报导
登录后保持更新
药物交易
使用我们的药物交易数据加速您的研究。
登录
或
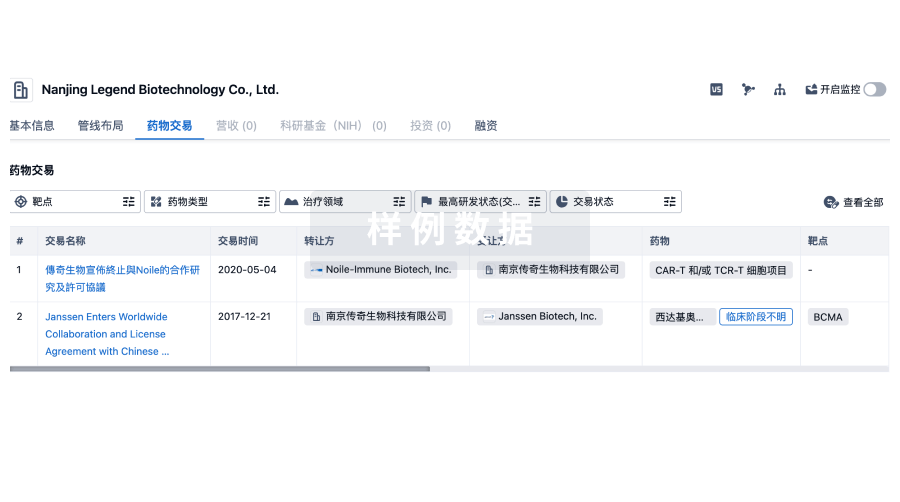
转化医学
使用我们的转化医学数据加速您的研究。
登录
或
营收
使用 Synapse 探索超过 36 万个组织的财务状况。
登录
或
科研基金(NIH)
访问超过 200 万项资助和基金信息,以提升您的研究之旅。
登录
或
投资
深入了解从初创企业到成熟企业的最新公司投资动态。
登录
或
融资
发掘融资趋势以验证和推进您的投资机会。
登录
或
生物医药百科问答
全新生物医药AI Agent 覆盖科研全链路,让突破性发现快人一步
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。
生物序列数据库
生物药研发创新
免费使用
化学结构数据库
小分子化药研发创新
免费使用