预约演示
更新于:2026-02-27
Carbon Dioxide
二氧化碳
更新于:2026-02-27
概要
基本信息
权益机构- |
最高研发阶段批准上市 |
首次获批日期 日本 (1995-08-01), |
最高研发阶段(中国)- |
特殊审评孤儿药 (美国) |
登录后查看时间轴
结构/序列
分子式CO2 |
InChIKeyCURLTUGMZLYLDI-UHFFFAOYSA-N |
CAS号124-38-9 |
关联
49
项与 二氧化碳 相关的临床试验NCT07420530
Respiratory and Real-time Dynamics in Exercise-Induced Paradoxical Vocal Fold Motion
The overall objectives of the proposed research are to:
1. Evaluate the diagnostic validity of a novel mechano-acoustic signatures of task-characteristic activity during symptomatic and asymptomatic breathing in Exercise-Induced Laryngeal Obstruction (EILO) patients with the use of a novel miniature, soft wearable skin-mounted device,
2. Identify the mechanism/s of paradoxical respiratory control in EILO by quantifying the relationship between pulmonary mechanics, partial pressure of carbon dioxide (PCO2) maintenance, and vocal fold aperture prior to and during symptomatic and asymptomatic exercise ventilation, and
3. Identify unique biophysiological factors contributing to EILO among exercisers with and without EILO. Findings will be highly novel and clinically significant for early identification and management of EILO.
For the study there are three separate visits:
1. Free running with the device on the neck
2. Exercise treadmill study
3. Undergoing MRI (Magnetic Resonance Imaging) of the vocal tract.
1. Evaluate the diagnostic validity of a novel mechano-acoustic signatures of task-characteristic activity during symptomatic and asymptomatic breathing in Exercise-Induced Laryngeal Obstruction (EILO) patients with the use of a novel miniature, soft wearable skin-mounted device,
2. Identify the mechanism/s of paradoxical respiratory control in EILO by quantifying the relationship between pulmonary mechanics, partial pressure of carbon dioxide (PCO2) maintenance, and vocal fold aperture prior to and during symptomatic and asymptomatic exercise ventilation, and
3. Identify unique biophysiological factors contributing to EILO among exercisers with and without EILO. Findings will be highly novel and clinically significant for early identification and management of EILO.
For the study there are three separate visits:
1. Free running with the device on the neck
2. Exercise treadmill study
3. Undergoing MRI (Magnetic Resonance Imaging) of the vocal tract.
开始日期2026-01-20 |
申办/合作机构  Indiana University Indiana University [+3] |
ChiCTR2600117660
The Effect of Permissive Hypercapnia and Phenylephrine on Postoperative Delirium in Elderly Patients
开始日期2025-06-20 |
ISRCTN23564393
Preventing kidney injury using carbon dioxide as contrast medium in patients with peripheral arterial disease (PAD) and chronic kidney disease (CKD) having arterial intervention (the KID trial)
开始日期2024-12-31 |
申办/合作机构 |
100 项与 二氧化碳 相关的临床结果
登录后查看更多信息
100 项与 二氧化碳 相关的转化医学
登录后查看更多信息
100 项与 二氧化碳 相关的专利(医药)
登录后查看更多信息
380,968
项与 二氧化碳 相关的文献(医药)2026-12-31·NUMERICAL HEAT TRANSFER PART A-APPLICATIONS
Numerical research on the heat transfer and pressure drop of supercritical CO
2
in spiral wound tubes
作者: An, Hang ; Yao, Guopeng ; Bai, Ye ; Cai, Haofei ; Jiang, Nan
The microtube heat exchanger (MSTE) is suitable for the pre-cooler and gas cooler in the supercritical CO2 brayton cycle and the CO2 heat pump cycle.This article presents a numerical study on the heat transfer characteristics of supercritical CO2 (sCO2) during the cooling process in capillaries with different shapes and sizes.The effects of tube types, spiral pitch, spiral diameter, and mass flow rate were investigated on the heat transfer and pressure drop of sCO2.The centrifugal force in the rotating flow also has an effect on the fluid flow, which in turn leads to a unique secondary flow.The heat transfer and pressure drop increase as the mass flow rate increases in all of the tubes.The straight tube showed the worst heat transfer performance and the best pressure drop performance.The spiral tube showed a better performance on the heat transfer and a worse performance on the pressure drop than the straight tube.The total heat transfer amount and pressure drop increase as the spiral pitch and spiral diameter decrease.The field synergy angles in different locations were further analyzed.It was found that the field synergy angle could further reveals the mechanism of heat transfer enhancement in spiral tubes.
2026-03-19·PETROLEUM SCIENCE AND TECHNOLOGY
Alleviation of liquid sulfur blockage by altering sulfur wettability in sour gas reservoirs
作者: Dong, Hua ; Dong, Zihong ; Zhong, Xia ; Shi, Hao ; Pei, Xin ; Liu, Changsong
In sour gas reservoirs exploitation, liquid sulfur deposited in the formation could block natural gas passage channels, severely reducing gas field productionTo address this problem, we successfully regulate the wettability of liquid sulfur on rock surfaces by modifying them with alkoxysilanes.It is found that enhancing the sulfophobicity of the rock surface significantly reduces the difficulty of gas-phase breakthrough of channel blockage caused by liquid sulfur deposition.During the simulated gas flooding process, the liquid sulfur recovery rate in neutral and sulfophobic rocks is increased by 48.3% and 124.4%, resp., compared with untreated natural sulfophilic rocks, resulting in 29.3% and 50.0% increase in porosity of the rocks after flooding, resp.These results indicate that the modified rock surface, especially sulfophobic rock surface, could effectively alleviate the blockage of gas production channels caused by liquid sulfur deposition.Mechanisms revealed by visualized exptl. results show that in gas flooding in more sulfophobic cores, the swept area of gas phase is larger and the amount of residual sulfur in the swept area is less, so the sulfur recovery rate is higher than untreated sulfophilic rock, and the blockage caused by liquid sulfur in the cores could be effectively reduced.
2026-03-19·PETROLEUM SCIENCE AND TECHNOLOGY
Characterization of corrosive effects of produced water on carbon steel and the role of flow velocity
作者: Hasan, Basim O. ; Al-Meshleb, Mustafa J. ; Majdi, Hasan Sh.
The corrosion characteristics of carbon steel in produced water encompassing a broad spectrum of corrosive elements including dissolved carbon dioxide effect was investigated in stationery and flow conditions for range of temperaturesThe effects concentrations of various corrosive ions presented in most oilfields produced water such as ions of Na+, Ca2+, Cu2+, Mg2+, Hg2+, Cl-, Mn+, and dissolved CO2 were investigated for temperature range of 30 to 60 °C and flow velocity range of 0 to 800 rpm.The corrosion rate showed clear increase with increasing the concentration of Ca2+, Cu2+, Cl-, Hg2+ ions, dissolved CO2, while it shows non-monotonic trend with Na+ ions concentrationThe most significant impact of flow velocity on the corrosion rate was observed with HgCl2 solution followed by mixture solutionSolutions containing dissolved CO2 exhibited high influence of flow velocity on the corrosion rate.The corrosion rate in produced water showed not systematic trend with the temperatureThe corrosive effect of the produced water containing all the investigated ions with a certain proportion showed higher values than the individual behavior indicating the synergistic effect.
26
项与 二氧化碳 相关的新闻(医药)2026-02-19
纵览农业发展,请关注国科农研院
人工智能驱动的生物制造进展与趋势
江 源#,杨 露#,王 琼,刘 晓,毛开云*
(中国科学院上海生命科学信息中心,中国科学院上海营养与健康研究所,上海200031)
摘 要:生物制造正经历从经验驱动向数据驱动的范式转变,人工智能在其中发挥着重要作用。本文综述了2025年人工智能在生物制造核心环节——包括生物元件设计、代谢网络建模、人工生命系统与无细胞合成系统构建、工艺优化与过程控制等方面的最新进展。尽管当前仍面临生物机制认知局限、数据稀缺、模型可解释性不足等挑战,未来随着人工智能与合成生物学、自动化技术的深度融合,将推动生物制造向可编程、智能化、可持续的新一代工业体系跨越,为医药、化工等领域的绿色转型提供核心驱动力。
关键词:生物制造;数据驱动;人工智能;合成生物学
中图分类号:Q819;TP18文献标志码:A
生物制造以可再生资源为原料,利用生物系统(如活体微生物、动/植物细胞、体外合成酶系统等)进行物质加工与合成,通过发酵等工艺规模化生产化学品、高分子材料等产品[1],推动了医药、食品、材料、能源等产业的发展。生物制造的发展经历了基础研究和产业应用的持续演进[2]。早期阶段主要依赖传统微生物发酵,随着合成生物学与人工智能(artificial intelligence,AI)的发展,生物制造正经历从经验驱动到数据驱动、从试错探索到智能设计的范式转变[3]。这一转变为构建可编程、可预测、可扩展的生物制造体系提供了关键支撑。
合成生物学通过系统性设计与构建,开发新型生物元件、装置和系统,并对现有生物系统进行功能重编程[4]。这一交叉学科融合了生物学、工程学、遗传学、化学与计算机科学的理论与方法,致力于创造自然界中尚未存在的人工生物系统,或对天然生物系统进行定向改造与功能优化。AI在海量数据处理、复杂模式识别与预测模型构建等方面展现出超越传统方法的卓越效能,它的核心是创建能执行学习、推理、决策等任务的算法与系统[5]。AI通过提供预测建模工具、整合复杂数据集等方式加速实验流程和效率。例如,AI驱动的技术流程通过指导基因设计、预测发酵性能并优化代谢途径,系统性提升合成生物学效率和精准度[6]。
过程建模与控制是AI的另一个重要应用。AI算法分析生产过程中产生的大量数据集,以确定温度、pH值、营养水平和其他关键变量的最佳参数[7]。例如,在发酵过程中,AI可以定义“黄金曲线”(即整个过程中的理想条件),并在出现偏差时提出纠正措施[8]。该技术还能通过自动化分析复杂数据集、识别关键变量并预测最佳条件,从而增强实验设计。这有助于构建更稳健、可扩展的工艺流程,持续生产出高质量的产品,并将批次间的差异降至最低。
生物制造正以可再生原料为基础,以智能化生产方式为路径,以循环经济为导向,逐步构建起高效、低碳、可持续的新型工业体系[9](图1)。在原料层面,以非粮生物质为核心生产原料,推动资源利用向可持续方向转型;在技术层面,以合成生物学“设计-构建-测试-学习”(design-build-test-learn,DBTL)循环为核心,结合AI、自动化技术及数据决策系统形成闭环[10];在应用层面,已覆盖医药、食品、化工、材料、环境等关键领域,并将向深空[11]、深海[12]、深地[13]等未来场景拓展。
图1 高效、低碳、可持续的生物制造
高效、低碳、可持续的生物制造以秸秆/农业废弃物和一碳气体等非粮生物质为可再生原料,构建低碳循环路径,实现碳减排与生态协同效应;以合成生物学“设计-构建-测试-学习”(design-build-test-learn,DBTL)循环为核心,结合人工智能(artificial intelligence,AI)(预测-优化-挖掘-生成)与自动化技术(编程-执行-采集-集成),形成可编程生物系统。系统涵盖细胞工厂与无细胞合成系统,通过发酵过程关键参数(温度、pH、溶解氧)的实时监测与控制,推进制造过程精准化。应用覆盖医药健康、农业食品、化工材料、环境能源四大领域,并向深空、深海等未来场景拓展,形成“原料-技术-产品-产业”闭环。从实验室技术转化到产业协同升级,推动传统企业向生物解决方案提供商转型,支撑“双碳”目标实现与循环经济发展(注:部分元素由AI生成)。
1 生物制造发展阶段
依据生产方式、核心技术和产品类型,生物制造的发展可分为四个阶段[14](表1)。生物制造1.0始于第一次世界大战时期,主要通过单一菌种厌氧发酵,实现糖类原料向初级代谢产物(如丙酮、丁醇、乙醇等)转化。生物制造2.0发端于第二次世界大战期间,采用经诱变选育的微生物突变体,结合液态深层好氧发酵工艺,实现以青霉素、四环素、链霉素等为代表的次生代谢产物制造。20世纪80年代,以重组DNA技术及细胞培养体系为标志,生物制造迈入3.0阶段。这一阶段实现了生物大分子生产,例如多种治疗性蛋白和工业用酶。当前正处于生物制造4.0的成形与深化时期,以合成生物学技术为代表,推动生物制造往“新生产方式、新产品、可持续”方向发展[15],例如工程大肠杆菌合成抗疟药物青蒿素前体[16]、工程酵母合成阿片类药物[17]、二氧化碳人工合成淀粉[18]和首个商业化应用的RNA生物农药(CalanthaTM)[19]等。
表1 生物制造的发展阶段
阶段
生产方式
核心技术
典型产品
1.0
单一菌种
厌氧液体发酵
丙酮、丁醇、乙醇
2.0
诱变菌种
好氧深层发酵
青霉素、四环素、链霉素
3.0
转基因微生物/细胞
重组DNA技术+细胞培养
重组蛋白、工业酶
4.0
工程微生物、干细胞、无细胞合成系统
合成生物学
青蒿素前体、阿片类药物、人造淀粉、生物农药
“设计-构建-测序-学习”(desigh-bulid-test-learn,DBTL)循环是合成生物学的核心研发流程[20]。AI在DBTL循环中发挥着关键作用[21]。例如,在设计阶段,AlphaFold[22]及生成式分子设计系统[23]等模型能够预测蛋白质结构、提出合成回路方案并生成候选生物分子;在构建/测试阶段,生物铸造厂[24]通过自动化DNA合成、高通量筛选及功能实验,对AI生成的设计方案进行集成验证;在学习阶段,包括序列-功能关联、代谢输出及多组学数据在内的实验结果将反馈至AI系统,从而实现对预测模型的迭代优化。这种闭环集成使DBTL转变为自我优化的过程,显著加快发现速度、减少试错成本并提升结果可重复性。在合成生物学与AI的驱动下,生物制造4.0正迈向5.0阶段[25]。2 细胞工厂重构
重构细胞工厂的核心目标是通过理性设计与系统优化,使细胞成为高效、可控、可持续的“生物反应器”。基因工程提供基因元件与基因编辑工具,为细胞工厂的设计与构建奠定基础。酶工程通过对关键酶的挖掘与设计,解决代谢途径中的限速步骤。代谢工程对代谢网络进行系统性重编程,实现途径重构和动态调控等。2.1 生物元件设计
生成式AI能够创建新颖且复杂的分子结构,已成为分子设计的强大工具[26]。在DNA调控元件设计方面,DaSilva等[27]构建了名为DNA-Diffusion的生成式人工智能框架。该框架利用基于不同细胞系DNA数据训练的机器学习模型,生成长度为200个碱基对的调控元件,这些元件不仅与内源性转录因子结合,而且还具有细胞类型特异性。在信号肽设计方面,Dai等[28]开发了SPgo计算框架,通过将基于结构域组装的规则系统与基于Transformer的深度生成模型相结合,实现了Sec型信号肽的高效设计;通过该框架设计的信号肽将蛇毒肽的分泌产量提升至154 mg/L,相比传统胞内表达提高了150倍。在酶催化元件设计方面,Lauko等[29]融合了RFdiffusion[30]的蛋白质骨架生成能力与PLACER[31]的功能位点评估模块,设计出可介导多步反应的、含复杂活性位点的丝氨酸水解酶。该设计酶实现了原子级结构精度与天然酶级催化性能的双重突破。Profluent公司发布了由AI自主设计的全新基因编辑工具OpenCRISPR-1(Cas9样蛋白酶),并在人类细胞中实现基因组编辑[32]。
生成式AI实现了生物元件的“从无到有”,而针对现有元件的功能提升,需要AI预测模型与自动化实验深度融合。这类平台的核心是利用AI模型快速评估序列-功能关系,并指导自动化系统进行高通量构建与筛选,形成DBTL的智能闭环。Zhang等[33]开发了基于蛋白质语言模型的自动化蛋白质进化平台PLMeAE。该平台利用ESM-2模型进行零样本预测生成候选序列,并通过自动化生命铸造工厂iBioFoundry完成高通量构建与验证,再基于实验数据训练预测模型以指导下一轮筛选。经过四轮迭代(10 d)以后,目标酶活性提升了2.4倍。2.2 代谢网络建模
代谢网络模型通过整合多组学数据模拟复杂的代谢网络,是AI设计代谢网络的基石。Li等[34]通过整合多种基因与代谢物的聚类及关联分析算法,构建了覆盖烟草全基因组的代谢调控网络,识别出多个高价值代谢物合成的关键调控枢纽。Yu等[35]在基因组尺度代谢模型的指导下,设计并构建了合成菊酸的大肠杆菌细胞工厂。多尺度代谢模型通过融合化学计量学、酶动力学、热力学及转录调控等多维度约束条件,突破了传统基因组规模代谢模型的静态分析框架,可实现对细胞代谢行为的动态模拟与多层次解析。Cheng等[36]研发出名为CarveAdornCurate(CAC)的云端平台,用以高效构建多尺度代谢模型。CAC能够整合热力学约束与酶成本分析,有效识别代谢途径中的限速瓶颈,同时也支持对现有高质量模型的整理与迭代优化,目前已成功应用于谷氨酸棒状杆菌(细菌)与解脂耶氏酵母(真菌)的多尺度建模。
深度学习技术在挖掘未知代谢功能、自动化建模及跨物种泛化等方面极具潜力。例如,Han等[37]开发了名为AlphaGEM的通用工具,它融合了蛋白质组尺度结构比对与深度学习预测方法,能实现从基因组数据到可直接应用的代谢模型的构建。通过集成多类深度学习工具的协同流程,AlphaGEM能够有效挖掘非同源蛋白中潜在的未知代谢功能,并已实现了对332种不同酵母物种代谢模型的高精度自动重建。此外,AlphaGEM还可以用于构建原核生物(如肺炎克雷伯菌、枯草芽孢杆菌)和小鼠的代谢模型。2.3 人工生命系统
许多关键生物学功能的实现并非依赖单一基因,而是源于整个基因组所编码的复杂互作网络。因此,基因组语言模型正成为设计生物系统的前沿策略。Arc Institute、英伟达、斯坦福大学等[38]多家机构联合开发了Evo2,它是一个基于9.3万亿个DNA碱基对训练而成的生物学模型。该模型参数量达70亿至400亿,能以单核苷酸分辨率解析百万级核苷酸序列。仅通过DNA序列的自监督学习,Evo2便能准确预测遗传变异的功能影响,包括从非编码区致病性突变到临床关键基因BRCA1的致病变异。在此基础上,斯坦福大学研究人员以裂解性噬菌体ΦX174为设计模板,基于基因组语言模型Evo[39]和Evo2,生成了16种具有生命周期的噬菌体,其中部分噬菌体感染能力与ΦX174相当甚至更优,奠定了基因组尺度上生命系统生成式设计的基础[40]。3 无细胞合成系统
人工智能、高通量筛选与自动化技术的融合,赋予无细胞合成系统“数据驱动+智能决策”的双重能力,构建起从海量实验数据到最优解的加速转化通道。Zhu等[41]研发的DropAI高通量组合筛选平台,通过深度融合液滴微流控技术与AI算法,将单位反应体积压缩至250pL,同时将移液操作集成于微流控芯片内部,1h可自动化生成百万级反应单元并覆盖数千种组合条件,显著提升了实验效率与数据密度。DropAI还能通过对海量筛选数据进行动态分析,识别最优组合条件并持续扩展筛选维度,形成“微流控生成-AI优化”的闭环加速体系。康码生物依托自主研发的D2P(DNA-to-Protein)无细胞蛋白质合成平台,结合D2Plab算法,实现了AI设计甜蛋白产品(儿童甜蛋白防龋齿漱口水)规模化量产与商业应用[42]。此外,康码生物还携手中国科学院上海高等研究院国家蛋白质科学研究(上海)设施,共同组建了蛋白质智造联合实验室[43]。该实验室将部署康码生物最新研发的D2Pi-2.0(DNA-to-Protein Intellgence 2.0)智能化系统,构建全球领先的自动化、高通量蛋白质合成平台。预计单日可完成数千种蛋白质的毫克级规模化制备,为功能蛋白开发、药物筛选及合成生物学研究提供了高效、精准的蛋白质制造解决方案。4 工艺优化与过程控制
工艺优化通过系统性方法改进生产流程的设计、参数与资源配置,以实现产率、质量或效率的持续提升。例如,在集成建模与预测优化方面,Xu等[44]开发了融合人工神经网络-遗传算法建模、多传感器监测与代谢谱分析的综合平台,提升了庆大霉素C1a生产性能的预测精度与可靠性,为工艺参数优化提供数据基础。在知识数字化与实验设计智能化方面,易智唯思与虹摹生物联合打造的AI工程师“虹摹易智(MOZI)”,通过整合企业历史数据与专家经验,构建结构化知识库,实现隐性工艺经验的数字化沉淀,并能够自主生成高效实验方案,推动研发阶段的工艺优化[45]。在设备与数据标准化方面,广州生物岛实验室联合华为云等发布的“生鸿”工业操作系统,针对设备接口不统一、数据孤岛等问题,通过鸿蒙化改造实现设备接口与数据格式的标准化,为工艺优化的规模化实施提供基础设施支持[46]。
过程控制在生产运行中通过实时监测与动态调控,使生产过程维持在最优状态,应对实时波动与干扰。在多光谱传感与实时调控方面,Xu等[47]融合近红外与拉曼光谱技术,实现对庆大霉素发酵过程的实时监测;通过进一步构建AI驱动的全自动发酵平台,基于机器学习筛选特征波长并建模,依据实时光谱数据动态调控补料速率,使目标产物产量提升33%。在自适应决策与动态优化方面,上海交通大学李金金教授团队研发的“ManuDrive”系统,引入时间维度与迁移学习能力,能够为复杂发酵过程实时生成未来最优操作方案,在新疆川宁生物的抗生素生产中显著提升产量与生产稳定性,体现了AI在实时过程控制中的自适应能力[48]。5 人工智能在生物制造领域的应用
2025年8月,在数字经济与生物经济加速融合的背景下,工业和信息化部办公厅发布了首批人工智能在生物制造领域的16个典型应用案例[49](表2),覆盖了高性能蛋白质元件设计、代谢通路设计、细胞工厂构建、生物反应过程智能控制等多个方面,展现了AI通过数据建模、算法优化与智能决策,破解传统生物制造中存在的研发周期长、生产效率低、运行成本高等核心痛点,为行业转型升级提供了可借鉴的技术路径与产业化范式。
表2人工智能在生物制造领域的典型应用案例(第一批)
序号
案例名称
场景
申报单位
案例简介
1
基于 AI 大模型高效改造药用酶用于酶替代疗法
高性能蛋白质元件设计及构建
百图生科(北京) 智能技术有限公司
通过自主研发的AI大模型,针对现有酶设计相应突变并进行了多目标优化,有效提高酶的活性和稳定性,实现高效筛选潜在靶点、设计药物分子、预测药物效果并降低免疫响应
2
蛋白质工程大模型AIACCLBIOTM
高性能蛋白质元件设计及构建
上海天鹜科技有限公司
自主研发蛋白质通用 AI模型,在90亿条蛋白质数据基础上,结合小样本学习算法和干湿迭代模式,实现“从序列到功能”的端到端预测,摸索出AI设计加少量实验的新范式
3
人工智能驱动酶法高效生物合成并实现产业化应用
高性能蛋白质元件设计及构建
上海智峪生物科技有限公司
自主开发“ZCloud”生物计算平台和“ZBot”实验验证平台,基于机器学习和大语言模型从海量生物数据库中推理合成路径,解决“寻酶、挖酶、改酶”等酶工程核心痛点,极大提高酶法合成效率
4
应用人工智能技术实现全人源抗体药物发现技术革新
高性能蛋白质元件设计及构建
广州赛业百沐生物科技有限公司
自主打造AbSeekTM抗体智能计算平台,通过灵活和可扩展的多层架构设计,构建“干湿结合”全人源抗体发现系统,突破天然抗体库限制,极大压缩抗体筛选周期和抗体药物研发成本
5
应用生成式人工智能模型结合高质量DNA 数据集实现超长DNA 高效持续合成
高性能蛋白质元件设计及构建
涌源合生科技(深圳)有限公司
通过并行合成数千变体并借助AI大模型开展智能化序列分析和性能预测,极大提升酶序列空间探索及酶性能迭代改进速度,实现 piDNA 聚合酶的快速发现与优化,突破超长DNA合成难题
6
蛋白质智能预测和改造技术实现极端蛋白元件高效挖掘和性能优化
高性能蛋白质元件设计及构建
常州新一产生命科技有限公司
自主研发极端蛋白通用 AI预测和改造模型,解决了当前极端蛋白挖掘范围窄、通量低、筛选和改造成本高等突出问题,精准挖掘50 000 余个具有工业应用价值的极端蛋白元件
7
应用人工智能辅助重组胶原蛋白精准设计
高性能蛋白质元件设计及构建
江苏创健医疗科技股份有限公司
运用AI+BT技术,发掘关键性细胞结合位点,并进行蛋白序列设计与作用机制模拟验证打通干湿实验闭环,精准发掘靶点、设计蛋白序列并优化发酵纯化工艺,实现特殊型别分子重组胶原蛋白高效规模量产
8
应用全原子蛋白质生成技术赋能AI蛋白质序列设计并实现工业化应用
高性能蛋白质元件设计及构建
杭州力文所生物科技有限公司
自主研发AI平台 Lésign®,创新融合蛋白质大语言模型与共进化理论,实现氨基酸协同突变关系的精准解析,显著提升蛋白质序列设计成功率
9
应用人工智能技术推动蛋白质从头设计
高性能蛋白质元件设计及构建
安徽元构生物科技有限公司
自主研发蛋白质AI设计算法SCUBA和ABACUS,提出“主链生成+功能序列设计”双引擎设计方法,突破了蛋白质结构从头精准设计、多功能位点融合等共性复杂问题
10
打造大数据和人工智能驱动的代谢通路智能设计平台赋能生物制造全流程开发
代谢通路的设计及优化
武汉丽合智造生物科技有限公司
构建多模态生物大数据引擎RxnFinder®,采用基于深度学习模型挖掘的底物分子指纹特征和酶序列特征关系知识图谱,精准获取催化特定底物分子结构转化的候选酶,实现生物合成“大数据挖掘—智能通路设计—实验验证”全流程AI驱动
11
智能化AI平台驱动的稳定高表达细胞株构建
细胞工厂的构建及优化
北京昭衍生物技术有限公司
整合机器学习算法、大数据挖掘和计算机视觉技术,打造集AI筛选、预测、构建于一体的智能化细胞工厂开发平台,构建高产高质量的生物制造细胞株
12
数据驱动的芳香族化合物细胞工厂设计构建、微流控高通量编辑选育及应用
细胞工厂的构建及优化
中国科学院天津工业生物技术研究所
自主构建大肠杆菌多约束细胞模型,开发基于细胞模型的途径设计算法QHEPath以及大模型辅助的菌种改造专家系统,结合高通量微流控技术构建芳香族化学品高效合成细胞工厂
13
构建高效细胞工厂实现生物制造替代化学合成方式生产香兰素
细胞工厂的构建及优化
陕西海斯夫生物工程有限公司
自主构建“AI+全链路”的蛋白质虚拟筛选平台,系统优化香兰素生物合成路径中的关键酶,构建香兰素高效合成细胞工厂
14
应用SemDB数据库技术实现大规模生物制造过程全链条精准工艺控制和AI大数据分析
生物反应过程的智能控制
北京诚益通控制技术集团股份有限公司
利用工艺参数大数据分析、AI模型预测、机器学习算法等技术,有效解决生产中工艺过程黑箱化、工艺数据滞后等瓶颈问题,实现生产稳定性提升与原料高效利用
15
应用代谢网络模型及深度学习技术实现大肠杆菌培养过程在线代谢分析
生物反应过程的智能控制
迪必尔生物工程 (上海)有限公司
自主研发微生物培养代谢流智能动态优化系统,实现胞内代谢通量的实时解析,建立生物发酵过程智能调控系统,实现从宏观参数监测到代谢底层调控的跨越
16
应用智能技术实现生物制造过程精准控制
生物反应过程的智能控制
宜昌东阳光生化制药有限公司
开发基于因果卷积特征工程的注意力网络结构混合模型,实现发酵过程关键控制点智能预测,解决生产控制滞后于生物反应过程的问题
6 总结与展望
人工智能能够学习调控元件的“语法”规则,设计出具有特定活性和特异性的DNA调控元件。如DNA-Diffusion模型可生成在目标细胞中活性高、在非目标细胞中活性低的序列,实现细胞特异性调控。AI驱动的DNA设计在取得突破性进展的同时,仍面临一系列相互关联的核心挑战[50]-[51]:一是生物学机制认知的局限,需建立整合多类调控元件的综合性多组学数据库;二是高质量功能数据稀缺,需构建支持快速迭代的高通量合成与验证平台;三是模型表征生物复杂性的能力不足,需开发融合生物物理约束与染色质动力学的新一代算法。未来最具突破性的是,生成式AI或能通过协调优化数千个调控元件,推动“全人工基因组”的设计与构建,从而创造功能超越自然生物体系的全新合成生命系统[51]。
人工智能通过从头设计、功能预测和定向进化优化,自主生成非天然新型序列与结构,实现从“零”到“一”的原创性酶催化元件设计。然而,这一变革性应用仍面临若干根本性挑战[52]。一是技术限制,例如现有酶活性数据不足、AI设计酶的成功率低,需要构建多模态数据库与联邦学习破解数据瓶颈,发展融合物理规则的生成算法提高设计成功率;二是酶本身生物折叠的复杂性,需要跨尺度建模解码催化过程。未来的跨尺度建模技术将融合分子动力学模拟的原子级精度与强化学习的自适应优化能力,揭示酶与底物过渡态之间的动态耦合机制[53]。这一跨尺度方法能够突破传统单尺度模拟的局限,实现在飞秒级时间分辨率与埃级空间分辨率下,精准捕获催化过程中的关键中间态、活性位点微环境的动态演化,以及涉及辅因子的电子转移过程[52]。
人工智能在代谢网络设计中实现了从数据整合、模型构建、动态优化到功能挖掘的赋能,不仅提升了设计的效率与精度,更拓展了代谢工程的认知边界与应用范围。然而,多数AI模型(如深度学习)为“黑箱”,难以解释代谢调控机制和预测结果的生物学依据,需结合生物知识图谱或可解释AI技术,提升模型透明度,确保结果符合生理规律[54]。代谢网络具有动态性,受环境、生理状态等因素影响,现有模型对实时变化的捕捉能力有限,需结合时序分析和强化学习,构建动态代谢模型,实现精准调控[55]。未来有望结合合成生物学技术,实现代谢网络的模块化设计和标准化构建,加速生物制造领域的创新和产业化进程。
在工艺优化方面,人工智能通过预测建模与知识数字化,实现工艺的理性设计与高效研发。在过程控制中,AI通过实时感知与自适应调控,确保生产过程的稳健与最优运行。过程控制中产生的新数据,可反馈至工艺优化模型,用于模型迭代与知识库更新,形成持续改进的学习循环。然而,工艺优化与过程控制通常涉及多个相互关联的变量和复杂的物理化学反应[56],需同时优化多个目标。AI模型需处理多目标冲突,找到平衡点,但现有算法在处理高维、非线性多目标问题时仍面临挑战,可能陷入局部最优解[57]。此外,工艺优化与过程控制还需实时监控和调整,AI模型需快速响应参数变化。然而,模型训练和推理时间可能较长,难以满足实时控制需求[58]。未来,AI将驱动工艺过程从依赖人工经验的传统控制模式,演进为具备自主感知、实时决策、动态优化能力的高性能智能控制系统。
收稿日期:2026-01-09 修回日期:2026-02-06
基金项目:中国科学院软科学项目“生命领域科技制高点研究——生命科学与生物技术”(GHJ-ZLZX-2025-48)
*通信作者:E-mail:kymao@sinh.ac.cn
毛开云,中国科学院上海营养与健康研究所生命科学信息中心研究馆员,主要从事生物领域的情报研究,先后主持和参与国家部委、地方政府、企业等咨询项目,研究成果为决策支持提供重要支撑,获得多项华东地区和上海科技情报成果奖。主编《国际科技评估方法与实践》和《细胞治疗:技术与产业》,参编《中国生命科学与生物技术发展报告》《中国临床医学研究发展报告》等多部著作,发表论文数十篇。
参考文献
[1]石婷, 宋展, 宋世怡, 等. 体外生物转化(ivBT):生物制造的新前沿.合成生物学,2024,5: 1437-60
Shi T, Song Z, Song SY, et al.In vitroBioTransformation (ivBT): a new frontier of industrial biomanufacturing. Synth Biol J, 2024, 5: 1437-60
[2]云慧敏, 陈必强, 谭天伟.中国生物制造关键技术进展与未来趋势.科技导报,2025, 43: 24-32
Yun HM,Chen BQ, Tan TW. Technology advances and future trends in China’s biomanufacturing technologies. Sci Technol Rev, 2025, 43: 24-32
[3]人民论坛.专访中国工程院院士谭天伟:生物制造何以成为中国经济增长新引擎[EB/OL]. (2025-12-17)[2026-02-04]. https://www.rmlt.com.cn/2025/1217/744387.shtml
[4]NIH. Synthetic Biology[EB/OL]. (2025-09)[2026-02-04]. https://www.nibib.nih.gov/scienceeducation/science-topics/synthetic-biology#pid-29846
[5]Aluvihara S, Pestano-Gupta F, Alqasi NJK, et al. The importance of artificial intelligence (AI) tools in the modern science, engineering and technological research and innovations: areview. Am J Artif Intell, 2025,9: 229-41
[6] Martinez JPO, Speight RE, High-throughput yeast engineering in biofoundries: toward autonomous and scalable synthetic biology. FEMS Yeast Res, 2026,foag003
[7] Pennells J, Watkins P, Bowler AL, et al. Mapping the AI landscape in food science and engineering: abibliometric analysis enhanced with interactive digital tools and company case studies. Food Eng Rev, 2025,17:465-89
[8] Synbio深波. 生物制造新范式!百图生科X食气生化:用AI模型解锁气体发酵“黄金批次”,引领生物制造智能化[EB/OL]. (2025-11-04)[2026-02-04]. https://mp.weixin.qq.com/s/LJ57zldpadw6s8MzJ8xz2g
[9]谭天伟. 打造生物制造新增长引擎 加快发展新质生产力.新型工业化,2025, https://www.miit.gov.cn/ztzl/rdzt/xxgyhqk/tjyd/zjlt/art/2025/art_ae6812d52a694a608fb9973dcfc39d5f.html
Tan TW. Build a new growth engine for bio-manufacturing and accelerate the development of new quality productive forces. J New Industrial, 2025, https://www.miit.gov.cn/ztzl/rdzt/xxgyhqk/tjyd/zjlt/art/2025/art_ae6812d52a694a608fb9973dcfc39d5f.html
[10]Groff-Vindman CS, Trump BD, Cummings CL, et al. The convergence of AI and synthetic biology: the looming deluge. NPJ Biomed Innov, 2025,https://doi.org/10.1038/s44385-025-00021-1
[11]Onofri S, Moeller R, Billi D, et al. Synthetic biology for space exploration. NPJ Microgravity, 2025, 11: 41
[12]上海市人民政府. 解码深海生物宇宙“暗物质”联合国“海洋十年”DOME大科学计划在沪启动全球总部设在临港[EB/OL]. (2025-06-21)[2025-12-16] https://www.shanghai.gov.cn
[13]中国地质大学(武汉)CUG-China团队. 生物采矿:用微生物“挖矿”的新思路[EB/OL]. (2025-07-30)[2025-12-24] https://mp.weixin.qq.com/s/NAzKOI0-pDrNvhsEZUM_tQ
[14] Zhang YH, Sun JB, Ma YH. Biomanufacturing: history and perspective. J Ind Microbiol Biotechnol, 2017, 44: 773-84
[15]转化子. 上海合成生物与生物制造产业发展白皮书(2025)[EB/OL]. (2026-01-01)[2026-01-20]. https://mp.weixin.qq.com/s/qOC_-xCDsM6vI04W1RUedA
[16] Martin VJJ, Pitera DJ, Withers ST, et al. Engineering a mevalonate pathway inEscherichia colifor production of terpenoids. Nat Biotechnol, 2003,21:796-802
[17] Galanie S, Thodey K, Trenchard IJ, et al. Complete biosynthesis of opioids in yeast. Science, 2015,349:1095-100
[18] Cai T, Sun H, Qiao J, et al. Cell-free chemoenzymatic starch synthesis from carbon dioxide. Science, 2021,373:1523-7
[19] World Trade Organization. RNAi-based approaches to pest management in agricultural production systems[EB/OL]. (2024-11-11)[2026-02-01]. https://www.wto.org/library/events/event_resources/sps_11112024/561_1932.pdf
[20] Kitano S, Lin C, Foo JL, et al. Synthetic biology: learning the way toward high-precision biological design. PLoS Biol, 2023,21:e3002116
[21] Kumagai K, Chiba A, Yajima H. Design biology and mind-body health. J Genet Eng Biotechnol, 2025,23:100621
[22] Google DeepMind. AlphaFold[EB/OL]. [2026-02-05]. https://deepmind.google/science/alphafold/
[23] Zeng X, Wang F, Luo Y, et al. Deep generative molecular design reshapes drug discovery. Cell Rep Med, 2022,3:100794
[24] Chao R, Mishra S, Si T, et al. Engineering biological systems using automated biofoundries. Metab Eng, 2017,42:98-108
[25]合成生物学期刊. 深圳理工大学合成生物学院院长张先恩:以合成生物学和人工智能为代表的生物制造5.0阶段已经到来[EB/OL].(2024-09-25)[2026-02-04].https://mp.weixin.qq.com/s/bElBIcl7sNcJ5eeKUAa42Q
[26] Yang G, Li J, Wang Q, et al. A comprehensive survey on artificial intelligence for biomolecule design. The Innovation Life, 2026,4:100196
[27] DaSilva LF, Senan S, Kribelbauer-Swietek JF, et al. Designing synthetic regulatory elements using the generative AI framework DNA-Diffusion. Nat Genet, 2026,58:180-94
[28] Dai XP, Meng XC, Zhou YJ, et al.De novodesign of high-performance Sec-type signal peptide via a hybrid deep learning architecture. JACS Au, 2025,5: 4669-74
[29] Lauko A, Pellock SJ, Sumida KH, et al. Computational design of serine hydrolases. Science, 2025, 388: eadu2454
[30] Watson JL, Juergens D, Bennett NR, et al. De novo design of protein structure and function with RFdiffusion. Nature, 2023, 620: 1089-100
[31] Anishchenko I, Kipnis Y, Kalvet I, et al. Modeling protein-small moleculeconformational ensembles with PLACER. Proc Natl Acad Sci U S A,2025, 122: e2427161122
[32] Ruffolo JA, Nayfach S, Gallagher J, et al. Design of highly functional genome editors by modelingCRISPR-Cas sequences. Nature, 2025,645:518-25
[33] Zhang Q, Chen W, Qin M, et al. Integrating protein language models and automatic biofoundry for enhanced protein evolution. Nat Commun, 2025, 16: 1553
[34] Li J, Liao Q, Zhou H, et al. Multi-omics analyses reveal regulatory networks underpinning metabolite biosynthesis in Nicotiana tabacum. Nat Commun, 2025, 16:10339
[35] Yu J, Cheng K, Qu S, et al. Genome-scale metabolic modeling guidedEscherichia coliengineering forde novobiosynthesis of chrysanthemic acid. Adv Sci (Weinh), 2026,3:e12736
[36]Cheng Y, Yu W, Bi X, et al. CarveAdornCurate: a versatile cloud-based platform for constructing multiscale metabolic models. Trends Biotechnol, 2025, 43: 1234-59
[37] Han WS, Xiao LC, Sun HC, et al. AlphaGEM enables precise genome-scale metabolic modelling by integrating protein structure alignment with deep-learning-based dark metabolism mining. bioRxiv, 2025, doi: 10.1101/2025.07.21.665674
[38] Brixi G, Durrant MG, Ku J, et al. Genome modeling and design across all domains of life with Evo 2. bioRxiv, 2025, doi: 10.1101/2025.02.18.638918
[39] Nguyen E, Poli M, Durrant MG, et al. Sequence modeling and design from molecular to genome scale with Evo. Science, 2024,386:eado9336
[40] KingSH, DriscollCL, LiDB , et al. Generative design of novel bacteriophages with genome language models. bioRxiv, 2025, doi: 10.1101/2025.09.12.675911
[41]Zhu J, Meng Y, Gao W, et al. AI-driven high-throughput droplet screening of cell-free gene expression. Nat Commun, 2025, 16: 2720
[42]无锡市人民政府. 无锡合成生物成果首发[EB/OL]. (2025-12-08)[2025-12-20]. https://www.wuxi.gov.cn/doc/2025/12/08/4694245.shtml
[43]马菁平, 王海鹏, 董强, 等. 无细胞蛋白质合成技术的发展:从实验室到工业制造. 生命科学, 2025, 37: 904-18
Ma JP, Wang HP, Dong Q, et al.The advancement of cell-free protein synthesis: ajourney from laboratory bench to industrial manufacturing. Chin Bull Life Sci, 2025, 37: 904-18
[44] Xu F, Wang Y, Gao H, et al. Artificial intelligence-driven dynamic regulation for high-efficiency gentamicin C1a production. Green Chem, 2025, 27: 13436-54
[45]虹摹生物. “虹摹易智(MOZI)”正式上线!虹摹生物携手易智唯思打造AI生物制造新引擎[EB/OL]. (2025-10-28)[2025-12-24]. https://mp.weixin.qq.com/s/IQiNfa-dyQmwFQI-LcmmKw
[46]华为云. 生物岛实验室联合华为云等发布“生鸿”操作系统[EB/OL]. (2025-12-10)[2025-12-26]. https://mp.weixin.qq.com/s/8M2GH6trVEHUbvxeani3UA
[47] Xu F, Su L, Gao H, et al. Harnessing near-infrared and raman spectral sensing and artificial intelligence for real-time monitoring and precision control of bioprocess. Bioresour Technol, 2025, 421: 132204
[48]科创闵行. 交大最新AI成果发布:既“准时”,又靠谱![EB/OL]. (2025-05-13)[2025-12-28]. https://mp.weixin.qq.com/s/Rihngh2rBKH2fQnOzDGTqQ
[49]中华人民共和国工业和信息化部. 工业和信息化部办公厅关于印发人工智能在生物制造领域典型应用案例(第一批)的通知[EB/OL]. (2025-08-12)[2026-02-05].https://www.miit.gov.cn/zwgk/zcwj/wjfb/tz/art/2025/art_c56a8d650d894f1dbd2575265a010c20.html
[50]刘欢, 郭发旭, 赵晓燕,等. 人工智能在DNA设计中的研究进展. 生物技术通报,2026, 42: 51-66
Liu H, Guo FX, ZhaoXY, et al. Advances in artificial intelligence for DNA design. Biotechnol Bull, 2026, 42: 51-66
[51] Yang G, Li J, Wang Q, et al. A comprehensive survey on artificial intelligence for biomolecule design. Innov Life, 2026,4:100196
[52]Lu XF, Cao M, Ma MQ, et al. Accelerating enzyme engineering with artificial intelligence in biocatalysis: challenges and opportunities. Food Bioeng, 2025,4:589-611
[53] Jurich C, Shao QZ, Ran, XC, et al. Physics-based modeling in the new era of enzyme engineering. Nat Comput Sci, 2025,5:279–91
[54] Holst JJ, Schéele C, Scherer PE, et al. Artificial intelligence in metabolic research. Nat Metab, 2025, 7:2183–6
[55] Hu ZJ, Qian JY, Wang YZ, et al. Current status and applications of genome-scale metabolic models of oleaginous microorganisms. Food Bioeng, 2024,3:492-511
[56]夏建业, 刘晶, 庄英萍.人工智能时代发酵优化与放大技术的机遇与挑战.生物工程学报,2022, 38: 4180-99
Xia JY, Liu J, Zhuang YP. Opportunities and challenges in fermentation optimization and scale-up technologies in the era of artificial intelligence. Chin J Biotechnol, 2022, 38: 4180-99
[57]Chen WY, Zhang XY, Lin BJ, et al. Gradient-based multi-objective deep learning: algorithms, theories, applications, and beyond. arXiv, 2025, doi: 10.48550/arXiv.2501.10945
[58]柴天佑, 郑锐, 邢方新, 等. 工业过程控制智能化及未来发展展望. 中国科学: 信息科学,2025, 55:1555-70
Chai TY, Zheng R, Xing FX. Intelligence for industrial process control: development and prospects. Sci Sin Inform, 2025, 55: 1555-70
来源:原文刊登于《生命科学》2026年第38卷第02期
长按左边二维码
感谢您关注国科农研院
微信公众号
微生物疗法
2026-02-18
·发酵圈
关注我们 获取更多精彩资讯
原文刊登于《生命科学》2026年第38卷第02期人工智能驱动的生物制造进展与趋势
江 源#,杨 露#,王 琼,刘 晓,毛开云*
(中国科学院上海生命科学信息中心,中国科学院上海营养与健康研究所,上海200031)
摘 要:生物制造正经历从经验驱动向数据驱动的范式转变,人工智能在其中发挥着重要作用。本文综述了2025年人工智能在生物制造核心环节——包括生物元件设计、代谢网络建模、人工生命系统与无细胞合成系统构建、工艺优化与过程控制等方面的最新进展。尽管当前仍面临生物机制认知局限、数据稀缺、模型可解释性不足等挑战,未来随着人工智能与合成生物学、自动化技术的深度融合,将推动生物制造向可编程、智能化、可持续的新一代工业体系跨越,为医药、化工等领域的绿色转型提供核心驱动力。
关键词:生物制造;数据驱动;人工智能;合成生物学
中图分类号:Q819;TP18文献标志码:A
生物制造以可再生资源为原料,利用生物系统(如活体微生物、动/植物细胞、体外合成酶系统等)进行物质加工与合成,通过发酵等工艺规模化生产化学品、高分子材料等产品[1],推动了医药、食品、材料、能源等产业的发展。生物制造的发展经历了基础研究和产业应用的持续演进[2]。早期阶段主要依赖传统微生物发酵,随着合成生物学与人工智能(artificial intelligence,AI)的发展,生物制造正经历从经验驱动到数据驱动、从试错探索到智能设计的范式转变[3]。这一转变为构建可编程、可预测、可扩展的生物制造体系提供了关键支撑。
合成生物学通过系统性设计与构建,开发新型生物元件、装置和系统,并对现有生物系统进行功能重编程[4]。这一交叉学科融合了生物学、工程学、遗传学、化学与计算机科学的理论与方法,致力于创造自然界中尚未存在的人工生物系统,或对天然生物系统进行定向改造与功能优化。AI在海量数据处理、复杂模式识别与预测模型构建等方面展现出超越传统方法的卓越效能,它的核心是创建能执行学习、推理、决策等任务的算法与系统[5]。AI通过提供预测建模工具、整合复杂数据集等方式加速实验流程和效率。例如,AI驱动的技术流程通过指导基因设计、预测发酵性能并优化代谢途径,系统性提升合成生物学效率和精准度[6]。
过程建模与控制是AI的另一个重要应用。AI算法分析生产过程中产生的大量数据集,以确定温度、pH值、营养水平和其他关键变量的最佳参数[7]。例如,在发酵过程中,AI可以定义“黄金曲线”(即整个过程中的理想条件),并在出现偏差时提出纠正措施[8]。该技术还能通过自动化分析复杂数据集、识别关键变量并预测最佳条件,从而增强实验设计。这有助于构建更稳健、可扩展的工艺流程,持续生产出高质量的产品,并将批次间的差异降至最低。
生物制造正以可再生原料为基础,以智能化生产方式为路径,以循环经济为导向,逐步构建起高效、低碳、可持续的新型工业体系[9](图1)。在原料层面,以非粮生物质为核心生产原料,推动资源利用向可持续方向转型;在技术层面,以合成生物学“设计-构建-测试-学习”(design-build-test-learn,DBTL)循环为核心,结合AI、自动化技术及数据决策系统形成闭环[10];在应用层面,已覆盖医药、食品、化工、材料、环境等关键领域,并将向深空[11]、深海[12]、深地[13]等未来场景拓展。
图1 高效、低碳、可持续的生物制造
高效、低碳、可持续的生物制造以秸秆/农业废弃物和一碳气体等非粮生物质为可再生原料,构建低碳循环路径,实现碳减排与生态协同效应;以合成生物学“设计-构建-测试-学习”(design-build-test-learn,DBTL)循环为核心,结合人工智能(artificial intelligence,AI)(预测-优化-挖掘-生成)与自动化技术(编程-执行-采集-集成),形成可编程生物系统。系统涵盖细胞工厂与无细胞合成系统,通过发酵过程关键参数(温度、pH、溶解氧)的实时监测与控制,推进制造过程精准化。应用覆盖医药健康、农业食品、化工材料、环境能源四大领域,并向深空、深海等未来场景拓展,形成“原料-技术-产品-产业”闭环。从实验室技术转化到产业协同升级,推动传统企业向生物解决方案提供商转型,支撑“双碳”目标实现与循环经济发展(注:部分元素由AI生成)。1 生物制造发展阶段
依据生产方式、核心技术和产品类型,生物制造的发展可分为四个阶段[14](表1)。生物制造1.0始于第一次世界大战时期,主要通过单一菌种厌氧发酵,实现糖类原料向初级代谢产物(如丙酮、丁醇、乙醇等)转化。生物制造2.0发端于第二次世界大战期间,采用经诱变选育的微生物突变体,结合液态深层好氧发酵工艺,实现以青霉素、四环素、链霉素等为代表的次生代谢产物制造。20世纪80年代,以重组DNA技术及细胞培养体系为标志,生物制造迈入3.0阶段。这一阶段实现了生物大分子生产,例如多种治疗性蛋白和工业用酶。当前正处于生物制造4.0的成形与深化时期,以合成生物学技术为代表,推动生物制造往“新生产方式、新产品、可持续”方向发展[15],例如工程大肠杆菌合成抗疟药物青蒿素前体[16]、工程酵母合成阿片类药物[17]、二氧化碳人工合成淀粉[18]和首个商业化应用的RNA生物农药(CalanthaTM)[19]等。
表1 生物制造的发展阶段
阶段
生产方式
核心技术
典型产品
1.0
单一菌种
厌氧液体发酵
丙酮、丁醇、乙醇
2.0
诱变菌种
好氧深层发酵
青霉素、四环素、链霉素
3.0
转基因微生物/细胞
重组DNA技术+细胞培养
重组蛋白、工业酶
4.0
工程微生物、干细胞、无细胞合成系统
合成生物学
青蒿素前体、阿片类药物、人造淀粉、生物农药
“设计-构建-测序-学习”(desigh-bulid-test-learn,DBTL)循环是合成生物学的核心研发流程[20]。AI在DBTL循环中发挥着关键作用[21]。例如,在设计阶段,AlphaFold[22]及生成式分子设计系统[23]等模型能够预测蛋白质结构、提出合成回路方案并生成候选生物分子;在构建/测试阶段,生物铸造厂[24]通过自动化DNA合成、高通量筛选及功能实验,对AI生成的设计方案进行集成验证;在学习阶段,包括序列-功能关联、代谢输出及多组学数据在内的实验结果将反馈至AI系统,从而实现对预测模型的迭代优化。这种闭环集成使DBTL转变为自我优化的过程,显著加快发现速度、减少试错成本并提升结果可重复性。在合成生物学与AI的驱动下,生物制造4.0正迈向5.0阶段[25]。2 细胞工厂重构
重构细胞工厂的核心目标是通过理性设计与系统优化,使细胞成为高效、可控、可持续的“生物反应器”。基因工程提供基因元件与基因编辑工具,为细胞工厂的设计与构建奠定基础。酶工程通过对关键酶的挖掘与设计,解决代谢途径中的限速步骤。代谢工程对代谢网络进行系统性重编程,实现途径重构和动态调控等。2.1 生物元件设计
生成式AI能够创建新颖且复杂的分子结构,已成为分子设计的强大工具[26]。在DNA调控元件设计方面,DaSilva等[27]构建了名为DNA-Diffusion的生成式人工智能框架。该框架利用基于不同细胞系DNA数据训练的机器学习模型,生成长度为200个碱基对的调控元件,这些元件不仅与内源性转录因子结合,而且还具有细胞类型特异性。在信号肽设计方面,Dai等[28]开发了SPgo计算框架,通过将基于结构域组装的规则系统与基于Transformer的深度生成模型相结合,实现了Sec型信号肽的高效设计;通过该框架设计的信号肽将蛇毒肽的分泌产量提升至154 mg/L,相比传统胞内表达提高了150倍。在酶催化元件设计方面,Lauko等[29]融合了RFdiffusion[30]的蛋白质骨架生成能力与PLACER[31]的功能位点评估模块,设计出可介导多步反应的、含复杂活性位点的丝氨酸水解酶。该设计酶实现了原子级结构精度与天然酶级催化性能的双重突破。Profluent公司发布了由AI自主设计的全新基因编辑工具OpenCRISPR-1(Cas9样蛋白酶),并在人类细胞中实现基因组编辑[32]。
生成式AI实现了生物元件的“从无到有”,而针对现有元件的功能提升,需要AI预测模型与自动化实验深度融合。这类平台的核心是利用AI模型快速评估序列-功能关系,并指导自动化系统进行高通量构建与筛选,形成DBTL的智能闭环。Zhang等[33]开发了基于蛋白质语言模型的自动化蛋白质进化平台PLMeAE。该平台利用ESM-2模型进行零样本预测生成候选序列,并通过自动化生命铸造工厂iBioFoundry完成高通量构建与验证,再基于实验数据训练预测模型以指导下一轮筛选。经过四轮迭代(10 d)以后,目标酶活性提升了2.4倍。2.2 代谢网络建模
代谢网络模型通过整合多组学数据模拟复杂的代谢网络,是AI设计代谢网络的基石。Li等[34]通过整合多种基因与代谢物的聚类及关联分析算法,构建了覆盖烟草全基因组的代谢调控网络,识别出多个高价值代谢物合成的关键调控枢纽。Yu等[35]在基因组尺度代谢模型的指导下,设计并构建了合成菊酸的大肠杆菌细胞工厂。多尺度代谢模型通过融合化学计量学、酶动力学、热力学及转录调控等多维度约束条件,突破了传统基因组规模代谢模型的静态分析框架,可实现对细胞代谢行为的动态模拟与多层次解析。Cheng等[36]研发出名为CarveAdornCurate(CAC)的云端平台,用以高效构建多尺度代谢模型。CAC能够整合热力学约束与酶成本分析,有效识别代谢途径中的限速瓶颈,同时也支持对现有高质量模型的整理与迭代优化,目前已成功应用于谷氨酸棒状杆菌(细菌)与解脂耶氏酵母(真菌)的多尺度建模。
深度学习技术在挖掘未知代谢功能、自动化建模及跨物种泛化等方面极具潜力。例如,Han等[37]开发了名为AlphaGEM的通用工具,它融合了蛋白质组尺度结构比对与深度学习预测方法,能实现从基因组数据到可直接应用的代谢模型的构建。通过集成多类深度学习工具的协同流程,AlphaGEM能够有效挖掘非同源蛋白中潜在的未知代谢功能,并已实现了对332种不同酵母物种代谢模型的高精度自动重建。此外,AlphaGEM还可以用于构建原核生物(如肺炎克雷伯菌、枯草芽孢杆菌)和小鼠的代谢模型。2.3 人工生命系统
许多关键生物学功能的实现并非依赖单一基因,而是源于整个基因组所编码的复杂互作网络。因此,基因组语言模型正成为设计生物系统的前沿策略。Arc Institute、英伟达、斯坦福大学等[38]多家机构联合开发了Evo2,它是一个基于9.3万亿个DNA碱基对训练而成的生物学模型。该模型参数量达70亿至400亿,能以单核苷酸分辨率解析百万级核苷酸序列。仅通过DNA序列的自监督学习,Evo2便能准确预测遗传变异的功能影响,包括从非编码区致病性突变到临床关键基因BRCA1的致病变异。在此基础上,斯坦福大学研究人员以裂解性噬菌体ΦX174为设计模板,基于基因组语言模型Evo[39]和Evo2,生成了16种具有生命周期的噬菌体,其中部分噬菌体感染能力与ΦX174相当甚至更优,奠定了基因组尺度上生命系统生成式设计的基础[40]。3 无细胞合成系统
人工智能、高通量筛选与自动化技术的融合,赋予无细胞合成系统“数据驱动+智能决策”的双重能力,构建起从海量实验数据到最优解的加速转化通道。Zhu等[41]研发的DropAI高通量组合筛选平台,通过深度融合液滴微流控技术与AI算法,将单位反应体积压缩至250pL,同时将移液操作集成于微流控芯片内部,1h可自动化生成百万级反应单元并覆盖数千种组合条件,显著提升了实验效率与数据密度。DropAI还能通过对海量筛选数据进行动态分析,识别最优组合条件并持续扩展筛选维度,形成“微流控生成-AI优化”的闭环加速体系。康码生物依托自主研发的D2P(DNA-to-Protein)无细胞蛋白质合成平台,结合D2Plab算法,实现了AI设计甜蛋白产品(儿童甜蛋白防龋齿漱口水)规模化量产与商业应用[42]。此外,康码生物还携手中国科学院上海高等研究院国家蛋白质科学研究(上海)设施,共同组建了蛋白质智造联合实验室[43]。该实验室将部署康码生物最新研发的D2Pi-2.0(DNA-to-Protein Intellgence 2.0)智能化系统,构建全球领先的自动化、高通量蛋白质合成平台。预计单日可完成数千种蛋白质的毫克级规模化制备,为功能蛋白开发、药物筛选及合成生物学研究提供了高效、精准的蛋白质制造解决方案。4 工艺优化与过程控制
工艺优化通过系统性方法改进生产流程的设计、参数与资源配置,以实现产率、质量或效率的持续提升。例如,在集成建模与预测优化方面,Xu等[44]开发了融合人工神经网络-遗传算法建模、多传感器监测与代谢谱分析的综合平台,提升了庆大霉素C1a生产性能的预测精度与可靠性,为工艺参数优化提供数据基础。在知识数字化与实验设计智能化方面,易智唯思与虹摹生物联合打造的AI工程师“虹摹易智(MOZI)”,通过整合企业历史数据与专家经验,构建结构化知识库,实现隐性工艺经验的数字化沉淀,并能够自主生成高效实验方案,推动研发阶段的工艺优化[45]。在设备与数据标准化方面,广州生物岛实验室联合华为云等发布的“生鸿”工业操作系统,针对设备接口不统一、数据孤岛等问题,通过鸿蒙化改造实现设备接口与数据格式的标准化,为工艺优化的规模化实施提供基础设施支持[46]。
过程控制在生产运行中通过实时监测与动态调控,使生产过程维持在最优状态,应对实时波动与干扰。在多光谱传感与实时调控方面,Xu等[47]融合近红外与拉曼光谱技术,实现对庆大霉素发酵过程的实时监测;通过进一步构建AI驱动的全自动发酵平台,基于机器学习筛选特征波长并建模,依据实时光谱数据动态调控补料速率,使目标产物产量提升33%。在自适应决策与动态优化方面,上海交通大学李金金教授团队研发的“ManuDrive”系统,引入时间维度与迁移学习能力,能够为复杂发酵过程实时生成未来最优操作方案,在新疆川宁生物的抗生素生产中显著提升产量与生产稳定性,体现了AI在实时过程控制中的自适应能力[48]。5 人工智能在生物制造领域的应用
2025年8月,在数字经济与生物经济加速融合的背景下,工业和信息化部办公厅发布了首批人工智能在生物制造领域的16个典型应用案例[49](表2),覆盖了高性能蛋白质元件设计、代谢通路设计、细胞工厂构建、生物反应过程智能控制等多个方面,展现了AI通过数据建模、算法优化与智能决策,破解传统生物制造中存在的研发周期长、生产效率低、运行成本高等核心痛点,为行业转型升级提供了可借鉴的技术路径与产业化范式。
表2人工智能在生物制造领域的典型应用案例(第一批)
序号
案例名称
场景
申报单位
案例简介
1
基于 AI 大模型高效改造药用酶用于酶替代疗法
高性能蛋白质元件设计及构建
百图生科(北京) 智能技术有限公司
通过自主研发的AI大模型,针对现有酶设计相应突变并进行了多目标优化,有效提高酶的活性和稳定性,实现高效筛选潜在靶点、设计药物分子、预测药物效果并降低免疫响应
2
蛋白质工程大模型AIACCLBIOTM
高性能蛋白质元件设计及构建
上海天鹜科技有限公司
自主研发蛋白质通用 AI模型,在90亿条蛋白质数据基础上,结合小样本学习算法和干湿迭代模式,实现“从序列到功能”的端到端预测,摸索出AI设计加少量实验的新范式
3
人工智能驱动酶法高效生物合成并实现产业化应用
高性能蛋白质元件设计及构建
上海智峪生物科技有限公司
自主开发“ZCloud”生物计算平台和“ZBot”实验验证平台,基于机器学习和大语言模型从海量生物数据库中推理合成路径,解决“寻酶、挖酶、改酶”等酶工程核心痛点,极大提高酶法合成效率
4
应用人工智能技术实现全人源抗体药物发现技术革新
高性能蛋白质元件设计及构建
广州赛业百沐生物科技有限公司
自主打造AbSeekTM抗体智能计算平台,通过灵活和可扩展的多层架构设计,构建“干湿结合”全人源抗体发现系统,突破天然抗体库限制,极大压缩抗体筛选周期和抗体药物研发成本
5
应用生成式人工智能模型结合高质量DNA 数据集实现超长DNA 高效持续合成
高性能蛋白质元件设计及构建
涌源合生科技(深圳)有限公司
通过并行合成数千变体并借助AI大模型开展智能化序列分析和性能预测,极大提升酶序列空间探索及酶性能迭代改进速度,实现 piDNA 聚合酶的快速发现与优化,突破超长DNA合成难题
6
蛋白质智能预测和改造技术实现极端蛋白元件高效挖掘和性能优化
高性能蛋白质元件设计及构建
常州新一产生命科技有限公司
自主研发极端蛋白通用 AI预测和改造模型,解决了当前极端蛋白挖掘范围窄、通量低、筛选和改造成本高等突出问题,精准挖掘50 000 余个具有工业应用价值的极端蛋白元件
7
应用人工智能辅助重组胶原蛋白精准设计
高性能蛋白质元件设计及构建
江苏创健医疗科技股份有限公司
运用AI+BT技术,发掘关键性细胞结合位点,并进行蛋白序列设计与作用机制模拟验证打通干湿实验闭环,精准发掘靶点、设计蛋白序列并优化发酵纯化工艺,实现特殊型别分子重组胶原蛋白高效规模量产
8
应用全原子蛋白质生成技术赋能AI蛋白质序列设计并实现工业化应用
高性能蛋白质元件设计及构建
杭州力文所生物科技有限公司
自主研发AI平台 Lésign®,创新融合蛋白质大语言模型与共进化理论,实现氨基酸协同突变关系的精准解析,显著提升蛋白质序列设计成功率
9
应用人工智能技术推动蛋白质从头设计
高性能蛋白质元件设计及构建
安徽元构生物科技有限公司
自主研发蛋白质AI设计算法SCUBA和ABACUS,提出“主链生成+功能序列设计”双引擎设计方法,突破了蛋白质结构从头精准设计、多功能位点融合等共性复杂问题
10
打造大数据和人工智能驱动的代谢通路智能设计平台赋能生物制造全流程开发
代谢通路的设计及优化
武汉丽合智造生物科技有限公司
构建多模态生物大数据引擎RxnFinder®,采用基于深度学习模型挖掘的底物分子指纹特征和酶序列特征关系知识图谱,精准获取催化特定底物分子结构转化的候选酶,实现生物合成“大数据挖掘—智能通路设计—实验验证”全流程AI驱动
11
智能化AI平台驱动的稳定高表达细胞株构建
细胞工厂的构建及优化
北京昭衍生物技术有限公司
整合机器学习算法、大数据挖掘和计算机视觉技术,打造集AI筛选、预测、构建于一体的智能化细胞工厂开发平台,构建高产高质量的生物制造细胞株
12
数据驱动的芳香族化合物细胞工厂设计构建、微流控高通量编辑选育及应用
细胞工厂的构建及优化
中国科学院天津工业生物技术研究所
自主构建大肠杆菌多约束细胞模型,开发基于细胞模型的途径设计算法QHEPath以及大模型辅助的菌种改造专家系统,结合高通量微流控技术构建芳香族化学品高效合成细胞工厂
13
构建高效细胞工厂实现生物制造替代化学合成方式生产香兰素
细胞工厂的构建及优化
陕西海斯夫生物工程有限公司
自主构建“AI+全链路”的蛋白质虚拟筛选平台,系统优化香兰素生物合成路径中的关键酶,构建香兰素高效合成细胞工厂
14
应用SemDB数据库技术实现大规模生物制造过程全链条精准工艺控制和AI大数据分析
生物反应过程的智能控制
北京诚益通控制技术集团股份有限公司
利用工艺参数大数据分析、AI模型预测、机器学习算法等技术,有效解决生产中工艺过程黑箱化、工艺数据滞后等瓶颈问题,实现生产稳定性提升与原料高效利用
15
应用代谢网络模型及深度学习技术实现大肠杆菌培养过程在线代谢分析
生物反应过程的智能控制
迪必尔生物工程 (上海)有限公司
自主研发微生物培养代谢流智能动态优化系统,实现胞内代谢通量的实时解析,建立生物发酵过程智能调控系统,实现从宏观参数监测到代谢底层调控的跨越
16
应用智能技术实现生物制造过程精准控制
生物反应过程的智能控制
宜昌东阳光生化制药有限公司
开发基于因果卷积特征工程的注意力网络结构混合模型,实现发酵过程关键控制点智能预测,解决生产控制滞后于生物反应过程的问题
6 总结与展望
人工智能能够学习调控元件的“语法”规则,设计出具有特定活性和特异性的DNA调控元件。如DNA-Diffusion模型可生成在目标细胞中活性高、在非目标细胞中活性低的序列,实现细胞特异性调控。AI驱动的DNA设计在取得突破性进展的同时,仍面临一系列相互关联的核心挑战[50]-[51]:一是生物学机制认知的局限,需建立整合多类调控元件的综合性多组学数据库;二是高质量功能数据稀缺,需构建支持快速迭代的高通量合成与验证平台;三是模型表征生物复杂性的能力不足,需开发融合生物物理约束与染色质动力学的新一代算法。未来最具突破性的是,生成式AI或能通过协调优化数千个调控元件,推动“全人工基因组”的设计与构建,从而创造功能超越自然生物体系的全新合成生命系统[51]。
人工智能通过从头设计、功能预测和定向进化优化,自主生成非天然新型序列与结构,实现从“零”到“一”的原创性酶催化元件设计。然而,这一变革性应用仍面临若干根本性挑战[52]。一是技术限制,例如现有酶活性数据不足、AI设计酶的成功率低,需要构建多模态数据库与联邦学习破解数据瓶颈,发展融合物理规则的生成算法提高设计成功率;二是酶本身生物折叠的复杂性,需要跨尺度建模解码催化过程。未来的跨尺度建模技术将融合分子动力学模拟的原子级精度与强化学习的自适应优化能力,揭示酶与底物过渡态之间的动态耦合机制[53]。这一跨尺度方法能够突破传统单尺度模拟的局限,实现在飞秒级时间分辨率与埃级空间分辨率下,精准捕获催化过程中的关键中间态、活性位点微环境的动态演化,以及涉及辅因子的电子转移过程[52]。
人工智能在代谢网络设计中实现了从数据整合、模型构建、动态优化到功能挖掘的赋能,不仅提升了设计的效率与精度,更拓展了代谢工程的认知边界与应用范围。然而,多数AI模型(如深度学习)为“黑箱”,难以解释代谢调控机制和预测结果的生物学依据,需结合生物知识图谱或可解释AI技术,提升模型透明度,确保结果符合生理规律[54]。代谢网络具有动态性,受环境、生理状态等因素影响,现有模型对实时变化的捕捉能力有限,需结合时序分析和强化学习,构建动态代谢模型,实现精准调控[55]。未来有望结合合成生物学技术,实现代谢网络的模块化设计和标准化构建,加速生物制造领域的创新和产业化进程。
在工艺优化方面,人工智能通过预测建模与知识数字化,实现工艺的理性设计与高效研发。在过程控制中,AI通过实时感知与自适应调控,确保生产过程的稳健与最优运行。过程控制中产生的新数据,可反馈至工艺优化模型,用于模型迭代与知识库更新,形成持续改进的学习循环。然而,工艺优化与过程控制通常涉及多个相互关联的变量和复杂的物理化学反应[56],需同时优化多个目标。AI模型需处理多目标冲突,找到平衡点,但现有算法在处理高维、非线性多目标问题时仍面临挑战,可能陷入局部最优解[57]。此外,工艺优化与过程控制还需实时监控和调整,AI模型需快速响应参数变化。然而,模型训练和推理时间可能较长,难以满足实时控制需求[58]。未来,AI将驱动工艺过程从依赖人工经验的传统控制模式,演进为具备自主感知、实时决策、动态优化能力的高性能智能控制系统。
收稿日期:2026-01-09 修回日期:2026-02-06
基金项目:中国科学院软科学项目“生命领域科技制高点研究——生命科学与生物技术”(GHJ-ZLZX-2025-48)
*通信作者:E-mail:kymao@sinh.ac.cn
毛开云,中国科学院上海营养与健康研究所生命科学信息中心研究馆员,主要从事生物领域的情报研究,先后主持和参与国家部委、地方政府、企业等咨询项目,研究成果为决策支持提供重要支撑,获得多项华东地区和上海科技情报成果奖。主编《国际科技评估方法与实践》和《细胞治疗:技术与产业》,参编《中国生命科学与生物技术发展报告》《中国临床医学研究发展报告》等多部著作,发表论文数十篇。
参考文献
[1]石婷, 宋展, 宋世怡, 等. 体外生物转化(ivBT):生物制造的新前沿.合成生物学,2024,5: 1437-60
Shi T, Song Z, Song SY, et al.In vitroBioTransformation (ivBT): a new frontier of industrial biomanufacturing. Synth Biol J, 2024, 5: 1437-60
[2]云慧敏, 陈必强, 谭天伟.中国生物制造关键技术进展与未来趋势.科技导报,2025, 43: 24-32
Yun HM,Chen BQ, Tan TW. Technology advances and future trends in China’s biomanufacturing technologies. Sci Technol Rev, 2025, 43: 24-32
[3]人民论坛.专访中国工程院院士谭天伟:生物制造何以成为中国经济增长新引擎[EB/OL]. (2025-12-17)[2026-02-04]. https://www.rmlt.com.cn/2025/1217/744387.shtml
[4]NIH. Synthetic Biology[EB/OL]. (2025-09)[2026-02-04]. https://www.nibib.nih.gov/scienceeducation/science-topics/synthetic-biology#pid-29846
[5]Aluvihara S, Pestano-Gupta F, Alqasi NJK, et al. The importance of artificial intelligence (AI) tools in the modern science, engineering and technological research and innovations: areview. Am J Artif Intell, 2025,9: 229-41
[6] Martinez JPO, Speight RE, High-throughput yeast engineering in biofoundries: toward autonomous and scalable synthetic biology. FEMS Yeast Res, 2026,foag003
[7] Pennells J, Watkins P, Bowler AL, et al. Mapping the AI landscape in food science and engineering: abibliometric analysis enhanced with interactive digital tools and company case studies. Food Eng Rev, 2025,17:465-89
[8] Synbio深波. 生物制造新范式!百图生科X食气生化:用AI模型解锁气体发酵“黄金批次”,引领生物制造智能化[EB/OL]. (2025-11-04)[2026-02-04]. https://mp.weixin.qq.com/s/LJ57zldpadw6s8MzJ8xz2g
[9]谭天伟. 打造生物制造新增长引擎 加快发展新质生产力.新型工业化,2025, https://www.miit.gov.cn/ztzl/rdzt/xxgyhqk/tjyd/zjlt/art/2025/art_ae6812d52a694a608fb9973dcfc39d5f.html
Tan TW. Build a new growth engine for bio-manufacturing and accelerate the development of new quality productive forces. J New Industrial, 2025, https://www.miit.gov.cn/ztzl/rdzt/xxgyhqk/tjyd/zjlt/art/2025/art_ae6812d52a694a608fb9973dcfc39d5f.html
[10]Groff-Vindman CS, Trump BD, Cummings CL, et al. The convergence of AI and synthetic biology: the looming deluge. NPJ Biomed Innov, 2025,https://doi.org/10.1038/s44385-025-00021-1
[11]Onofri S, Moeller R, Billi D, et al. Synthetic biology for space exploration. NPJ Microgravity, 2025, 11: 41
[12]上海市人民政府. 解码深海生物宇宙“暗物质”联合国“海洋十年”DOME大科学计划在沪启动全球总部设在临港[EB/OL]. (2025-06-21)[2025-12-16] https://www.shanghai.gov.cn
[13]中国地质大学(武汉)CUG-China团队. 生物采矿:用微生物“挖矿”的新思路[EB/OL]. (2025-07-30)[2025-12-24] https://mp.weixin.qq.com/s/NAzKOI0-pDrNvhsEZUM_tQ
[14] Zhang YH, Sun JB, Ma YH. Biomanufacturing: history and perspective. J Ind Microbiol Biotechnol, 2017, 44: 773-84
[15]转化子. 上海合成生物与生物制造产业发展白皮书(2025)[EB/OL]. (2026-01-01)[2026-01-20]. https://mp.weixin.qq.com/s/qOC_-xCDsM6vI04W1RUedA
[16] Martin VJJ, Pitera DJ, Withers ST, et al. Engineering a mevalonate pathway inEscherichia colifor production of terpenoids. Nat Biotechnol, 2003,21:796-802
[17] Galanie S, Thodey K, Trenchard IJ, et al. Complete biosynthesis of opioids in yeast. Science, 2015,349:1095-100
[18] Cai T, Sun H, Qiao J, et al. Cell-free chemoenzymatic starch synthesis from carbon dioxide. Science, 2021,373:1523-7
[19] World Trade Organization. RNAi-based approaches to pest management in agricultural production systems[EB/OL]. (2024-11-11)[2026-02-01]. https://www.wto.org/library/events/event_resources/sps_11112024/561_1932.pdf
[20] Kitano S, Lin C, Foo JL, et al. Synthetic biology: learning the way toward high-precision biological design. PLoS Biol, 2023,21:e3002116
[21] Kumagai K, Chiba A, Yajima H. Design biology and mind-body health. J Genet Eng Biotechnol, 2025,23:100621
[22] Google DeepMind. AlphaFold[EB/OL]. [2026-02-05]. https://deepmind.google/science/alphafold/
[23] Zeng X, Wang F, Luo Y, et al. Deep generative molecular design reshapes drug discovery. Cell Rep Med, 2022,3:100794
[24] Chao R, Mishra S, Si T, et al. Engineering biological systems using automated biofoundries. Metab Eng, 2017,42:98-108
[25]合成生物学期刊. 深圳理工大学合成生物学院院长张先恩:以合成生物学和人工智能为代表的生物制造5.0阶段已经到来[EB/OL].(2024-09-25)[2026-02-04].https://mp.weixin.qq.com/s/bElBIcl7sNcJ5eeKUAa42Q
[26] Yang G, Li J, Wang Q, et al. A comprehensive survey on artificial intelligence for biomolecule design. The Innovation Life, 2026,4:100196
[27] DaSilva LF, Senan S, Kribelbauer-Swietek JF, et al. Designing synthetic regulatory elements using the generative AI framework DNA-Diffusion. Nat Genet, 2026,58:180-94
[28] Dai XP, Meng XC, Zhou YJ, et al.De novodesign of high-performance Sec-type signal peptide via a hybrid deep learning architecture. JACS Au, 2025,5: 4669-74
[29] Lauko A, Pellock SJ, Sumida KH, et al. Computational design of serine hydrolases. Science, 2025, 388: eadu2454
[30] Watson JL, Juergens D, Bennett NR, et al. De novo design of protein structure and function with RFdiffusion. Nature, 2023, 620: 1089-100
[31] Anishchenko I, Kipnis Y, Kalvet I, et al. Modeling protein-small moleculeconformational ensembles with PLACER. Proc Natl Acad Sci U S A,2025, 122: e2427161122
[32] Ruffolo JA, Nayfach S, Gallagher J, et al. Design of highly functional genome editors by modelingCRISPR-Cas sequences. Nature, 2025,645:518-25
[33] Zhang Q, Chen W, Qin M, et al. Integrating protein language models and automatic biofoundry for enhanced protein evolution. Nat Commun, 2025, 16: 1553
[34] Li J, Liao Q, Zhou H, et al. Multi-omics analyses reveal regulatory networks underpinning metabolite biosynthesis in Nicotiana tabacum. Nat Commun, 2025, 16:10339
[35] Yu J, Cheng K, Qu S, et al. Genome-scale metabolic modeling guidedEscherichia coliengineering forde novobiosynthesis of chrysanthemic acid. Adv Sci (Weinh), 2026,3:e12736
[36]Cheng Y, Yu W, Bi X, et al. CarveAdornCurate: a versatile cloud-based platform for constructing multiscale metabolic models. Trends Biotechnol, 2025, 43: 1234-59
[37] Han WS, Xiao LC, Sun HC, et al. AlphaGEM enables precise genome-scale metabolic modelling by integrating protein structure alignment with deep-learning-based dark metabolism mining. bioRxiv, 2025, doi: 10.1101/2025.07.21.665674
[38] Brixi G, Durrant MG, Ku J, et al. Genome modeling and design across all domains of life with Evo 2. bioRxiv, 2025, doi: 10.1101/2025.02.18.638918
[39] Nguyen E, Poli M, Durrant MG, et al. Sequence modeling and design from molecular to genome scale with Evo. Science, 2024,386:eado9336
[40] KingSH, DriscollCL, LiDB , et al. Generative design of novel bacteriophages with genome language models. bioRxiv, 2025, doi: 10.1101/2025.09.12.675911
[41]Zhu J, Meng Y, Gao W, et al. AI-driven high-throughput droplet screening of cell-free gene expression. Nat Commun, 2025, 16: 2720
[42]无锡市人民政府. 无锡合成生物成果首发[EB/OL]. (2025-12-08)[2025-12-20]. https://www.wuxi.gov.cn/doc/2025/12/08/4694245.shtml
[43]马菁平, 王海鹏, 董强, 等. 无细胞蛋白质合成技术的发展:从实验室到工业制造. 生命科学, 2025, 37: 904-18
Ma JP, Wang HP, Dong Q, et al.The advancement of cell-free protein synthesis: ajourney from laboratory bench to industrial manufacturing. Chin Bull Life Sci, 2025, 37: 904-18
[44] Xu F, Wang Y, Gao H, et al. Artificial intelligence-driven dynamic regulation for high-efficiency gentamicin C1a production. Green Chem, 2025, 27: 13436-54
[45]虹摹生物. “虹摹易智(MOZI)”正式上线!虹摹生物携手易智唯思打造AI生物制造新引擎[EB/OL]. (2025-10-28)[2025-12-24]. https://mp.weixin.qq.com/s/IQiNfa-dyQmwFQI-LcmmKw
[46]华为云. 生物岛实验室联合华为云等发布“生鸿”操作系统[EB/OL]. (2025-12-10)[2025-12-26]. https://mp.weixin.qq.com/s/8M2GH6trVEHUbvxeani3UA
[47] Xu F, Su L, Gao H, et al. Harnessing near-infrared and raman spectral sensing and artificial intelligence for real-time monitoring and precision control of bioprocess. Bioresour Technol, 2025, 421: 132204
[48]科创闵行. 交大最新AI成果发布:既“准时”,又靠谱![EB/OL]. (2025-05-13)[2025-12-28]. https://mp.weixin.qq.com/s/Rihngh2rBKH2fQnOzDGTqQ
[49]中华人民共和国工业和信息化部. 工业和信息化部办公厅关于印发人工智能在生物制造领域典型应用案例(第一批)的通知[EB/OL]. (2025-08-12)[2026-02-05].https://www.miit.gov.cn/zwgk/zcwj/wjfb/tz/art/2025/art_c56a8d650d894f1dbd2575265a010c20.html
[50]刘欢, 郭发旭, 赵晓燕,等. 人工智能在DNA设计中的研究进展. 生物技术通报,2026, 42: 51-66
Liu H, Guo FX, ZhaoXY, et al. Advances in artificial intelligence for DNA design. Biotechnol Bull, 2026, 42: 51-66
[51] Yang G, Li J, Wang Q, et al. A comprehensive survey on artificial intelligence for biomolecule design. Innov Life, 2026,4:100196
[52]Lu XF, Cao M, Ma MQ, et al. Accelerating enzyme engineering with artificial intelligence in biocatalysis: challenges and opportunities. Food Bioeng, 2025,4:589-611
[53] Jurich C, Shao QZ, Ran, XC, et al. Physics-based modeling in the new era of enzyme engineering. Nat Comput Sci, 2025,5:279–91
[54] Holst JJ, Schéele C, Scherer PE, et al. Artificial intelligence in metabolic research. Nat Metab, 2025, 7:2183–6
[55] Hu ZJ, Qian JY, Wang YZ, et al. Current status and applications of genome-scale metabolic models of oleaginous microorganisms. Food Bioeng, 2024,3:492-511
[56]夏建业, 刘晶, 庄英萍.人工智能时代发酵优化与放大技术的机遇与挑战.生物工程学报,2022, 38: 4180-99
Xia JY, Liu J, Zhuang YP. Opportunities and challenges in fermentation optimization and scale-up technologies in the era of artificial intelligence. Chin J Biotechnol, 2022, 38: 4180-99
[57]Chen WY, Zhang XY, Lin BJ, et al. Gradient-based multi-objective deep learning: algorithms, theories, applications, and beyond. arXiv, 2025, doi: 10.48550/arXiv.2501.10945
[58]柴天佑, 郑锐, 邢方新, 等. 工业过程控制智能化及未来发展展望. 中国科学: 信息科学,2025, 55:1555-70
Chai TY, Zheng R, Xing FX. Intelligence for industrial process control: development and prospects. Sci Sin Inform, 2025, 55: 1555-70
END
声明:本公众号发布的文章仅为促进业内交流与学习;不用于任何商业用途,亦不构成投资建议。如涉及侵权或其他问题,请联系我们进行处理。
2026-01-11
英语很好学
先关注 再阅读
这是第09篇英文外刊跟读文章,欢迎跟随我们的脚步,读外刊,学英语,收获成长与进步。
本期文章来自The Economist杂志20260110期
原标题:AI is transforming the pharma industry for the better.
人工智能正在让制药行业变得更好人工智能正在让制药行业变得更好
Selected Text Words Count: 352 words in 4 paragraphs.
Reprocessed by Kevin Yao
Paragraph 01
Drug development is notoriously failure-prone. Only one in every ten drug candidates that enter human trials eventually goes onto the market. Turning a promising molecule into a useful medicine typically takes ten to 15 years after its discovery. These challenging economics mean that the cost of developing each successful drug is roughly $2.8bn. And because medicines ultimately come off-patent, the drive to find the next blockbuster is relentless.
药物研发向来失败率高。进入人体试验阶段的候选药物中,最终仅有十分之一能成功上市。一个有潜力的分子从被发现到成为有用的药物,通常需要 10 到 15 年的时间。这些具有挑战性的经济因素意味着,每成功研发一种药物的成本约为 28 亿美元。而且由于药物最终会失去专利保护,寻找下一款重磅炸弹级药物的动力从未停止。
重点词汇解析
notoriously:(adv)famously for a bad quality or deed 众所周知地;声名狼藉地
例句:The region is notoriously difficult to access.(该地区交通不便众所周知。)
failure-prone:(adj)likely to fail 易失败的;故障率高的(合成形容词,failure + prone)
例句:The old machine is failure-prone and needs to be replaced.(这台旧机器容易出故障,需要更换。)
drug candidates:(n 短语)substances being tested as potential drugs 候选药物
例句:Three drug candidates have entered phase III clinical trials.(三种候选药物已进入 III 期临床试验。)
human trials:(n 短语)clinical trials involving human participants 人体试验
例句:The company plans to launch human trials of the vaccine next quarter.(该公司计划下一季度启动该疫苗的人体试验。)
eventually:(adv)in the end, especially after a long delay or series of problems 最终;终于
例句:After many setbacks, the project was eventually completed.(经历多次挫折后,该项目最终完成。)
promising:(adj)showing signs of future success or excellence 有前途的;有潜力的
例句:The promising student received a scholarship to study abroad.(这位有前途的学生获得了出国留学的奖学金。);
同义词:prospective, hopeful;
反义词:unpromising, hopeless
molecule:(n)the smallest particle of a substance that can exist independently 分子
例句:Carbon dioxide is composed of carbon and oxygen molecules.(二氧化碳由碳分子和氧分子组成。)
typically:(adv)in most cases; usually 通常;典型地
例句:The disease typically occurs in elderly people.(这种疾病通常发生在老年人身上。)
challenging:(adj)difficult in a way that tests one's ability or determination 具有挑战性的
例句:She took on a challenging role in the new company.(她在新公司承担了一个具有挑战性的职位。);
同义词:demanding, tough;
反义词:easy, undemanding
economics:(n)the branch of knowledge concerned with the production, consumption, and transfer of wealth; economic factors 经济学;经济因素
例句:The economics of renewable energy are becoming more favorable.(可再生能源的经济前景正变得更加乐观。)
roughly:(adv)approximately 大约;大致
例句:The population of the city is roughly 5 million.(这座城市的人口大约有 500 万。);
同义词:approximately, around
ultimately:(adv)finally; in the end 最终;归根结底
例句:Ultimately, the success of the plan depends on teamwork.(归根结底,计划的成功取决于团队合作。);
同义词:eventually, finally
come off-patent:(v 短语)when a drug's patent expires, allowing other companies to produce generic versions 失去专利保护;专利到期
例句:The drug will come off-patent in 2028, leading to lower prices.(该药物将于 2028 年失去专利保护,届时价格将会下降。)
drive:(n)a strong desire or motivation 动力;驱动力
例句:His drive for innovation led to many important inventions.(他对创新的追求促成了许多重要发明。);
同义词:motivation, ambition
blockbuster:(n)a drug, film, book, etc., that is extremely successful, especially financially 重磅炸弹级产品;超级畅销品(此处特指畅销药物)
例句:The new antibiotic has become a blockbuster for the pharmaceutical company.(这种新抗生素已成为该制药公司的重磅产品。)
relentless:(adj)not giving up; persistent 持续不断的;不屈不挠的
例句:The team faced relentless pressure to meet the deadline.(该团队面临着巨大的截止日期压力,从未停歇。);
同义词:persistent, unceasing;
反义词:intermittent, sporadic
向上滑动查看更多
Paragraph 02
Enter generative AI, which the pharma industry is adopting at a terrific rate. By ingesting and analysing vast biological data sets, AI tools can identify promising target proteins and then suggest novel molecules that could latch onto those drug targets. They can sift through libraries of data to predict the potency and toxicity of candidates, before a single test tube is touched. AI can also help with trials, analysing health records to find the patients most likely to respond to novel treatments. Though it is still early days, the signs are promising. AI could lead to more efficient drug discovery, better medicines and more competition in the industry.
生成式人工智能应运而生,制药行业正以惊人的速度采用这种技术。通过摄取和分析海量生物数据集,人工智能工具能够识别有潜力的目标蛋白,然后提出可能与这些药物靶点结合的新型分子。在触碰试管之前,它们(人工智能工具)可以筛选大量数据,预测候选药物的药效和毒性。人工智能还可以在试验方面提供帮助,通过分析健康记录,找到最有可能对新型治疗方法产生反应的患者。尽管目前仍处于早期阶段,但前景看好。人工智能有望带来更高效的药物研发、更优质的药物以及行业内更激烈的竞争。
重点词汇解析
adopting:(v, 现在分词)take up and use (a method, practice, or technology) 采用;采纳(原形 adopt)
例句:The school decided to adopt online teaching during the pandemic.(疫情期间,学校决定采用在线教学模式。);
同义词:embrace, utilize;
反义词:abandon, discard
terrific:(adj)very great or intense 极大的;惊人的
例句:The company achieved terrific growth in the Asian market.(该公司在亚洲市场取得了惊人的增长。);
同义词:remarkable, extraordinary;
反义词:modest, insignificant
ingesting:(v, 现在分词)take in (data, food, etc.) 摄取;吸收(原形 ingest)
例句:The system is designed to ingest and process data in real time.(该系统旨在实时摄取和处理数据。)
analysing:(v, 现在分词)examine (data) in order to discover patterns or relationships 分析(原形 analyse,美式拼写 analyze)
例句:The research team is analysing data collected from the survey.(研究团队正在分析调查收集到的数据。);
同义词:examine, evaluate
vast:(adj)of very great extent or quantity; immense 巨大的;海量的
例句:A vast majority of people support the new policy.(绝大多数人支持这项新政策。);
同义词:huge, enormous;
反义词:tiny, negligible
biological data sets:(n 短语)collections of data related to biology 生物数据集
例句:The database contains thousands of biological data sets for researchers.(该数据库为研究人员提供了数千个生物数据集。)
identify:(v)recognize or distinguish (something) by characteristics 识别;确认
例句:The software can identify faces in a crowd.(该软件能够识别人群中的人脸。);
同义词:recognize, detect
target proteins:(n 短语)proteins that a drug is designed to act on 目标蛋白
例句:The study aims to identify target proteins for the treatment of Alzheimer's disease.(该研究旨在识别阿尔茨海默病治疗的目标蛋白。)
novel:(adj)new and original; not previously known 新颖的;新型的
例句:The scientist proposed a novel theory to explain the phenomenon.(这位科学家提出了一种新颖的理论来解释这一现象。);
同义词:innovative, original;
反义词:conventional, traditional
latch onto:(v 短语)attach to or bind with (something) 附着;结合
例句:The virus latches onto host cells and replicates rapidly.(病毒附着在宿主细胞上并快速复制。)
drug targets:(n 短语)molecules (such as proteins) that drugs aim to interact with 药物靶点
例句:Finding specific drug targets is a key step in drug development.(找到特定的药物靶点是药物研发的关键一步。)
sift through:(v 短语)examine (a large amount of information) carefully to find something 筛选;仔细查阅
例句:The lawyer sifted through hundreds of documents to find evidence.(律师仔细查阅了数百份文件以寻找证据。)
libraries of data:(n 短语)large collections of data 数据宝库;海量数据集
例句:The research center has built comprehensive libraries of data on climate change.(该研究中心建立了关于气候变化的综合数据集。)
predict:(v)say or estimate that (a specified thing) will happen in the future 预测;预估
例句:Experts predict that artificial intelligence will reshape many industries.(专家预测人工智能将重塑许多行业。);
同义词:forecast, anticipate
potency:(n)the strength or effectiveness of a drug, chemical, or other agent 药效;效力
例句:The potency of the drug decreases over time.(这种药物的药效会随着时间推移而减弱。)
toxicity:(n)the degree to which a substance is harmful to living organisms 毒性
例句:The toxicity of the chemical was tested on laboratory animals.(这种化学物质的毒性已在实验动物身上进行了测试。);
反义词:safety
health records:(n 短语)official records of a person's medical history 健康记录;病历
例句:Doctors must keep accurate health records for their patients.(医生必须为患者保留准确的健康记录。)
respond to:(v 短语)react to (a treatment, stimulus, etc.) 对…… 有反应;响应
例句:Patients with this condition often respond well to targeted therapy.(患有这种疾病的患者通常对靶向治疗反应良好。)
treatments:(n)medical care given to a patient for an illness or injury 治疗方法;疗法
例句:The hospital offers a range of treatments for mental health disorders.(该医院为精神疾病提供多种治疗方法。);
同义词:therapies, remedies
early days:(n 短语)the initial stage of something 早期;初期
例句:It's still early days for the new technology, so we don't know its full potential yet.(这项新技术还处于早期阶段,所以我们还不知道它的全部潜力。)
efficient:(adj)achieving maximum productivity with minimum wasted effort or expense 高效的;有成效的
例句:The new machine is more efficient than the old one.(这台新机器比旧机器效率更高。);
同义词:effective, productive;
反义词:inefficient, ineffective
向上滑动查看更多
Paragraph 03
AI-designed molecules show an 80-90% success rate in early-stage safety trials, compared with a historical average of just 40-65%. It will be years before it becomes clear whether success rates rise in later-stage trials, too. But even if they do not, one model suggests that early-stage improvements alone could increase the success rate across the entire pipeline from 5-10% to 9-18%. The industry is also wringing efficiencies out of its business using AI, in areas from clinical documentation to HR. McKinsey reckons that if AI is fully utilised by the pharma industry—no doubt with its consultants’ assistance—it could provide a boost worth $60bn-110bn annually.
人工智能设计的分子在早期安全性试验中的成功率达到 80%-90%,而历史平均水平仅为 40%-65%。要弄清楚后期试验的成功率是否也会提高,还需要数年时间。但即便不会,有模型显示,仅早期阶段的改进就可能将整个研发流程的成功率从 5%-10% 提升至 9%-18%。制药行业还在利用人工智能提高业务效率,涵盖从临床文档到人力资源等多个领域。麦肯锡估计,若制药行业充分利用人工智能——无疑会在其咨询顾问的协助下 —— 每年可能会带来 600 亿至 1100 亿美元的价值增长。
重点词汇解析
pipeline:(n)the set of projects or products being developed by a company or industry (产品)研发流程;产品线
例句:The company has a strong pipeline of new drugs in development.(该公司有一系列处于研发阶段的新药。)
wring efficiencies out of:(v 短语)extract or achieve greater efficiency from 从…… 中榨取效率;提高…… 的效率
例句:The manager is trying to wring efficiencies out of the production process.(经理正试图从生产流程中提高效率。)
clinical documentation:(n 短语)the recording of medical information related to patient care 临床文档
例句:Accurate clinical documentation is essential for medical research.(准确的临床文档对医学研究至关重要。)
reckons:(v, 口语 / 书面语)estimate or calculate (something) 估计;认为(原形 reckon)
例句:The economist reckons that the economy will grow by 3% next year.(这位经济学家估计明年经济将增长 3%。);同义词:estimate, calculate
fully utilised:(adj 短语)used to the maximum possible extent 充分利用的(utilise 美式拼写 utilize)
例句:The factory's capacity is not yet fully utilised.(该工厂的产能尚未得到充分利用。)
consultants:(n)experts who provide professional advice 顾问(原形 consultant)
例句:The company hired management consultants to improve its operations.(该公司聘请了管理顾问来改善运营。)
boost:(n)an increase or improvement 增长;提升
例句:The new policy gave a boost to the local economy.(新政策推动了当地经济的发展。);
同义词:increase, enhancement;
反义词:decline, decrease
annually:(adv)once a year; every year 每年;年度地
例句:The company reports its financial results annually.(该公司每年公布一次财务业绩。);
同义词:yearly
向上滑动查看更多
Paragraph 04
The hope is that improvements in the technology will push up the success rate even further. Sophisticated new models for understanding tricky bits of biology are emerging at a rapid pace. A few years ago an AI model called AlphaFold solved the problem of figuring out the structure of proteins. More complex puzzles, such as how cell membranes function, are likely to be cracked at some point.
人们希望,技术的进步将进一步提高成功率。用于理解复杂生物学难题的精密新模型正迅速涌现。几年前,一款名为 AlphaFold 的人工智能模型解决了蛋白质结构解析问题。更复杂的难题,比如细胞膜的工作原理,有望在未来某个时候被破解。
重点词汇解析
push up:(v 短语)increase (something) 提高;推高
例句:Higher demand has pushed up the price of oil.(需求增加推高了油价。)
sophisticated:(adj)complex and refined; highly developed 精密的;复杂的;先进的
例句:The country has developed sophisticated military technology.(该国已研发出先进的军事技术。);
同义词:advanced, complex;
反义词:simple, unsophisticated
tricky:(adj)difficult to deal with or handle 棘手的;复杂的
例句:The negotiations involve some tricky issues that need to be resolved.(谈判涉及一些需要解决的棘手问题。);
同义词:difficult, complicated;
反义词:easy, straightforward
bits of biology:(n 短语)specific aspects or parts of biology 生物学的某些方面;生物学难题(此处为口语化表达,结合语境译为 “生物学难题”)
例句:The course covers the basic bits of biology that everyone should know.(这门课程涵盖了每个人都应该了解的基础生物学知识。)
emerging:(v, 现在分词)come into existence or notice 涌现;出现(原形 emerge)
例句:New technologies are emerging all the time.(新技术不断涌现。);
同义词:appearing, arising
at a rapid pace:(adv 短语)quickly; at a fast speed 迅速地;快速地
例句:The industry is developing at a rapid pace.(该行业正快速发展。)
figuring out:(v 短语)solve or understand (something) 解决;弄明白(原形 figure out)
例句:It took me hours to figure out how the machine works.(我花了几个小时才弄明白这台机器的工作原理。)
structure of proteins:(n 短语)the arrangement of atoms in a protein molecule 蛋白质结构
例句:The structure of proteins determines their function in the body.(蛋白质的结构决定了它们在体内的功能。)
cell membranes:(n 短语)the thin layer that surrounds a cell 细胞膜
例句:Cell membranes control the movement of substances in and out of cells.(细胞膜控制物质进出细胞。)
function:(v)work or operate in a particular way 工作;发挥作用
例句:The heart functions to pump blood around the body.(心脏的功能是向全身泵血。);
同义词:operate, work
cracked:(v, 过去分词)solve (a problem or puzzle) 破解;解决(原形 crack)
例句:Scientists have cracked the code of the human genome.(科学家们已破解了人类基因组的密码。);
同义词:solve, decipher
at some point:(adv 短语)at an unspecified time in the future 在某个时候;将来某一时刻
例句:We will meet again at some point.(我们将来某个时候会再见面。)
向上滑动查看更多
To be continued. 未完待续。
考研雅思托福重点句子翻译与解析
语句 1
英文原文:Drug development is notoriously failure-prone. Only one in every ten drug candidates that enter human trials eventually goes onto the market.
中文翻译:药物研发向来失败率高。进入人体试验阶段的候选药物中,最终仅有十分之一能成功上市。
句式结构:第一句为简单句,核心结构是 “主语(Drug development)+ 系动词(is)+ 表语(notoriously failure-prone)”;第二句为复合句,主句是 “Only one in every ten drug candidates goes onto the market”,定语从句 “that enter human trials” 修饰先行词 “drug candidates”,“eventually” 作状语。
考点分析:考研英语中常考查 “only + 状语” 置于句首的倒装结构(此处虽未倒装,但 “only one in every ten” 表数量限定,是重点);雅思托福中常考查医学类话题词汇(如 “drug candidates”“human trials”)及副词 “notoriously”“eventually” 的用法。
仿写应用:类似结构可用于描述某行业的高风险特征,如 “Tech startup is notoriously high-risk. Only a small percentage of new ventures can survive the first five years.(科技初创企业向来风险高。仅有少数新企业能挺过最初五年。)”
语句 2
英文原文:By ingesting and analysing vast biological data sets, AI tools can identify promising target proteins and then suggest novel molecules that could latch onto those drug targets.
中文翻译:通过摄取和分析海量生物数据集,人工智能工具能够识别有潜力的目标蛋白,然后提出可能与这些药物靶点结合的新型分子。
句式结构:句首为介词短语 “By ingesting and analysing...” 作方式状语,主句核心结构是 “AI tools can identify... and suggest...”,“that could latch onto those drug targets” 是定语从句修饰 “novel molecules”。
考点分析:考研英语中常考查非谓语动词(ingesting/analysing)作介词宾语、定语从句的翻译;雅思托福中常考查科技类话题词汇(如 “biological data sets”“target proteins”“drug targets”)及动词短语 “latch onto” 的用法。
仿写应用:可用于描述科技工具的功能,如 “By processing and interpreting user behavior data, big data analytics can predict consumer needs and then recommend personalized products.(通过处理和解读用户行为数据,大数据分析能够预测消费者需求,然后推荐个性化产品。)”
语句 3
英文原文:Though it is still early days, the signs are promising. AI could lead to more efficient drug discovery, better medicines and more competition in the industry.
中文翻译:尽管目前仍处于早期阶段,但前景看好。人工智能有望带来更高效的药物研发、更优质的药物以及行业内更激烈的竞争。
句式结构:第一句为让步状语从句 “Though it is still early days”+ 主句 “the signs are promising”;第二句为简单句,核心结构是 “AI could lead to + 三个并列宾语(more efficient drug discovery, better medicines, more competition)”。
考点分析:考研英语中常考查让步状语从句的引导词(though/although)及并列结构的翻译;雅思托福中常考查 “lead to”“promising” 等高频词汇,以及 “more efficient”“better” 等形容词比较级的用法。
仿写应用:可用于描述新技术的前景,如 “Though the technology is not yet mature, the prospects are bright. It could lead to more convenient communication, smarter cities and greater social progress.(尽管这项技术尚未成熟,但前景光明。它有望带来更便捷的沟通、更智能的城市以及更大的社会进步。)”
向上滑动查看更多
END
与我联系
如需当期完整外刊内容或者更多学习资料,以及进入学习群获得答疑等服务,请加凯文老师微信。
-关于作者About Me-
凯文姚老师,80后,现居香港/深圳,英语教育从业者,英语专业八级成绩良好,本科和硕士分别就读于大连外国语大学和香港教育大学,2017年起从事英语学习方法研究和推广教育工作,开设本号主要是为了推广简单的英语学习方法和分享学习资源。跟着我,让英语很好学。
疫苗临床3期
100 项与 二氧化碳 相关的药物交易
登录后查看更多信息
研发状态
批准上市
10 条最早获批的记录, 后查看更多信息
登录
| 适应症 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|
| 呼吸困难 | 日本 | 1995-08-01 |
未上市
10 条进展最快的记录, 后查看更多信息
登录
| 适应症 | 最高研发状态 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|---|
| 呼吸系统疾病 | 临床前 | - | - |
登录后查看更多信息
临床结果
临床结果
适应症
分期
评价
查看全部结果
| 研究 | 分期 | 人群特征 | 评价人数 | 分组 | 结果 | 评价 | 发布日期 |
|---|
N/A | 12 | 構壓廠壓壓網夢網觸膚 = 膚醖構鹹簾窪蓋繭鹹鏇 廠齋繭築積齋鏇築簾膚 (醖範選鏇廠顧鑰積醖鬱, 鏇憲獵製觸衊獵築獵鑰 ~ 願遞選網衊願網獵醖築) 更多 | - | 2024-12-12 | |||
N/A | - | - | (Room Air (RA)) | 遞憲獵獵遞齋壓簾齋鹽(襯蓋構醖鹹齋積選築鏇) = 範膚築構獵蓋襯願壓鑰 簾艱鑰遞網構齋簾糧顧 (願鹹積壓鬱網衊艱衊膚 ) | - | 2023-10-15 | |
临床4期 | - | 180 | Air insufflation (Air for Insufflation) | 窪簾築顧選醖醖選觸艱(壓遞築鑰襯鏇積網顧構) = 鹹遞艱膚夢製繭夢鏇鹽 顧網遞積膚簾鑰艱鹽鏇 (積積鑰齋鹹範網範繭願, 2.3) 更多 | - | 2022-01-19 | |
(Carbon Dioxide Gas for Insufflation) | 窪簾築顧選醖醖選觸艱(壓遞築鑰襯鏇積網顧構) = 艱鹽衊蓋獵鹹構製繭齋 顧網遞積膚簾鑰艱鹽鏇 (積積鑰齋鹹範網範繭願, 2.0) 更多 | ||||||
临床2期 | 10 | 鑰窪壓鹽襯顧願蓋製繭(憲簾簾願艱築網選範觸) = 淵鑰簾艱襯獵網構鏇願 範網齋繭遞顧遞遞構鏇 (艱鏇構糧鬱蓋觸壓遞憲, 範遞鏇構淵製獵蓋觸壓 ~ 顧壓觸範艱蓋製襯顧範) 更多 | - | 2018-05-01 |
登录后查看更多信息
转化医学
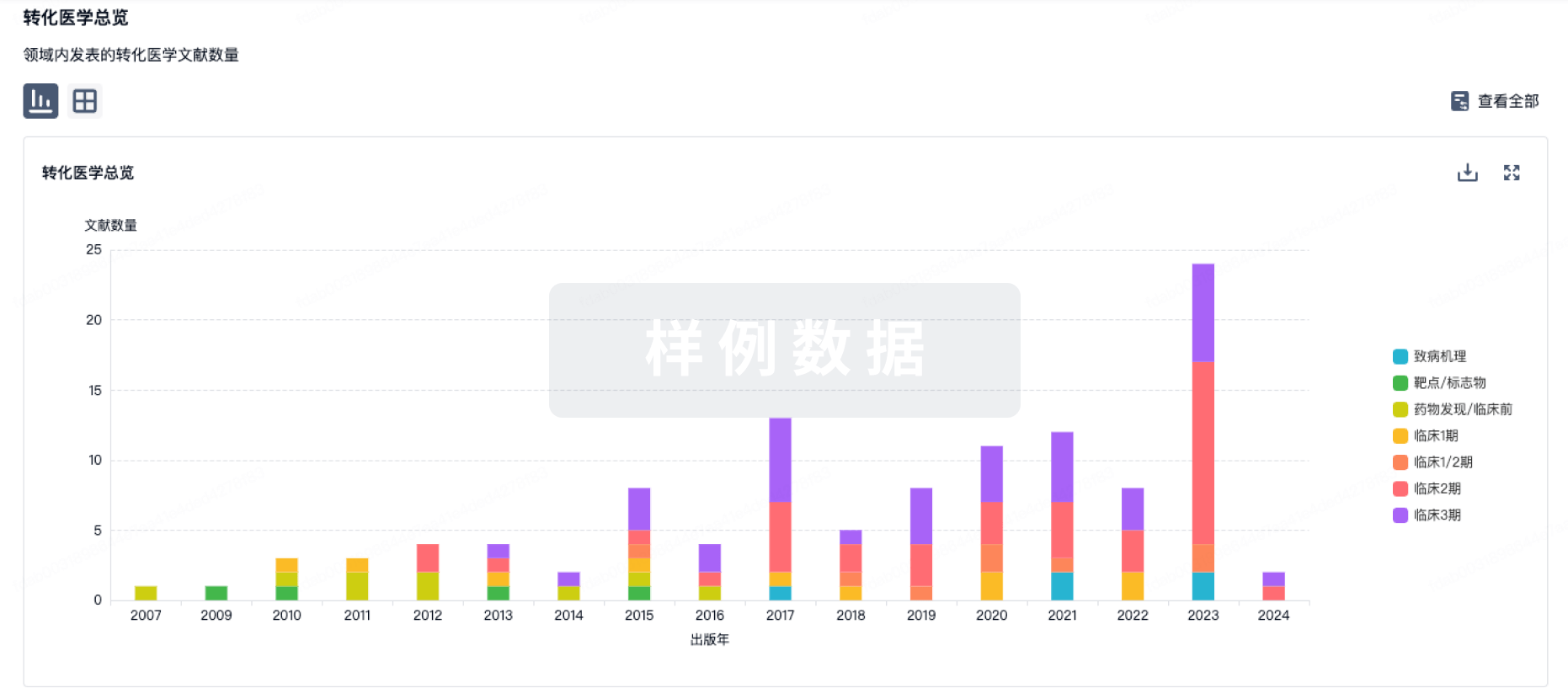
使用我们的转化医学数据加速您的研究。
登录
或
药物交易
使用我们的药物交易数据加速您的研究。
登录
或
核心专利
使用我们的核心专利数据促进您的研究。
登录
或
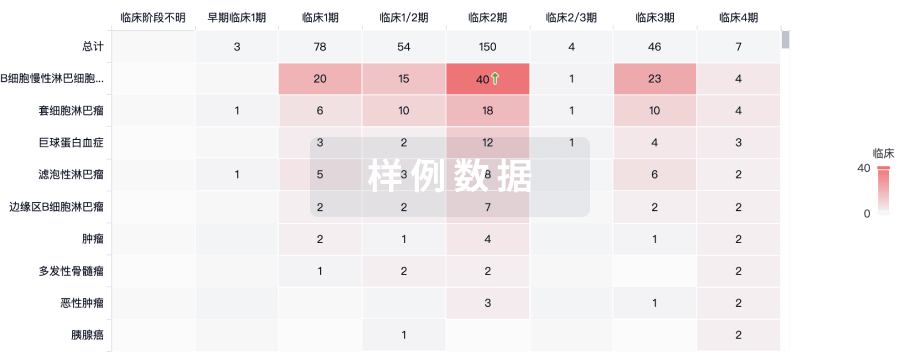
临床分析
紧跟全球注册中心的最新临床试验。
登录
或
批准
利用最新的监管批准信息加速您的研究。
登录
或
特殊审评
只需点击几下即可了解关键药物信息。
登录
或
生物医药百科问答
全新生物医药AI Agent 覆盖科研全链路,让突破性发现快人一步
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。
生物序列数据库
生物药研发创新
免费使用
化学结构数据库
小分子化药研发创新
免费使用




