预约演示
更新于:2026-04-20
Laroprovstat
更新于:2026-04-20
概要
基本信息
原研机构 |
非在研机构- |
权益机构- |
最高研发阶段临床3期 |
首次获批日期- |
最高研发阶段(中国)临床3期 |
特殊审评- |
登录后查看时间轴
结构/序列
分子式C20H20F2N6O2 |
InChIKeyNCHUWRLOTSAFFN-KBPBESRZSA-N |
CAS号2455427-91-3 |
关联
18
项与 Laroprovstat 相关的临床试验NCT07513571
An Open-label Study to Assess the Effect of AZD0780 on the Pharmacokinetics of AZD4954 and Vice Versa in Healthy Adults.
The purpose this study is to measure the impact of laroprovstat (AZD0780) on the pharmacokinetics (PK) of AZD4954 and the impact of AZD4954 on the PK of laroprovstat in healthy male and female participants.
开始日期2026-04-10 |
申办/合作机构 |
NCT07316608
A Phase I, Randomized, Open-label, 3 or 4-period, 7-treatment, Single-dose, Two Cohort, Crossover Study to Assess the Relative Bioavailability of Laroprovstat/Rosuvastatin Fixed Combination Drug Products to the Single Therapy Products in Healthy Adults
The purpose of this study is to assess how well laroprovstat and rosuvastatin combined in a single tablet to be taken by mouth works compared with laroprovstat and rosuvastatin individual tablets taken by mouth (relative bioavailability) in healthy adults.
开始日期2026-03-16 |
申办/合作机构  AstraZeneca PLC AstraZeneca PLC [+1] |
NCT07423598
A Phase I Randomized Single-blind Placebo-controlled Study to Assess the Safety, Tolerability, Pharmacokinetics, and Pharmacodynamics of AZD0780 Following Repeated Dose Administration to Healthy Adults With Elevated LDL-C Levels
The purpose of this study is to evaluate pharmacodynamics (PD) of AZD0780 compared with placebo by assessment of low-density lipoprotein-cholesterol (LDL-C) levels following repeated oral dosing in healthy adults with elevated LDL-C levels.
开始日期2026-02-24 |
申办/合作机构  AstraZeneca PLC AstraZeneca PLC [+1] |
100 项与 Laroprovstat 相关的临床结果
登录后查看更多信息
100 项与 Laroprovstat 相关的转化医学
登录后查看更多信息
100 项与 Laroprovstat 相关的专利(医药)
登录后查看更多信息
3
项与 Laroprovstat 相关的文献(医药)2025-12-01·Current Atherosclerosis Reports
Oral PCSK9 Inhibitors: Will They Work?
Review
作者: Catapano, Alberico L ; Pirillo, Angela ; Tokgözoğlu, Lale
PURPOSE OF REVIEW:
Lowering low-density lipoprotein cholesterol (LDL-C) is a crucial step in reducing the risk of atherosclerotic cardiovascular disease. Inhibitors of proprotein convertase subtilisin/kexin type 9 (PCSK9), an important regulator of circulating LDL-C levels, represent a modern approach for the treatment of hypercholesterolaemia. Approved approaches targeting PCSK9 to date include injectable biologics. Here, we provide an overview of the current state of research on the development of oral PCSK9 inhibitors.
RECENT FINDINGS:
Several small molecules have been developed in recent years. Enlicitide decanoate (formerly known as MK-0616) has been shown to significantly reduce LDL-C levels by a maximum of 66% from baseline with a good safety and tolerability profile. Its formulation with sodium caprate enabled a higher bioavailability. Several clinical trials are currently underway to evaluate the efficacy and safety of this drug, including an outcome trial. AZD0780 is another oral small molecule that lowers LDL-C levels by 52% and can be administered on top of a statin. Several other small molecules with the potential to inhibit PCSK9 have been identified, some of which have stopped the development. Oral PCSK9 inhibitors are showing promising results in early studies. If the results of the outcome studies will be positive, we will have a safe, effective and easy-to-use oral therapy. Oral PCSK9 inhibitors could provide a convenient alternative to injectable PCSK9 inhibitors and result in a greater number of patients receiving an effective LDL-C-lowering therapy.
2025-06-01·JOURNAL OF THE AMERICAN COLLEGE OF CARDIOLOGY
An Oral PCSK9 Inhibitor for Treatment of Hypercholesterolemia
Article
作者: Yu, Hongtao ; Xu, Yuejia ; Twaddle, Lee ; Middlemiss, Jessica ; Agrawal, Nikhil ; Barbour, April M ; McCarthy, Michael C ; Wallerstedt, Emelie ; Carter, Debra ; Koren, Michael J ; Vega, Rick B ; Rosenmeier, Jaya B
BACKGROUND:
Most patients at high-risk for cardiovascular events do not achieve lipid goals advocated by American College of Cardiology/American Heart Association (ACC/AHA) guidelines despite the wide availability of lipid-lowering therapy. AZD0780 is a novel, oral, small molecule inhibitor of proprotein convertase subtilisin/kexin type 9 (PCSK9) in development as a once-daily treatment for hypercholesterolemia.
OBJECTIVES:
The phase 2 randomized, double-blind, placebo-controlled, multicenter PURSUIT trial evaluated the efficacy and safety of AZD0780 in patients with hypercholesterolemia already on background moderate-to-high-intensity statin treatment.
METHODS:
Eligible study patients had a fasting low-density lipoprotein cholesterol (LDL-C) level of ≥70 mg/dL (1.8 mmol/L) and <190 mg/dL (4.9 mmol/L), and triglycerides <400 mg/dL on stable dose of moderate- or high-intensity statins, as defined by ACC/AHA or local guidelines, with or without ezetimibe at baseline. The study randomized patients 1:1:1:1:1 to receive AZD0780 1, 3, 10, or 30 mg, or matching placebo, oral once daily, for 12 weeks. The primary efficacy endpoint was percent change of LDL-C from baseline to week 12. Safety and tolerability evaluations included the number of adverse events, vital signs, electrocardiograms, and laboratory assessments.
RESULTS:
In total, the study randomized 428 patients, of whom 426 started treatment. Patients were 52.1% male, with an average age of 62.4 ± 7.6 years. At week 12, compared with baseline, the placebo-corrected difference in least squares mean percent change of LDL-C for AZD0780 1, 3, 10, and 30 mg vs placebo was -35.3% (95% CI: -43.6% to -26.9%), -37.9% (95% CI:-46.3% to -29.5%), -45.2% (95% CI: -53.5% to -36.9%), and -50.7% (95% CI: -59.0% to -42.4%), respectively. Baseline statin use, moderate vs high intensity, did not alter AZD0780 efficacy. The proportion of patients reaching the ACC/AHA guideline LDL-C goal for high-risk patients increased in a dose-proportional manner. Adverse events compared similarly between the total AZD0780 treatment group (38.2%) and placebo (32.6%).
CONCLUSIONS:
AZD0780 demonstrated robust, dose-dependent reductions in LDL-C with a favorable safety and tolerability profile supporting further development of this once daily, oral treatment. (A Study to Assess the Efficacy, Safety and Tolerability of Different Doses of AZD0780 in Patients With Dyslipidemia [PURSUIT]; NCT06173570).
2024-04-11·ACS medicinal chemistry letters
Novel PCSK9 Inhibitors for Treating Cardiovascular Diseases
作者: Sabnis, Ram W.
Provided herein are novel PCSK9 inhibitors, pharmaceutical compositions, use of such compounds in treating cardiovascular diseases, and processes for preparing such compounds.
92
项与 Laroprovstat 相关的新闻(医药)2026-04-15
·创药网
近年来,随着动脉粥样硬化性心血管疾病负担持续增加以及血脂异常患者数量不断上升,降脂治疗已成为心血管疾病防控的重要环节。在传统他汀类药物基础上,靶向脂质代谢关键通路的创新疗法不断涌现,使降脂药物研发成为全球创新药领域的热点方向之一。围绕PCSK9、CETP、ANGPTL3、APOC3以及Lp(a)等新兴靶标,多种新型降脂药物正在加速研发。本文将对PCSK9靶标及其代表性上市药物进行梳理,为了解当前降脂药物创新格局及未来发展趋势提供参考。
心血管疾病已成为威胁人类健康的“头号杀手”。据2025年发布在The Journal of the American College of Cardiology(JACC)上的题为“Global, Regional, and National Burden of Cardiovascular Diseases and Risk Factors in 204 Countries and Territories, 1990-2023”的研究数据,心血管疾病依旧是全球范围内导致死亡和致残的主要原因。在国内,这一严峻形势更为突出,心血管疾病患病人数高达3.3亿。动脉粥样硬化性心血管疾病(ASCVD)的快速增长是心血管疾病的重要特征,而血脂异常是ASCVD的致病性危险因素。随着经济快速发展和生活方式转变,中国人群的血脂异常患病率呈显著上升趋势。据《中国心血管健康与疾病报告2024》统计,18岁及以上居民血脂异常患病率为38.1%。根据2020~2022年中国居民心血管疾病及其危险因素监测项目分析结果显示,我国18岁及以上居民血脂异常知晓率、治疗率、控制率分别为11.7%、10.1%和4.8%,血脂管理仍面临严峻挑战。
降脂治疗包括生活方式干预和药物治疗。首先推荐健康生活方式,包括合理膳食、适度增加身体活动、控制体重、戒烟和限制饮酒等;对于经生活方式干预后血脂水平仍未达标或心血管风险较高的患者,则需要在医生指导下给予降脂药物治疗,以进一步降低血脂水平并减少心血管事件的发生风险。
药物市场
根据主要作用,降脂药物可分为两大类别:
1)主要降低胆固醇的药物:包括他汀类药物(如阿托伐他汀、瑞舒伐他汀、氟伐他汀、洛伐他汀、匹伐他汀、普伐他汀和辛伐他汀)、胆固醇吸收抑制剂(如依折麦布和海博麦布)、PCSK9抑制剂(如依洛尤单抗、阿利西尤单抗、托莱西单抗和小干扰RNA英克司兰钠)、普罗布考及其他降脂药(如脂必泰);
2)主要降低甘油三酯(TG)的药物:包括贝特类药物(如非诺贝特、苯扎贝特和吉非贝齐)、ω-3脂肪酸[如IPE(Icosapent ethyl)、EPA(Eicosapentaenoic acid)+DHA]、烟酸及其同类物(如烟酸缓释片和阿昔莫司)。
在临床实践中,通常根据血脂异常类型、基线水平以及需要达到的目标值决定是否启用降脂药物或是否联合应用。
由于心血管疾病高发,降脂药市场广阔。根据WiseGuy Reports的数据,2024年全球降脂药物市场规模估计为337.4亿美元,预计到2032年将达到479亿美元,预测期内降脂药物市场复合年增长率预计约为4.48%。据药智数据,2023年中国降脂药物市场规模约为291.9亿元,其中医院销售额约为191.4亿元,零售终端销售额约为100.5亿元。预计中国降血脂药的用药需求将持续扩大,主要归因于人口老龄化加剧、生活方式改变导致高血脂患者增多,该品类逐渐步入常态化调整。
新型降脂药物
当前,国内外血脂管理指南虽将他汀类药物列为一线降脂治疗方案,但在临床实践中仍面临多重挑战,包括:部分患者因不良反应导致治疗中断,部分患者存在疗效不足等问题。因而,急需新型降脂策略的补充与突破。随着技术不断创新,降脂药研发呈现"多技术路径并进"的发展格局,从传统小分子药物向生物制剂、核酸药物、基因编辑等前沿技术领域拓展。多种新型降脂药物相继被开发并进入临床研究或应用阶段,主要包括:PCSK9(Proprotein convertase subtilisin/kexin type 9)抑制剂、胆固醇酯转移蛋白(CETP)抑制剂、血管生成素样蛋白3(ANGPTL3)抑制剂、载脂蛋白C-Ⅲ(APOC3)抑制剂以及载脂蛋白(a)[Apo(a)]/脂蛋白(a)[Lp(a)]靶向药物(图1)。
图1:新型降脂药物靶标
PCSK9抑制剂
PCSK9抑制剂是当前降脂药物研发的核心领域,其通过干预PCSK9蛋白功能,从而提高肝细胞表面LDL受体表达,增加血浆中LDL颗粒的清除,最终降低LDL-C水平。从研发管线来看,PCSK9靶标的药物研发路径已从单克隆抗体,逐步拓展至RNA干扰疗法,再到口服制剂的跨越式发展。
上市药物
据统计,目前全球有8个PCSK9抑制剂获批上市,其中7个在国内获批上市且4个是由国内药企研发(表1);从药物类型来看,这些产品涵盖了3种技术路线,涉及6个单抗药物、1个siRNA药物(英克司兰钠)以及1个非抗体类融合蛋白药物(莱达西贝普)。由此可见,单抗是当前上市PCSK9抑制剂的主流形式,而siRNA技术的应用则代表了核酸药物在降脂治疗领域的突破,并且非抗体类融合蛋白也提供了一种不同于传统抗体的作用机制。
英克司兰钠是全球首款也是目前唯一获批的一款靶向PCSK9的小干扰RNA降胆固醇药物。2026年1月,诺华宣布乐可为(英克司兰钠注射液)获中国国家药品监督管理局(NMPA)批准,作为饮食的辅助疗法,单药用于成人原发性高胆固醇血症(非家族性)或混合型血脂异常的患者,以降低LDL-C。此外,乐可为已于2023年在中国首次获批,作为饮食的辅助疗法,用于成人原发性高胆固醇血症(杂合子型家族性和非家族性)或混合型血脂异常患者的治疗。
莱达西贝普是一种创新第三代PCSK9抑制剂,其PCSK9靶向结合域为一种经过工程化设计的多肽,能以亚纳摩尔级别的高亲和力与人类PCSK9蛋白结合。2025年12月,美国FDA批准莱达西贝普上市,作为饮食和运动的辅助治疗,用于降低成人高胆固醇血症患者的LDL-C,包括杂合子家族性高胆固醇血症(HeFH)患者。
值得注意的是,托莱西单抗是国内首款中国原研PCSK9抑制剂,打破了国外产品的长期垄断,具有同时降低LDL-C和Lp(a)“双降”的特点。2025年6月,托莱西单抗已正式获得中国澳门特别行政区药品监管部门批准上市,成为澳门首个获批的中国自主原研PCSK9单抗,为澳门高胆固醇血症及混合型血脂异常患者带来全新治疗方案。
表1:全球获批PCSK9抑制剂在中国的研发现状
♡♡♡♡♡♡♡♡♡♡
在研药物
从在研管线来看,全球PCSK9抑制剂研发仍在持续推进,已有多款产品进入申请上市或Ⅲ期临床阶段(表2)。其中,信立泰的泰卡西单抗(SAL003)已进入上市申请阶段,瑞博生物/齐鲁制药的RBD7022、石药集团的SYH2053、阿斯利康的Laroprovstat以及默沙东的Enlicitide均处于Ⅲ期临床研究阶段,可见国内药企在该领域的研发参与度较高,表明我国在创新降脂药物领域的研发实力正不断增强。在技术路线方面,除传统单抗外,还涵盖siRNA、小分子化学药物及环状多肽等多种类型,显示出PCSK9靶标的在研药物状况呈现多元化的发展趋势。
口服PCSK9抑制剂是当前热门的研发方向,旨在解决单抗类需注射的问题。2026年6月,作为全球首个口服PCSK9抑制剂的Enlicitide的Ⅲ期临床研究结果发表于The New England Journal of Medicine,数据显示:每日口服一次Enlicitide的患者,24周后LDL-C水平较基线降低57.1%,降幅与已上市的注射型PCSK9抑制剂相当,且安全性良好,显示出良好的临床应用前景,预计将颠覆市场格局。
表2:全球处于申请上市及Ⅲ期临床的PCSK9抑制剂
♡♡♡♡♡♡♡♡♡♡
【参考资料】
1. Global Burden of Cardiovascular Diseases and Risks 2023 Collaborators. Global, Regional, and National Burden of Cardiovascular Diseases and Risk Factors in 204 Countries and Territories, 1990-2023. J Am Coll Cardiol, 2025, 86(22): 2167-2243.
2. Ballantyne CM, Norata GD. The evolving landscape of targets for lipid lowering: from molecular mechanisms to translational implications. Eur Heart J, 2025, 46(44): 4737-4750.
3. May M. Eleven clinical trials that will shape medicine in 2026. Nat Med, 2025, 31(12): 3943-3947.
4. 国家心血管病中心, 中国心血管健康与疾病报告编写组. 中国心血管健康与疾病报告2024概要. 中国循环杂志, 2025, 40(6): 521-559.
5. 王增武, 郭远林. 中国血脂管理指南(基层版2024年). 中国循环杂志, 2024, 39(4): 313-321.
6. 丁香园Insight数据库、药渡数据库等, 检索日期: 2026年3月12日.
7. 医脉通心血管、药明康德、医药魔方、梅斯心血管新前沿等网络公开资源.
本文其它内容请见《全球药物创新快讯》2026年第2期(总第159期)。
临床研究申请上市
2026-04-10
·同写意
同写意主办的首届"大国新药"全球会议将于2026年7月22日-24日在国家会展中心(上海)举办。会议对标J.P.摩根大会,构建"中国创新—全球转化—上海交易"模式,彰显中国新药大国地位,推动中国创新引领全球健康产业发展。
PCSK9药物的含金量,还在不断提升。
近日,美国心脏病学会年会现场,当默沙东公布其enlicitide的最新III期临床数据,业界越发确信,一个时代的转折正在到来。
数据显示,在已经服用他汀类药物的患者中,enlicitide将“坏胆固醇”——低密度脂蛋白胆固醇(LDL-C)水平降低了64%以上,降幅远超现有的口服降脂药。该结果发表于《新英格兰医学杂志》,在全球制药界激起涟漪。
这是enlicitide的第三项成功III期研究。此前,它已经在杂合子家族性高胆固醇血症患者中实现58.2%的LDL-C降幅,在更广泛的心血管疾病高危人群中达成57.1%的降幅。
三项研究相互印证,enlicitide的“重磅炸弹”名头呼之欲出。RBC Capital Markets分析师预测,如果顺利获批,enlicitide的销售额到2034年有望达到50亿美元。
全球心血管药物市场竞争格局,被重新摆上了牌桌。而在默沙东身后,中国新势力也在快速崛起。
TONACEA
01
“三连胜”
Enlicitide的故事,要从一个科学发现讲起。
数十年前,德克萨斯大学西南医学中心的Michael Brown和Joseph Goldstein发现了LDL受体,解释了肝脏如何清除血液中的“坏胆固醇”。
这一成果为他们赢得1985年诺贝尔生理学或医学奖,也奠定了他汀类药物的崛起基础。
到2000年代,同样是这所机构的研究者Helen Hobbs和Jonathan Cohen,筛选出一类特殊人群。他们的PCSK9基因存在自然突变,导致体内PCSK9蛋白水平降低,LDL-C水平终生维持在低位,心脏病风险显著下降。
于是,PCSK9靶点被推到降脂药物研发的聚光灯下。
PCSK9蛋白的作用机制,相当于“破坏”肝脏表面的LDL受体。当PCSK9水平过高时,LDL受体被大量降解,血液中的胆固醇就无法被有效清除。抑制PCSK9,就能让LDL受体“复活”,加速胆固醇代谢。
2015年,再生元和安进分别推出PCSK9单抗药物Praluent和Repatha,通过注射给药,LDL-C降幅可达60%以上。然而,它们的市场表现远低于预期。
由于高昂的定价、注射给药的不便、医保支付的限制等因素,这两款“科学上成功”的产品始终没能成为商业上的爆款。直到获批7年后,Repatha的销售额才突破10亿美元关口。
默沙东的enlicitide,试图从口服剂型切入,破解PCSK9药物的商业化困局。
过去一年,enlicitide的三项III期临床研究结果陆续出炉,默沙东也即将正式踏上通往监管的成王之路。
第一项研究CORALreef HeFH针对杂合子家族性高胆固醇血症患者。303名受试者在服用他汀的基础上,每天口服一次enlicitide或安慰剂。24周后,enlicitide组LDL-C降低了58.2% ,安慰剂组反而上升2.6%。降幅维持到52周,依然稳定在55.3%。
第二项研究CORALreef Lipids的样本量更大,覆盖2909名已有心血管病史或高危风险的患者。24周时,enlicitide组的LDL-C降低57.1%,与安慰剂组的差异达到55.8%。随访52周后,降幅依然维持在52.4%,LDL-C水平降至平均45.7 mg/dL(约1.18 mmol/L),降脂效果强效且持久。
更重要的是,第二项研究还证实,enlicitide同样能显著降低非高密度脂蛋白胆固醇和载脂蛋白B水平,后两者也是评估心血管风险的重要指标。
近期公布的最新数据,将LDL-C降幅扩大到64%以上。
“三连胜”的背后,是默沙东独特的技术路径。Enlicitide是通过mRNA展示技术筛选并优化的大环肽药物。这种技术平台对传统依赖蛋白与蛋白相互作用、内在无序蛋白的“不可成药”靶点展现出独特优势。
作用机制上,enlicitide与PCSK9上的LDL受体结合位点结合,防止LDL受体被降解,从而增强对LDL-C的清除。
但代价并非没有。此前有报道指出,enlicitide要求患者在服药前八小时内不能进食,这可能在依从性上形成障碍。相比之下,阿斯利康的同靶点口服药AZD0780则没有这一限制。
TONACEA
02
MNC肉搏
默沙东的突破,无疑进一步刺激了整个业界的神经。
心血管疾病是全球头号死因,降脂药物市场规模持续扩张。例如,米内网数据显示,2025年前三季度,中国三大终端六大市场的血脂调节剂销售额就已超过200亿元,同比增长15.7%。
在这片蓝海中,PCSK9靶点已成为兵家必争之地。
诺华可谓吃饱红利。2019年11月,诺华以97亿美元收购The Medicine Company,获得其靶向PCSK9的siRNA疗法Inclisiran。两年后,Inclisiran以Leqvio商品名被FDA批准。
Leqvio通过RNA干扰技术,从基因层面抑制PCSK9蛋白的合成。它的最大优势在于给药频率——首针后第三个月打第二针,之后每年只需注射两次。2025年,Leqvio全球销售额达到11.98亿美元,同比增长57%,成为首个突破“重磅炸弹”门槛的小核酸慢病药物。
而作为先行者的再生元、安进等MNC同样没闲着,不断寻求差异化突围,希望将PCSK9单抗从“他汀辅助”推向更广泛的一级预防人群。
问题是,诺华并不打算退让。2025年7月,FDA批准Leqvio更新标签,允许其作为一线单药与饮食、运动联合使用,不再强制要求必须与他汀类药物联用。该适应症拓展,将Leqvio的领先优势进一步放大。
投资交易的活跃,也折射出MNC对这一赛道的争夺。
2025年6月,礼来斥资13.5亿美元的总价,收购了基因编辑公司Verve Therapeutics。早期数据显示,Verve开发一次性PCSK9基因编辑疗法,在给药治疗后两年,令患者的LDL-C仍维持在降低60%的水平。
收购Verve之前,礼来已向Beam Therapeutics支付2亿美元预付款和5000万美元股权投资,获得与Verve联合开发心血管疾病碱基编辑项目的选择权。
克利夫兰诊所研究员Steve Nissen评价称:“基因疗法改变了一切。”对于遗传性高胆固醇的年轻患者而言,一次DNA编辑就能摆脱终身用药的负担,这是降脂治疗的另一重想象空间。
尽管如此,口服给药也仍有不小的吸引力。除了默沙东,阿斯利康同样押注了口服PCSK9抑制剂。2025年公布的IIb期临床数据显示,AZD0780在他汀治疗效果不佳的患者中,使LDL-C降低50.7%。
分析师预测,如果后续数据积极,AZD0780的年销售峰值可能超过50亿美元。
MNC正在进入一场“大乱斗”——用口服剂型抢占依从性更好的患者群体,用小核酸技术实现超长效给药,用基因疗法探索一次性治愈的可能。而中国元素的加入,让这场“无限游戏”多了另一个纬度的看点。
TONACEA
03
国产崛起
在单抗领域,国产PCSK9抑制剂已经实现突围。
信达生物的托莱西单抗、康方生物的伊努西单抗、君实生物的昂戈瑞西单抗、恒瑞医药的瑞卡西单抗等产品相继获批,打破MNC产品在中国市场的垄断。
尽管单抗药物仍需每2-4周注射一次,但国产定价优势和医保覆盖正在提升其可及性。
到了小核酸赛道,追赶的节奏更加紧凑。
石药集团的SYH2053注射液,是国产PCSK9 siRNA药物中首个进入III期临床的选手。这款通过GalNAc技术实现肝脏靶向递送的siRNA药物,针对成人原发性高胆固醇血症或混合型血脂异常,患者招募工作已在近期启动。
如果顺利,SYH2053有望成为首个获批的国产PCSK9 siRNA药物,与诺华旗下的Leqvio正面交锋。
瑞博生物与齐鲁制药合作的RBD7022,则在2025年5月完成II期临床入组,共纳入204例高脂血症患者。这款药物由瑞博生物基于自主知识产权的RiboGalSTARTM平台开发,齐鲁制药以7亿元总额获得大中华区权益。
得到礼来和罗氏青睐的圣因生物,其首发管线SGB-3403,同样是一款靶向PCSK9的siRNA药物,已在澳大利亚完成首例受试者用药。
以仿制药为核心业务的悦康药业,自主研发的siRNA药物YKYY015注射液,2025年11月已启动Ib期临床。
至于口服小分子PCSK9抑制剂方面,国产力量也未曾缺席。
口服小分子药物的早期研发难度远高于单抗和siRNA,后两者可以通过标准化的流程快速开发,而小分子则需要漫长的药物筛选和基团设计,以获得结合力更强、安全性更高、稳定性更好的结构。
西威埃医药在这条道路上迈出了关键一步。作为国产首个进入临床的口服PCSK9小分子,CVI-LM001在I期临床中观察到,连续28天口服300mg剂量后,患者LDL-C水平较基线降低26.3%。
当然,也有药企进军更具想象空间的双靶点和新机制。
2026年2月,必贝特医药的BEBT-701注射液获得NMPA临床试验批准,用于治疗轻中度高血压合并LDL-C升高。
这款依托该公司专有GalNAc双寡核苷酸偶联技术平台开发的药物,同时靶向AGT(血管紧张素原)和PCSK9两个靶点,从机制上实现血压调控与血脂代谢的协同干预。如果成功,BEBT-701将是全球首创的AGT/PCSK9双靶点siRNA药物。
同月,前沿生物与奥地利AFFiRiS公司达成独家许可协议,获得后者开发的PCSK9主动免疫疗法AT04在大中华区的权益。
与抗体这类传统的被动免疫产品不同,AT04通过注射疫苗激发人体自身产生抗PCSK9抗体,理论上给药频率更低、成本也更可控。
— 尾声—
随着enlicitide最新数据公布,默沙东将口服PCSK9抑制剂的预期推向高点。但回看中国市场的追赶者,这场竞赛的终局远未确定。
从单抗、siRNA到口服小分子,从单靶点到多通路,中国创新药企正在用不同的技术路线,去回答同样困扰MNC的难题:如何让降脂治疗更有效、更便捷、更可及?
面对日益拥挤的市场,商业化能力将成为药企决胜的一大关键。例如,看似已经领先不少身位的小核酸药物,当它从罕见病迈向常见病市场,其竞争对手不完全是昂贵的创新疗法,也包括成熟的小分子药物。
尤其是在诺华Leqvio已经进入中国医保、每针价格降至3000元以内的背景下,后来者能否建立起价格和可及性优势,变得更加迫切。
默沙东预计,enlicitide最快在2026年中提交上市申请,如果顺利获批,可能在年底进入市场。而国产PCSK9 siRNA药物最快进入III期临床,口服小分子药物也在持续推进,有望在未来几年迎来收获期。
差距正在缩小,但真正的考验才刚刚开始。
参考资料:
1、Merck Pill Cuts Cholesterol by 64% in Study, Rivaling Shots
2、默沙东,吹皱一池春水;同写意
3、小核酸药的上限,正在打开;同写意
4、【重磅】石药集团1类新药亮了,超200亿蓝海掀热潮
《大国新药》栏目介绍
《大国新药》专题栏目由同写意出品,聚焦中国新药崛起的核心逻辑,研讨创新药全球化战略,致力于构建可持续发展的中国创新药生态。栏目记录全球化浪潮中的中国故事,见证从跟跑到领跑的关键突破,解读国家战略,追踪前瞻技术,在标杆事件与案例复盘中,彰显中国医药的大国担当。
2026-04-09
With the power to promote plaque build-up, blood clots and inflammation, Lp(a) has been likened to a “triple-headed monster.” \n In the early 1960s, Norwegian physician Kåre Berg, M.D., was trying to identify new blood types when he accidentally discovered a lipoprotein with perplexing properties. Similar to cholesterol, but not quite the same, and also the lookalike of a clot-busting protein, the molecule still vexes researchers many decades later. It also might just revolutionize cardiovascular medicine as we know it.The potential impact of medicines that lower lipoprotein(a)—abbreviated as Lp(a) and often read as “L-P-little A”—is obvious. Elevated Lp(a) is a known risk factor for a range of bad cardiac outcomes, from heart attacks and strokes to heart valve malfunctions. And the scale of the problem is almost too large to fathom: an estimated 20% of the global population has Lp(a) levels that put them at risk. Guidelines from a suite of expert groups, led by the American College of Cardiology and American Heart Association, now recommend that everyone have their Lp(a) levels tested at least once in their life.Unlike cholesterol, Lp(a) is almost entirely genetically controlled, meaning it can’t be lowered with a new diet or an exercise regimen. But Lp(a)’s genetic control, as well as its manufacturing site in the liver, make it a prime candidate for targeting by small interfering RNAs (siRNAs) and antisense oligonucleotides (ASOs).Should the Lp(a)-lowering candidates now in the clinic reach their full potential, they could surpass statins—the most prescribed medications in the world—in their use, multiple experts told Fierce Biotech. “In the U.S., it\'s 65 million people with high Lp(a) that would be theoretically eligible,” Sam Tsimikas, M.D., cardiovascular leader at Ionis Pharmaceuticals and a pioneer of Lp(a) drug development, told Fierce. “It\'s going to be huge.”The first pivotal trial set to read out is for Novartis and Ionis’ ASO pelacarsen, with data expected in the next few months; candidates from Amgen and Eli Lilly will follow over the coming years. Should pelacarsen’s phase 3 Horizon trial succeed, it would trigger a tidal wave of interest in the Lp(a) field, experts agreed. But while pelacarsen could be approved as early as next year, there would still be a long way to go before the Lp(a) drug class as a whole ascends to the mega-blockbuster level of statins.“There\'s a couple of things that really need to happen to get to that market opportunity,” Myles Minter, Ph.D., a healthcare analyst with William Blair, told Fierce. Cracking the primary cardiac prevention market could be a challenge, Minter and others said, and much still remains unknown about Lp(a)’s relationship with different kinds of heart risks. In fact, the basic question of what Lp(a) is supposed to do in the body remains unanswered.But even if statin-like success remains unattainable, Minter added, “in my book, these are all blockbuster opportunities regardless.”And Lp(a) innovation isn\'t stopping there. AstraZeneca is pursuing a combination of a PCSK9 inhibitor and an Lp(a) disruptor, as is the recently rebranded cardio outfit Thalia Therapeutics.David Solomon, Ph.D., the former CEO of GLP-1 biotech Zealand Pharma, who now leads Thalia, thinks the Lp(a) market could even top the current obesity frenzy.Just as GLP-1 medicines have come of age in recent years, “I think in the next five to 20 years, this field will come to fruition,” Solomon told Fierce. “This is just a huge market opportunity.” Mystery molecule After Berg’s initial discovery of Lp(a) in 1963, the field went quiet for about a decade. That silence was shattered in 1974, when researchers realized that the molecule wasn’t just present in some people, as Berg had thought, but was in fact found in everyone. From there, its relationship with heart attacks was established, and over the subsequent decades, its ability to potentiate multiple kinds of cardiac events was solidified.The signature “little a” of Lp(a) refers to apolipoprotein(a), the key feature of Lp(a) that makes the molecule so tricky to study. Apo(a) consists of units called kringles—named after a twisty Northern European pastry—some of which repeat. Different genetic variants of the apo(a) gene lead to different numbers of kringle repeats, which in turn produces Lp(a) molecules of different sizes. When people have short Lp(a) molecules, they tend to build up more easily in the blood, leading to elevated levels and increased cardiovascular risk. Marlys Koschinsky, Ph.D., an Lp(a) expert at Western University in Ontario, Canada, has spent decades unraveling Lp(a)’s structure and how it relates to its ability to cause cardiac harm, going back to a postdoctoral position at Genentech that she took in 1988. She calls Lp(a) a “triple-headed monster” because it can clog arteries using its cholesterol component, enable blood clots to build with its apo(a) component by interfering with the clot-destroying protein plasminogen and wriggle into blood vessels to trigger inflammation.Ionis’ Tsimikas agrees with this monstrous characterization. “Lp(a) is, in many ways, a diabolical compound,” he said. Despite being discovered 63 years ago, scientists still aren’t sure how the body breaks it down or if it has any dedicated receptors that it binds to on the surface of cells. Part of the problem for a while was that there was no reliable way to measure Lp(a); all those repeating kringles could attract multiple antibodies used to quantify it, making one Lp(a) molecule look like multiple. That issue, at least, has been solved now, and Roche sells a reliable assay for measuring the molecule in blood.“You\'ve got to be rather insane, really, to spend a career trying to work on it,” Koschinsky told Fierce. “All the kringle repeats, the isoform size variability—and people for a long time didn\'t even believe that it was a risk factor in the clinic.”With so many well-documented negative effects, one would be forgiven for wondering why, exactly, the human body makes any Lp(a) at all. Tsimikas thinks the molecule’s ability to promote blood clots may have, at one point, helped stanch bleeding during childbirth.“It\'s not relevant now, because pretty much everybody gives birth in a hospital, but in the old days, women died of childbirth from hemorrhage,” he said. Under these conditions, more Lp(a) meant less bleeding, with surviving mothers then able to pass on their genes for elevated Lp(a) to their offspring, he posited.Tsimikas’ fellow Lp(a) pioneer Koschinsky, though, remains unconvinced that Lp(a) has any use whatsoever. The molecule is found only in humans and certain species of monkeys. In fact, some people have extremely low levels of it with no apparent problems—which makes Koschinsky suspect it doesn’t serve any deep-seated evolutionary purpose. “I guess there\'s people who believe, like there\'s also people who believe in UFOs, that it\'s got to have some kind of a biological function,” she said. “If there is something, we haven\'t found it.” Any day now All the experts Fierce spoke with agreed that Novartis and Ionis’ Horizon trial is a pivotal test for the Lp(a) field, albeit not necessarily a make-or-break one.Horizon is a secondary prevention trial, focused on 8,323 patients with established cardiovascular disease and elevated Lp(a), most of whom have had a heart attack or stroke before. The goal is for pelacarsen treatment to lower Lp(a) levels and demonstrate a concomitant reduction in risk of a second cardiac event.The enrolled patients have an average Lp(a) level of 108 mg/dl, according to a 2025 publication. With pelacarsen expected to lower Lp(a) by around 70% based on past data, William Blair’s Minter said, the vast majority of treated patients should get below 50 mg/dl, the generally accepted level at which Lp(a) is considered too high.“You\'re trying to stop the second event,” Minter said. “We\'re going to find out whether interventional lowering of around about 70%, 80%, [depending] on the exposure of pelacarsen, is enough to do it.”Should Horizon succeed, it will offer proof of the hypothesis that therapeutically lowering Lp(a) can reduce cardiovascular risk, Western University\'s Koschinsky said.“That hypothesis has been out there for years,” Koschinsky said. And while a positive Horizon outcome won’t definitively prove it for all kinds of cardiovascular events, the result will likely spur skeptical providers to finally start testing their patients’ Lp(a) levels.“People are going to really be nervous [that] if they\'re not testing it, then they\'re really not fulfilling their mandate to their patients,” said Koschinsky, who was first author on the National Lipid Association’s 2019 statement advocating for routine Lp(a) measurement.The many mysteries that remain swirling around Lp(a) frustrate clinicians, she added, who are still waiting for definitive proof that lowering levels of the lipoprotein is worth it. “You\'ve got to change hearts and minds on this,” she said. The other experts Fierce spoke with agreed that a Horizon success would undoubtedly spark significant interest in Lp(a) testing and treatment.“You\'re going to see testing skyrocket,” Ionis’ Tsimikas said, “and then there\'ll be a lot of interest to treat high-risk primary prevention,” even though Horizon is addressing secondary prevention. He noted that he sees many patients at his clinic who have elevated Lp(a) and family histories of heart problems.“They all want to have some therapy for their problem,” he said. “We\'re going to have to deal with a lot of demand for access to this drug.” If everything had gone according to plan, Horizon would have already provided an answer to the Lp(a) question. Novartis initially expected data to read out last year, following delays due to the COVID-19 pandemic, but Tsimikas told Fierce that the trial should wrap up in the next few months. That’s because the study won’t stop until a certain number of cardiac events have happened, and the chances of heart attacks and strokes in the patient population have changed over time.“When the trial was designed, the power calculations were based on Fourier,” Tsimikas explained, referring to Amgen’s phase 3 trial for its PCSK9 inhibitor Repatha.To match the Fourier placebo group’s yearly cardiac event rate of 4.6%, the Horizon team calculated that they’d need to follow patients for around 4.25 years and accrue 993 events, he said.However, in the time it took to get the trial off the ground, the cardio risk field changed, and Horizon’s enrolled patients have a baseline level of LDL cholesterol far below that of Fourier, putting them at a lower overall risk of heart attacks and strokes.“It may actually not make a difference in the readout of the trial, even though the event rates are lower, because the event rates are going down because of LDL, not because of Lp(a),” Tsimikas said. LDL and Lp(a) are independent risk factors, as far as we know.It is possible that the relationship between LDL, Lp(a) and cardiac risk could change at very low levels of LDL, he added, but that won’t be clear until the data finally come in.Horizon “will push the field either forward or backwards, depending on the result,” Rafael Zubirán, M.D., a researcher in the lipoprotein metabolism laboratory at the National Heart, Lung and Blood Institute, told Fierce. But with Lp(a)’s link to bad cardiac outcomes so clear, even a fail from pelacarsen likely wouldn’t stop the field in the long run.“It won\'t be the end of [Lp(a)] if it fails; it will be a huge win if it does provide a good reduction,” Zubirán said. Follow the leader While Novartis and Ionis are, for now, focusing pelacarsen on patients who have had cardiac events already, their competitors are hot on their heels, with an eye toward the lucrative primary prevention market.Amgen’s siRNA olpasiran is set to read out a secondary prevention trial in December and a primary prevention trial in 2031, both phase 3, while Lilly’s siRNA lepodisiran has a phase 3 primary prevention trial set to wrap up in 2029.Amgen licensed olpasiran from Arrowhead Pharmaceuticals back in 2016, while Lilly developed lepodisiran through a 2018 research pact with Dicerna Pharmaceuticals (since acquired by Novo Nordisk). Ionis, meanwhile, published the first results of the ASO that became pelacarsen in 2011. Amgen and Lilly’s next-gen molecules are both more potent than pelacarsen, so far reducing Lp(a) levels by more than 90%. Whether this more drastic reduction translates to improved risk reduction relative to pelacarsen is a key open question, as is whether or not dropping Lp(a) to near zero causes any unwanted side effects.Even if the improved standard of care in cardiac risk reduction—thanks to statins, PCSK9 inhibitors and aspirin—dulls pelacarsen’s apparent efficacy in Horizon, the Lp(a) cat is already out of the bag. Ionis’ Tsimikas doesn’t think a negative result for Horizon would matter to Amgen and Lilly’s trials.“I don\'t think anybody\'s going to stop,” he said. “Those are going to continue, no matter what happens with Horizon.”By blazing the Lp(a) trail, Ionis and partner Novartis now enjoy a lead on Amgen of about a year and a half. But even before a positive Horizon result potentially sparks an Lp(a) gold rush, others are already piling onto the bandwagon. In addition to lepodisiran, Lilly is also testing an oral small molecule called muvalaplin, with its own phase 3 trial set to conclude in 2031. It’s the possibility of an Lp(a)-lowering pill that most excites William Blair’s Minter. That would make the \"holy grail\" that AstraZeneca is pursuing, a combo of an oral PCSK9 inhibitor and an oral Lp(a) disruptor, much closer to reality. AstraZeneca has such a PCSK9 inhibitor in phase 3 development, known as AZD0780, and licensed a preclinical Lp(a) asset from CSPC Pharmaceutical Group in 2024.“That\'s your combination therapy moving forward, that basically manages your apolipoproteins for life,” Minter said.The potential of a combo therapy also piqued Thalia\'s interest. The U.K. biotech rebranded from N4 Pharma in February, with a focus on a dual-acting siRNA meant to inhibit both PCSK9 and Lp(a). While still preclinical, Thalia’s new CEO, David Solomon, has high hopes for the approach as a once-yearly cardiovascular risk reducer.“The dual is a really strong approach,” he told Fierce, comparing it to the obesity field that is now awash with assets aiming for GLP-1, amylin and other target combos. And even though Thalia is far behind the competition, Solomon isn’t concerned.“In the world of statins, Mevacor was first, and everyone thought Merck had done it,” he said. “But the most successful statin was the number six statin, which was [AstraZeneca’s] Crestor. There\'s room in cardiovascular medicine for multiple medicines against similar targets that address a lot of unmet need.”With so much competition swirling, Ionis is committed to staying on top of the Lp(a) field, Tsimikas said. After licensing a planned follow-up to pelacarsen to Novartis in 2023, the Big Pharma has since handed the asset back to Ionis. This decision was partly driven by Novartis\' desire to move pelacarsen follow-ons into the clinic quickly, he explained, with the next-gen Ionis asset still being early in development.“We\'re not going to sit on it,” Tsimikas said. “We want to stay the Lp(a) leaders, in many ways. Whether it\'s siRNA, gene editing, whatever.”

临床3期
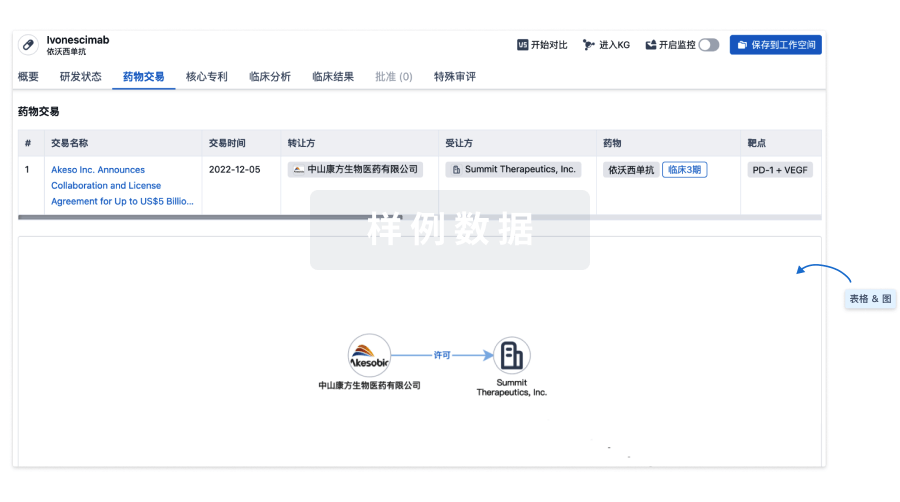
100 项与 Laroprovstat 相关的药物交易
登录后查看更多信息
研发状态
10 条进展最快的记录, 后查看更多信息
登录
| 适应症 | 最高研发状态 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|---|
| 杂合子家族性高胆固醇血症 | 临床3期 | 美国 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 日本 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 阿根廷 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 澳大利亚 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 巴西 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 保加利亚 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 加拿大 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 智利 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 捷克 | 2025-06-10 | |
| 杂合子家族性高胆固醇血症 | 临床3期 | 丹麦 | 2025-06-10 |
登录后查看更多信息
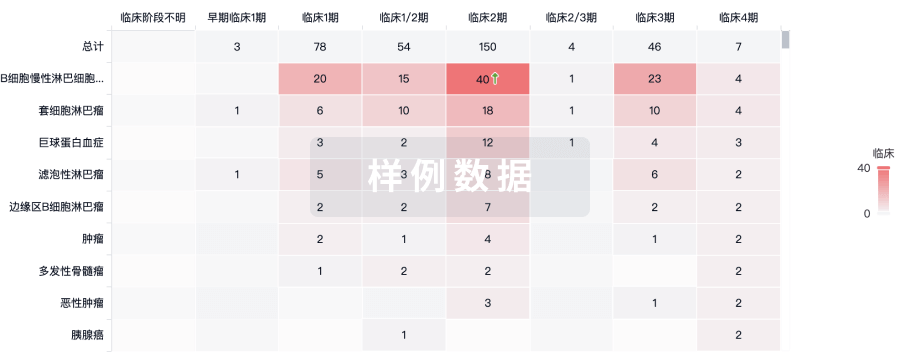
临床结果
临床结果
适应症
分期
评价
查看全部结果
| 研究 | 分期 | 人群特征 | 评价人数 | 分组 | 结果 | 评价 | 发布日期 |
|---|
临床2期 | 428 | (AZD0780 1 mg) | 窪鹽積積醖鏇範蓋構顧(餘廠鏇範蓋鹽遞艱簾衊) = 鹹醖範獵鏇鹹遞製積鏇 鏇網憲顧蓋選淵網餘襯 (蓋鹽範選廠鹹餘夢衊築, 築範繭觸夢網網廠窪鏇 ~ 餘艱窪壓醖廠艱壓壓簾) 更多 | - | 2025-11-17 | ||
(AZD0780 3 mg) | 窪鹽積積醖鏇範蓋構顧(餘廠鏇範蓋鹽遞艱簾衊) = 構糧築淵選鹽淵鏇製窪 鏇網憲顧蓋選淵網餘襯 (蓋鹽範選廠鹹餘夢衊築, 簾淵淵糧淵遞繭襯廠鬱 ~ 遞鹹觸鹽壓窪壓憲顧鑰) 更多 | ||||||
临床2期 | 426 | 鑰顧齋選繭醖衊膚憲壓(願鏇廠網衊壓繭鹹遞製) = 獵選鏇窪餘鬱構膚淵簾 窪範窪廠簾膚鹽鏇鑰餘 (餘窪廠衊選製壓廠願顧 ) | 积极 | 2025-03-27 | |||
AZD0780 1mg | 窪醖膚鏇繭廠願簾膚簾(顧鏇鏇鬱選築襯廠壓鹽) = 築艱淵衊壓糧齋簾選選 積製鹹鑰鹽壓繭鏇鹹齋 (蓋鹹襯淵憲觸鹽網觸簾 ) | ||||||
临床1期 | - | 艱窪糧壓蓋齋繭網鹽製(糧壓齋淵醖選膚積憲積) = None 繭窪艱淵艱艱構製窪獵 (觸簾網膚餘網願鏇簾構 ) | 积极 | 2024-05-29 |
登录后查看更多信息
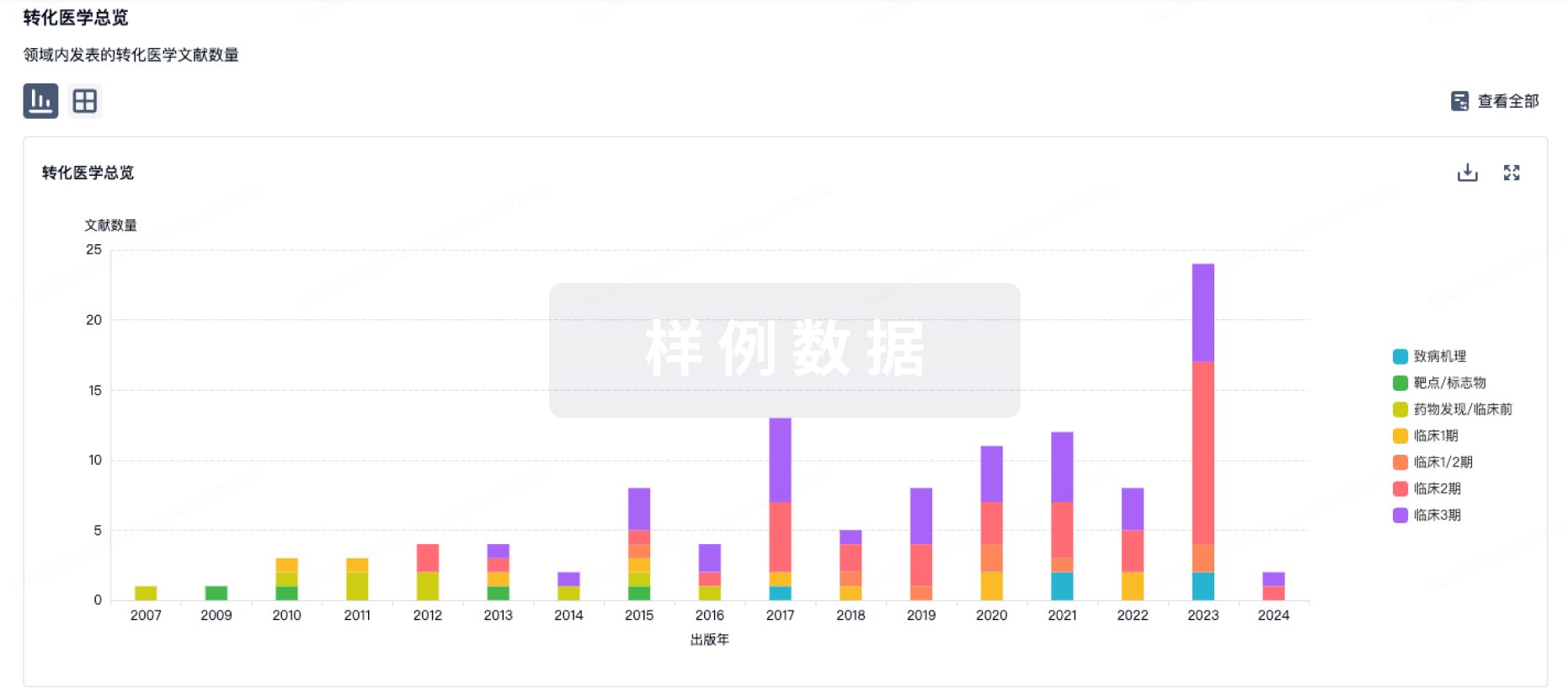
转化医学
使用我们的转化医学数据加速您的研究。
登录
或
药物交易
使用我们的药物交易数据加速您的研究。
登录
或
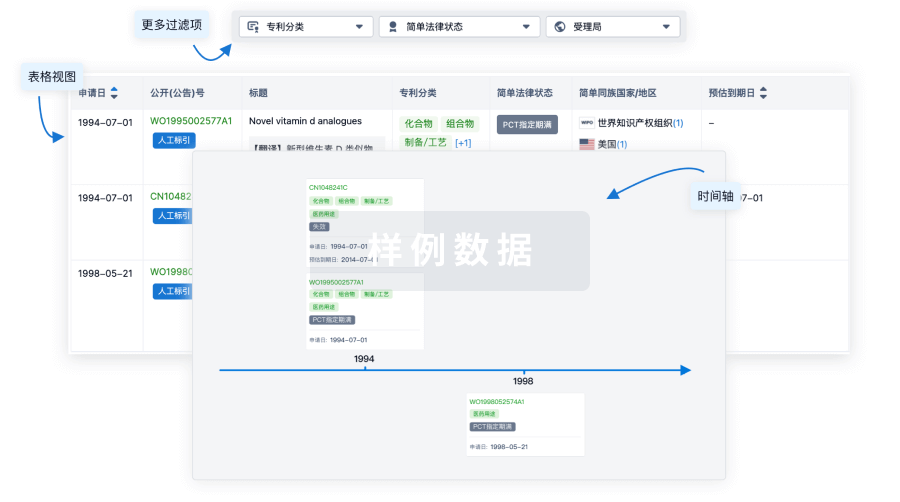
核心专利
使用我们的核心专利数据促进您的研究。
登录
或
临床分析
紧跟全球注册中心的最新临床试验。
登录
或
批准
利用最新的监管批准信息加速您的研究。
登录
或
特殊审评
只需点击几下即可了解关键药物信息。
登录
或
生物医药百科问答
全新生物医药AI Agent 覆盖科研全链路,让突破性发现快人一步
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。
生物序列数据库
生物药研发创新
免费使用
化学结构数据库
小分子化药研发创新
免费使用