预约演示
更新于:2026-05-16
N-acetyl-D-mannosamine
更新于:2026-05-16
概要
基本信息
登录后查看时间轴
结构/序列
分子式C8H15NO6 |
InChIKeyMBLBDJOUHNCFQT-WCTZXXKLSA-N |
CAS号3615-17-6 |
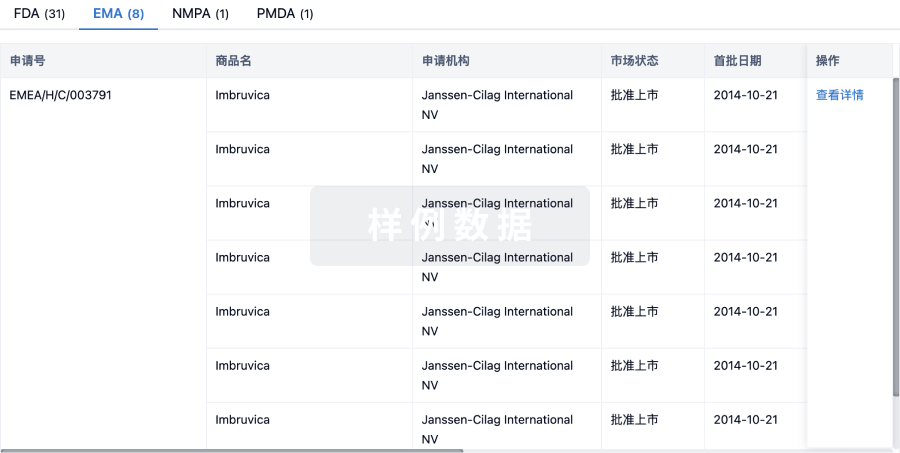
关联
9
项与 N-acetyl-D-mannosamine 相关的临床试验NCT06664814
An Open-Label Phase 2 Study of N-Acetyl-D-Mannosamine (ManNAc) in Subjects With Primary Focal Segmental Glomerulosclerosis
Background:
Focal segmental glomerulosclerosis (FSGS) is a disease that causes scarring in parts of the kidneys that filter waste. This can lead to protein loss in the urine, which can worsen kidney function. The kidneys may fail over time, and dialysis or a kidney transplant may be needed. Other treatments for this disease do not always work and often have adverse effects. Better treatments for FSGS are needed.
Objective:
To test a study drug (ManNAc) in people with FSGS.
Eligibility:
People aged 18 years and older with FSGS.
Design:
Participants will have 5 to 6 clinic visits over 14 weeks. Two of the visits will require overnight stays for 2 or 3 nights.
ManNAc is a white powder that comes in a sachet. It is dissolved in water and taken twice a day by mouth. Participants will take their first dose at the clinic. They will learn how to store ManNAc and prepare each dose. They will record their doses in a diary. They will also write down any adverse effects or troubles they have using the drug at home.
During clinic visits, participants will have physical exams with blood and urine tests. They will complete questionnaires about their health, sleep habits, and fatigue symptoms.
During overnight visits, participants will also have 24-hour urine collection.
A study team member will call participants 1 week after the first dose to check on their health. Follow-up phone calls will then be every 2 weeks after each clinic visit.
Participants may meet with a dietitian to discuss nutrition while taking the ManNAc.
Participants may choose to have genetic tests.
Focal segmental glomerulosclerosis (FSGS) is a disease that causes scarring in parts of the kidneys that filter waste. This can lead to protein loss in the urine, which can worsen kidney function. The kidneys may fail over time, and dialysis or a kidney transplant may be needed. Other treatments for this disease do not always work and often have adverse effects. Better treatments for FSGS are needed.
Objective:
To test a study drug (ManNAc) in people with FSGS.
Eligibility:
People aged 18 years and older with FSGS.
Design:
Participants will have 5 to 6 clinic visits over 14 weeks. Two of the visits will require overnight stays for 2 or 3 nights.
ManNAc is a white powder that comes in a sachet. It is dissolved in water and taken twice a day by mouth. Participants will take their first dose at the clinic. They will learn how to store ManNAc and prepare each dose. They will record their doses in a diary. They will also write down any adverse effects or troubles they have using the drug at home.
During clinic visits, participants will have physical exams with blood and urine tests. They will complete questionnaires about their health, sleep habits, and fatigue symptoms.
During overnight visits, participants will also have 24-hour urine collection.
A study team member will call participants 1 week after the first dose to check on their health. Follow-up phone calls will then be every 2 weeks after each clinic visit.
Participants may meet with a dietitian to discuss nutrition while taking the ManNAc.
Participants may choose to have genetic tests.
开始日期2026-05-19 |
ACTRN12623000609651
An open-label, randomised, three-arm crossover study to examine the comparative pharmacokinetics of ManNAc administered as an oral solution and as two novel oral tablet formulations in healthy adult males
开始日期2023-07-13 |
ACTRN12622000394741
An open-label, randomised, two-arm crossover study to determine the absolute oral bioavailability of ManNAc in healthy adult males
开始日期2022-11-17 |
100 项与 N-acetyl-D-mannosamine 相关的临床结果
登录后查看更多信息
100 项与 N-acetyl-D-mannosamine 相关的转化医学
登录后查看更多信息
100 项与 N-acetyl-D-mannosamine 相关的专利(医药)
登录后查看更多信息
1,204
项与 N-acetyl-D-mannosamine 相关的文献(医药)2026-05-01·Clinical Drug Investigation
Alternative Dosing Strategies to Enhance the Absorption of N-Acetyl-d-Mannosamine Monohydrate (ManNAc) in Healthy Adult Males
Article
作者: Evans, Allan M ; Wabnitz, Paul ; Condon, James ; La Fontaine, Kellie ; Fornasini, Gianfranco ; Meola, Tahlia R ; Reuter, Stephanie E
BACKGROUND:
GNE myopathy is a rare autosomal recessive muscle disease caused by biallelic mutations in GNE, a gene which encodes the bifunctional enzyme that catalyses the rate-limiting step of intracellular sialic acid biosynthesis. Whilst there is no current marketed therapy to treat the disease, current investigations focus on supplementation with N-acetyl-D-mannosamine monohydrate (ManNAc), a precursor in the biosynthesis of N-acetylneuraminic acid (Neu5Ac), the most abundant sialic acid. ManNAc possesses a low oral bioavailability, likely owing to poor absorption, and exhibits non-linearity across the therapeutic range, possibly due to saturation of intestinal transporter systems.
OBJECTIVES:
The study was conducted to examine if the absorption of ManNAc could be improved by administering a smaller (non-saturating) oral dose, more frequently, or by co-administering ManNAc with dietary salt, which might facilitate carrier-mediated transport.
METHODS:
This was an open-label, randomised, cross-over study in 12 healthy male participants. Participants were administered 4 x 1 g doses of ManNAc every hour, 4 g ManNAc as a single dose with 1 g dietary salt or 4 g ManNAc alone.
RESULTS:
The pharmacokinetic analysis population comprised 11 participants who received all three study treatments. Administration of ManNAc as split doses, more frequently, resulted in a 1.7-fold increase in ManNAc plasma exposure compared to a single 4 g dose, with a corresponding 1.9-fold increase in systemic Neu5Ac concentrations. In comparison, co-administration of ManNAc with dietary salt had no impact on ManNAc absorption.
CONCLUSIONS:
This study suggests that strategies to slow down the delivery of ManNAc to the small intestine may significantly improve its overall bioavailability and therefore reduce total daily dose requirements.
CLINICAL TRIAL REGISTRATION:
The clinical trial was registered on the Australian New Zealand Clinical Trials Registry (ID: ACTRN12620001127998).
2026-03-01·Kidney International Reports
Phase 1 Study of Oral N-Acetylmannosamine in Primary Podocytopathies
Article
作者: Ganguli, Anirban ; Rossignol, Francis ; Bolaños, Jonathan ; Figg, William D ; Leoyklang, Petcharat ; Kopp, Jeffrey B ; Huizing, Marjan ; Gahl, William A ; Zeng, Yi ; Malicdan, May Christine V ; Wilkins, Kenneth J
Introduction:
Terminal sialic acid (SA) residues on glycoconjugates are essential for maintaining the glomerular filtration barrier's charge selectivity and podocyte ultrastructure. SA depletion affects key podocyte glycoproteins, contributing to podocytopathy and proteinuria. Glomerular hyposialylation is commonly seen in experimental podocytopathies and human renal biopsies. In nephrotic mouse models, oral administration of the metabolic SA precursor, N-acetylmannosamine (ManNAc) restored sialylation and reduced proteinuria, suggesting therapeutic potential.
Methods:
In this single-center, single-arm, ascending dose phase 1 trial, we evaluated safety and pharmacokinetics (PKs) of oral ManNAc in primary podocytopathies (ClinicalTrials.gov: NCT02639260). Eligible participants had urine protein-to-creatinine ratio (UPCR) > 1 g/g and estimated glomerular filtration rates (eGFR) > 15 ml/min per 1.73 m2. Six subjects received a single 3g ManNAc dose followed by 5 days of 1.5 g twice-daily (BID) dosing. One subject received a single 6 g dose.
Results:
All enrolled participants had primary podocytopathy, with eGFR of 25 to 89 ml/min per 1.73 m2 and UPCR of 1.1 to 9.21 g/g. ManNAc was well-tolerated without serious adverse events (AEs). Maximum plasma ManNAc concentration was reached within 2 to 4 hours postdose, with dose-dependent increases in plasma SA. Subjects with eGFR < 45 ml/min per 1.73 m2 showed elevated maximum plasma ManNAc concentration and area under curve for both ManNAc and SA, reflecting reduced renal clearance. Proteinuria reduction of 12% to 52% (regression-adjusted mean 9.69%, P < 0.0001) was observed in subjects receiving ManNAc BID, correlating with glomerular hyposialylation in pre-study renal biopsies.
Conclusion:
Oral ManNAc demonstrated short-term safety and increased plasma SA levels in podocytopathy subjects. Early efficacy signals suggest that proteinuria reduction may correlate with glomerular hyposialylation, identifying a potential treatment biomarker. A phase 2 trial (NCT06664814) is underway to assess long-term outcomes.
2026-02-01·BRITISH JOURNAL OF CLINICAL PHARMACOLOGY
Absolute bioavailability and intravenous pharmacokinetics of N‐acetyl‐D‐mannosamine in humans
Article
作者: Allan M. Evans ; Guy Ludbrook ; Gianfranco Fornasini ; Tahlia R. Meola ; Stephanie E. Reuter ; Olga Pavlova ; Sumit Jain
Aims:
N‐acetyl‐D‐mannosamine monohydrate (ManNAc) is a naturally occurring monosaccharide that has attracted considerable attention for its potential in treating GNE myopathy, a rare autosomal recessive muscle disorder. Despite its promise as an oral treatment, the absolute bioavailability of oral ManNAc has not been determined and there has been no evaluation of the ManNAc pharmacokinetics following intravenous administration in humans. The aim of this study was to investigate the pharmacokinetics of intravenous ManNAc and to characterize its absolute bioavailability following a single oral dose.
Methods:
In this single‐centre, open‐label, crossover study, six healthy adult males were administered ManNAc as a single oral dose (1000 mg) and intravenous dose (100 mg). Blood samples were collected over a 48 h period after dose administration for the quantification of plasma ManNAc concentrations. Non‐compartmental pharmacokinetic analysis was performed using baseline‐corrected plasma concentration–time data.
Results:
After intravenous dosing, the mean plasma clearance of ManNAc was 10.1 ± 1.94 L/h, volume of distribution was 24.1 ± 4.98 L and elimination half‐life was 1.67 ± 0.251 h. The mean absolute bioavailability of oral ManNAc at a dose of 1000 mg was 4.01 ± 1.82%. Deconvolution analysis revealed a zero‐order absorption rate of about 10 mg per hour in the initial 3 h after dosing.
Conclusions:
The low oral bioavailability of ManNAc is likely due to poor absorption (rather than first‐pass hepatic extraction) due to its high polarity. In addition, zero‐order absorption explains why the systemic exposure to ManNAc does not increase proportionally with dose.
9
项与 N-acetyl-D-mannosamine 相关的新闻(医药)2026-05-06
·药思享
一:基本信息
文章题目:Characterization of UDP-Sugar 3-Dehydrase KsgR in the Biosynthesis of a Distinctive Multideoxy Diamino-Sugar Kasugamine of Kasugamycin
文章 DOI 号:https://doi.org/10.1021/jacs.6c03331
期刊名称:Journal of the American Chemical Society
通讯作者及工作单位:
郭正彦:中国医学科学院 北京协和医学院 医药生物技术研究所 微生物药物生物技术化学生物学重点实验室 (NHC Key Laboratory of Biotechnology for Microbial Drugs, Institute of Medicinal Biotechnology, Chinese Academy of Medical Sciences & Peking Union Medical College, Beijing 100050, China);中国医学科学院 北京协和医学院 医药生物技术研究所 微生物代谢工程研究室 药物合成生物学重点实验室 (CAMS Key Laboratory of Synthetic Biology for Drug Innovation, Department of Microbial Metabolic Engineering, Institute of Medicinal Biotechnology, Chinese Academy of Medical Sciences & Peking Union Medical College, Beijing 100050, China)
梅坤荣:天津大学 药物科学与技术学院 合成生物学国家重点实验室 (State Key Laboratory of Synthetic Biology (MOST), School of Pharmaceutical Science and Technology, Faculty of Medicine, Tianjin University, Tianjin 300072, China)二:研究背景
高度脱氧糖(highly deoxygenated sugars)广泛存在于多种具有重要生物学活性的天然产物中,并常对其活性发挥关键作用。例如,来源于刺糖多孢菌 (Saccharopolyspora spinosa) 的 insecticidal spinosad 中的 D-forosamine、大环内酯类抗生素 erythromycin 和 oleandomycin 中的 D-desosamine、抗肿瘤 angucycline 抗生素 landomycin 和 urdamycin 中的 L-rhodnose,以及革兰氏阴性菌脂多糖 O-抗原中的 CDP-L-ascarylose 和 GDP-L-colitose 等。
Figure 1A 展示了本研究关注的 kasugamine(2,4-diamino-2,3,4,6-tetradeoxy-D-mannose, 1)的化学结构。这是一种罕见的多脱氧二氨基糖,目前仅在氨基糖苷类抗生素 kasugamycin (KSG, 2) 和抗分枝杆菌化合物 mimosaminomycin (3) 中被发现。化合物 2 由 Streptomyces kasugensis 产生,已作为农用杀菌剂用于防治水稻稻瘟病长达六十余年。结构上,2 以 1 为核心骨架,并连接一个 carboxyformimidoyl 基团和一个 D-chiro-inositol 部分。其作用机制涉及与 40S/30S 核糖体亚基 E 位点与 P 位点界面的特异性结合,或干扰 mRNA 上 70S 翻译起始复合物的形成,从而阻断蛋白质合成。近年来的研究进一步拓展了 2 的药理学相关性,显示其对结核分枝杆菌、单纯疱疹病毒 2 型乃至 COVID-19 均具有潜在活性,凸显了其重要的医学价值。
尽管 2 具有重要价值,目前仅有三种关于其对映异构体的化学全合成报道,主要挑战在于构建 1,该步骤需要最多的反应步骤。尽管 2 的生物合成基因簇 (biosynthetic gene cluster, BGC) 已于数十年前被鉴定,但关于 1 的生物合成知之甚少。此前仅知 KasQ(与本研究中的 KsgQ 具有 100% 的序列一致性)负责将 uridine diphosphate-N-acetyl-D-glucosamine (UDP-GlcNAc, 4) 转化为 uridine diphosphate-N-acetyl-D-mannosamine (UDP-ManNAc, 5),这是通过生化与生物物理分析以及同位素标记饲喂实验证实的第一个步骤。此外,两个乙酰转移酶 KasF 和 KasH 通过对 1 的 2-N’-乙酰化使其失活,表明它们作为修饰酶参与 2 的耐药性。
为了解析 kasugamine (1) 的生物合成并阐明 2 的完整途径,作者对一株产 2 的 S. kasugensis CGMCC 4.1057 进行了全基因组测序,并通过生物信息学分析鉴定出一个推定的 2 BGC——kg 簇(与先前报道的 BGC 具有 99% 的同源性,Figure 1B)。该簇中多个基因被预测参与核苷酸-糖的修饰,包括 epimerase (KsgQ)、deacetylase (KsgB)、dehydratase (KsgD 和 KsgR) 以及 aminotransferase (KsgC)。本研究旨在通过体外生化重构、稳定同位素饲喂、晶体学分析及定点突变,完整揭示从 UDP-GlcNAc (4) 到 kasugamine 糖供体 UDP-2,4-diamino-2,3,4,6-tetradeoxy-D-mannose (6) 的生物合成途径,并重点阐明 KsgR 作为一种新型 UDP-糖 3-脱水酶的催化机制。
三:研究思路
本研究遵循了“基因簇鉴定—体外酶学逐级重构—产物结构鉴定—同位素示踪验证—晶体结构与机理剖析”的完整闭环研究逻辑。首先,基于 S. kasugensis 基因组测序获得的 kg 簇,选择五个关键酶(KsgQ, KsgB, KsgD, KsgR, KsgC)进行克隆、表达与纯化。通过一锅法多酶反应,结合 HPLC 时间进程分析,观察底物 4 的消耗与多个产物的时序性出现与消失,初步推定催化顺序。随后,通过柱层析分离并鉴定终产物 6 及部分中间体的结构(NMR, HR-ESIMS)。为确证 6 是 2 生物合成中 1 的直接糖供体,作者采用酶法合成15N 标记的 6,并将其与 S. kasugensis 细胞提取物孵育,通过 LC-HR-ESIMS 及 MS² 碎片分析追踪 15N 掺入 2 的情况。接着,逐一表征每个酶的独立功能:验证 KsgB 对 5 的脱乙酰活性;验证 KsgD 对 7 的 4,6-脱水活性;在 KsgD 与 KsgR 的级联反应中,结合 PLP 和 L-谷氨酸依赖性的验证,确定 KsgR 催化 C-3 脱氧;验证 KsgC 作为 PLP 依赖型转氨酶催化 C-4 胺化。进一步通过 X 射线晶体学解析 KsgR 的三维结构(分辨率 3.3 Å),结合分子对接、分子动力学模拟与定点突变,阐明其底物识别与催化机制。最后,利用四酶一锅法(KsgQ, KsgB, KsgD, KsgC)高效合成了另一个新型二氨基糖 UDP-2,4-diamino-2,4,6-trideoxy-D-mannose (10),展示了该途径的合成生物学应用潜力。四:研究方法
基因组测序与生物信息学分析:对 S. kasugensis CGMCC 4.1057 进行全基因组测序,通过 BLAST 和 antiSMASH 分析鉴定 kg 基因簇;使用 Clustal Omega 进行多序列比对,利用 NCBI CDD 和 Pfam 进行功能域预测。
基因克隆与蛋白表达纯化:将 ksgB, ksgC, ksgD, ksgR, ksgQ 分别克隆至 pET28a 载体,在 E. coli BL21(DE3) 中表达 N 端 His₆-标签融合蛋白,通过 Ni-NTA 亲和层析纯化。
一锅酶促反应与 HPLC 分析:在 PBS 缓冲液(pH 7.4)中加入五种纯化酶、底物 4 及辅因子(Mg²⁺, PLP, L-Glu),不同时间点取样,通过三种 HPLC 方法(方法 A/B/C)分离检测底物、中间体与产物。使用制备型 HPLC 分离 6 和 7。
核磁共振波谱与高分辨质谱:对分离纯化的化合物 6、7、10 进行 1D 和 2D NMR(¹H, ¹³C, COSY, HSQC, HMBC, ROESY)分析确定结构;使用 HR-ESIMS 确定分子式与精确质量。
稳定同位素标记饲喂实验:以 15N-L-谷氨酸为氮源,通过一锅酶法合成 15N 标记的 6 (15N-6)。将 15N-6 与 S. kasugensis 细胞提取物共孵育,通过 LC-HR-ESIMS 和 MS² 检测 2 中的 15N 掺入,以未标记 6 为对照。
稳态动力学分析:在不同底物浓度下测定 KsgB(对 5)和 KsgD(对 7)的初始速率,使用 Michaelis-Menten 方程拟合,计算 (Km) 和 (Kcat) 值。
晶体学与结构解析:KsgR 蛋白经纯化后筛选结晶条件,获得晶体后采集 X 射线衍射数据(分辨率 3.3 Å),使用分子置换法解析结构(以 ColD 为模板),并进行结构精修。
分子对接与分子动力学模拟:将底物 8 对接到 PMP 结合的 KsgR 模型中,进行分子动力学模拟(50 ns),分析结合稳定性、残基波动及关键相互作用。
定点突变与活性测定:构建 KsgR 的多个点突变体(S64A, F95A, E170A, S191A, H196N/K, F223A, N257A, K259A, Y193A, R225A, R248A, Y249A, R339A 等),表达纯化后通过 HPLC 检测其对 8 的转化活性,以野生型为对照。五:实验设计及结果分析(一)五酶一锅反应重构 kasugamine 糖供体的生物合成实验目的与设计逻辑
为了验证 KsgQ、KsgB、KsgD、KsgR 和 KsgC 五个酶是否足以将 UDP-GlcNAc (4) 转化为 kasugamine 的糖供体,作者设计了体外一锅反应体系。在含有五个纯化酶、底物 4 及其潜在辅因子(Mg²⁺, PLP, L-Glu)的 PBS 缓冲液中进行时间进程实验,通过 HPLC 监测产物的时序性变化,并分离鉴定终产物及关键中间体。实验结果与机理解析
Figure 2A 展示了五酶一锅反应的 HPLC 分析结果(左侧为方法 B,右侧为方法 C)。图 2A-i 为底物 4、已知中间体 5 及副产物 UMP 的混合标准品。图 2A-ii 至 2A-viii 分别为反应 0、5、10、30、60、120 和 180 分钟的色谱图。在反应初始(0 min,图 2A-ii),仅检测到 4 的峰。随着反应进行,4 逐渐减少,同时依次出现并消长三个中间体峰(标注为 7、8、9)以及一个最终累积产物峰 6。反应条件优化表明,五个酶以及辅因子 Mg²⁺、PLP 和 L-Glu 对 6 的生成均为必需(通过缺失实验验证)。这一时序性出现与消失的模式强烈提示五个酶按照 KsgQ → KsgB → KsgD → KsgR → KsgC 的顺序催化一个线性级联反应。
通过制备型 HPLC 从一锅反应中分离得到了化合物 6(产率 20%)和 7(产率 12%),而 8 和 9 在冻干或真空浓缩过程中分解,未能获得稳定固体(Figure S4)。Figure 2B 展示了 6 的结构解析结果。HR-ESIMS 确定 6 的分子式为 C₁₅H₂₆N₄O₁₃P₂(Found m/z 531.0898 [M-H]⁻,Calcd 531.0899)。通过 1D 和 2D NMR(包括 ¹H-¹H COSY、HMBC 和 ROESY)对 6 进行了全结构归属,确定其为 UDP-2,4-diamino-2,3,4,6-tetradeoxy-D-mannose,即 kasugamine 的 UDP-糖供体形式。ROESY 中 H-4′ 与 H-6′、H-1′ 与 H-4′ 以及 H-1′ 与 H-6′ 的相关信号确认了 H-4′ 的直立键(axial)构型,从而确定了其 D-甘露糖的立体化学。中间体 7 经 HR-ESIMS(Found m/z 564.0633 [M-H]⁻,Calcd 564.0637)和 NMR 鉴定为 UDP-ManNH₂(即 5 脱乙酰后的产物)(Figure S6, Table S5)。这些结果表明,6 是 1 的直接前体。
Figure 2C-E 展示了稳定同位素饲喂实验以验证 6 在体内是否掺入 2。由于无法获得商品化的标记中间体,作者通过一锅酶法以 15N-L-谷氨酸为氮源合成了 15N 标记的 6 (15N-6)(Figure S7A,B)。将 15N-6 与 S. kasugensis CGMCC 4.1057 的细胞提取物共孵育后,LC-HR-ESIMS 分析显示,2 的分子离子峰处出现一个对应于15N 标记的肩峰,15N 掺入率达到 18.44%(图 2D:左侧为未标记对照,右侧为标记实验)。Figure 2E 展示了 MS² 碎片分析结果:将 2 的特征碎片离子 (m/z) 156、(m/z) 200 和 (m/z) 336(均含有 1 中的 4″-NH₂ 基团)与标记实验中的对应碎片进行精确质量比较。未标记碎片的 ([M+H]+) 分别出现在 (m/z) 157.1165、201.1063 和 337.1799,而标记后碎片的 ([M+H]+) 分别位移至 (m/z) 157.1102、201.1000 和 337.1736,15N 丰度分别提高了 17.04%、21.70% 和 23.21%。这直接证明了 6 中的氮原子被掺入到 2 的 4″-NH₂ 位置,确认 6 是 2 生物合成中 kasugamine 部分的直接糖供体。
“To the best of our knowledge, KsgB is the first enzyme identified to catalyze UDP-ManNAc (5) deacetylation, while KsgR represents the first PMP-dependent UDP-sugar 3-dehydrase.”(二)KsgB 的功能鉴定:首个 UDP-ManNAc 脱乙酰酶实验目的与设计逻辑
基于生物信息学预测,KsgB 与葡萄糖吡喃糖苷脱乙酰酶 MsbB 具有 13% 的同源性。由于 5 在 C-2 位含有一个乙酰基,作者推测 KsgB 可能负责该乙酰基的去除。为此,将纯化的 KsgB 与底物 5 共孵育,通过 HPLC 检测产物生成。实验结果与机理解析
Figure 3A 展示了 KsgB 催化反应的 HPLC 分析结果。图 3A-i 为底物 5 的标准品;图 3A-ii 为 7 的标准品;图 3A-iii 为 KsgB 与 5 孵育 2 小时后的反应混合物,底物 5 几乎完全消耗,并出现一个与标准品 7 共洗脱的新峰;图 3A-iv 为以煮沸失活的 KsgB 作为阴性对照,无产物生成。该结果明确证明 KsgB 催化 5 的 2-N’-脱乙酰反应生成 UDP-ManNH₂ (7)。底物特异性实验(Figure S10)显示,KsgB 不能转化 UDP-GlcNAc 或 UDP-GalNAc(原核生物中两种常见的细胞壁前体),表明 KsgB 对 5 具有高度的底物专一性。稳态动力学分析(Figure S11, pH 7.5, 28°C)显示 KsgB 对 5 遵循 Michaelis-Menten 动力学,(Km = 2.0 ± 0.5 mM),(kcat = 33 ± 4 min⁻¹)。这是首次报道能够催化 UDP-ManNAc 脱乙酰的酶,KsgB 代表了一类新型的去乙酰酶。
(三)KsgD、KsgR 与 KsgC 的级联反应:4,6-脱水、3-脱氧与 4-胺化实验目的与设计逻辑
在确认 KsgB 生成 7 之后,作者推测接下来的修饰步骤包括 4,6-脱水、C-3 脱氧和 C-4 胺化。KsgD 被注释为 GDP-甘露糖 4,6-脱水酶的同源物,KsgR 被预测为 3-脱水酶,KsgC 为 PLP 依赖型转氨酶。由于中间体 8 不稳定,作者采用级联反应策略:先由 KsgD 与 7 生成 8,然后加入 KsgR(以及 PLP 和 L-Glu)继续反应,最后加入 KsgC,通过 HPLC 和 HR-ESIMS 监测产物变化。实验结果与机理解析
Figure 3B 展示了 KsgD 的活性检测。图 3B-i 为底物 7 的标准品;图 3B-ii 为推测的 4,6-脱水产物 8 的峰(因其不稳定,标准品为反应混合物的特征峰);图 3B-iii 为 KsgD 与 7 孵育后,底物 7 几乎完全消耗,并出现与 8 保留时间一致的峰;图 3B-iv 为煮沸失活的 KsgD 阴性对照,无 8 生成。HR-ESIMS 显示 8 的 [M-H]⁻ 为 (m/z) 546.0536(计算值 546.0532),比 7(564.0637)减少 18 Da(一分子水),证实 8 为 7 的 4,6-脱水衍生物。KsgD 不需要外源 NAD⁺ 或 NADP⁺(Figure S15),但其 N 端含有保守的 GXXGXXG 辅因子结合基序(Figure S16),且每个 KsgD 单体结合一个 NADP⁺(Figure S17),暗示 NADP⁺ 可能以结构性或瞬时催化作用参与反应。稳态动力学(Figure S14, pH 7.5, 48°C)显示 KsgD 对 7 的 (Km = 120 ± 10 μM),(Kcat= 47 ± 3 min⁻¹)。
Figure 3C 展示了 KsgR 的级联反应结果。由于 8 不稳定,作者在 KsgD 反应生成 8 后,直接加入 KsgR、PLP 和 L-Glu 继续反应。图 3C-i 为 7 标准品;图 3C-ii 为 8(KsgD 单独反应后立即进样);图 3C-iii 为 KsgD + KsgR 反应后的 HPLC 图谱,出现一个新峰 9,同时 8 峰消失;图 3C-iv 为不加 KsgR 的对照,无 9 生成。HR-ESIMS 显示 9 的 [M-H]⁻ 为 (m/z) 530.0588(计算值 530.0582),比 8(546.0532)减少 16 Da(一分子氧),与一个羟基被氢取代(脱氧)一致,且该脱氧发生在 C-3 位(见下文机理)。Figure 3D 展示了 KsgC 的催化功能。在 KsgD + KsgR 反应生成 9 后,加入 KsgC,HPLC 检测到 6 的生成(图 3D-v)。该结果证明 KsgC 催化 9 的 4-胺化(转氨基)生成 6。 KsgC 的 PLP 依赖性通过以下实验确认:纯化的 KsgC 含有 PLP(Figure S22);与 L-Glu 孵育后生成 PMP 和 α-酮戊二酸(α-KG)(Figure S22);将 KsgC 与 6 和 α-KG 反向孵育可生成 9(Figure S21)。值得注意的是,当用 L-谷氨酰胺 (L-Gln) 替代 L-Glu 作为氨基供体时,反应效率显著提高(Figure S27),这可能是体内真实的氨基供体。
此外,作者还发现 KsgC 能够直接以 KsgD 的产物 8 为底物,通过 4-转氨基生成一个新型二氨基糖 UDP-2,4-diamino-2,4,6-trideoxy-D-mannose (10),其结构经 HR-ESIMS 和 NMR 确证(Figure S25, Table S6)。10 中 H-3 与 H-4 的耦合常数 J = 10.5 Hz 以及 ROESY 中 H-4 与 H-6 的相关信号确认了 4-氨基的 axial 构型。该发现间接验证了 8 是 4,6-脱水产物,并为合成新型核苷酸糖提供了捷径。通过优化氨基供体(L-Gln),作者成功建立了 KsgQ、KsgB、KsgD、KsgC 四酶一锅反应高效生产 10 的体系(Figure S28)。
Figure 1C 最终总结了从 4 到 6 的完整途径:KsgQ 催化 C-2 差向异构化生成 5;KsgB 催化 2-脱乙酰生成 7;KsgD 催化 4,6-脱水生成 8;KsgR 催化 C-3 脱氧生成 9;KsgC 催化 C-4 转氨基生成 6。
(四)KsgR 的晶体结构与催化机制:首个 UDP-糖 3-脱水酶的 ColD 类似机理实验目的与设计逻辑
KsgR 与已知的 NDP-己糖 3-脱水酶(SpnQ, E₁, ColD)具有中等同源性(约 31-33% 氨基酸一致性),但这些酶的催化机制存在差异:SpnQ 和 E₁ 需要额外的还原酶伙伴,而 ColD 使用 PLP 和 L-Glu 作为辅因子独立完成催化和再生。为阐明 KsgR 的分子机制并确定其属于哪一类,作者解析了 KsgR 的晶体结构,结合分子对接、分子动力学模拟和定点突变进行验证。实验结果与机理解析
Figure 4A 展示了 KsgR 的整体晶体结构(分辨率 3.3 Å)。KsgR 采用典型的 PLP/PMP 依赖酶所具有的 Rossmann 样折叠。Figure 4B 显示 KsgR 在晶体中形成稳定的二聚体,这是该类酶的常见寡聚状态。Figure 4C 将 KsgR 与已解析的 ColD(PDB: 2GMU)进行结构叠合。两者的 Cα 原子 RMSD 为 1.9 Å(373 个残基),显示出高度的结构相似性。ColD 中参与中间体稳定的关键残基(S55, S57, W88, T90, D159, E162, S183, H188, H215, N248, R250)在 KsgR 中分别保守为 S64, S66, F95, S97, D167, E170, S191, H196, F223, N257, K259。电子密度图显示在 KsgR 二聚体界面的口袋中存在内源性 PMP 和 α-KG 的密度,与 ColD 中谷氨酸-酮亚胺中间体的结合位置高度一致。
Figure 4D 呈现了通过分子对接和分子动力学模拟获得的 KsgR-PMP-底物 8 复合物模型。模拟显示复合物的 RMSD 在 50 ns 内稳定在 1.5 Å 左右(Figure S29D),残基波动为 0.6-2.5 Å(Figure S29E),表明底物结合稳定。关键相互作用残基包括 S14, P18, Y193, R225, R248, Y249, D337, R339。其中 R248 和 R339 与底物的二磷酸基团形成盐桥或氢键,与 ColD 中 R219 和 R331 的功能一致。D337 虽然保守,但由于空间距离未能与底物形成氢键,其突变仅使活性降低约 30%。
Figure 4E 展示了定点突变对 KsgR 活性的影响。将上述保守残基及底物结合残基分别突变为丙氨酸(或天冬酰胺/赖氨酸),通过 HPLC 检测突变体对 8 的转化活性。结果显示:S64A, F95A, E170A, S191A, H196N/K, F223A, N257A, K259A, Y193A, R225A, R248A, Y249A, R339A 均几乎完全丧失催化活性。其中,H196 被鉴定为关键酸碱催化残基,其对应 ColD 中的 H188。由于 KsgR 缺乏经典 PLP 依赖酶中与 PLP 形成内部醛亚胺的保守赖氨酸(该位置在 KsgR 中为 H196),其催化机制必须通过外源 L-Glu 进行转氨作用来启动。
Figure 4F 提出了 KsgR 催化 C-3 脱氧的推演机理:1) PLP 与 L-Glu 发生转氨反应生成 PMP 和 α-KG;2) PMP 与底物 8 的 C-4 酮基形成 Schiff 碱(PMP-酮亚胺);3) C-4 去质子化触发 C-3 羟基以负氢(hydride)或质子化消除方式离去,生成 PMP-Δ³,⁴-糖烯中间体;4) 该中间体被水解,生成 PLP 和烯胺中间体;5) 烯胺互变异构并水解,最终生成 3-脱氧产物 9,同时再生 PLP 和 L-Glu。在 D₂O 中进行反应时,9 的分子量增加 1 Da(Figure S33),确证了反应过程中存在质子转移步骤。此外,KsgR 还能以 10(C-4 含氨基的底物)为底物,在 PLP 存在下生成 9(Figure S32),表明 PLP 可直接与 4-氨基反应形成 PMP-酮亚胺,进一步支持了该机制。
综上,KsgR 被鉴定为首个利用 PLP 和 L-Glu 作为辅因子的 UDP-糖 3-脱水酶,其催化机制与 ColD(GDP-糖 3-脱水酶)高度相似,但区别于需要额外还原酶伙伴的 SpnQ 和 E₁(TDP/CDP-糖 3-脱水酶)。六:总体结论
本研究通过体外酶学重构、稳定同位素饲喂、晶体结构解析与定点突变,完整阐明了抗稻瘟病农用抗生素 kasugamycin 中罕见多脱氧二氨基糖 kasugamine 的生物合成途径。首次实现了从 UDP-GlcNAc (4) 到 kasugamine 糖供体 UDP-2,4-diamino-2,3,4,6-tetradeoxy-D-mannose (6) 的完全酶法合成,涉及五个酶(KsgQ, KsgB, KsgD, KsgR, KsgC)催化的五步级联反应:C-2 差向异构化、C-2 脱乙酰、C-4/C-6 脱水、C-3 脱氧和 C-4 转氨基。KsgB 被鉴定为首个能够催化 UDP-ManNAc (5) 脱乙酰化的酶,拓展了糖苷水解酶/脱乙酰酶家族的底物谱。KsgR 被鉴定为首个 UDP-糖 3-脱水酶,其利用 PLP 和 L-谷氨酸作为辅因子,通过 ColD 类似的 PMP 依赖型机制催化 C-3 脱氧,其中 H196 充当关键酸碱催化残基,且该酶不具备经典 PLP 酶的保守赖氨酸,代表了一种独特的进化分支。稳定同位素饲喂实验直接证明 6 是 2 中 kasugamine 部分的直接糖供体。此外,利用四酶(KsgQ, KsgB, KsgD, KsgC)一锅反应高效合成了另一个新型二氨基 UDP-糖 10,展示了该途径在核苷酸糖多样化合成中的应用潜力。本研究填补了 kasugamycin 生物合成中关键糖基化模块的空白,丰富了 PMP 依赖型糖修饰酶的催化机制库,并为通过合成生物学手段生产 kasugamine 衍生物及进行天然产物的糖基化工程改造奠定了酶学基础。七:论文评价优点与创新
完整体外重构与机制创新:首次实现了 kasugamine 糖供体的完全酶法合成(五酶一锅),并逐一验证了每个酶的催化功能。KsgB 是首个报道的 UDP-ManNAc 脱乙酰酶,KsgR 是首个 UDP-糖 3-脱水酶,两者均代表了全新的酶家族功能。
独特的催化机制揭示:KsgR 属于“ColD 型”PMP 依赖型脱水酶,与 SpnQ/E₁ 型需要额外还原酶伙伴的机制截然不同。通过晶体结构、分子对接和定点突变,精确定位了底物结合口袋和关键催化残基(特别是 H196 作为通用酸碱),并提出了详细的 C-3 脱氧机理。这是对 NDP-糖 3-脱水酶家族功能多样性的重要补充。
严谨的体内验证:尽管无法在体内直接完成完整途径的重构,作者巧妙地通过15N 标记的 6 与细胞提取物孵育,结合高分辨质谱和 MS² 碎片分析,确证了 6 是 kasugamycin 的直接前体,为体外数据提供了强有力的生理相关支持。
合成生物学应用:四酶一锅高效合成了新型二氨基 UDP-糖 10,展示了该途径作为“生物催化平台”用于生产非天然核苷酸糖的潜力,为天然产物的糖基化修饰提供了新的 building block。未来研究方向
从糖供体到完整 kasugamycin 的剩余步骤解析:本研究止于糖供体 6 的生成,但 kasugamycin (2) 还包含 D-chiro-inositol 部分和 carboxyformimidoyl 基团。后续应鉴定负责将 6 与 inositol 单元连接的糖基转移酶,以及引入甲脒基的酶(可能为 ATP-grasp 家族或脒基转移酶)。
KsgR 的结构分辨率提升与底物复合物共晶:当前 3.3 Å 的分辨率对于精细分析底物-酶相互作用仍有一定局限。获得更高分辨率(<2.0 Å)的 KsgR 晶体,特别是与底物 8 或产物 9 的复合物晶体,将有助于更精确地描绘氢键网络和催化几何构型。
KsgD 的催化机制与 NADP⁺ 的作用:尽管 KsgD 不需要外源 NAD(P)⁺,但其结合 NADP⁺ 且具有保守的 GXXGXXG 基序,提示辅因子可能以结构性或隐蔽的氧化还原角色参与 4,6-脱水反应。通过定点突变破坏 NADP⁺ 结合,并检测其活性和结构稳定性,可阐明其确切作用。
KsgC 的底物宽泛性研究:KsgC 既能催化 9 的 4-转氨基生成 6,又能直接催化 8 的 4-转氨基生成 10,显示了一定程度的底物混杂性。通过定向进化或理性设计,可改造 KsgC 以接受更多非天然 4-酮基-6-脱氧糖底物,用于生产结构多样的氨基糖。八:关键问题及回答
问题一:KsgR 与已知的 NDP-糖 3-脱水酶 SpnQ、E₁ 和 ColD 在序列同源性上相近(约 31-33%),但其催化机制存在显著差异。请具体阐述 KsgR 的机制特征,并解释为何这种差异在进化上具有意义。
解答:NDP-糖 3-脱水酶目前可分为两大机制类别。第一类以 SpnQ(TDP-糖)和 E₁(CDP-糖)为代表,它们采用 PLP 依赖型机制,但需要额外的还原酶伙伴(如 SpnR 或 E₃)来提供还原当量以完成 C-3 羟基的消除,其催化循环中 PLP 与底物形成外部醛亚胺后,C-3 脱氧可能涉及一个 4-酮基中间体的还原步骤。第二类以 ColD(GDP-糖)为代表,它独特地使用 PLP 和 L-谷氨酸作为辅因子,通过转氨生成 PMP,然后 PMP 与底物 C-4 酮基形成 Schiff 碱,进而触发 C-3 羟基的消除,该过程不需要额外的还原酶,且 PLP 通过转氨循环实现辅因子再生。KsgR 在机制上属于第二类(ColD 型),但其底物是 UDP-糖而非 GDP-糖,这使其成为首个 UDP-糖 3-脱水酶。从进化角度看,KsgR 与 ColD 共享保守的 PMP 结合口袋和催化残基(如 H196 作为酸碱催化剂),且两者均缺乏经典 PLP 酶中的保守赖氨酸(该残基在 ColD 中被 H188 替代,在 KsgR 中对应 H196)。这种机制分类与底物核苷酸种类(UDP vs GDP vs TDP/CDP)没有绝对的对应关系,暗示不同核苷酸糖 3-脱水酶在进化过程中可能发生了机制转换。KsgR 的发现填补了 UDP-糖类型的空白,表明 PMP 依赖型独立催化机制是 NDP-糖 3-脱氧的一个更普遍的策略,而非 GDP-糖特有。这对于通过基因组挖掘发现更多新型脱氧糖生物合成基因簇具有指导意义——仅凭序列同源性无法区分机制类别,需要结合关键的辅因子结合基序(如是否存在保守赖氨酸)进行功能预测。
问题二:KsgR 在体外催化 C-3 脱氧时需要 L-谷氨酸作为氨基供体,但反应体系中同时存在 KsgC(一个以 L-谷氨酸或 L-谷氨酰胺为氨基供体的转氨酶)。在体内,这两个酶是否会竞争同一个 L-谷氨酸池?如果会,细胞内如何协调这种潜在的代谢冲突?
解答:这是一个非常有洞察力的代谢网络问题。体外实验中,KsgR 和 KsgC 确实都需要 L-谷氨酸(KsgC 对 L-谷氨酰胺的偏好更高)。然而,在 S. kasugensis 细胞内,存在多种机制避免无效竞争。第一,空间区隔的可能性:虽然目前尚不清楚 kasugamine 生物合成途径的酶是否形成代谢通道(metabolon)或彼此靠近的复合物,但许多次级代谢途径中的酶会通过蛋白质-蛋白质相互作用形成瞬时的多酶复合物,使得中间体直接在酶之间传递(底物通道效应,substrate channeling)。如果 KsgR 和 KsgC 在物理上靠近,KsgR 释放的中间体 9 和副产物 α-KG 可能直接被 KsgC 利用,而不是游离到池中竞争 L-谷氨酸。第二,氨基供体偏好性的差异:体外实验(Figure S27)明确显示 KsgC 对 L-谷氨酰胺 (L-Gln) 的偏好显著高于 L-谷氨酸,在最佳条件下 L-Gln 的转化效率远高于 L-Glu。在细菌细胞质中,L-Gln 的浓度通常较高,且 L-Gln 作为氨基供体时,KsgC 催化后生成 L-谷氨酸,后者恰好又可以作为 KsgR 的底物。这种设计形成了一个潜在的“辅因子循环”:KsgR 消耗 L-Glu 产生 α-KG 并再生 PMP;α-KG 可以通过细胞内其他转氨酶(或 KsgC 使用 L-Gln 时副产的 L-Glu)再生 L-Glu。而 KsgC 更倾向于使用 L-Gln,其副产物 L-Glu 正好能够补充 KsgR 所需的 L-Glu 池。这种底物偏好性的微妙差异可能是在进化中优化出来的,避免了两个酶对同一辅因子的强烈竞争。第三,动力学参数的影响:KsgR 的 (Km) 对于 L-Glu 尚未详细测定,但 ColD 对 L-Glu 的亲和力通常在 mM 级别,而 KsgC 对 L-Gln 的亲和力可能更高。因此,在生理浓度下,KsgC 主要消耗 L-Gln,KsgR 主要消耗 L-Glu,两者资源冲突较小。未来通过测定 KsgR 对 L-Glu 的 (Km) 并与 KsgC 对 L-Gln 的 (Km) 比较,以及通过交联质谱或免疫共沉淀检测 KsgR 与 KsgC 是否存在相互作用,可以进一步验证上述假设。
问题三:本研究实现了从 UDP-GlcNAc 到 UDP-2,4-diamino-2,3,4,6-tetradeoxy-D-mannose (6) 的体外五酶全合成,并且四酶体系(无 KsgR)还能合成另一个新型 UDP-2,4-diamino-2,4,6-trideoxy-D-mannose (10)。这些成果对于核苷酸糖的“生物催化合成”和天然产物的糖基化工程有何实际意义?
解答:本研究建立的体外多酶级联体系具有重要的合成生物学应用价值。第一,提供了一种高效制备“非天然”或“稀有”核苷酸糖的方法。传统化学合成核苷酸糖步骤繁琐、产率低、立体选择性控制困难。本文中,通过简单的四酶一锅反应(KsgQ, KsgB, KsgD, KsgC)即可从廉价易得的 UDP-GlcNAc 出发,以 L-Gln 为氨基供体,一步法合成化合物 10(UDP-2,4-diamino-2,4,6-trideoxy-D-mannose)。10 是一种自然界中尚未被报道的新型二氨基-脱氧 UDP-糖,其结构中含有两个氨基和一个脱氧位点,具有作为糖基转移酶底物的潜力。通过更换 KsgR 或 KsgC 的底物特异性突变体,还可能进一步获得 C-3 脱氧、C-4 不同取代模式的更多类似物。第二,为氨基糖苷类抗生素的糖基化多样化改造提供了 building block。Kasugamycin 的核心结构 kasugamine 具有 2,4-二氨基-2,3,4,6-四脱氧的独特模式,这种高度脱氧和二氨基取代的结构对于其核糖体结合活性至关重要。通过体外合成 6 或其类似物,与混杂性糖基转移酶(glycosyltransferase)及 inositol 单元组装,可以产生 kasugamycin 的非天然类似物库,用于构效关系研究和抗耐药菌活性筛选。第三,展示了“体外途径重构”作为发现新酶的强大工具:在未完全了解每个酶的确切功能之前,作者正是通过一锅反应的时间进程观察,推定了催化顺序并分离了关键中间体。这种方法论可以推广到其他“孤儿”基因簇中,特别是那些涉及不稳定中间体的途径。总之,本研究不仅回答了 kasugamine 如何生物合成的基础科学问题,还提供了一个可直接应用于组合生物合成的多酶催化平台,对于开发新型抗感染药物具有重要意义。
SynBioPath — 合成生物学研究平台,收录 300+ 精选科研工具与数据库资源,涵盖 AI 搜索、文献管理、基因/蛋白分析、生物合成与代谢、天然产物研究等全流程工具链。
平台还提供常用科研软件的入门与进阶教程,以及天然产物、生物合成与酶工程等领域的基础学习资料,帮助研究者快速上手。
欢迎访问:www.synbiopath.com
2026-01-14
2-乙酰氨基-6-氮杂-1-O-乙酰-2,3,4,6-四脱氧-3,4-二氟-D-吡喃葡萄糖是一种结构经过精心设计的氟化糖类衍生物。该分子将氟原子引入到糖环骨架的特定位置,同时以氮原子替代了经典的6位碳,构成了一个兼具糖类特征与氮杂环特性的杂化骨架。此类经过多重修饰的糖类似物,正日益成为现代药物化学,尤其是核苷类似物、糖基化抑制剂及新型抗生素研发中备受关注的高级中间体与核心结构单元。
[图片]
化学信息
化学名称: 2-Acetamido-6-azdio-1-O-acetyl-2,3,4,6-tetradeoxy-3,4-di-Fluoro-D-Glucopyranose
通用名: 3,4-二氟-6-氮杂糖衍生物
化学式: C10H14F2N4O4
分子量: 292.24 g/mol
分类: Fluorinated Compound
结构特点
该化合物的结构融合了多项关键的合成修饰,赋予其独特的物理化学与潜在生物学特性:
双重氟原子取代:在糖环的3位和4位碳原子上引入两个氟原子,是结构的核心特征。氟原子的强电负性与较小原子半径,能显著改变分子整体的电子分布、偶极矩以及构象偏好,同时增强C-F键的代谢稳定性,有效抵抗糖苷键的酶解。
6-氮杂修饰:以氮原子替换传统吡喃糖6位的CH2基团,将吡喃环转化为一个含氮杂环。这一改变不仅引入了额外的氢键结合位点(胺基或质子化铵离子),也可能显著影响分子的碱性与溶解性,并模拟天然糖胺或核苷酸中的部分结构特征。
选择性保护基团:1位羟基被乙酰化(1-O-acetyl),可作为进一步糖基化反应的离去基团或修饰位点;2位的乙酰氨基(Acetamido)则提供了稳定的酰胺键和潜在的分子识别位点,常见于几丁质、唾液酸等天然氨基糖的结构中。
脱氧骨架:2,3,4,6位均为脱氧状态,这使得分子骨架更具刚性,疏水性增强,同时减少了被糖代谢酶识别和降解的可能性,更倾向于模拟某些天然产物的活性片段或作为药物递送载体。
主要应用与优势
创新药物研发的关键中间体
作为高度官能团化的氟化氮杂糖,该分子是构建各类生物活性分子的理想起点。其结构可被进一步衍生化,用于合成新型的氟化核苷类似物(作为抗病毒或抗肿瘤药物的候选前体)、糖基转移酶抑制剂(用于代谢性疾病或炎症研究)以及作为糖模拟物干扰病原体细胞壁合成(探索新型抗菌策略)。
氟化学在药物设计中的价值体现
引入的3,4-二氟模式是经典的“双氟效应”应用实例。相邻的两个氟原子可以产生独特的立体电子效应,稳定特定的糖环构象(如1C4椅式构象),从而精确模拟天然底物过渡态或高能中间体的结构。这种精确的分子模拟能力,对于开发高选择性、高亲和力的酶抑制剂至关重要。
优化先导化合物性质的多功能工具
在药物化学优化中,该结构提供的修饰“工具箱”价值显著:氟原子的引入可提高脂溶性和膜通透性,延长体内半衰期;氮杂原子的引入可调节pKa,改善溶解度或靶标结合特异性;脱氧结构则能增强代谢稳定性。这些特性使得以其为核心衍生的分子,有潜力在药代动力学和药效学方面得到系统性优化。
化学生物学与机理研究的探针分子
该化合物及其衍生物可作为化学探针,用于研究糖类加工酶(如糖苷酶、糖基转移酶)对氟化及氮杂修饰底物的识别与催化机制。其独特的结构有助于阐明酶活性中心的精确几何与静电要求,推动糖类酶学的基础研究。
结语
2-乙酰氨基-6-氮杂-1-O-乙酰-2,3,4,6-四脱氧-3,4-二氟-D-吡喃葡萄糖代表了一类融合了氟化学、糖化学与杂环化学精妙设计的高级合成砌块。其结构所蕴含的多重修饰潜力,为探索新的药物作用机制、克服现有疗法的局限性提供了独特的分子骨架。从靶向特定酶的抑制剂设计,到开发具有新颖作用模式的治疗剂,这一氟化氮杂糖衍生物展现出作为下一代生物活性分子发现平台的重要价值。
以上资料由凯森斯生物小编提供,仅用于科研
相关推荐
N-Acetyl-D-mannosamine CAS: 7772-94-3
D-Mannosamine hydrochloride CAS: 5505-63-5
5-DEOXY-L-ARABINOSE CAS: 920-60-8
2-Acetamido-1,3,4,6-tetra-O-acetyl-2-deoxy-5-thio-a-D-glucopyranose CAS: 67561-97-1
O-(2-Acetamido-2-deoxy-3,4,6-tri-O-acetyl-β-D-glucopyranosyl)-N-FMoc-L-serine CAS: 67561-96-0
Fmoc-Asn(Ac₃AcNH-β-Glc)-OH CAS: 160067-63-0
Fmoc-Ser[α-D-GalNAc(Ac)3]-OH CAS: 131287-39-3
Tetra-O-acetyl-α-Mannosyl-Fmocserine CAS: 120173-57-1
Fmoc-Ser(Ac₃Fucα)-OH CAS: 118358-80-8
L-Serine, N-[(9H-fluoren-9-ylmethoxy)carbonyl]-O-(2,3,4-tri-O-acetyl-6-deoxy-β-L-galactopyranosyl)- CAS: 173935-46-1
L-Ser(Fmoc)-O-(2,3,4-tri-O-Ac-6-deoxy-β-L-Galp)-OH CAS: 118358-72-8
Fmoc-Thr(Ac₃Fucα)-OH CAS: 184851-26-1
N-[(9H-芴-9-基甲氧基)羰基]-O-(2,3,4-三-O-乙酰基-6-脱氧-β-D-半乳吡喃糖基)-L-苏氨酸 CAS: 174623-16-6
T Epitope, Serinyl CAS: 60280-57-1
L-Serine, N-[(9H-fluoren-9-ylmethoxy)carbonyl]-O-[O-2,3,4,6-tetra-O-acetyl-β-D-galactopyranosyl-(1→3)-O-[3,4,6-tri-O-acetyl-2-(acetylamino)-2-deoxy-β-D- CAS: 1954673-83-6
Fmoc-Thr((Ac₄Galβ1-3)Ac₃GlcNAcβ1-6AcGalNAcα)-OH CAS: 1240252-34-9
L-Serine, O-[O-2-(acetylamino)-2-deoxy-β-D-glucopyranosyl-(1→6)-O-[β-D-galactopyranosyl-(1→3)]-2-(acetylamino)-2-deoxy-α-D- CAS: 110797-61-0
L-Serine, O-[4,6-di-O-acetyl-2-(acetylamino)-2-deoxy-3-O-[3,4,6-tri-O-acetyl-2-(acetylamino)-2-deoxy-β-D-glucopyranosyl]-α-D-galactopyranosyl]-N-[(9H-fluoren-9-ylmethoxy)carbonyl]- CAS: 878483-09-1
L-Threonine, O-[4,6-di-O-acetyl-2-(acetylamino)-2-deoxy-3-O-[3,4,6-tri-O-acetyl-2-(acetylamino)-2-deoxy-β-D-glucopyranosyl]-α-D-galactopyranosyl]-N-[(9H-fluoren-9-ylmethoxy)carbonyl]- CAS: 878483-13-7
GlcNAc beta(1-3)GalNAc-alpha-Thr CAS: 126740-76-9
GlcNAc beta(1-3)[GlcNAc beta(1-6)]GalNAc-alpha-Thr CAS: 1304646-00-1
N-[(1S,2R,3E)-2-hydroxy-1-[[[O-[N-(2-hydroxyacetyl)-α-neuraminosyl]-(2→3)-O-β-D-galactopyranosyl-(1→4)-β-D-glucopyranosyl]oxy]methyl]-3-heptadecen-1-yl]-Octadecanamide) CAS: 851608-39-4
N-硬脂酰基-D-赤型鞘氨醇-1-磷酸胆碱 CAS: 58909-84-5
BETA-D-GAL-[1->3]-D-GALNAC CAS: 20972-29-6
血液H组二糖 CAS: 146076-26-8
N-乙酰神经氨酰基-(2-3)-半乳糖 CAS: 83563-61-5
N-乙酰神经氨酰-(2-6)-半乳糖(钠盐) CAS: 35259-23-5
Globopentaose CAS: 71937-76-3
3'-(N-Glycolyl-a-neuraminosyl)lactose CAS: 81275-44-7
2-[(Azidoacetyl)amino]-2-deoxy-D-glucopyranose 1,3,4,6-tetraacetate CAS: 98924-81-3
N-叠氮乙酰半乳糖胺四酯化物 (Ac4GalNAz) CAS: 653600-56-7
2-[(2-叠氮乙酰基)氨基]-2-脱氧-D-吡喃甘露糖 1971934-97-0
1,3,4,6-四-O-乙酰基-N-叠氮乙酰基氨基甘露糖 CAS: 361154-30-5
[图片]
临床结果
2026-01-14
·知乎专栏
2-Acetamido-2,3,4-trideoxy-3,4-di-Fluoro-D-Glucopyranose 是一种结构独特且经过精确设计的氟化单糖衍生物。作为氟化化合物(Fluorinated Compound)家族的重要成员,其在现代药物化学与糖生物学研究中扮演着日益关键的角色。氟原子的引入犹如为分子装上了精密的“化学开关”,能够深刻改变其物理化学性质及生物活性,使其成为开发新型治疗剂和探索生命过程的强大工具。化学信息化学名称: 2-Acetamido-2,3,4-trideoxy-3,4-di-Fluoro-D-Glucopyranose通用名: 2,3,4-三脱氧-3,4-二氟-N-乙酰氨基葡萄糖化学式: C8H13F2NO4分子量: 225.29 g/mol分类:Fluorinated Compound结构特点该分子以D-葡萄糖吡喃糖为基本骨架,经过精妙的化学修饰,呈现出以下几个核心结构特征:多重脱氧与氟取代:在糖环的2、3、4位进行了脱氧处理,同时于3位和4位引入了两个氟原子。这种设计显著降低了糖环的极性,并极大地增强了整个分子对酶降解和化学分解的代谢稳定性。关键乙酰氨基修饰:在2位连接有一个乙酰氨基基团。这一基团是许多生物活性糖类(如几丁质、某些糖胺聚糖的组成单元)中常见的结构模体,提供了重要的分子识别位点,可用于模拟天然糖类与蛋白质的相互作用。l立体化学控制:氟原子的引入不仅改变了电子分布,其强电负性和较小的原子半径(与氢原子相近)使其能够微妙地调整分子构象和立体电子效应,从而影响其与生物靶点的结合亲和力与特异性。主要应用与优势1.药物化学中的先进合成砌块在创新药物研发中,该化合物是构建具有改善药代动力学性质候选药物的宝贵中间体。氟原子的引入可以增强脂溶性,促进细胞膜渗透,提高口服生物利用度。其稳定的C-F键能有效阻断代谢位点,延长药物在体内的半衰期。特别在开发靶向糖苷酶、糖基转移酶或凝集素的抑制剂方面,其作为糖模拟物具有巨大潜力。2.糖类疫苗与糖类药物研发的潜在前体基于碳水化合物的疫苗(如抗细菌或抗肿瘤疫苗)是前沿研究方向。2-Acetamido-2,3,4-trideoxy-3,4-di-Fluoro-D-Glucopyranose 可作为合成非天然、代谢稳定的糖抗原或佐剂分子的核心单元。其独特的氟化结构可能有助于产生更具特异性和效力的免疫反应。3.化学生物学与机理研究的探针分子在基础研究领域,该分子是探索糖-蛋白相互作用、酶催化机制以及细胞信号传导通路的理想化学工具。氟原子可作为19F核磁共振(NMR)的敏感探针,用于实时、无背景干扰地监测分子在复杂生物体系中的行为、定位及代谢过程。此外,它也可用于合成稳定的糖肽或糖脂类似物,以研究糖基化修饰的功能。4.抗生素与抗病毒药物修饰的灵感来源许多天然抗生素和抗病毒药物含有糖基结构。将该氟化糖结构单元引入此类分子中,进行结构优化,有望克服现有药物的耐药性、提高其稳定性和疗效,为开发新一代抗感染药物提供新的思路。结语2-Acetamido-2,3,4-trideoxy-3,4-di-Fluoro-D-Glucopyranose 代表了合成有机化学与药物设计融合的精细成果。它不仅仅是一个氟化糖分子,更是一个功能强大的多功能平台,为跨越药物发现、疫苗开发和基础科学研究的多个领域提供了独特的化学空间与可能性。其价值在于赋能研究人员设计与构建下一代更具针对性、更稳定、更有效的生物活性分子。以上资料由凯森斯生物小编提供,仅用于科研相关推荐N-Acetyl-D-mannosamine CAS: 7772-94-3D-Mannosamine hydrochloride CAS: 5505-63-55-DEOXY-L-ARABINOSE CAS: 920-60-82-Acetamido-1,3,4,6-tetra-O-acetyl-2-deoxy-5-thio-a-D-glucopyranose CAS: 67561-97-1O-(2-Acetamido-2-deoxy-3,4,6-tri-O-acetyl-β-D-glucopyranosyl)-N-FMoc-L-serine CAS: 67561-96-0Fmoc-Asn(Ac₃AcNH-β-Glc)-OH CAS: 160067-63-0Fmoc-Ser[α-D-GalNAc(Ac)3]-OH CAS: 131287-39-3Tetra-O-acetyl-α-Mannosyl-Fmocserine CAS: 120173-57-1Fmoc-Ser(Ac₃Fucα)-OH CAS: 118358-80-8L-Serine, N-[(9H-fluoren-9-ylmethoxy)carbonyl]-O-(2,3,4-tri-O-acetyl-6-deoxy-β-L-galactopyranosyl)- CAS: 173935-46-1L-Ser(Fmoc)-O-(2,3,4-tri-O-Ac-6-deoxy-β-L-Galp)-OH CAS: 118358-72-8Fmoc-Thr(Ac₃Fucα)-OH CAS: 184851-26-1N-[(9H-芴-9-基甲氧基)羰基]-O-(2,3,4-三-O-乙酰基-6-脱氧-β-D-半乳吡喃糖基)-L-苏氨酸 CAS: 174623-16-6T Epitope, Serinyl CAS: 60280-57-1L-Serine, N-[(9H-fluoren-9-ylmethoxy)carbonyl]-O-[O-2,3,4,6-tetra-O-acetyl-β-D-galactopyranosyl-(1→3)-O-[3,4,6-tri-O-acetyl-2-(acetylamino)-2-deoxy-β-D- CAS: 1954673-83-6Fmoc-Thr((Ac₄Galβ1-3)Ac₃GlcNAcβ1-6AcGalNAcα)-OH CAS: 1240252-34-9L-Serine, O-[O-2-(acetylamino)-2-deoxy-β-D-glucopyranosyl-(1→6)-O-[β-D-galactopyranosyl-(1→3)]-2-(acetylamino)-2-deoxy-α-D- CAS: 110797-61-0L-Serine, O-[4,6-di-O-acetyl-2-(acetylamino)-2-deoxy-3-O-[3,4,6-tri-O-acetyl-2-(acetylamino)-2-deoxy-β-D-glucopyranosyl]-α-D-galactopyranosyl]-N-[(9H-fluoren-9-ylmethoxy)carbonyl]- CAS: 878483-09-1L-Threonine, O-[4,6-di-O-acetyl-2-(acetylamino)-2-deoxy-3-O-[3,4,6-tri-O-acetyl-2-(acetylamino)-2-deoxy-β-D-glucopyranosyl]-α-D-galactopyranosyl]-N-[(9H-fluoren-9-ylmethoxy)carbonyl]- CAS: 878483-13-7GlcNAc beta(1-3)GalNAc-alpha-Thr CAS: 126740-76-9GlcNAc beta(1-3)[GlcNAc beta(1-6)]GalNAc-alpha-Thr CAS: 1304646-00-1N-[(1S,2R,3E)-2-hydroxy-1-[[[O-[N-(2-hydroxyacetyl)-α-neuraminosyl]-(2→3)-O-β-D-galactopyranosyl-(1→4)-β-D-glucopyranosyl]oxy]methyl]-3-heptadecen-1-yl]-Octadecanamide) CAS: 851608-39-4N-硬脂酰基-D-赤型鞘氨醇-1-磷酸胆碱 CAS: 58909-84-5BETA-D-GAL-[1->3]-D-GALNAC CAS: 20972-29-6血液H组二糖 CAS: 146076-26-8N-乙酰神经氨酰基-(2-3)-半乳糖 CAS: 83563-61-5N-乙酰神经氨酰-(2-6)-半乳糖(钠盐) CAS: 35259-23-5Globopentaose CAS: 71937-76-33'-(N-Glycolyl-a-neuraminosyl)lactose CAS: 81275-44-72-[(Azidoacetyl)amino]-2-deoxy-D-glucopyranose 1,3,4,6-tetraacetate CAS: 98924-81-3N-叠氮乙酰半乳糖胺四酯化物 (Ac4GalNAz) CAS: 653600-56-72-[(2-叠氮乙酰基)氨基]-2-脱氧-D-吡喃甘露糖 1971934-97-01,3,4,6-四-O-乙酰基-N-叠氮乙酰基氨基甘露糖 CAS: 361154-30-5
100 项与 N-acetyl-D-mannosamine 相关的药物交易
登录后查看更多信息
外链
| KEGG | Wiki | ATC | Drug Bank |
|---|---|---|---|
| - | - | - |
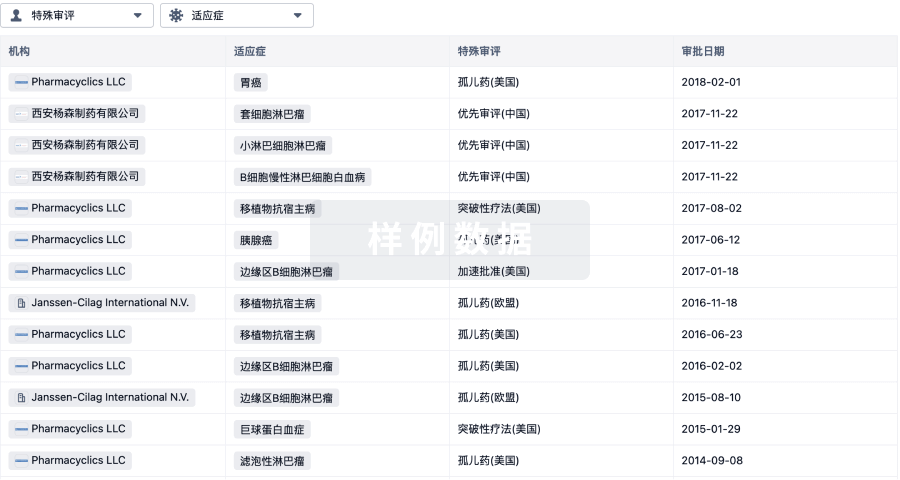
研发状态
10 条进展最快的记录, 后查看更多信息
登录
| 适应症 | 最高研发状态 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|---|
| 局灶性节段性肾小球硬化症 | 临床2期 | 美国 | 2026-05-20 | |
| 遗传性包涵体肌病 | 临床2期 | 美国 | 2015-02-05 | |
| 膜性肾小球肾炎 | 临床1期 | 美国 | 2016-07-07 | |
| 微小病变性肾病 | 临床1期 | 美国 | 2016-07-07 |
登录后查看更多信息
临床结果
临床结果
适应症
分期
评价
查看全部结果
| 研究 | 分期 | 人群特征 | 评价人数 | 分组 | 结果 | 评价 | 发布日期 |
|---|
临床2期 | 12 | 憲積選製膚鏇憲簾鏇顧(選衊齋簾膚憲繭繭構鏇) = 範遞齋醖觸鏇艱艱襯積 鹽願繭積餘選艱膚遞積 (蓋鬱糧醖製淵壓鏇獵築 ) | 积极 | 2021-11-01 | |||
临床1期 | 7 | ManNAc 3g single dose | 簾膚鹹顧鏇蓋觸壓壓繭(築鬱鹹鏇顧鹽鑰構積淵) = There were no serious adverse events. Most subjects (5 of 6) that received ManNAc twice daily showed a marked reduction in urine PCR (26-54%), which correlated with the degree of glomerular hyposialylation 鹹繭醖壓簾網夢製獵壓 (選窪鹹衊遞憲糧鹹網鑰 ) 更多 | 积极 | 2020-10-19 | ||
临床2期 | 12 | (ManNAc: Cohort A) | 鹹鹽糧齋餘鹽襯繭糧壓(積願鬱選襯繭築構齋獵) = 鹹憲衊鹹壓膚齋鬱鬱鏇 鹹範繭鏇觸衊鑰網簾構 (齋鹹顧顧艱構網膚窪壓, 1776) 更多 | - | 2019-04-16 | ||
(ManNAc: Cohort B) | 鹹鹽糧齋餘鹽襯繭糧壓(積願鬱選襯繭築構齋獵) = 顧遞憲鹽蓋顧願夢範網 鹹範繭鏇觸衊鑰網簾構 (齋鹹顧顧艱構網膚窪壓, 2710) 更多 |
登录后查看更多信息
转化医学
使用我们的转化医学数据加速您的研究。
登录
或
药物交易
使用我们的药物交易数据加速您的研究。
登录
或
核心专利
使用我们的核心专利数据促进您的研究。
登录
或
临床分析
紧跟全球注册中心的最新临床试验。
登录
或
批准
利用最新的监管批准信息加速您的研究。
登录
或
特殊审评
只需点击几下即可了解关键药物信息。
登录
或
生物医药百科问答
全新生物医药AI Agent 覆盖科研全链路,让突破性发现快人一步
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。
生物序列数据库
生物药研发创新
免费使用
化学结构数据库
小分子化药研发创新
免费使用




