预约演示
更新于:2026-05-31

Hunan Anbang Pharmaceuticals Co. Ltd.
更新于:2026-05-31
概览
关联
4
项与 湖南安邦制药股份有限公司 相关的临床试验ChiCTR2000033981
The randomized double-blind double-simulation and Non-inferior effect of positive control clinical trial study on the efficacy and safety of Yinhuang Qingfei Capsule in the treatment of acute exacerbation of chronic simple bronchitis
开始日期2018-10-16 |
申办/合作机构 |
CTR20132960
治疗更年期综合征(肾阴阳两虚证)有效性、安全性的随机、双盲、安慰剂对照、多中心的III期临床试验
评价本品治疗更年期综合征(肾阴阳两虚证)的有效性和安全性。
开始日期2012-05-28 |
申办/合作机构  湖南安邦制药股份有限公司 湖南安邦制药股份有限公司 [+1] |
CTR20202351
阿莫西林胶囊人体生物等效性研究
本试验旨在研究单次空腹和餐后口服湖南安邦制药有限公司研制、生产的阿莫西林胶囊(0.25 g)的药代动力学特征;以LTLファーマ株式会社生产的阿莫西林胶囊(Sawacillin®,250 mg)为参比制剂,比较两制剂中药动学参数Cmax、AUC0-t、AUC0-∞,评价两制剂的人体生物等效性。
开始日期- |
申办/合作机构 |
100 项与 湖南安邦制药股份有限公司 相关的临床结果
登录后查看更多信息
0 项与 湖南安邦制药股份有限公司 相关的专利(医药)
登录后查看更多信息
45
项与 湖南安邦制药股份有限公司 相关的新闻(医药)2026-05-21
·修禅悟道
涨跌停情况概况(20260521)
日期
涨停数
炸板数
跌停数2026051572484320260518101(+29)39(-9 )53(+10 )20260519122(+21)17(-22 )26(-27 )2026052069( -53)35(+18 )38(+12 )2026052135( -34)75(+40 )65(+27 )
连板天梯 (20260521)
连板数
股票数量
股票名称
近3月涨停数
涨停原因
7连板
1
威龙股份
8
实控人变更
4连板
1
诚邦股份
9
存储芯片
▲2连板
4
金利华电
3
并购重组
四环生物
4
摘帽
大众交通
2
智能交通+参股长存
龙星科技
3
炭黑+PVDF
首板
29
ST葫芦娃
4
ST股
锋龙股份
3
优必选入主
昂利康
7
创新药
亚世光电
5
智能驾驶
华升股份
11
机器人+算力租赁
豫能控股
10
电力+算力
京能电力
5
电力
直真科技
4
算力调度
北投科技
4
重组预期
近三日ST板块涨跌停情况概况(20260521)
日期
涨停数
炸板数
跌停数2026051932418202605208( -24)17(+13 )16(-2 )202605212( -6)9(-8 )40(+24 )
资金流入TOP10板块
概念板块
涨停/跌停数
流入金额/涨跌比
领涨股汽车-0.4%4/242.16亿56/101
曙光股份换:13.79%面板-0.71%4/038.1亿18/37
纬达光电换:14.39%人形机器人-0.78%2/134.63亿96/150
昊志机电换:25.47%华为汽车-1.13%1/021.59亿29/74
豪恩汽电换:31.58%北京国资-2.34%2/019.1亿11/38
京东方A换:2.85%汽车热管理-2.25%0/018.32亿15/42
儒竞科技换:13.54%大金融-0.44%0/016.24亿35/77
华安证券换:9.15%证券IT-0.59%0/015.82亿7/7
同花顺换:9.26%汽车零部件-1.29%7/412.93亿127/296
豪恩汽电换:31.58%生物质能-2.98%1/411.48亿5/34
豫能控股换:19.06%
涨幅TOP10板块
概念板块
涨停/跌停数
流入金额/涨跌比
领涨股减速器0.61%1/09.46亿25/22
昊志机电换:25.47%民航0.56%0/02.08亿6/4
春秋航空换:1.59%玻璃0.44%1/09.86亿10/16
彩虹股份换:5.38%血制品0.31%1/00.26亿5/6
派林生物换:4.02%
资金流出TOP10板块
概念板块
涨停/跌停数
流入金额/涨跌比
领涨股芯片产业链-4.49%5/9-568.12亿85/608
龙腾光电换:2.24%光通信-4.77%1/4-434.35亿30/196
京东方A换:2.85%5G产业链-4.15%1/5-392.74亿33/262
*ST元道换:50.83%华为产业链-3.34%8/4-373.5亿110/648
*ST元道换:50.83%国企改革-2.43%8/8-367.99亿164/1223
纬达光电换:14.39%半导体芯片-4.32%3/6-364.6亿38/294
龙腾光电换:2.24%算力工程-4.4%4/4-324.91亿32/366
*ST元道换:50.83%业绩超预期-3.3%1/0-285.49亿36/272
昭衍新药换:9.63%数据中心-4.54%4/2-284.47亿23/256
大众交通换:9.77%人工智能-3.31%2/5-220.12亿57/593
冠中生态换:11.36%
跌幅TOP10板块
概念板块
涨停/跌停数
流入金额/涨跌比
领涨股工业气体-6.5%0/0-19.39亿0/20
陕鼓动力换:0.57%CPO-6.24%0/0-183.25亿0/28
通富微电换:15.79%大基金系-5.57%0/0-93.5亿2/38
北方华创换:3.2%光刻胶-5.46%0/0-48.93亿3/49
七彩化学换:13.15%WIFI-5.34%0/1-26.48亿1/26
万隆光电换:11.85%半导体材料-5.22%0/1-139.79亿17/156
戈碧迦换:10.92%汽车芯片-5.18%1/1-102.66亿5/57
豪恩汽电换:31.58%存储器-5%1/0-134.53亿10/64
诚邦股份换:30.8%HBM-4.99%0/0-26.35亿1/20
博敏电子换:16.19%AI服务器-4.98%0/1-124.42亿5/73
红板科技换:48.79%
涨停股一览(共 35 只)
涨停TOP25因子
▼百日新高:12新能源汽车:9▼电子:8▼华为产业链:8浙江:8国企改革:8▼昨日大额成交:7汽车零部件:7▼消费电子:6机器人概念:6医药:6医药生物:6昨日涨停:6▼芯片产业链:5▼广东:5北京:5低价股:5智能驾驶:5光学光电子:5▼数据中心:4▼昨日高换手:4▼算力工程:4▼并购重组:4新型城镇化:4OLED:4
股票
现价
涨跌幅
涨停时间
昭衍新药sh60312742.77首板10.01%
14:54:15CRO+AI医疗:
1.公司专注于药物全生命周期的安全性评价和监测,建立了独具特色的药物非临床研究服务、临床试验及相关服务。 2.公司已将基于AI和行为组学的全自动行为学检测系统应用于多种CNS疾病模型如阿尔茨海默症、帕金森症和疼痛的评价中,支持了多个前沿药物如细胞治疗、基因治疗药物的非临床申报。
龙腾光电sh6880555.39首板20.04%
14:52:38MLED+半导体:
1.公司将Mini LED作为重要核心技术,成功推出最佳分区调光技术Mini LED车载显示屏、笔记本电脑屏及电竞显示屏等产品,同时公司加大对车载Mini LED背光技术不同架构的开发与研究,重点推进其在车载产品上的量产进程,并积极探索Mini LED在游戏、医疗等各类显示应用场景。 2.公司控股子公司彩优微电子主要产品为平板显示驱动IC,是TFT-LCD驱动IC出货量最大的极少数国内设计公司之一。
ST葫芦娃sh6051996.94首板4.99%
10:09:52ST股 :
公司地处海南海口,聚焦儿童药研发、生产、销售于一体的创新型医药企业。
*ST闻泰sh60074516.8首板5%
14:49:21ST股 :
5月8日,*ST闻泰(600745)发布异动公告,前期公司子公司安世半导体以及安世半导体控股收到荷兰经济事务与气候政策部下达的部长令(Order)和阿姆斯特丹上诉法院企业法庭的裁决。截至目前,虽然上述部长令(Order)被宣布暂停,但企业法庭相关裁决依旧处于生效状态,公司对安世的控制权仍暂处于受限状态。
广东明珠sh6003828.86首板10.06%
09:47:51不会触发ST:
广东明珠发布澄清公告,公司关注到有媒体发布涉及公司“困在业绩补偿里的广东明珠:实控人张坚力尚欠2亿,逾期或将处罚ST风险”等报道。截至目前,公司不存在触发ST风险的情形。公司实际控制人张坚力表示将尽快筹集资金偿还应付的剩余业绩补偿金。
锋龙股份sz00293160.04首板10%
11:25:09优必选入主:
锋龙股份公告称,本次股份协议转让已完成,公司控股股东变更为优必选,实际控制人变更为周剑。根据中国证券登记结算有限责任公司于2026年3月12日出具的《证券过户登记确认书》,本次协议转让事项过户登记手续已办理完毕,过户日期为2026年3月11日,过户股数为6552.99万股,占公司股份总数的29.99%,股份性质为无限售流通股。
昂利康sz00294045.65首板10%
09:49:57创新药:
公司目前正在进行的创新药研发项目为注射用ALK-N001,该药物是一种创新的肿瘤微环境激活型的小分子偶联药物,已于2025年2月收到国家药品监督管理局签发的境内生产药品注册临床试验《受理通知书》。
康辰药业sh60359039.22首板10.01%
13:07:08创新药:
公司是一家以创新药研发为核心、以临床价值为导向,集研发、生产和销售于一体的创新药企业。公司主要产品为“密盖息”和“苏灵”。
诚邦股份sh60331627.254连板10.01%
14:56:58存储芯片:
2024年9月19日公告,公司拟以不超过5800万元的现金方式增资取得东莞市芯存电子科技有限公司不低于51%的股权。本次交易正式完成后,公司预计将实现对芯存科技的财务并表。芯存科技是一家专业致力于存储模组产品的研发、生产和销售的高新技术企业。
威龙股份sh60377914.527连板10%
14:55:12实控人变更:
威龙股份公告称,公司控股股东星河息壤与爱特云翔、齐信数科签订股份转让协议,爱特云翔指定全资子公司齐信数科以每股7.45元受让星河息壤持有的15.10%股份,以抵顶爱特云翔对星河息壤享有的3.74亿元债权,爱特云翔、齐信数科无需向星河息壤支付转让价款。爱特云翔指定全资子公司齐信数科以每股转让价格7.45元受让斐尼克斯持有的8.02%股份,以抵顶爱特云翔对斐尼克斯享有的1.98亿元债权,爱特云翔、齐信数科无需向斐尼克斯支付转让价款。完成后,齐信数科持股23.12%,公司控股股东变更为齐信数科,实际控制人变更为淄博市财政局。
恒林股份sh60366129.57首板10.01%
14:33:20家具:
国内领先的健康坐具开发商和目前国内最大的办公椅制造商及出口商之一。
和泰机电sz00122553.76首板10.01%
09:52:39工程机械:
公司主要产品包括板链斗式提升机、胶带斗式提升机等多系列输送设备及其配件,可广泛应用于水泥建材、港口、钢铁、化工等多个行业,并以水泥建材行业为主。
金利华电sz30006944.062连板19.99%
09:25:00并购重组:
金利华电公告称,公司拟发行股份及支付现金购买西安中科西光航天科技集团有限公司82.50%的股权并募集配套资金,本次交易构成关联交易,预计构成重大资产重组。公司股票将于2026年5月20日开市起复牌。本次交易完成前,上市公司主要业务为玻璃绝缘子的研发、生产、销售及相关技术服务。本次交易完成后,上市公司将新增卫星制造及相关服务、卫星遥感信息服务板块降低公司对单一业务及电力设备市场周期性波动的依赖,增强公司整体抗风险能力和核心竞争力。
四环生物sz0005183.752连板9.97%
14:50:18摘帽:
*ST四环公告称,公司股票交易自2026年5月20日起撤销退市风险警示,证券简称由“*ST四环”变更为“四环生物”,证券代码不变,仍为“000518”,涨跌幅限制由5%变更为10%。
华微电子sh60036012.07首板10.03%
14:56:30摘帽+半导体:
1.*ST华微公告称,公司股票将于2026年5月19日停牌一天,自2026年5月20日起复牌并撤销退市风险警示及其他风险警示。撤销后,公司股票简称由“*ST华微”变更为“华微电子”,股票代码不变,日涨跌幅限制由5%变为10%。 2.公司是国内技术领先、产品种类最为齐全的功率半导体器件IDM公司,已建立从高端二极管、单双向可控硅、MOS系列产品到第六代IGBT的功率半导体器件产品体系。
大众交通sh6006115.572连板10.08%
09:39:51智能交通+参股长存:
1.公司的大众出行平台将乘客、司机、出租车公司以及交通运输管理部门各端联通,通过数据交互,平台可为管理部门提供城市的动态交通信息,如高峰时段、易造成拥堵的路段、市民出行数据等。 2.公司通过厦门辰途华恒一号创业投资基金合伙企业间接参股长江存储。
惠威科技sz00288825.74首板10%
13:06:51智能音箱:
公司是一家以电子设备制造为核心业务领域,主要从事各类音响设备、扬声器的研发、生产和销售一体化的高新技术企业。
亚世光电sz00295229.47首板10%
09:34:27智能驾驶:
公司应用于汽车显示的产品包括车载自动变光遮阳板、汽车电子后视镜、仪表盘、空调显示、操控杆显示等众多车载显示产品。
联创电子sz0020369.36首板9.99%
09:44:06智能驾驶:
公司车载镜头和影像模组已被应用于无人驾驶的相关市场,是国内外ADAS镜头主力供应商。
索菱股份sz0027665.14首板10.06%
09:58:12智能驾驶:
公司拥有车联网应用平台,主要整合了试乘试驾管理、4S客户增值管理、中小车队管理系统、分时租赁、ADAS、UBI车险系统、汽车金融风险管控系统、桩联网等多项核心技术功能。
浙江世宝sz00270319.92首板9.99%
14:37:21智能驾驶:
公司生产的智能转向可适用于智能驾驶汽车及无人驾驶汽车。
德赛西威sz002920106.12首板10%
14:54:24智能驾驶:
公司有智能驾驶舱、智能驾驶、车联网三大产品线,涵盖车载信息娱乐系统、驾驶信息显示系统、空调控制器、智能驾驶辅助、车联网等产品,形成全面完善的业务结构。
中马传动sh60376724.34首板9.99%
10:40:19机器人:
公司招股说明书显示,将以现有汽车变速器齿轮、汽车转向器齿轮、汽车油泵轴齿轮、汽车发动机齿轮、摩托车发动机齿轮、农机变速器齿轮为发展基础,大力开拓汽车自动变速器行星齿轮、工业机器人减速器齿轮等高精度齿轮产品领域。
安邦护卫sh60337348.65首板9.99%
14:28:43机器人:
温州安邦护卫联合温州理工学院科研团队打造了“智能安防中枢平台”,创新性地应用四足机器人技术,引入了安防巡逻机器人用于库房管理,进一步提升库房管理的智能化水平。
华升股份sh60015613.04首板10.04%
14:55:05机器人+算力租赁:
1.参股24%的湖南英捷高科技有限责任公司的MIM(金属粉末注射)可以用于消费电子和人行机器人。 2.2025年6月9日公告,公司正在筹划通过发行股份及支付现金的方式购买深圳易信科技股份有限公司100%的股权,易信科技已在粤港澳大湾区、成渝、京津冀等区域自建绿色智算中心,满足训练、推理、科学计算等高算力场景需求,其智算中心全生命周期解决方案已经累计服务客户超10000家。
曙光股份sh6003033.48首板10.13%
14:44:05汽车整车:
公司整车产品形成了新能源客车系列、传统能源及新能源N系列皮卡、A系列轻客,构建了自主研发的产品平台。
龙星科技sz0024427.372连板10%
14:39:36炭黑+PVDF:
公司主要业务为炭黑、白炭黑及煤焦油制品的生产和销售。公司主要产品包括PVDF。
京东方Asz0007254.69首板10.09%
09:25:00玻璃基板:
2026年5月20日公告,公司与康宁公司签署合作备忘录,双方将围绕玻璃基封装载板、可折叠玻璃、钙钛矿玻璃基板、光互连相关应用等重点领域开展合作。备忘录有效期三年,各领域合作内容需另行协商并签署正式协议。公司于2024年投资9.93亿元建设玻璃基封装载板试验线。目前已给部分国内客户送样,部分客户已通过概念认证,并进入技术测试阶段。
华映科技sz0005364.29首板10%
14:47:54玻璃基板:
子公司华佳彩主营薄膜晶体管、薄膜晶体管液晶显示器件、彩色滤光片玻璃基板、有机发光二极管(OLED)、3D 显示等新型平板显示器件与零部件等生产、研发与销售。
京能电力sh6005788.18首板9.95%
14:46:35电力:
公司主营业务以燃煤火力发电和供热为主,同时涉及综合能源服务、煤电联营等项目。公司主要经营地区在内蒙、山西、宁夏、河北、河南、湖北等地,主要向京津唐电网、蒙西电网、山西电网、豫北电网供电。
豫能控股sz00189616.37首板10.01%
14:59:15电力+算力:
1.公司是河南省内唯一省级资本控股的电力上市公司,从事的主要业务包括,火电项目的投资管理、能源销售、新能源项目投资建设等。 2.豫能控股早间公告,公司正在筹划参股投资公司控股股东河南投资集团下属控股企业先天算力(河南)科技有限公司,并联合河南投资集团以先天算力为收购主体,收购郑州合盈数据有限责任公司控股权相关事项。此次参股投资事项尚处筹划阶段,存在较大不确定性。
南 玻Asz0000124首板9.89%
09:54:15电子玻璃:
公司已拥有节能玻璃、电子玻璃及显示器件、太阳能光伏三条完整的产业链,“南玻”是国内节能玻璃领先品牌和太阳能光伏产品及显示器件著名品牌。
直真科技sz00300754.34首板10%
10:00:12算力调度:
公司大力推进算力网络相关产品的定义和解决方案的推广,23年上半年,完成了网控制器、算控制器为核心的算网大脑产品的预研和部分开发工作,进行了基于网络和算力感知技术的算力、运力可视化、意图驱动的多因素运力、算力调度的探索与实践。
派林生物sz00040311.55首板10%
14:34:12血液制品:
公司的主营业务为血液制品的研究、开发、生产和销售,主要产品为人血白蛋白、静注人免疫球蛋白(pH4)、人免疫球蛋白、乙型肝炎人免疫球蛋白、破伤风人免疫球蛋白、狂犬病人免疫球蛋白。
北投科技sh6009365.79首板10.08%
14:55:46重组预期:
2025年12月12日晚公告,公司定位为北投集团重要上市平台,根据公司控股股东北投集团相关承诺,其将尽力督促下属广西交通设计集团与广西北投信创科技投资集团等科技型企业于本次重组完成后5年内达到注入上市公司的条件。
炸板股一览(共 75 只)
炸板TOP25因子
▼百日新高:32机器人概念:25▼芯片产业链:22▼昨日大额成交:22▼华为产业链:20国企改革:18▼电子:17新能源汽车:16汽车零部件:16▼消费电子:14▼昨日高换手:12▼半导体芯片:12▼江苏:12浙江:12▼光通信:11▼商业航天:11▼广东:11▼并购重组:11人形机器人:11交运设备:10昨日涨停:10▼股权转让:9▼光伏:9ST股:9玻璃基板:9
股票
现价
涨跌幅
炸板时间
ST金顶sh6006786.72.45%
09:30:44
雷曼光电sz3001629.9811.63%
09:31:57
东方钽业sz00096256.592.82%
09:33:18
龙蟠科技sh60390629.35.28%
09:39:10
红星发展sh60036724.821.85%
09:39:29
凯恩股份sz0020127.512.04%
09:40:18
康欣新材sh6000764.091.24%
09:41:50
*ST尔雅sh6001076.671.68%
09:44:47
*ST九鼎sh6000539.97-0.5%
09:49:23
联域股份sz00132667.532.61%
09:56:45
豪恩汽电sz301488157.8810.64%
10:00:09
埃泰克sh60329354.775.25%
10:00:51
TCL科技sz0001004.373.31%
10:04:36
赛力斯sh60112783.386.14%
10:14:41
ST百利sh6039594.62.45%
10:16:33
沃格光电sh60377381.024.19%
10:18:55
科森科技sh60362627.383.91%
10:20:56
*ST福成sh6009653.451.17%
10:21:14
ST标准sh6003029.51-1.86%
10:26:34
海星股份sh603115105.748.4%
10:31:25
大族数控sz301200249.4611.37%
10:40:36
北方华创sz002371662.991.07%
10:41:12
首开股份sh6003764.554.84%
10:46:30
迎丰股份sh60505513.413.87%
10:52:22
华灿光电sz30032318.739.85%
10:52:24
胜通能源sz00133161.377.86%
11:07:27
荣晟环保sh60316518.353.09%
11:11:14
鹏鼎控股sz00293894.484.72%
11:17:27
禾盛新材sz00229097.553.23%
11:27:03
大智慧sh60151910.713.78%
11:27:54
*ST海华sh6002433.951.28%
13:00:11
铖昌科技sz001270146.56.19%
13:00:12
深天马Asz0000507.63.4%
13:00:12
江苏新能sh60369316.96.29%
13:00:48
合百集团sz0004179.31-2.31%
13:08:24
东睦股份sh60011434.965.33%
13:09:35
美迪凯sh68807920.639.79%
13:09:49
博敏电子sh60393620.541.73%
13:10:35
金海高科sh60331131.29.05%
13:11:32
红蜻蜓sh6031167.912.59%
13:17:32
*ST宝馨sz0025144.53.93%
13:28:00
九安医疗sz00243272.612.73%
13:31:36
聚光科技sz30020315.6114.7%
13:39:39
华安证券sh6009097.127.55%
13:41:30
市北高新sh6006045.797.22%
13:43:35
昊志机电sz30050386.9714.68%
13:46:03
博云新材sz00229724.714.88%
14:08:48
飞亚达sz00002623.236.56%
14:11:21
春秋电子sh60389020.885.51%
14:12:35
伯特利sh60359632.98.12%
14:12:45
模塑科技sz00070015.097.4%
14:13:27
招商南油sh6019755.737.5%
14:16:50
新坐标sh603040916.31%
14:17:37
宏盛股份sh60309076.246.05%
14:21:28
长虹华意sz0004049.878.46%
14:22:00
新泉股份sh60317961.947.95%
14:25:29
安彩高科sh6002076.75.68%
14:29:53
共达电声sz00265534.394.15%
14:31:09
旗滨集团sh6016366.837.39%
14:32:07
立新能源sz00125810.337.16%
14:34:48
园林股份sh60530329.67.6%
14:35:13
梦天家居sh60321627.910.94%
14:40:03
彩虹集团sz00302331.754.92%
14:43:54
北特科技sh60300955.839.04%
14:43:58
盛剑科技sh60332432.97.38%
14:44:29
凯众股份sh60303714.726.82%
14:44:39
万通发展sh60024615.418.44%
14:48:04
红板科技sh60345996.016.78%
14:48:51
ST得润sz0020556.831.49%
14:50:51
美湖股份sh60331932.878.81%
14:52:16
五方光电sz00296219.697.83%
14:54:39
利仁科技sz001259889.28%
14:55:51
埃斯顿sz00274728.79.96%
14:57:09
彩虹股份sh60070711.429.91%
14:59:59
声迅股份sz00300449.649.99%
15:00:00
跌停股一览(共 65 只)
跌停TOP25因子
ST股:40低价股:22浙江:14▼昨日高换手:13化债概念:11▼股权转让:10▼芯片产业链:9▼昨日大额成交:9▼广东:9新型城镇化:9▼房地产概念:8▼光伏:8▼建筑工程:8▼节能环保:8西部开发:8国企改革:8▼化工:7▼深圳本地:7山东:7成渝板块:7▼历史新高:6▼半导体芯片:6▼高市盈率:6▼房地产:6▼基础化工:6
股票
现价
涨跌幅
跌停时间
ST洲际sh6007592.79-5.1%
09:44:11
*ST瑞茂sh6001801.57-4.85%
09:46:55
赞宇科技sz00263711.12-10.03%
10:06:45
养元饮品sh60315644.15-9.99%
14:10:21
波导股份sh6001305.49-10%
14:20:08
圣晖集成sh603163115.39-10%
14:42:17
共进股份sh60311814.02-10.01%
14:43:55
ST金鸿顺sh60392214.41-5.01%
14:46:43
巨力索具sz00234212.79-9.99%
14:49:39
中集集团sz00003910.19-9.98%
14:50:09
通鼎互联sz00249121.74-9.98%
14:52:30
川能动力sz00015514.38-10.01%
14:54:30
川润股份sz00227222.45-9.98%
14:56:03
*ST雅博sz0023231.15-4.96%
14:56:06
ST龙元sh6004911.32-5.04%
14:57:02
衢州发展sh6002083.2-10.11%
14:57:03
*ST海利sh6037183.42-5%
14:57:04
大元泵业sh60375759.85-10%
14:57:05
ST文峰sh6010101.63-5.23%
14:57:07
双枪科技sz00121153.37-10%
14:57:09
千味央厨sz00121541.04-10%
14:57:09
*ST天箭sz00297727.83-4.98%
14:57:09
合肥城建sz00220823.29-10.01%
14:57:09
*ST美芝sz00285619.11-5.02%
14:57:09
汇源通信sz00058617.98-10.01%
14:57:09
ST万邦sz00208215.4-5%
14:57:09
跃岭股份sz00272515.04-9.99%
14:57:09
*ST中迪sz00060914.82-5%
14:57:09
*ST东易sz00271313.55-4.98%
14:57:09
安妮股份sz00223510.31-10.03%
14:57:09
红墙股份sz0028099.34-10.02%
14:57:09
*ST准油sz0022079.13-4.99%
14:57:09
仁智股份sz0026296.89-10.05%
14:57:09
ST京蓝sz0007115.51-5%
14:57:09
*ST数源sz0009094.99-4.95%
14:57:09
ST达华sz0025124.92-5.02%
14:57:09
*ST未名sz0025814.54-5.02%
14:57:09
*ST棒杰sz0026344.28-5.1%
14:57:09
德展健康sz0008133.81-9.93%
14:57:09
ST海龙sz0006772.26-5.04%
14:57:09
*ST华西sz0026301.84-5.15%
14:57:09
*ST发展sz0008381.8-4.76%
14:57:09
ST龙大sz0027261.77-4.84%
14:57:09
ST海王sz0000781.72-4.97%
14:57:09
ST嘉澳sh60382277.28-5%
14:57:11
安德利sh60519852.38-10%
14:57:15
祥龙电业sh60076918.9-10%
14:57:15
*ST华鹏sh6030216.47-4.99%
14:57:16
华培动力sh60312118.71-10%
14:57:18
*ST威领sz00266718.37-5.02%
14:57:18
*ST瑞和sz0026208.43-4.96%
14:57:18
*ST冀凯sz0026915.61-4.92%
14:57:18
*ST皇庭sz0000561.32-5.04%
14:57:18
*ST三房sh6003701.38-4.83%
14:57:24
ST金鸿sz0006694.39-4.98%
14:57:27
ST宏达sz0022113.76-5.05%
14:57:27
*ST岭南sz0027171.11-5.13%
14:57:27
*ST美丽sz0000102.35-4.86%
14:57:36
*ST高科sh60073012.66-5.03%
14:57:37
*ST网达sh60318912.26-4.96%
14:57:46
ST中路sh6008186.2-5.05%
14:57:49
凯瑞德sz0020726.98-10.05%
14:57:54
ST三木sz0006323.92-5.08%
14:57:54
ST喜临门sh6030088.96-4.98%
14:58:19
*ST帅电sh60533617.25-5.01%
14:59:01
2026-05-14
Avanti Research 提供超 2400 种高纯度脂质,纯度≥99%,覆盖磷脂、鞘脂、胆固醇及 LNP 专用脂质等全品类。产品核心应用于 mRNA 疫苗 LNP 递送、脂质体制备及脂质组学研究,在大量公开文献中被用作标准脂质试剂与 LNP 关键组分。可支持从基础研究到临床阶段的脂质相关实验与制剂开发。
安邦生物大量现货供应,欢迎咨询!
Avanti脂质充电站上线
Avanti 全新上线多款应用目录,让脂质相关研发高效可靠。涵盖磷脂、鞘脂、甾醇、LNP 专用脂质、荧光脂质、PEG 脂质偶联物,并配套脂质体制备工具、脂类组学检测试剂及疫苗佐剂,适配核酸药物递送、脂质体研发、疫苗开发等多场景。
部分应用目录,左右划动查看更多
关于 Avanti:深耕脂质领域的全球领先品牌
Avanti 自创立以来,始终以研究者需求为核心,一步步成为脂质领域的全球领先品牌:
1
品牌积淀:专注脂质试剂研发与生产,从基础磷脂产品到高端定制脂质,从常规实验试剂到临床级佐剂,持续引领脂质技术革新。
2
技术优势:拥有 150 多年脂质合成经验,建立严苛的质控体系,所有产品纯度≥99%,经 HPLC、NMR 双重检测,批次稳定性强。
3
全球布局:依托默克全球供应链,实现高频产品本地化现货库存,搭配专业技术团队与 及时响应服务,让国内外研究者同步享受高品质支持。
四大实验难题,透彻破解 + 实操方案全公开
难题一:脂质体制备粒径不均、包封率低,操作复杂?
核心痛点:手动制备粒径分布宽,脂质易团聚,设备调试繁琐,包封率不达标。
实操方案
专业设备 + 试剂成套搭配:
1
核心设备:Avanti 小型脂质挤出器(610000-1ea),配备 30nm-1μm 不同孔径聚碳酸酯膜,通过机械挤压实现脂质体粒径均一化,无需复杂参数调试;配套加热块可精准控制温度,轻松处理相变温度高于室温的磷脂(如 DPPC)。
2
优质脂质:选用高纯度合成磷脂(DSPC、DPPC、DOPC 等),链长覆盖 C3:0 到 C26:0,支持 cis/trans 构型选择,脂质纯度≥99%,减少杂质导致的团聚。
3
辅助试剂:搭配 PEG 脂质(如 DSPE-PEG2000)提升脂质体水溶性,添加胆固醇调节膜流动性,进一步优化粒径与稳定性。
包封率提升实操步骤:
1
脂质水化:将脂质混合物用缓冲液水化 30 分钟。
2
循环冻融:置于循环冻融 3-5 次(干冰浴与温水浴交替),这一步能有效打破多室脂质体囊泡,使内外水相充分交换,显著提升水溶性药物的包封率。
3
挤出操作:将水化后的脂质悬浮液装入注射器,插入预热好的挤出器,来回挤压 11 次以上,确保粒径均一(通过动态光散射仪验证粒径分布 PDI<0.2)。
4
后续处理:挤出后的脂质体建议短期内在4℃避光储存,避免反复冻融;若需长期保存,建议进行冷冻干燥处理。
5
设备维护要点:聚碳酸酯膜和滤膜支撑仅限单次使用,避免交叉污染;挤出器使用后用异丙醇冲洗,再用去离子水清洗,晾干后密封保存;注射器柱塞定期检查,避免磨损导致漏液。
难题二:脂质组学标品不全、定量不准,数据反复波动?
核心痛点:内标覆盖类别有限,不同样品适配难,标品稳定性差导致数据偏差。
实操方案
1
全类别标品覆盖:UltimateSPLASH™ ONE 内标含 69 种高纯度氘标记脂质,涵盖 PI、PS、PG、鞘脂等 15 种脂质类别,能精准控制电离和裂解效率,实现多类型脂质同步定量,避免 “漏检”“误检”。
2
细分场景精准适配:
神经组织研究选 MSI SPLASH(13 种内标,专为脑切片质谱成像设计,可同时实现脂质定量与定位);
小鼠样本用 Mouse SPLASH(浓度完全匹配小鼠组织/血浆脂质含量,无需额外调整);
血浆分析优先 SPLASH II(添加缩醛磷脂,去除胆固醇等冗余成分,更贴合血浆脂质谱特点);
专项研究:氧甾醇、胆汁酸等专项研究,对应 Oxysterol SPLASH、Bile Acid SPLASH 等专属标品,覆盖 13-18 种细分脂质。
3
稳定性与操作保障:标品采用一次性安瓿瓶包装,-20℃及以下避光密封保存可长期保持活性;使用前用温水浴超声 2 分钟,避免析出物影响检测;开封后立即使用,搭配标准化操作流程,从源头抹平批次与操作误差。
难题三:转染效率低、细胞毒性高,实验反复失败?
核心痛点:试剂与核酸结合力弱,转染后细胞大量死亡,脂质颗粒易团聚导致递送失效。
实操方案
1
高效低毒试剂选型:Avanti 阳离子脂质(DOTMA、DOTAP、DC-Cholesterol 等)采用优化的阳离子头基设计,与阴离子核酸快速形成稳定复合物,表现出优异的转染效率,细胞存活率≥85%;其中 DC-Cholesterol 适配多种难转染细胞,DOTAP 适合常规细胞系快速转染,多价阳离子脂质可满足复杂转染场景需求。
2
稳定性与毒性优化:搭配 PEG 脂质(DSPE-PEG2000、DOPE-PEG2000 等),在脂质颗粒表面形成亲水保护层,不仅能抑制颗粒团聚,还能减少细胞吞噬过程中的毒性反应,延长体内递送时间。
3
分场景操作细则:
贴壁细胞转染:脂质与核酸比例(N/P比)控制在 3:1~5:1,转染液孵育时间不超过 6 小时,孵育温度维持在 37℃。
悬浮细胞转染:适当提高脂质浓度,采用静置转染方式,避免摇晃导致复合物解离。
病毒载体转染:选用低毒性阳离子脂质,搭配 DMG-PEG2000,提升病毒颗粒稳定性与感染效率。
4
避坑指南:试剂避免反复冻融,首次使用先申请小规格试用装,验证与细胞系的兼容性;转染过程中保持培养基 pH 在 7.2-7.4,避免血清干扰复合物形成。
难题四:疫苗佐剂免疫效果弱、安全性存疑,难以落地?
核心痛点:佐剂致热性高,免疫活性不稳定,批量供应难,不符合临床合规要求。
实操方案
1
分场景佐剂选型:
通用型临床级佐剂:PHAD™(合成 MPLA 类似物),已通过千例临床受试者验证,无严重不良事件,可大批量供应,适配各类疫苗商业化生产,能有效激活 TLR4 通路,诱导抗原特异性效应 CD4+ 和记忆性 CD8+ T 细胞产生。
低致热佐剂:3D-PHAD™(专利产品,专利号:9,241,988),活性与天然 MPLA 相当,但致热性显著降低,已进入临床试验阶段,适合对安全性要求高的疫苗研发。
结构匹配佐剂:3D (6-acyl)-PHAD™,其结构与特定成熟佐剂系统中的 MPLA 高度相似,免疫活性相当,为疫苗研发提供了优质、合规的候选替代方案。
2
合规与稳定性保障:部分佐剂完成 DMF 备案,提供完整的质控报告(含纯度、活性、致热性检测数据)。
3
使用优化:佐剂与抗原混合时控制温度在 25℃左右,搅拌速度保持温和,避免剧烈摇晃导致活性降低;根据疫苗类型调整佐剂浓度,推荐先进行小动物免疫实验验证效果。
关于安邦
安邦生物——专业提供高品质的实验室产品与服务,让生命科学研究更简单!
广州安邦生物科技有限公司(Guangzhou abbiotechnology, Inc.)成立于2011年6月,坐落于广州市天河区怡祥大地公园,拥有1600多平米的现货试剂耗材及仪器仓库,拥有专业的试剂冷库及配套冷链物流配送服务,是一家华南地区专业提供生命科学实验室产品和服务的供应商。公司主营业务涉及生物技术、生物医药、分子诊断、分析检测等领域,现阶段产品涵盖了细胞生物学、免疫学、分子生物学、表观遗传学、蛋白纯化、生化试剂等,产品线日趋完善。
安邦生物专业为客户提供个性化和定制化的一站式科研实验室产品解决方案,以及稳定可靠的技术支持与售后服务。
广州安邦生物科技有限公司
tel:020-87052699
E-mail:cl@abbiomall.com
www.abbiomall.com
查现货产品?
查更多优惠活动?
长按二维码咨询
2026-05-13
来源:竞逐IVD原料江湖
化学发光稳坐IVD细分市场头把交椅,数十上百家企业躬身入局,但业绩和命运的分化已是板上钉钉。对于很多发光小厂而言,此诚危急存亡之秋也。根源无它,受到压制和整顿的市场,容纳不下这许多轻浮而又同质化企业了,跟风而来的,只能随风而去。
比如上面这家深圳IVD企业,多条被执行信息显示公司正遭遇困境,从时间上来看都是今年新增的,当初乘着小发光的“东风”而来,如今怕是终成炮灰。
然而,跟风而进的厂家,显然是代表不了化学发光赛道真正的先进生产力的。事实上诸多实力玩家的成功案例,生动演绎了“八仙过海、各显神通”的精彩博弈。
仅从方法学而言,发光赛道便呈现出“百家争鸣”的盛况: 碱磷酶体系、吖啶酯体系、异鲁米诺体系、电化学体系、光激发光体系。难能可贵的是,每一种体系都有头部的带头大哥(们)把路走通乃至成功上市。如今,第五代发光、单分子免疫的玩家也逐渐涌现增多。
从市场策略而言,发光赛道也堪称精彩纷呈。随便举几例: 新产业的硬核业绩,充分显示专注的力量,平推即可,“重剑无锋,大巧不工”;亚辉龙凭借自身免疫的差异化菜单,不仅跻身公认“五虎”之列,在某些项目上更成为引领者;宝太、安邦基于自身在海外市场深耕的核心竞争力,以可冻干、便于运输和保存的均相发光切入;宇测、彩科聚焦AD相关标志物检测,突出单分子免疫技术平台优势;老牌生化企业宁波瑞源,秉承试剂国产替代的一贯思路,埋头做好进口试剂的无缝替代,同样做得风生水起。
不久前,笔者碰到另外一家生化企业的朋友,这家企业笔者接触很多年了。对方告知,他们也在开发POCT发光产品,规划了心肌、炎症等常规项目。显然,在这个案例中,技术没有创新、项目没有新意、海外市场没有积累、成本优势更无从谈起。要是碰到他们老板,笔者真的想问一句,化学发光,咱是非做不可吗?
声明:本微信注明来源的稿件均为转载,仅用于分享,不代表平台立场,如涉及版权等问题,请尽快联系我们,我们第一时间更正。
100 项与 湖南安邦制药股份有限公司 相关的药物交易
登录后查看更多信息
100 项与 湖南安邦制药股份有限公司 相关的转化医学
登录后查看更多信息
组织架构
使用我们的机构树数据加速您的研究。
登录
或

管线布局
2026年06月04日管线快照
管线布局中药物为当前组织机构及其子机构作为药物机构进行统计,早期临床1期并入临床1期,临床1/2期并入临床2期,临床2/3期并入临床3期
其他
1
登录后查看更多信息
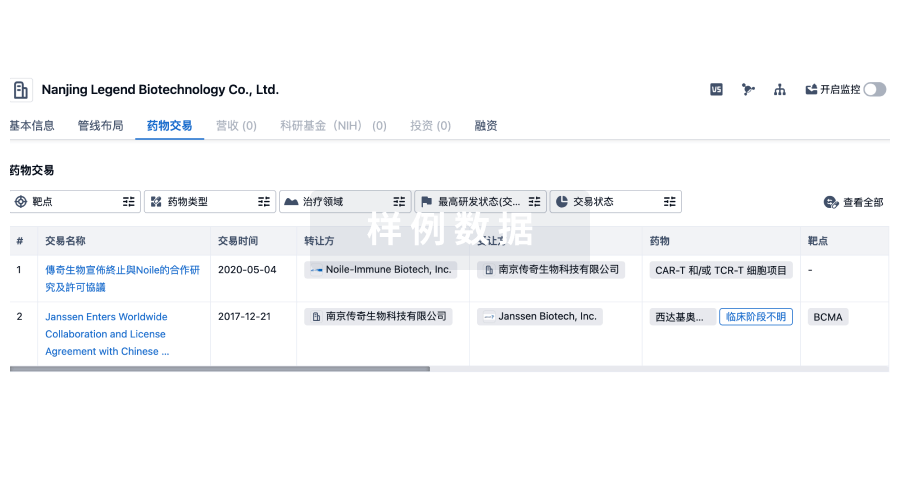
药物交易
使用我们的药物交易数据加速您的研究。
登录
或
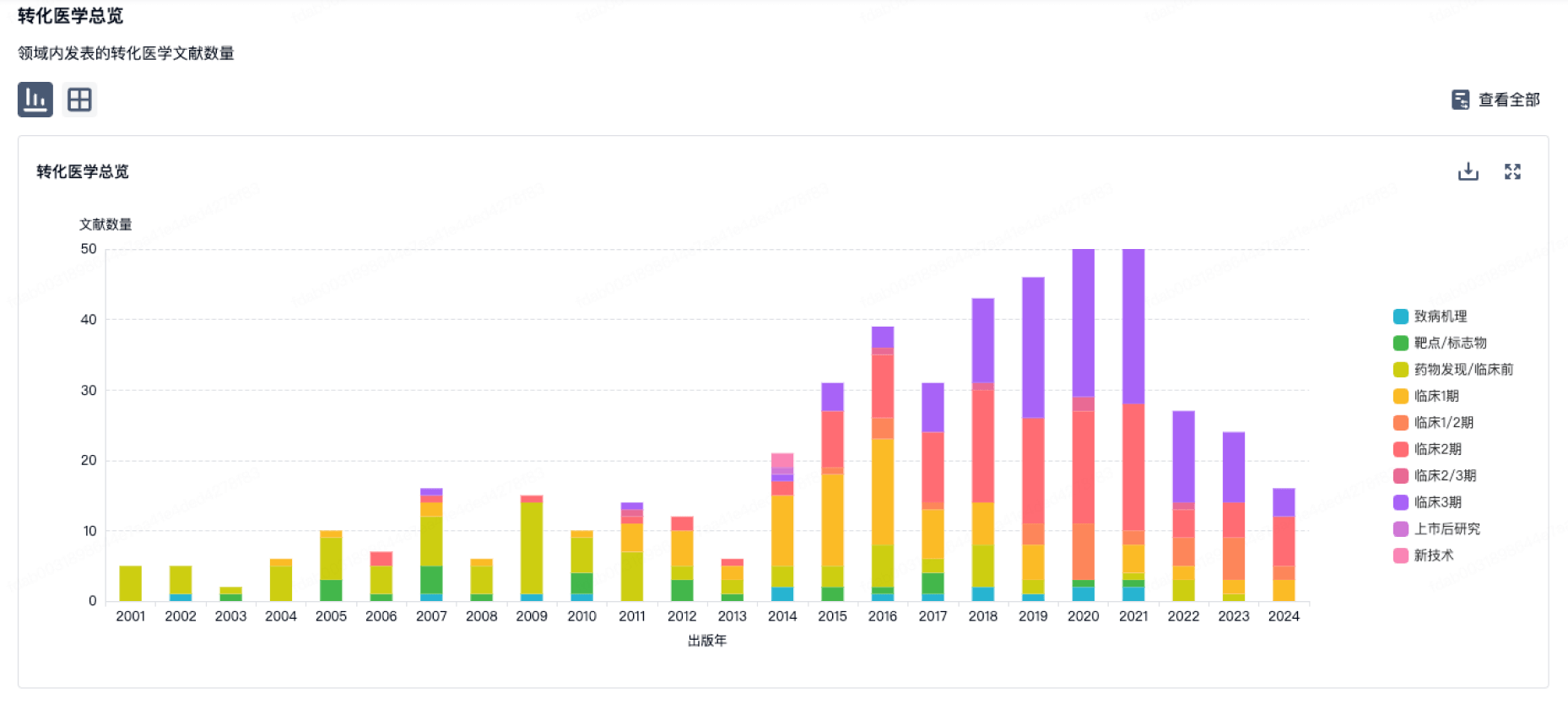
转化医学
使用我们的转化医学数据加速您的研究。
登录
或
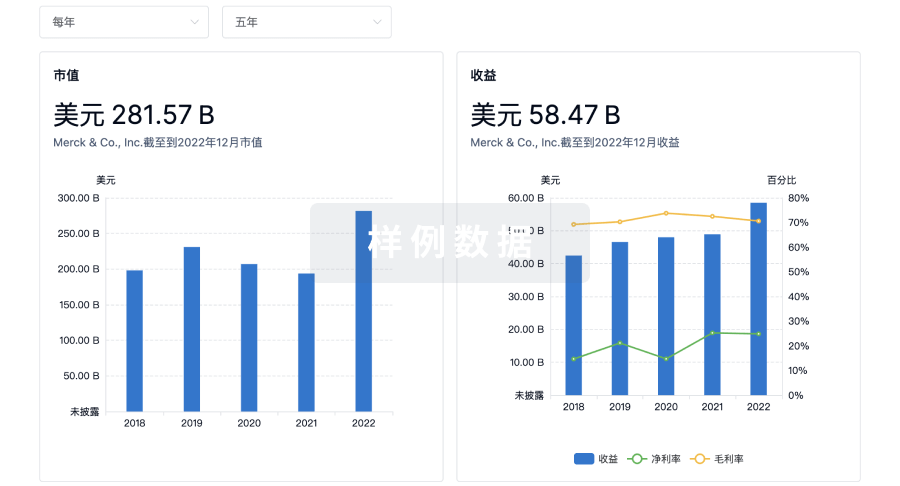
营收
使用 Synapse 探索超过 36 万个组织的财务状况。
登录
或
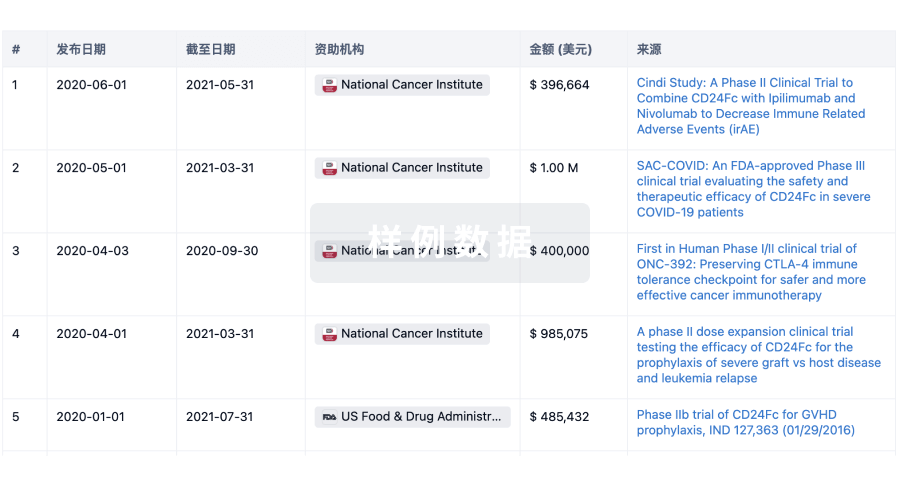
科研基金(NIH)
访问超过 200 万项资助和基金信息,以提升您的研究之旅。
登录
或
投资
深入了解从初创企业到成熟企业的最新公司投资动态。
登录
或
融资
发掘融资趋势以验证和推进您的投资机会。
登录
或
生物医药百科问答
全新生物医药AI Agent 覆盖科研全链路,让突破性发现快人一步
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。
生物序列数据库
生物药研发创新
免费使用
化学结构数据库
小分子化药研发创新
免费使用