预约演示
更新于:2026-05-08
Cobicistat /Darunavir/Emtricitabine/Tenofovir Alafenamide Fumarate
乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他
更新于:2026-05-08
概要
基本信息
药物类型 小分子化药 |
别名 Cobicistat/darunavir/emtricitabine/GS 7340、Cobicistat/darunavir/emtricitabine/tenofovir alafenamide、Darunavir / Cobicistat / Emtricitabine / Tenofovir Alafenamide + [7] |
作用方式 抑制剂 |
作用机制 CYP3A抑制剂(细胞色素P450家族成员3A家族抑制剂)、HIV-1 pol抑制剂(人类免疫缺陷病毒1型蛋白酶抑制剂)、RT抑制剂(逆转录酶抑制剂) |
在研适应症 |
非在研适应症- |
权益机构- |
最高研发阶段批准上市 |
首次获批日期 欧盟 (2017-09-21), |
最高研发阶段(中国)- |
特殊审评- |
登录后查看时间轴
结构/序列
分子式C25H33N6O9P |
InChIKeyMEJAFWXKUKMUIR-FHPNUNMMSA-N |
CAS号1392275-56-7 |
查看全部结构式(4)
关联
15
项与 乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他 相关的临床试验NCT05463783
Effect of Darunavir/Cobicistat/Emtricitabine/Tenofovir Alafenamide and Bictegravir/Emtricitabine/Tenofovir Alafenamide on the Circulatory microRNA Profile in Treatment naïve HIV Patients, and Its Correlation With Change in Body Weight
The purpose of this research study is to understand why certain HIV medication regimens (called anti-retroviral or ARV medications) cause more weight gain than others. In this research, the investigators will compare micro-RNA profiles of people who take Symtuza(darunavir(D)/cobicistat(C)/emtricitabine(F)/tenofovir alafenamide (TAF))[D/C/F/TAF] with those who take Biktarvy(bictegravir(B)/emtricitabine(F)/tenofovir alafenamide (TAF))[B/F/TAF] and try to correlate this with the change in body weight and BMI over a course of 48 weeks. The investigators will also attempt to monitor the calorie intake of the participants in the two groups and correlate it with treatment-induced weight gain. Micro-RNAs are small molecules that are produced naturally in the human body, and which are responsible for modifying the expressions of genes. They have the potential to be used in diagnostic and therapeutic medicine and their putative role has been explored in many diseases across many clinical trials. By doing this research, the investigators hope to learn more about their role in HIV disease and its correlation with treatment-induced weight gain.
开始日期2023-03-14 |
申办/合作机构 |
NCT04388904
A Phase 4, Single-arm, Open-label Study to Evaluate the Efficacy and Safety of Darunavir/Cobicistat/Emtricitabine/Tenofovir Alafenamide (D/C/F/TAF) Once Daily Fixed-dose Combination (FDC) Regimen in Antiretroviral Treatment-experienced Human Immunodeficiency Virus Type 1 (HIV-1) Infected Subjects Not Currently Receiving Any Antiretroviral Therapy.
The purpose of this study is to demonstrate the effectiveness of Symtuza® in a rapid reinitiation model of care in patients with HIV-1 infection and who are treatment-experienced but have been off of antiretroviral therapy (ART) for 12 or more weeks.
开始日期2021-09-01 |
申办/合作机构 |
NCT04661397
A Single-Dose, Open-Label, Randomized, Replicate Crossover Pivotal Bioequivalence Study in Healthy Adult Participants to Assess the Bioequivalence of Darunavir 675 mg, Emtricitabine 200 mg, and Tenofovir Alafenamide 10 mg in the Presence of Cobicistat 150 mg When Administered as a Fixed Dose Combination (Darunavir/Cobicistat/Emtricitabine/Tenofovir Alafenamide) Compared to the Co-administration of the Separate Agents (Darunavir, Cobicistat, and Emtricitabine/Tenofovir Alafenamide), Under Fed Conditions
The purpose of the study is to evaluate the single-dose pharmacokinetics (PK) and pivotal bioequivalence of 3 compounds Darunavir (DRV), emtricitabine (FTC), and tenofovir alafenamide (TAF) in the presence of cobicistat (COBI) when administered as an fixed dose combination (FDC) (Darunavir/Cobicistat/Emtricitabine/Tenofovir Alafenamide [D/C/F/TAF]) compared to the co-administration as the separate commercial formulations (DRV and F/TAF and COBI), under fed conditions, in healthy adult participants.
开始日期2021-01-05 |
100 项与 乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他 相关的临床结果
登录后查看更多信息
100 项与 乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他 相关的转化医学
登录后查看更多信息
100 项与 乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他 相关的专利(医药)
登录后查看更多信息
10
项与 乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他 相关的文献(医药)2025-12-02·AIDS REVIEWS
Rapid Initiation of Antiretroviral Therapy after HIV Diagnosis
Review
作者: García-Deltoro, Miguel
Roughly, 38 million people are living with HIV worldwide. Despite the success of antiretroviral therapy (ART) for suppressing virus replication and restore immunity in infected persons, the HIV epidemics are not controlled globally. Each year 1.8 million new HIV infections occur. This rate has declined only slightly during the past decade, despite huge efforts for expanding ART coverage, pre- and post-exposure prophylaxis, and stopping vertical transmission. To achieve the United Nations Programme on HIV/AIDS goals of 95-95-95 by 2030, renewed efforts and innovative strategies must be undertaken. The source of most new HIV infections is people unaware of their HIV-positive status and/or not linked to care. Thus, efforts for unveiling HIV positives and, especially, rapid initiation of ART and retention in care would be the most effective interventions for halting HIV spreading globally. In certain settings, access to point-of-care diagnostic tests and immediate start of ART (even the same day) must be implemented at large scale. Selection of the most convenient ART to be prescribed empirically is an important caveat to minimize the risks of treatment failure. Ideally, it must be easy to take, coformulated as single-tablet regimen (STR), well tolerated, with no requests for prior human leukocyte antigen testing, depict few drug interactions, keep activity against transmitted drug-resistant viruses, remain efficacious in patients with elevated HIV-RNA, and/or low CD4 counts, and when present, suppress hepatitis B coinfection. At this time, the coformulation of darunavir, cobicistat, emtricitabine, and tenofovir alafenamide (Symtuza®) is the only regimen that has been evaluated in a Phase 3 trial as "test-and-treat" strategy. Results at 48 weeks in the DIAMOND study are reassuring, as more than 90% of individuals achieve undetectable viremia.
2023-03-01·HIV medicine
Darunavir/cobicistat/emtricitabine/tenofovir alafenamide in treatment‐naïve (AMBER ) and virologically suppressed (EMERALD ) participants with neurological and/or psychiatric comorbidities: Week 96 subgroup analysis
Article
作者: Dunn, Keith ; Cai, Jiyun ; Bushen, Jennifer ; Anderson, David ; Simonson, Richard Bruce ; Luo, Donghan
Abstract:
Objective:
Our objective was to evaluate the prevalence of pre‐existing neurological and/or psychiatric comorbidities (NPCs) and efficacy/safety outcomes for participants with versus without baseline NPCs in AMBER and EMERALD.
Methods:
AMBER (treatment‐naïve population) and EMERALD (virologically suppressed population) were phase III randomized studies of darunavir/cobicistat/emtricitabine/tenofovir alafenamide (D/C/F/TAF) 800/150/200/10 mg. The primary objective of this post hoc analysis was to assess virological response (HIV‐1 RNA <50 copies/mL) at week 48 by intent‐to‐treat US Food and Drug Administration snapshot analysis comparing participants with and without baseline NPCs.
Results:
Among participants in AMBER, 88/362 (24%) in the D/C/F/TAF arm and 99/363 (27%) in the control arm had baseline NPCs; in EMERALD, 294/763 (39%; D/C/F/TAF) and 166/378 (44%; control) participants had baseline NPCs. At baseline, psychiatric NPCs were more common than neurological NPCs in both studies; the most common of each type were depression and headache, respectively. High virological response rates were achieved with D/C/F/TAF across studies regardless of baseline NPCs at weeks 48 (range 86%–95%) and 96 (range 80%–91%). No participants in either study with a baseline NPC prematurely discontinued because of a study drug–related neurological or psychiatric adverse event.
Conclusion:
D/C/F/TAF may be a suitable treatment option for individuals with HIV‐1 and NPCs.
2021-03-04·HIV research & clinical practice4区 · 医学
Rapid initiation of darunavir/cobicistat/emtricitabine/tenofovir alafenamide in acute and early HIV-1 infection: a DIAMOND subgroup analysis
4区 · 医学
Article
作者: Dunn, Keith ; Rogers, Rachel ; Seyedkazemi, Sareh ; Kassam, Purnima T. ; Simonson, Richard Bruce ; Sheng, Shubin ; Hardy, Hélène ; Luo, Donghan
BACKGROUND:
Treatment during acute or early human immunodeficiency virus (HIV)-1 infection is associated with immunologic and virologic benefits.
OBJECTIVE:
To evaluate darunavir/cobicistat/emtricitabine/tenofovir alafenamide (D/C/F/TAF) efficacy/safety among patients with acute or early HIV-1 infection who rapidly initiate treatment.
METHODS:
DIAMOND (ClinicalTrials.gov Identifier: NCT03227861), a phase 3 study, evaluated the efficacy/safety of D/C/F/TAF 800/150/200/10 mg in rapid initiation. Adults aged ≥18 years began D/C/F/TAF within 14 days of diagnosis, prior to the availability of screening/baseline laboratory results. In this subgroup analysis, virologic response (HIV-1 RNA <50 copies/mL) was assessed at Week 48 by intent-to-treat FDA snapshot (ITT-FDA snapshot) and observed (excluding patients with missing data) analyses in patients with acute (HIV-1 antibody negative and HIV-1 RNA positive/p24 positive) or early (HIV-1 antibody positive and suspected infection ≤6 months before screening/baseline) infection.
RESULTS:
Among 109 patients, 13 had acute and 43 had early HIV-1 infection. High rates of virologic response were demonstrated at Week 48 by ITT-FDA snapshot (acute: 10/13 [76.9%]; early: 37/43 [86.0%]) and observed (acute: 10/11 [90.9%]; early: 37/38 [97.4%]) analyses. No patients discontinued or required regimen change due to baseline resistance or lack of efficacy, or developed protocol-defined virologic failure. Through Week 48, 7 (53.8%) acute and 22 (51.2%) early infection patients had a D/C/F/TAF-related adverse event (AE); none had a D/C/F/TAF-related grade 4 or serious AE.
CONCLUSIONS:
High rates of viral suppression during acute/early infection were achieved with D/C/F/TAF rapid initiation, no treatment-emergent resistant mutations were observed, and D/C/F/TAF was safe and well tolerated.
36
项与 乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他 相关的新闻(医药)2026-05-07
Product Sales Excluding Veklury Increased 8% Year-Over-Year to $6.8 billion
Biktarvy Sales Increased 7% Year-Over-Year to $3.4 billion
FOSTER CITY, Calif.--(BUSINESS WIRE)-- Gilead Sciences, Inc. (Nasdaq: GILD) announced today its results of operations for the first quarter 2026.
“Gilead teams have delivered another strong quarter with 8% year-over-year growth in our base business and 10% growth in HIV, supported by the successful launch of Yeztugo. We have raised our full year revenue guidance as a reflection of our performance," said Daniel O’Day, Gilead’s Chairman and Chief Executive Officer. “Building on the strongest pipeline in Gilead’s history, we are adding potentially best-in-disease assets and platforms in oncology and inflammation from our acquisitions of Arcellx, Ouro Medicines and Tubulis. With up to four potential launches and five Phase 3 updates anticipated in 2026, Gilead is well-positioned for sustained growth in the near and long term.”
First Quarter 2026 Financial Results
Total first quarter 2026 revenues increased 4% to $7.0 billion compared to the same period in 2025, primarily driven by higher sales of HIV products, Trodelvy® (sacituzumab govitecan-hziy), and Livdelzi® (seladelpar), partially offset by lower sales of Veklury® (remdesivir), as well as chronic hepatitis C virus (“HCV”) and Cell Therapy products. Diluted earnings per share (“EPS”) was $1.61 in the first quarter 2026 compared to $1.04 in the same period in 2025. The increase was primarily driven by net unrealized gains from equity securities compared to net unrealized losses in 2025 and higher product sales, as well as lower acquired in-process research and development (“IPR&D”) expenses. The increase was partially offset by higher income tax and selling, general and administrative (“SG&A”) expenses. Non-GAAP diluted EPS was $2.03 in the first quarter 2026 compared to $1.81 in the same period in 2025. The increase was primarily driven by higher product sales and lower acquired IPR&D expenses, partially offset by higher income tax and SG&A expenses. As of March 31, 2026, Gilead had $8.6 billion of cash, cash equivalents and marketable debt securities compared to $10.6 billion as of December 31, 2025. The decrease was primarily driven by $2.8 billion of debt repayments, $1.0 billion of dividend payments and $419 million of common stock repurchases, partially offset by $2.5 billion of operating cash flow.
First Quarter 2026 Product Sales
Total first quarter 2026 product sales increased 5% to $6.9 billion compared to the same period in 2025. Total first quarter 2026 product sales excluding Veklury increased 8% to $6.8 billion compared to the same period in 2025, primarily due to higher sales of HIV products, Trodelvy and Livdelzi, partially offset by lower sales of HCV and Cell Therapy products.
HIV product sales increased 10% to $5.0 billion in the first quarter 2026 compared to the same period in 2025, primarily driven by higher demand and average realized price, partially offset by unfavorable inventory dynamics.
Biktarvy®(bictegravir 50mg/emtricitabine (“FTC”) 200mg/tenofovir alafenamide (“TAF”) 25mg) sales increased 7% to $3.4 billion in the first quarter 2026 compared to the same period in 2025, primarily driven by higher demand and average realized price, partially offset by unfavorable inventory dynamics. Descovy®(FTC 200mg/TAF 25mg) sales increased 38% to $807 million in the first quarter 2026 compared to the same period in 2025, primarily driven by higher average realized price and demand.
The Liver Disease portfolio sales increased 1% to $767 million in the first quarter 2026 compared to the same period in 2025, primarily reflecting higher demand for Livdelzi, partially offset by unfavorable inventory dynamics and lower sales for HCV products.
Veklury sales decreased 52% to $144 millionin the first quarter 2026 compared to the same period in 2025, primarily driven by lower rates of COVID-19-related hospitalizations.
Cell Therapy product sales decreased 12% to $407 million in the first quarter 2026 compared to the same period in 2025, reflecting ongoing competitive headwinds.
Yescarta® (axicabtagene ciloleucel) sales decreased 14% to $332 million in the first quarter 2026 compared to the same period in 2025, primarily driven by in- and out-of-class competition. Tecartus® (brexucabtagene autoleucel) sales decreased 4% to $75 million in the first quarter 2026 compared to the same period in 2025, primarily driven by in-class competition.
Trodelvy® (sacituzumab govitecan-hziy) sales increased 37% to $402 million in the first quarter 2026 compared to the same period in 2025, primarily driven by higher demand, favorable inventory dynamics and higher average realized price.
First Quarter 2026 Product Gross Margin, Operating Expenses and Effective Tax Rate
Product gross margin was 79.2% in the first quarter 2026 compared to 76.7% in the same period in 2025. Non-GAAP product gross margin was 87.5% in the first quarter 2026 compared to 85.5% in the same period in 2025. These increases are primarily due to the expiration of a royalty-related obligation and product mix. Research and development (“R&D”) expenses remained relatively flat at $1.4 billion in the first quarter 2026 compared to the same period in 2025, primarily due to lower oncology clinical study activity and lower restructuring costs being fully offset by higher investment in virology clinical manufacturing. Non-GAAP R&D expenses were $1.4 billion in the first quarter 2026 compared to $1.3 billion in the same period in 2025, primarily driven by higher investment in virology clinical manufacturing, partially offset by lower oncology clinical study activity. Acquired IPR&D expenses were $107 million in the first quarter 2026, primarily related to an $80 million upfront payment related to our collaboration with Suzhou Genhouse Bio Co., Ltd. (“Genhouse”). SG&A expenses were $1.5 billion in the first quarter 2026 compared to $1.3 billion in the same period in 2025, primarily driven by higher HIV promotional expenses and donations of equity securities made to the Gilead Foundation. Non-GAAP SG&A expenses were $1.4 billion in the first quarter 2026 compared to $1.2 billion in the same period in 2025, primarily due to higher HIV promotional expenses. The effective tax rate (“ETR”) was 21.7% in the first quarter 2026 compared to 20.2% in the same period in 2025. The non-GAAP ETR was 18.3% in the first quarter 2026 compared to 16.3% in the same period in 2025. These increases are primarily driven by a prior year state tax benefit that did not recur.
Guidance and Outlook
For the full year 2026, Gilead now expects:
(in millions, except per share amounts)
May 7, 2026 Guidance
Comparison to February 10, 2026 Guidance
Low End
High End
Product sales
$
30,000
$
30,400
Previously $29,600 to $30,000
Product sales excluding Veklury
$
29,400
$
29,800
Previously $29,000 to $29,400
Veklury
$
600
$
600
Unchanged
Diluted (loss) earnings per share
$
(3.25
)
$
(2.85
)
Previously $6.75 to $7.15
Non-GAAP diluted (loss) earnings per share
$
(1.05
)
$
(0.65
)
Previously $8.45 to $8.85
As compared to our February guidance, our updated full year 2026 GAAP and non-GAAP diluted earnings per share guidance was reduced by approximately $9.50 due to the anticipated acquired IPR&D charges of $11.5 billion as well as financing costs related to the Arcellx, Inc. (“Arcellx”), Ouro Medicines, LLC (“Ouro”), and Tubulis GmbH (“Tubulis”) transactions discussed further below.
Additional information and a reconciliation between GAAP and non-GAAP financial information for the 2026 guidance is provided in the accompanying tables. The financial guidance is subject to a number of risks and uncertainties. See the Forward-Looking Statements section below.
Key Updates Since Our Last Quarterly Release
Virology
Announced U.S. Food and Drug Administration (“FDA”) accepted New Drug Application for bictegravir and lenacapavir (“BIC/LEN”) for virologically suppressed people with HIV under priority review, with a Prescription Drug User Fee Act (“PDUFA”) target action date of August 27, 2026. Presented late-breaking Phase 3 results from the ARTISTRY-1 and ARTISTRY-2 trials at the 2026 Conference on Retroviruses and Opportunistic Infections (CROI), evaluating the investigational daily oral single-tablet regimen of BIC/LEN for virologically suppressed people with HIV. BIC/LEN maintained high levels of virologic suppression, demonstrating comparable efficacy to complex regimens and to Biktarvy at Week 48 in people with HIV who switched antiretroviral therapy. These data support global regulatory filings. Announced a $12 million investment to the Community Health Worker Comprehensive HIV Prevention Initiative program to expand HIV prevention initiatives across 14 U.S. states and the District of Columbia. Announced a new investment from the U.S. State Department, the U.S. President’s Emergency Plan for AIDS Relief (“PEPFAR”) and The Global Fund to deliver lenacapavir for HIV prevention to an additional 1 million people, bringing the total commitment up to 3 million people in countries supported by both PEPFAR and the Global Fund.
Oncology
Completed the acquisition of Arcellx for $115 per share, or an implied equity value of $7.8 billion, and one contingent value right of $5 per share. This acquisition builds on an existing collaboration agreement with Arcellx for the development of anitocabtagene autoleucel (“anito-cel”) in relapsed or refractory (“R/R”) multiple myeloma (“MM”), and also adds Arcellx’s D-Domain BCMA binder that has the potential to strengthen Gilead’s portfolio in oncology and inflammation. Announced that the Biologics License Application for anito-cel in 4L+ R/R MM has been accepted by FDA, with a PDUFA target action date of December 23, 2026. Announced a definitive agreement to acquire Tubulis, a private clinical-stage biotechnology company developing next-generation antibody-drug conjugates (“ADC”), including lead asset TUB-040, a NaPi2b-directed topoisomerase-I inhibitor ADC currently in Phase 1b/2 development for platinum-resistant ovarian cancer and non-small cell lung cancer. Closing of the transaction is subject to expiration or termination of certain regulatory filings and other customary conditions. Received FDA full approval for Tecartus in adult patients with R/R mantle cell lymphoma, following an accelerated approval in this setting in July 2020. Tecartus’ label now includes efficacy, safety and pharmacokinetic data from Cohort 3 of the ZUMA-2 study in patients who are R/R after one or more lines of therapy and who are Bruton tyrosine kinase inhibitor-naïve.
Inflammation
Announced a definitive agreement to acquire Ouro, a private clinical-stage biotechnology company developing T cell engager (“TCE”) therapies for autoimmune diseases. This acquisition adds Ouro’s lead asset, OM336 (gamgertamig), a BCMAxCD3 TCE, to Gilead’s portfolio. Closing of the transaction is subject to expiration or termination of certain regulatory filings and other customary conditions. Gilead has entered into a framework agreement with Galapagos NV (“Galapagos”) in relation to this acquisition, which includes equally splitting the $1.675 billion upfront payment and up to $500 million in milestone payments, among other terms.
Corporate
The Board declared a quarterly dividend of $0.82 per share of common stock for the second quarter of 2026. The dividend is payable on June 29, 2026, to stockholders of record at the close of business on June 15, 2026. Future dividends will be subject to Board approval.
Certain amounts and percentages in this press release may not sum or recalculate due to rounding.
Conference Call
At 1:30 p.m. Pacific Time today, Gilead will host a conference call to discuss Gilead’s results. A live webcast will be available on http://investors.gilead.com and will be archived on www.gilead.com for one year.
Non-GAAP Financial Information
The information presented in this document has been prepared in accordance with U.S. generally accepted accounting principles (“GAAP”), unless otherwise noted as non-GAAP. Management believes non-GAAP information is useful for investors, when considered in conjunction with Gilead’s GAAP financial information, because management uses such information internally for its operating, budgeting and financial planning purposes. Non-GAAP information is not prepared under a comprehensive set of accounting rules and should only be used to supplement an understanding of Gilead’s operating results as reported under GAAP. Non-GAAP financial information generally excludes acquisition-related expenses including amortization of acquired intangible assets and other items that are considered unusual or not representative of underlying trends of Gilead’s business, fair value adjustments of equity securities, the related tax charges or benefits associated with such exclusions and other discrete tax charges or benefits not representative of underlying trends such as changes in tax laws, transfers of intangible assets between certain legal entities, and effects of legal entity restructurings. Although Gilead consistently excludes the amortization of acquired intangible assets from the non-GAAP financial information, management believes that it is important for investors to understand that such intangible assets were recorded as part of acquisitions and contribute to ongoing revenue generation.Non-GAAP measures may be defined and calculated differently by other companies in the same industry. Reconciliations of the non-GAAP financial measures to the most directly comparable GAAP financial measures are provided in the accompanying tables.
About Gilead Sciences
Gilead Sciences, Inc. is a biopharmaceutical company that has pursued and achieved breakthroughs in medicine for more than three decades, with the goal of creating a healthier world for all people. The company is committed to advancing innovative medicines to prevent and treat life-threatening diseases, including HIV, viral hepatitis, COVID-19, cancer and inflammation. Gilead operates in more than 35 countries worldwide, with headquarters in Foster City, California.
Forward-Looking Statements
Statements included in this press release that are not historical in nature are forward-looking statements within the meaning of the Private Securities Litigation Reform Act of 1995. Gilead cautions readers that forward-looking statements are subject to certain risks and uncertainties that could cause actual results to differ materially. These risks and uncertainties include those relating to: Gilead’s ability to achieve its full year 2026 financial guidance, including as a result of the uncertainty of the amount and timing of Veklury revenues, the impact from Medicare Part D pricing reform in the Inflation Reduction Act, the expiration of subsidies related to the Affordable Care Act, our most-favored-nation pricing agreement with the U.S. government, changes in U.S. regulatory or legislative policies, and changes in U.S. trade policies, including tariffs; Gilead’s ability to make progress on any of its long-term ambitions or priorities laid out in its corporate strategy; Gilead’s ability to accelerate or sustain revenues for its virology, oncology, inflammation and other programs; Gilead’s ability to realize the potential benefits of acquisitions, collaborations or licensing arrangements, including the arrangements with Arcellx, Galapagos, Genhouse, Ouro, PEPFAR, The Global Fund, and Tubulis; the possibility that various closing conditions for any proposed acquisitions, collaborations or licensing arrangements may not be satisfied or waived, including that a governmental entity may prohibit, delay or refuse to grant approval for the consummation of any such transaction; the risk that Gilead’s U.S. manufacturing and R&D investment may not achieve their intended benefits; patent protection and estimated loss of exclusivity for our products and product candidates; Gilead’s ability to initiate, progress or complete clinical trials within currently anticipated timeframes or at all, the possibility of unfavorable results from ongoing and additional clinical trials, including those involving Tecartus, bictegravir, and lenacapavir, (such as ARTISTRY-1, ARTISTRY-2, and ZUMA-2), and the risk that safety and efficacy data from clinical trials may not warrant further development of Gilead’s product candidates or the product candidates of Gilead’s strategic partners; Gilead’s ability to resolve the issues cited by the FDA in pending clinical holds to the satisfaction of the FDA and the risk that FDA may not remove such clinical holds, in whole or in part, in a timely manner or at all; Gilead’s ability to submit new drug applications for new product candidates or expanded indications in the currently anticipated timelines; Gilead’s ability to receive or maintain regulatory approvals in a timely manner or at all, and the risk that any such approvals, if granted, may be subject to significant limitations on use and may be subject to withdrawal or other adverse actions by the applicable regulatory authority, including those involving BIC/LEN and anito-cel; Gilead’s ability to successfully commercialize its products; the risk of potential disruptions to the manufacturing and supply chain of Gilead’s products; pricing and reimbursement pressures from government agencies and other third parties, including required rebates and other discounts; a larger than anticipated shift in payer mix to more highly discounted payer segments; market share and price erosion caused by the introduction of generic versions of Gilead products; the risk that physicians and patients may not see advantages of Gilead’s products over other therapies and may therefore be reluctant to prescribe the products, including Tecartus; Gilead’s ability to effectively manage the access strategy relating to lenacapavir for HIV PrEP, subject to necessary regulatory approvals; and other risks identified from time to time in Gilead’s reports filed with the SEC, including annual reports on Form 10-K, quarterly reports on Form 10-Q and current reports on Form 8-K. In addition, Gilead makes estimates and judgments that affect the reported amounts of assets, liabilities, revenues and expenses and related disclosures. Gilead bases its estimates on historical experience and on various other market specific and other relevant assumptions that it believes to be reasonable under the circumstances, the results of which form the basis for making judgments about the carrying values of assets and liabilities that are not readily apparent from other sources. There may be other factors of which Gilead is not currently aware that may affect matters discussed in the forward-looking statements and may also cause actual results to differ significantly from these estimates. Further, results for the quarter ended March 31, 2026 are not necessarily indicative of operating results for any future periods. Gilead directs readers to its press releases, annual reports on Form 10-K, quarterly reports on Form 10-Q and other subsequent disclosure documents filed with the SEC. Gilead claims the protection of the Safe Harbor contained in the Private Securities Litigation Reform Act of 1995 for forward-looking statements.
The reader is cautioned that forward-looking statements are not guarantees of future performance and is cautioned not to place undue reliance on these forward-looking statements. All forward-looking statements are based on information currently available to Gilead and Gilead assumes no obligation to update or supplement any such forward-looking statements other than as required by law. Any forward-looking statements speak only as of the date hereof or as of the dates indicated in the statements.
Additional information is available on our Investor Relations website, https://investors.gilead.com. Among other things, an estimate of Acquired IPR&D expenses is expected to be made available on the Quarterly Results page within the first ten (10) days after the end of each quarter.
# # #
Gilead owns or has rights to various trademarks, copyrights and trade names used in its business, including the following: GILEAD®, GILEAD SCIENCES®, KITE®, AMBISOME®, ATRIPLA®, BIKTARVY®, CAYSTON®, COMPLERA®, DESCOVY®, DESCOVY FOR PREP®, EMTRIVA®, EPCLUSA®, EVIPLERA®, GENVOYA®, HARVONI®, HEPCLUDEX®, HEPSERA®, JYSELECA®, LIVDELZI®/LYVDELZI®, LETAIRIS®, ODEFSEY®, SOVALDI®, STRIBILD®, SUNLENCA®, TECARTUS®, TRODELVY®, TRUVADA®, TRUVADA FOR PREP®, TYBOST®, VEKLURY®, VEMLIDY®, VIREAD®, VOSEVI®, YESCARTA®, YEZTUGO®/YEYTUO® and ZYDELIG®. Other trademarks and trade names are the property of their respective owners.
For more information on Gilead Sciences, Inc., please visit www.gilead.com or call the Gilead Public Affairs Department at 1-800-GILEAD-5 (1-800-445-3235).
GILEAD SCIENCES, INC.
CONDENSED CONSOLIDATED STATEMENTS OF OPERATIONS
(unaudited)
Three Months Ended
March 31,
(in millions, except per share amounts)
2026
2025
Revenues:
Product sales
$
6,946
$
6,613
Royalty, contract and other revenues
14
54
Total revenues
6,960
6,667
Costs and expenses:
Cost of goods sold
1,445
1,540
Research and development expenses
1,372
1,379
Acquired in-process research and development expenses
107
253
Selling, general and administrative expenses
1,451
1,258
Total costs and expenses
4,374
4,430
Operating income
2,586
2,237
Interest expense
240
260
Other (income) expense, net
(235
)
328
Income before income taxes
2,580
1,649
Income tax expense
559
334
Net income
$
2,021
$
1,315
Basic earnings per share
$
1.63
$
1.06
Diluted earnings per share
$
1.61
$
1.04
Shares used in basic earnings per share calculation
1,242
1,246
Shares used in diluted earnings per share calculation
1,254
1,259
Supplemental Information:
Cash dividends declared per share
$
0.82
$
0.79
Product gross margin
79.2
%
76.7
%
Research and development expenses as a % of revenues
19.7
%
20.7
%
Selling, general and administrative expenses as a % of revenues
20.9
%
18.9
%
Operating margin
37.2
%
33.6
%
Effective tax rate
21.7
%
20.2
%
GILEAD SCIENCES, INC.
TOTAL REVENUE SUMMARY
(unaudited)
Three Months Ended
March 31,
(in millions, except percentages)
2026
2025
Change
Product sales:
HIV
$
5,030
$
4,587
10
%
Liver Disease
767
758
1
%
Oncology
810
757
7
%
Other
196
209
(6
)%
Total product sales excluding Veklury
6,802
6,311
8
%
Veklury
144
302
(52
)%
Total product sales
6,946
6,613
5
%
Royalty, contract and other revenues
14
54
(75
)%
Total revenues
$
6,960
$
6,667
4
%
GILEAD SCIENCES, INC.
NON-GAAP FINANCIAL INFORMATION(1)
(unaudited)
Three Months Ended
March 31,
(in millions, except percentages)
2026
2025
Change
Non-GAAP:
Cost of goods sold
$
869
$
961
(10
)%
Research and development expenses
$
1,355
$
1,338
1
%
Acquired IPR&D expenses
$
107
$
253
(58
)%
Selling, general and administrative expenses
$
1,363
$
1,222
12
%
Other (income) expense, net
$
(92
)
$
(98
)
(6
)%
Diluted earnings per share
$
2.03
$
1.81
12
%
Shares used in non-GAAP diluted earnings per share calculation
1,254
1,259
—
%
Product gross margin
87.5
%
85.5
%
202 bps
Research and development expenses as a % of revenues
19.5
%
20.1
%
-61 bps
Selling, general and administrative expenses as a % of revenues
19.6
%
18.3
%
126 bps
Operating margin
46.9
%
43.4
%
356 bps
Effective tax rate
18.3
%
16.3
%
195 bps
________________________________
(1)
Refer to Non-GAAP Financial Information section above for further disclosures on non-GAAP financial measures. A reconciliation between GAAP and non-GAAP financial information is provided in the tables below.
GILEAD SCIENCES, INC.
RECONCILIATION OF GAAP TO NON-GAAP FINANCIAL INFORMATION
(unaudited)
Three Months Ended
March 31,
(in millions, except percentages and per share amounts)
2026
2025
Cost of goods sold reconciliation:
GAAP cost of goods sold
$
1,445
$
1,540
Acquisition-related – amortization(1)
(576
)
(579
)
Restructuring
(1
)
—
Non-GAAP cost of goods sold
$
869
$
961
Product gross margin reconciliation:
GAAP product gross margin
79.2
%
76.7
%
Acquisition-related – amortization(1)
8.3
%
8.8
%
Restructuring
—
%
—
%
Non-GAAP product gross margin
87.5
%
85.5
%
Research and development expenses reconciliation:
GAAP research and development expenses
$
1,372
$
1,379
Acquisition-related – other costs(2)
(3
)
(2
)
Restructuring
(14
)
(38
)
Non-GAAP research and development expenses
$
1,355
$
1,338
Selling, general and administrative expenses reconciliation:
GAAP selling, general and administrative expenses
$
1,451
$
1,258
Restructuring
(25
)
(36
)
Other(3)
(63
)
—
Non-GAAP selling, general and administrative expenses
$
1,363
$
1,222
Operating income reconciliation:
GAAP operating income
$
2,586
$
2,237
Acquisition-related – amortization(1)
576
579
Acquisition-related – other costs(2)
3
2
Restructuring
40
74
Other(3)
63
—
Non-GAAP operating income
$
3,267
$
2,893
Operating margin reconciliation:
GAAP operating margin
37.2
%
33.6
%
Acquisition-related – amortization(1)
8.3
%
8.7
%
Acquisition-related – other costs(2)
—
%
—
%
Restructuring
0.6
%
1.1
%
Other(3)
0.9
%
—
%
Non-GAAP operating margin
46.9
%
43.4
%
Other (income) expense, net reconciliation:
GAAP other (income) expense, net
$
(235
)
$
328
Gain (loss) from equity securities, net
142
(426
)
Non-GAAP other (income) expense, net
$
(92
)
$
(98
)
Income before income taxes reconciliation:
GAAP income before income taxes
$
2,580
$
1,649
Acquisition-related – amortization(1)
576
579
Acquisition-related – other costs(2)
3
2
Restructuring
40
74
(Gain) loss from equity securities, net
(142
)
426
Other(3)
63
—
Non-GAAP income before income taxes
$
3,119
$
2,731
GILEAD SCIENCES, INC.
RECONCILIATION OF GAAP TO NON-GAAP FINANCIAL INFORMATION - (Continued)
(unaudited)
Three Months Ended
March 31,
(in millions, except percentages and per share amounts)
2026
2025
Income tax expense reconciliation:
GAAP income tax expense
$
559
$
334
Income tax effect of non-GAAP adjustments:
Acquisition-related – amortization(1)
118
120
Acquisition-related – other costs(2)
—
—
Restructuring
6
14
(Gain) loss from equity securities, net
(66
)
20
Discrete and related tax charges(4)
(46
)
(42
)
Non-GAAP income tax expense
$
570
$
446
Effective tax rate reconciliation:
GAAP effective tax rate
21.7
%
20.2
%
Income tax effect of above non-GAAP adjustments and discrete and related tax adjustments(4)
(3.4
)%
(3.9
)%
Non-GAAP effective tax rate
18.3
%
16.3
%
Net income reconciliation:
GAAP net income
$
2,021
$
1,315
Acquisition-related – amortization(1)
458
459
Acquisition-related – other costs(2)
3
2
Restructuring
34
61
(Gain) loss from equity securities, net
(77
)
406
Discrete and related tax charges(4)
46
42
Other(3)
63
—
Non-GAAP net (loss) income
$
2,549
$
2,285
Diluted earnings per share reconciliation:
GAAP diluted earnings per share
$
1.61
$
1.04
Acquisition-related – amortization(1)
0.37
0.36
Acquisition-related – other costs(2)
—
—
Restructuring
0.03
0.05
(Gain) loss from equity securities, net
(0.06
)
0.32
Discrete and related tax charges(4)
0.04
0.03
Other(3)
0.05
—
Non-GAAP diluted earnings per share
$
2.03
$
1.81
Non-GAAP adjustment summary:
Cost of goods sold adjustments
$
576
$
579
Research and development expenses adjustments
17
40
Selling, general and administrative expenses adjustments
88
36
Total non-GAAP adjustments to costs and expenses
681
656
Other (income) expense, net, adjustments
(142
)
426
Total non-GAAP adjustments before income taxes
539
1,082
Income tax effect of non-GAAP adjustments above
(58
)
(154
)
Discrete and related tax charges(4)
46
42
Total non-GAAP adjustments to net income
$
528
$
970
________________________________
(1)
Relates to amortization of acquired intangibles.
(2)
Adjustments include integration expenses and contingent consideration fair value adjustments associated with Gilead’s recent acquisitions.
(3)
Adjustments include donations of equity securities to the Gilead Foundation, a California nonprofit organization, during the first quarter of 2026.
(4)
Represents discrete and related deferred tax charges or benefits primarily associated with transfers of intangible assets from a foreign subsidiary to Ireland and the United States.
GILEAD SCIENCES, INC.
RECONCILIATION OF GAAP TO NON-GAAP 2026 FULL-YEAR GUIDANCE(1)
(unaudited)
(in millions, except percentages and per share amounts)
Provided February 10, 2026
Updated May 7, 2026
Projected product gross margin GAAP to non-GAAP reconciliation:
GAAP projected product gross margin
~ 79.0%
~ 79.0%
Acquisition-related expenses
~ 8.0%
~ 8.0%
Non-GAAP projected product gross margin
~ 87.0%
~ 87.0%
Projected operating income (loss) GAAP to non-GAAP reconciliation:
GAAP projected operating income (loss)
$11,400 - $11,900
$(1,000) - $(500)
Acquisition-related, restructuring and other expenses
~ 2,400
~ 3,400
Non-GAAP projected operating income
$13,800 - $14,300
$2,400 - $2,900
Projected effective tax rate GAAP to non-GAAP reconciliation:(2)
GAAP projected effective tax rate
~ 21%
~ (150%) - (220%)
Income tax effect of above non-GAAP adjustments and fair value adjustments of equity securities, and discrete and related tax adjustments
(~ 1%)
NM
Non-GAAP projected effective tax rate
~ 20%
~ 190% - 140%
Projected diluted earnings (loss) per share GAAP to non-GAAP reconciliation:
GAAP projected diluted earnings (loss) per share
$6.75 - $7.15
$(3.25) - $(2.85)
Acquisition-related, restructuring and other expenses, fair value adjustments of equity securities and discrete and related tax adjustments
~ 1.70
~ $2.20
Non-GAAP projected diluted earnings (loss) per share
$8.45 - $8.85
$(1.05) - $(0.65)
________________________________
NM - Not Meaningful
(1)
Our full-year guidance excludes the potential impact of any (i) acquisitions or business development transactions that have not been executed, (ii) future fair value adjustments of equity securities and (iii) discrete tax charges or benefits associated with changes in tax related laws and guidelines that have not been enacted, as Gilead is unable to project such amounts. The non-GAAP full-year guidance includes non-GAAP adjustments to actual current period results as well as adjustments for the known future impact associated with events that have already occurred, such as future amortization of our intangible assets and the future impact of discrete and related deferred tax charges or benefits primarily associated with transfers of intangible assets from a foreign subsidiary to Ireland and the United States.
(2)
The GAAP and non-GAAP projected effective tax rates for the May 7, 2026 guidance update include the impact of forecasted Acquired IPR&D expenses related to the acquisitions of Arcellx, Ouro and Tubulis, which are not deductible for tax purposes. Without these Acquired IPR&D expenses, the GAAP and non-GAAP projected effective tax rate for FY26 would be ~22% and ~20%, respectively.
GILEAD SCIENCES, INC.
CONDENSED CONSOLIDATED BALANCE SHEETS
(unaudited)
March 31,
December 31,
(in millions)
2026
2025
Assets
Cash, cash equivalents and marketable debt securities
$
8,625
$
10,605
Accounts receivable, net
4,741
4,913
Inventories(1)
4,339
4,368
Property, plant and equipment, net
5,638
5,606
Intangible assets, net
16,382
16,978
Goodwill
8,314
8,314
Other assets
8,239
8,239
Total assets
$
56,278
$
59,023
Liabilities and Stockholders’ Equity
Current liabilities
$
9,476
$
11,813
Long-term liabilities
23,371
24,592
Stockholders’ equity(2)
23,431
22,618
Total liabilities and stockholders’ equity
$
56,278
$
59,023
________________________________
(1)
Includes current and long-term inventories, which are disclosed separately in the notes to our financial statements in Form 10-K and Form 10-Q.
(2)
As of March 31, 2026 and December 31, 2025, there were 1,242 and 1,241 shares of common stock issued and outstanding, respectively.
GILEAD SCIENCES, INC.
SELECTED CASH FLOW INFORMATION
(unaudited)
Three Months Ended
March 31,
(in millions)
2026
2025
Net cash provided by operating activities
$
2,544
$
1,757
Net cash provided by (used in) investing activities
1,770
(415
)
Net cash used in financing activities
(4,239
)
(3,426
)
Effect of exchange rate changes on cash and cash equivalents
(11
)
19
Net change in cash and cash equivalents
65
(2,065
)
Cash and cash equivalents at beginning of period
7,564
9,991
Cash and cash equivalents at end of period
$
7,628
$
7,926
Three Months Ended
March 31,
(in millions)
2026
2025
Net cash provided by operating activities
$
2,544
$
1,757
Purchases of property, plant and equipment
(117
)
(104
)
Free cash flow(1)
$
2,427
$
1,653
________________________________
(1)
Free cash flow is a non-GAAP liquidity measure. Please refer to our disclosures in the Non-GAAP Financial Information section above.
GILEAD SCIENCES, INC.
PRODUCT SALES SUMMARY
(unaudited)
Three Months Ended
March 31,
(in millions)
2026
2025
HIV
Biktarvy
U.S.
$
2,573
$
2,474
Europe
437
375
Rest of World
352
301
3,361
3,150
Descovy
U.S.
761
538
Europe
23
21
Rest of World
23
27
807
586
Genvoya
U.S.
215
305
Europe
33
40
Rest of World
16
19
264
364
Odefsey
U.S.
153
215
Europe
59
57
Rest of World
9
10
221
281
Symtuza - Revenue share(1)
U.S.
107
82
Europe
28
29
Rest of World
3
3
138
114
Yeztugo
U.S.
158
—
Europe
—
—
Rest of World
7
—
166
—
Other HIV(2)
U.S.
36
50
Europe
27
31
Rest of World
9
10
73
91
Total HIV
U.S.
4,004
3,664
Europe
607
553
Rest of World
419
370
5,030
4,587
GILEAD SCIENCES, INC.
PRODUCT SALES SUMMARY - (Continued)
(unaudited)
Three Months Ended
March 31,
(in millions)
2026
2025
Liver Disease
Livdelzi
U.S.
115
40
Europe
18
—
Rest of World
—
—
133
40
Sofosbuvir / Velpatasvir(3)
U.S.
141
166
Europe
60
80
Rest of World
82
99
283
346
Vemlidy
U.S.
91
100
Europe
13
12
Rest of World
132
140
237
252
Other Liver Disease(4)
U.S.
15
28
Europe
78
76
Rest of World
21
17
114
121
Total Liver Disease
U.S.
362
335
Europe
170
168
Rest of World
235
256
767
758
Veklury
Veklury
U.S.
112
199
Europe
14
22
Rest of World
18
82
144
302
Oncology
Cell Therapy
Tecartus
U.S.
30
40
Europe
37
31
Rest of World
8
8
75
78
Yescarta
U.S.
120
160
Europe
146
149
Rest of World
67
77
332
386
Total Cell Therapy
U.S.
150
200
Europe
183
180
Rest of World
74
84
407
464
Trodelvy
Trodelvy
U.S.
253
181
Europe
95
75
Rest of World
54
37
402
293
Total Oncology
U.S.
403
381
Europe
278
255
Rest of World
129
121
810
757
GILEAD SCIENCES, INC.
PRODUCT SALES SUMMARY - (Continued)
(unaudited)
Three Months Ended
March 31,
(in millions)
2026
2025
Other
AmBisome
U.S.
7
5
Europe
59
67
Rest of World
72
66
138
139
Other(5)
U.S.
39
47
Europe
8
9
Rest of World
11
14
58
70
Total Other
U.S.
46
52
Europe
67
76
Rest of World
83
81
196
209
Total product sales
U.S.
4,926
4,631
Europe
1,137
1,073
Rest of World
883
909
$
6,946
$
6,613
________________________________
(1)
Represents Gilead’s revenue from cobicistat (“C”), FTC and TAF in Symtuza (darunavir/C/FTC/TAF), a fixed dose combination product commercialized by Janssen Sciences Ireland Unlimited Company.
(2)
Includes Atripla, Complera/Eviplera, Emtriva, Stribild, Sunlenca, Truvada and Tybost.
(3)
Includes Epclusa and the authorized generic version of Epclusa sold by Gilead’s separate subsidiary, Asegua Therapeutics LLC (“Asegua”).
(4)
Includes ledipasvir/sofosbuvir (Harvoni and the authorized generic version of Harvoni sold by Asegua), Hepcludex, Hepsera, Sovaldi, Viread and Vosevi.
(5)
Includes Cayston, Jyseleca, Letairis and Zydelig.
Investors: Jacquie Ross, CFA investor_relations@gilead.com Media: Ashleigh Koss public_affairs@gilead.com
上市批准财报并购临床结果加速审批
2026-04-26
人工智能时代的药物靶点识别与评估
Target identification and assessment in the era of AI
论文基础发表信息
项目
核心信息
发表期刊
《自然综述:药物发现》(Nature Reviews Drug Discovery)
在线发表时间
2026年4月20日
录用时间
2026年2月25日
正式版本发布时间
2026年4月20日
永久数字对象标识符(DOI)
10.1038/s41573-026-01412-8
通讯作者
Alex Zhavoronkov
第一作者
Frank W. Pun
核心完成单位
英矽智能(Insilico Medicine)
作者与所属单位
Frank W. Pun¹, Dmitriy Podolskiy², Evgeny Izumchenko³, Andrew Mortlock⁴, Tudor I. Oprea⁵, Morten Scheibye-Knudsen⁶, Kristen Fortney⁷, Eric Morgen⁷, Feng Ren¹,⁸, Alex Zhavoronkov¹,⁸,⁹,¹⁰,¹¹
1.英矽智能香港有限公司,中国香港特别行政区
2.安斯泰来制药再生医学研究所,美国马萨诸塞州韦斯特伯勒市
3.芝加哥大学医学院血液学与肿瘤学系,美国伊利诺伊州芝加哥市
4.安斯泰来制药欧洲总部有限公司,英国阿德尔斯特恩市
5.Expert Systems Inc.,美国加利福尼亚州圣地亚哥市
6.哥本哈根大学细胞与分子医学系健康衰老研究中心,丹麦哥本哈根市
7.BioAge Labs,美国加利福尼亚州埃默里维尔市
8.英矽智能上海有限公司,中国上海市
9.英矽智能人工智能有限公司,阿联酋阿布扎比马斯达尔城
10.英矽智能美国有限公司,美国马萨诸塞州剑桥市
11.巴克衰老研究所,美国加利福尼亚州诺瓦托市
摘要
靶点识别与验证是创新药物研发的起点,也是决定临床转化成功率的核心环节。传统靶点发现模式高度依赖科研人员的经验积累与偶然性发现,存在研发周期长、转化失败率高、可成药靶点空间受限等核心瓶颈。近年来,人工智能(AI)技术的快速发展彻底重塑了靶点发现的底层逻辑,将原本经验驱动的随机化探索,转变为数据驱动的系统化、可预测化精准科学。
本综述系统梳理了AI时代药物靶点选择的核心评估框架,详细阐述了支撑靶点识别的多模态生物数据整合体系,全面拆解了从靶点预测、优先级排序到机制验证的全栈AI算法技术架构,并结合已进入临床阶段的管线案例,验证了AI驱动靶点发现全链路的可行性。最后,本综述总结了当前领域面临的核心挑战,并提出了未来的关键发展方向,为AI技术在药物靶点发现领域的落地应用与前沿探索提供了纲领性指导。
引言
在现代药物研发体系中,药物靶点是指能够被药物分子调控,进而干预疾病发生发展进程的生物分子(绝大多数为蛋白质)。能否筛选出兼具治疗有效性、成药性、安全性与商业价值的优质靶点,直接决定了一款创新药物从早期研发到最终上市的全生命周期成功率。
过去数十年间,人类基因组学、分子生物学与系统生物学的发展,为药物靶点发现奠定了坚实的科学基础。然而,行业仍面临着难以突破的效率瓶颈:人类基因组中约2万个蛋白编码基因里,仅有约4500个被认定具备成药潜力,而全球已获批的所有药物,仅作用于716个不同的人类靶点。传统靶点发现模式依赖于低通量的实验验证与科研人员的经验判断,一个全新靶点从提出治疗假设到完成临床前验证,往往需要数月甚至数十年的时间,且超过90%的候选靶点最终会在临床研发阶段因疗效不足或安全性问题宣告失败。
近年来,以机器学习、深度学习、生成式AI与大语言模型为代表的人工智能技术,在生物医药大数据处理、复杂生物机制解析、因果关系推断等方面展现出了前所未有的能力。AI技术能够整合多维度的生物医学数据,挖掘传统方法无法识别的疾病-靶点关联,实现靶点的高通量筛选、优先级排序与成药性评估,大幅缩短靶点发现周期,提升临床转化成功率。本综述将系统阐述AI时代药物靶点识别与评估的完整体系,为行业提供全面的技术框架与实践指导。
1 优质药物靶点选择的四大核心评估维度
本综述首次在AI技术框架下,系统性明确了创新药物靶点筛选与评估的四大核心维度。四大维度环环相扣,共同决定了靶点从早期发现到临床上市的全生命周期价值与成功率。
1.1 治疗假设的科学性与因果性
治疗假设是靶点成立的底层核心逻辑,必须清晰阐明“靶点调控如何影响疾病生物学进程”的完整分子机制与因果链条。与传统经验式的靶点筛选不同,AI时代的治疗假设构建,高度依赖人类遗传学证据、多组学数据与因果推断算法的支撑。
人类遗传学证据是靶点治疗假设最坚实的基础,已有研究证实,具备人类遗传学证据支持的药物靶点,其临床获批成功率是无遗传学证据靶点的2倍(原理:若某疾病相关基因变异,直接关联发病机制,以此基因为药物靶点,作用机制更精准、贴合疾病本质)。AI技术能够通过全基因组关联研究(GWAS)、表达数量性状位点(eQTL)分析、孟德尔随机化等方法,从海量基因组数据中挖掘疾病与靶点之间的因果关联,而非单纯的相关性,为治疗假设提供严谨的科学支撑。
全基因组关联研究( GWAS )、表达数量性状位点( eQTL )分析、孟德尔随机化1. 全基因组关联研究(GWAS)
核心:在全基因组范围,大规模比对病例 / 对照或不同性状人群的基因变异(SNP 等),目的:筛选与疾病、身高、代谢等复杂性状显著关联的遗传位点,局限:多为「相关性」,位点大多非功能基因,难解释致病机制。2. 表达数量性状位点(eQTL)分析
核心:关联基因遗传变异与基因表达量,目的:找到能调控基因转录水平的遗传位点,价值:打通「遗传变异→基因表达→性状 / 疾病」的中间环节,解释 GWAS 位点的功能机制。3. 孟德尔随机化(MR)
核心:以遗传变异为工具变量,利用基因随机分配的自然随机试验特性,目的:在观察性数据中,排除混杂、反向因果,推断暴露因素与疾病的因果关系,优势:弥补观察研究短板,低成本验证因果,衔接遗传 - 表型 - 疾病因果链。
三者串联逻辑:GWAS 找疾病相关遗传位点 → eQTL 解释位点如何影响基因表达 → MR 验证「分子 / 表型因素」是否真正导致疾病。
1.2 成药性与安全性
成药性与安全性是靶点实现临床转化的核心门槛。成药性评估的核心,是判断靶点是否具备可被药物分子有效结合并调控的结构基础,同时需评估不同药物 modality(小分子、抗体、反义寡核苷酸、mRNA、细胞治疗等)对靶点的可及性。
近年来,以AlphaFold为代表的蛋白质结构预测技术,彻底革新了靶点成药性评估的模式。AI技术能够精准预测靶点蛋白的三维结构、结合口袋与构象变化,实现对靶点可成药性的高通量预测,同时还能预判靶点的脱靶风险、组织分布特异性与潜在不良反应,为靶点的安全性评估提供全面的量化依据。
1.3 商业可行性
商业可行性评估的核心,是在靶点的研发风险与商业回报之间实现平衡。研发人员需权衡两类核心靶点的选择策略:一类是首创(first-in-class)靶点,即尚未有药物获批的全新靶点,具备突破性的临床价值与市场先发优势,但同时也伴随着更高的研发与转化风险;另一类是同类最优(best-in-class)靶点,即已有药物验证的成熟靶点,研发确定性更高,但需要面对激烈的市场竞争,需通过差异化的药物设计实现临床优势。
AI技术能够通过对科研文献、专利数据、临床试验进展、监管审批信息与市场格局的多维度分析,全面评估靶点的竞争格局、专利生命周期、临床未满足需求与商业回报潜力,为靶点的商业可行性决策提供数据支撑。
1.4 联合治疗与组合价值
联合治疗是当前复杂疾病治疗的核心发展方向,靶点的组合价值,已成为差异化竞争与提升临床获益的关键因素。靶点的组合价值评估,主要包括两个核心方向:一是与现有标准治疗方案的协同增效潜力,二是针对耐药机制的联合用药策略。
在肿瘤、纤维化、神经退行性疾病等复杂疾病领域,单一靶点调控往往难以实现理想的治疗效果,且易引发耐药性。AI技术能够通过生物网络分析、图神经网络与因果推断算法,预测靶点之间的合成致死性、协同调控作用与信号通路交叉影响,挖掘具备高临床价值的靶点组合,为联合治疗方案的开发提供科学依据。
评估维度
核心评估内容
AI技术的核心赋能价值
治疗假设
靶点-疾病的因果关联、分子机制清晰度、遗传学证据支撑
基于多组学数据与因果推断算法,挖掘疾病核心驱动因子,构建可验证的治疗假设
成药性与安全性
靶点结构可成药性、药物可及性、脱靶风险、潜在不良反应
基于蛋白质结构预测与深度学习模型,实现成药性与安全性的高通量、量化评估
商业可行性
临床未满足需求、竞争格局、专利生命周期、商业回报潜力
基于文本挖掘与大语言模型,整合文献、专利、临床与市场数据,实现商业价值的全景评估
组合价值
与现有疗法的协同性、耐药逆转潜力、联合用药临床价值
基于生物网络与图神经网络,预测靶点互作与协同效应,挖掘高价值靶点组合
2 AI驱动靶点识别的多模态数据整合体系
AI技术在靶点发现领域的核心价值,源于其对复杂多模态生物医学数据的超强处理与解析能力。通过对多维度、异质性生物数据的整合与融合,AI技术能够弥合分子活性与临床终点之间的鸿沟,挖掘传统方法无法识别的全新靶点。本章节系统梳理了支撑AI靶点识别的核心数据类型与应用模式。
2.1 多组学数据
多组学数据是AI靶点识别最核心的数据基础,涵盖基因组学、转录组学、蛋白质组学、代谢组学与表观遗传学等多个维度。多组学数据能够完整描绘疾病状态下的分子图谱变化,揭示疾病的核心驱动基因与通路。
AI技术能够对海量多组学数据进行整合分析,识别疾病相关的基因变异、差异表达基因、表观修饰变化与代谢异常,同时通过因果推断算法,区分疾病的“驱动因素”与“伴随现象”,锁定真正的疾病核心驱动靶点。目前,已有多款基于多组学的AI靶点发现平台实现了产业化应用,其中最具代表性的是英矽智能开发的PandaOmics平台,该平台已在多个疾病领域实现了全新靶点的发现与临床验证。
2.2 高内涵细胞成像数据
细胞成像数据能够直观反映细胞与细胞器的形态变化、表型特征与空间分布信息,是表型驱动靶点发现的核心数据来源。基于高内涵筛选的细胞表型成像,能够捕捉基因扰动或药物处理后细胞的细微表型变化,而这些变化往往与疾病的核心机制密切相关。
以卷积神经网络(CNN)为核心的深度学习技术,能够对海量细胞成像数据进行自动化、高通量的分析,精准识别细胞线粒体形态、细胞骨架结构、细胞核形态等细微的表型差异,通过表型-基因型关联分析,反向锁定调控疾病表型的核心靶点。目前,AI图像分析技术已在肠道纤维化、肌萎缩侧索硬化症(ALS)等疾病的靶点发现中实现了成功应用。
2.3 生物知识图谱与真实世界临床数据
生物知识图谱是整合了基因、蛋白、通路、疾病、药物等生物实体之间互作关系的结构化网络数据库,核心包括:
STRING、BioGRID、IntAct等蛋白互作数据库,
KEGG、Reactome等通路数据库,
以及DisGeNET、Open Targets等疾病-基因关联数据库。
图神经网络(GNN)技术能够基于知识图谱的固有网络结构,预测全新的生物实体相互作用、合成致死性与疾病-靶点关联,同时整合电子健康记录、临床试验数据等真实世界临床数据,搭建起基础研究与临床转化之间的桥梁,实现对靶点临床转化潜力的精准预判。
2.4 非结构化文本数据
生物医药领域的海量非结构化文本数据,包括科研文献、专利、临床试验报告、监管审批文件、科研经费数据等,蕴含了丰富的靶点相关信息,是验证靶点科学有效性、评估竞争格局与商业价值的核心资源。
以生物医药领域大语言模型为核心的自然语言处理(NLP)技术,能够对海量非结构化文本数据进行深度挖掘,提取基因-疾病关联、靶点作用机制、研究趋势与竞争格局等关键信息,同时能够模仿人类科研人员的推理逻辑,自主生成治疗假设,实现靶点发现的全流程智能化。
2.5 多模态数据的协同整合
当前AI靶点发现领域的核心发展趋势,是通过异构知识图谱、统一数据仓库与多模态深度学习架构,实现不同类型数据的协同整合与融合分析。多模态数据的整合,能够实现不同维度数据之间的交叉验证与信息互补,大幅提升靶点预测的准确性与可靠性,是AI靶点识别技术未来发展的核心基础。
3 靶点发现与评估的全栈AI算法框架
本综述系统性梳理了支撑现代AI靶点识别与评估的全栈算法技术体系,明确了不同技术路线的核心定位、应用场景与技术优势,形成了从靶点预测、优先级排序到机制验证的完整技术闭环。
3.1 监督学习算法
监督学习是当前AI靶点发现领域应用最广泛、技术最成熟的核心算法体系。该类算法基于已标注的药物-靶点配对、疾病-基因关联、靶点成药性等标注数据进行训练,实现对全新靶点的预测与优先级排序。
监督学习算法的核心应用场景包括:药物-靶点相互作用预测、疾病相关基因优先级排序、靶点成药性与安全性预测。代表性的技术成果包括英矽智能开发的PandaOmics靶点识别引擎、GeroScope衰老相关靶点挖掘算法、TargetPro临床阶段靶点特征学习模型,这些算法已在多个疾病领域实现了全新靶点的成功发现与验证。
3.2 无监督与半监督学习算法
无监督与半监督学习算法,是挖掘全新未知靶点的核心工具。该类算法能够在无标注或仅有部分标注数据的情况下,从海量生物数据中识别隐藏的疾病相关分子特征、基因网络模块与蛋白互作模式,突破标注数据不足的限制。
其核心应用场景包括:基因共表达网络中疾病相关模块识别、蛋白-蛋白相互作用特征提取、候选靶点成药性聚类分析与异常基因识别。在肿瘤、罕见病等标注数据稀缺的疾病领域,无监督与半监督学习算法展现出了独特的优势,能够挖掘传统监督学习方法无法识别的全新靶点。
3.3 深度学习与生物表示学习
表示学习是现代深度学习技术的核心,其能够将氨基酸序列、基因表达谱、蛋白质结构、细胞图像等各类生物实体,编码为高维数值嵌入向量,捕捉其上下文相关的生物学特性与功能信息,是AI解析复杂生物语义的核心底座。
其中,图神经网络(GNN) 是当前生物医学领域应用最广泛的深度学习架构之一。该类算法能够天然适配生物网络的图结构特征,精准捕捉基因、蛋白、疾病等实体之间的相互作用关系,预测多基因协同调控、合成致死性与疾病表型逆转的靶点组合,已成为靶点发现与网络药理学研究的核心工具。
3.4 生成式AI与生命科学基础模型
生成式AI与生命科学基础模型,是当前AI靶点发现领域最前沿的突破方向。该类模型基于数千万级的单细胞转录组、蛋白质序列、基因组等大规模生物数据进行预训练,能够精准捕捉基因调控网络的动态变化,模拟细胞对基因干扰的反应,高准确度锁定疾病的核心驱动因子。
代表性的生命科学基础模型包括:Geneformer、scGPT等单细胞预训练模型,以及英矽智能开发的PreciousGPT系列模型。其中,PreciousGPT系列模型不仅能够实现靶点的精准预测,还能够生成合成多组学数据,突破真实生物数据稀缺、隐私保护受限等行业瓶颈,为AI靶点发现模型的训练与优化提供了全新的数据来源。
3.5 生物医药大语言模型与AI智能体
以BioGPT、OriGene为代表的生物医药领域大语言模型,能够充当“虚拟生物学家”,模仿人类科研人员的完整科研推理逻辑。这类模型基于海量生物医药文献、专利、数据库信息进行预训练,能够自主完成文献挖掘、治疗假设生成、靶点优先级排序、实验方案设计等一系列靶点发现的核心步骤,实现靶点发现全流程的自动化与智能化。
当前,生物医药AI智能体的发展已进入全新阶段,其能够整合多模态数据处理、AI模型预测、自动化机器人实验验证等多个环节,形成“靶点预测-实验验证-数据反馈-模型优化”的完整闭环,是未来药物研发全流程智能化的核心载体。
4 AI靶点识别技术的临床转化验证案例
本综述以英矽智能的特发性肺纤维化(IPF)管线为核心临床证据,完整验证了AI驱动靶点识别技术从靶点发现、分子设计到临床转化的全链路可行性。该项目是全球首个由AI发现全新靶点、并设计全新小分子药物,成功推进至临床阶段的创新药项目,为AI驱动药物研发提供了里程碑式的实践范例。
4.1 靶点识别与验证
特发性肺纤维化是一种进展性、致死性的间质性肺疾病,患者确诊后的中位生存期仅2-3年,临床存在巨大的未满足治疗需求。研究团队通过英矽智能的PandaOmics AI靶点发现引擎,整合了IPF患者的多组学数据、单细胞测序数据、科研文献与知识图谱信息,通过深度学习算法与因果推断分析,最终锁定TNIK(TRAF2和NCK相互作用激酶) 为IPF的全新治疗靶点。
后续的体内外实验验证证实,TNIK是肺纤维化进程的核心驱动因子,抑制TNIK能够显著下调纤维化相关信号通路,改善肺组织纤维化病理表型,为治疗假设提供了充分的实验证据。
4.2 药物分子设计与临床前研发
在锁定TNIK靶点后,研究团队通过英矽智能的Chemistry42生成式化学AI平台,快速设计出了全球首创的高选择性、高活性小分子TNIK抑制剂——Rentosertib(研发代号:ISM001-055)。
该项目从靶点识别启动,到完成临床前候选化合物(PCC)的筛选与验证,仅耗时约18个月,研发成本远低于传统药物研发模式,大幅缩短了创新药的早期研发周期。
4.3 临床试验结果
Rentosertib已成功完成IIa期临床试验,研究结果证实,该药物在IPF患者中展现出良好的安全性与耐受性,且能够剂量依赖性地改善患者的用力肺活量(FVC)——这是IPF临床研发的核心疗效终点,也是评估抗纤维化药物临床获益的金标准。
该临床试验的成功,首次在人体中验证了AI发现的全新靶点的临床有效性,标志着AI驱动药物研发从技术概念,真正走向了临床转化的落地实践。
除IPF管线外,基于AI技术发现的靶点,目前已在肌萎缩侧索硬化症(ALS)、肿瘤、衰老相关疾病、子宫内膜异位症等多个疾病领域进入了临床前或临床研发阶段,充分证实了AI靶点识别技术的通用性与广泛应用前景。
5 领域现存挑战与未来发展方向
尽管AI技术在靶点识别与评估领域已取得了里程碑式的突破,但行业仍面临着一系列亟待解决的核心挑战。本综述在结尾系统梳理了当前领域的核心痛点,并提出了未来的关键发展方向,其终极目标是构建AI驱动的全自动化、闭环式药物研发平台。
5.1 领域现存核心挑战
1.高质量生物数据的稀缺与标准化问题:AI模型的性能高度依赖训练数据的质量与规模,而当前生物医药领域的多组学数据、临床数据存在样本量不足、异质性高、标准化程度低、数据孤岛严重等问题,同时还面临着严格的患者隐私保护限制,制约了AI模型的训练与优化。
2.AI模型的可解释性不足:当前多数深度学习模型属于“黑箱模型”,能够准确预测靶点与疾病的关联,但难以清晰阐明其背后的生物学机制,而机制的清晰度是靶点临床转化的核心前提,可解释性AI已成为领域亟待突破的关键方向。
3.行业缺乏统一的基准测试与评估框架:当前不同AI靶点发现模型的性能评估,缺乏统一的数据集、评价指标与验证标准,导致不同模型之间的性能难以进行客观对比,制约了技术的标准化发展与产业化落地。
4.计算预测与湿实验验证的脱节:当前多数AI靶点发现研究仍停留在计算预测层面,缺乏系统的实验验证与临床转化,如何实现AI预测与自动化实验平台的深度融合,形成完整的验证闭环,是行业面临的核心工程挑战。
5.2 未来核心发展方向
1.数据质量与可及性的提升:通过合成生物数据、联邦学习、隐私计算等技术,突破真实数据稀缺与隐私保护的限制,同时推动生物医药数据的标准化与共享体系建设,为AI模型的发展提供高质量的数据底座。
2.可解释性AI与生物学知情模型的开发:开发融合先验生物学知识的可解释性AI模型,让模型的预测结果能够对应清晰的生物学机制,实现“预测-机制解析-实验验证”的一体化,提升靶点预测的可靠性与临床转化成功率。
3.生命科学基础模型与数字孪生技术的规模化应用:基于大规模生物数据预训练的生命科学基础模型,能够实现对细胞、组织乃至器官的数字化孪生模拟,精准预测基因扰动对疾病表型的影响,为靶点发现提供全新的研究范式。
4.AI驱动的闭环式药物研发平台构建:整合AI靶点发现、生成式化学分子设计、自动化机器人湿实验验证、临床试验设计与数据分析等全链条环节,构建“计算预测-实验验证-数据反馈-模型迭代优化”的完整闭环,实现创新药物研发的全流程智能化、自动化,大幅提升研发效率,降低研发成本,最终让更多创新疗法更快惠及患者。
致谢
作者感谢英矽智能团队的J. Chen、X. Long、Y. Xin、B. H. M. Liu与H. Leung为本论文撰写提供的协助。Dmitriy Podolskiy同时感谢K. Tabata与S. Penrose提供的相关学术讨论支持。
作者贡献
Frank W. Pun与Alex Zhavoronkov完成了本研究的概念设计与项目统筹。所有作者均为本论文内容的学术讨论、撰写、审阅与修改做出了实质性贡献。
利益冲突声明
Frank W. Pun、Feng Ren与Alex Zhavoronkov任职于英矽智能——一家致力于开发并应用生成式人工智能及其他新一代AI技术与机器人平台,开展药物发现、研发与衰老相关研究的商业公司。Dmitriy Podolskiy为安斯泰来制药在职员工。Andrew Mortlock为安斯泰来制药欧洲总部在职员工。Tudor I. Oprea为Expert Systems Inc.在职员工。Kristen Fortney与Eric Morgen为BioAge Labs, Inc.在职员工。其余作者声明无相关利益冲突。
同行评审信息
《自然综述:药物发现》期刊感谢G. Doron、H. Fröhlich、S. Khader与N. Richmond为本论文同行评审工作做出的贡献。
出版说明
施普林格·自然(Springer Nature)对于已发表地图中的管辖权声明与机构隶属关系,保持中立立场。
术语表(Glossary)
英文术语与缩写
中文标准译法
术语定义
Artificial intelligence (AI)
人工智能(AI)
计算机科学的一个分支,致力于开发能够执行通常需要人类智能才能完成的任务的系统与算法。
Autoencoder
自编码器
一种用于无监督学习的神经网络,主要用于降维与特征学习。该网络由编码器与解码器两部分组成:编码器将输入数据压缩为低维潜空间表示,解码器基于该压缩表示重构原始输入。模型通过最小化输入与输出之间的重构损失进行训练,从而在保留核心特征的前提下,学习数据的高效表示。
Convolutional neural network
卷积神经网络
一种前馈架构的人工神经网络,信息从输入层经一个或多个隐藏层传递至输出层,核心通过卷积核实现对局部特征的提取,广泛应用于图像数据处理。
Generative adversarial networks (GANs)
生成对抗网络(GANs)
一类机器学习框架,由生成器与判别器两个神经网络通过对抗过程同步训练。生成器负责生成尽可能逼近真实数据的合成数据,判别器负责对输入数据进行评估,区分真实样本与生成样本。二者的对抗博弈推动生成器不断生成更具真实感的数据。
Large language models (LLMs)
大语言模型(LLMs)
一类基于海量文本数据训练的神经网络,能够生成类人文本、执行语言理解任务,并实现开放式对话交互。
Machine learning
机器学习
人工智能(AI)的一个分支,通过统计技术使计算机系统能够从数据中自主学习并优化性能,无需针对任务进行显式的编程。
Natural language processing (NLP)
自然语言处理(NLP)
人工智能(AI)的一个子领域,致力于实现计算机与人类之间的自然语言交互,开发能够让机器以符合语境的方式理解、解析、生成与响应人类语言的先进算法与计算模型。
Recurrent neural network (RNN)
循环神经网络(RNN)
一类专门处理序列数据(如文本、语音)的神经网络,通过内部状态的维护,实现对序列时间动态特征的捕捉与建模。
参考文献
[1] Finan, C. et al. The druggable genome and support for target identification and validation in drug development. Sci. Transl. Med. 9, eaag1166 (2017).中文译题:可成药基因组及其对药物研发中靶点识别与验证的支撑[2] Zhou, Y. et al. TTD: therapeutic target database describing target druggability information. Nucleic Acids Res. 52, D1465–D1477 (2024).中文译题:治疗靶点数据库(TTD):靶点成药性信息的整合与展示[3] Acharya, K. R., Sturrock, E. D., Riordan, J. F. & Ehlers, M. R. ACE revisited: a new target for structure-based drug design. Nat. Rev. Drug. Discov. 2, 891–902 (2003).中文译题:血管紧张素转换酶(ACE)的再研究:基于结构的药物设计新靶点[4] Zaman, M. A., Oparil, S. & Calhoun, D. A. Drugs targeting the renin–angiotensin–aldosterone system. Nat. Rev. Drug. Discov. 1, 621–636 (2002).中文译题:靶向肾素-血管紧张素-醛固酮系统的药物[5] Slamon, D. J. et al. Human breast cancer: correlation of relapse and survival with amplification of the HER-2/neu oncogene. Science 235, 177–182 (1987).中文译题:人乳腺癌中HER-2/neu癌基因扩增与患者复发和生存的相关性[6] Davies, H. et al. Mutations of the BRAF gene in human cancer. Nature 417, 949–954 (2002).中文译题:人类癌症中的BRAF基因突变[7] Sabatine, M. S. PCSK9 inhibitors: clinical evidence and implementation. Nat. Rev. Cardiol. 16, 155–165 (2019).中文译题:PCSK9抑制剂:临床证据与临床应用[8] Nelson, M. R. et al. The support of human genetic evidence for approved drug indications. Nat. Genet. 47, 856–860 (2015).中文译题:人类遗传学证据对已获批药物适应症的支撑作用[9] Pietzner, M. et al. Mapping the proteo-genomic convergence of human diseases. Science 374, eabj1541 (2021).中文译题:人类疾病的蛋白质组-基因组汇聚图谱绘制[10] McDonagh, E. M. et al. Human genetics and genomics for drug target identification and prioritization: Open Targets’ perspective. Annu. Rev. Biomed. Data Sci. 7, 59–81 (2024).中文译题:用于药物靶点识别与优先级排序的人类遗传学与基因组学:Open Targets的视角[11] Minikel, E. V., Painter, J. L., Dong, C. C. & Nelson, M. R. Refining the impact of genetic evidence on clinical success. Nature 629, 624–629 (2024).中文译题:遗传学证据对药物临床成功率影响的精准解析[12] Plenge, R. M., Scolnick, E. M. & Altshuler, D. Validating therapeutic targets through human genetics. Nat. Rev. Drug. Discov. 12, 581–594 (2013).中文译题:通过人类遗传学验证治疗靶点[13] Plenge, R. M. Disciplined approach to drug discovery and early development. Sci. Transl. Med. 8, 349ps315 (2016).中文译题:药物发现与早期研发的规范化方法[14] Michoel, T. & Zhang, J. D. Causal inference in drug discovery and development. Drug. Discov. Today 28, 103737 (2023).中文译题:药物研发中的因果推断[15] Zhu, Z. et al. Integration of summary data from GWAS and eQTL studies predicts complex trait gene targets. Nat. Genet. 48, 481–487 (2016).中文译题:整合GWAS与eQTL研究的汇总数据预测复杂性状的靶基因[16] Bretherick, A. D. et al. Linking protein to phenotype with Mendelian randomization detects 38 proteins with causal roles in human diseases and traits. PLoS Genet. 16, e1008785 (2020).中文译题:通过孟德尔随机化关联蛋白质与表型,识别38个在人类疾病和性状中发挥因果作用的蛋白质[17] Zhao, J. H. et al. Genetics of circulating inflammatory proteins identifies drivers of immune-mediated disease risk and therapeutic targets. Nat. Immunol. 24, 1540–1551 (2023).中文译题:循环炎症蛋白的遗传学研究识别免疫介导疾病的风险驱动因子与治疗靶点[18] Pavlidis, P. et al. Interleukin-22 regulates neutrophil recruitment in ulcerative colitis and is associated with resistance to ustekinumab therapy. Nat. Commun. 13, 5820 (2022).中文译题:白细胞介素22调控溃疡性结肠炎中的中性粒细胞募集,且与乌司奴单抗治疗耐药相关[19] Tsherniak, A. et al. Defining a cancer dependency map. Cell 170, 564–576.e16 (2017).中文译题:癌症依赖性图谱的构建[20] Gonzalez, G. et al. Combinatorial prediction of therapeutic perturbations using causally inspired neural networks. Nat. Biomed. Eng. https://doi.org/10.1038/s41551-025-01481-x (2025).中文译题:基于因果启发的神经网络实现治疗性扰动的组合预测[21] Cheng, A. C. et al. Structure-based maximal affinity model predicts small-molecule druggability. Nat. Biotechnol. 25, 71–75 (2007).中文译题:基于结构的最大亲和力模型预测小分子成药性[22] Bennett, C. F. Therapeutic antisense oligonucleotides are coming of age. Annu. Rev. Med. 70, 307–321 (2019).中文译题:治疗性反义寡核苷酸技术已走向成熟[23] Qin, S. et al. mRNA-based therapeutics: powerful and versatile tools to combat diseases. Signal. Transduct. Target. Ther. 7, 166 (2022).中文译题:mRNA疗法:对抗疾病的强大多功能工具[24] Sadelain, M., Riviere, I. & Riddell, S. Therapeutic T cell engineering. Nature 545, 423–431 (2017).中文译题:治疗性T细胞工程[25] Abramson, J. et al. Accurate structure prediction of biomolecular interactions with AlphaFold 3. Nature 630, 493–500 (2024).中文译题:基于AlphaFold 3实现生物分子相互作用的精准结构预测[26] Brennan, R. J. Target safety assessment: strategies and resources. Methods Mol. Biol. 1641, 213–228 (2017).中文译题:靶点安全性评估:策略与资源[27] Brennan, R. J. et al. The state of the art in secondary pharmacology and its impact on the safety of new medicines. Nat. Rev. Drug. Discov. https://doi.org/10.1038/s41573-024-00942-3 (2024).中文译题:次级药理学研究的技术现状及其对新药安全性的影响[28] Simonovsky, M. & Meyers, J. DeeplyTough: learning structural comparison of protein binding sites. J. Chem. Inf. Model. 60, 2356–2366 (2020).中文译题:DeeplyTough:基于深度学习的蛋白结合口袋结构比对算法[29] Pun, F. W., Ozerov, I. V. & Zhavoronkov, A. AI-powered therapeutic target discovery. Trends Pharmacol. Sci. 44, 561–572 (2023).中文译题:人工智能驱动的治疗靶点发现[30] Spring, L., Demuren, K., Ringel, M. & Wu, J. First-in-class versus best-in-class: an update for new market dynamics. Nat. Rev. Drug. Discov. 22, 531–532 (2023).中文译题:首创药物vs同类最优药物:新市场格局下的最新解读[31] Long, X. et al. AI-enabled cancer target prioritization with optimal profiles balancing novelty, confidence and commercial tractability. Future Medicine AI https://doi.org/10.2217/fmai-2023-0019 (2024).中文译题:基于AI实现兼顾创新性、可信度与商业可开发性的肿瘤靶点优先级排序[32] Hill, J. A. & Cowen, L. E. Using combination therapy to thwart drug resistance. Future Microbiol. 10, 1719–1726 (2015).中文译题:通过联合治疗克服耐药性[33] Wen, P. Y. et al. Dabrafenib plus trametinib in patients with BRAFV600E-mutant low-grade and high-grade glioma (ROAR): a multicentre, open-label, single-arm, phase 2, basket trial. Lancet Oncol. 23, 53–64 (2022).中文译题:达拉非尼联合曲美替尼治疗BRAFV600E突变型低级别和高级别胶质瘤(ROAR研究):一项多中心、开放标签、单臂、2期篮子试验[34] Subbiah, V. et al. Dabrafenib plus trametinib in BRAFV600E-mutated rare cancers: the phase 2 ROAR trial. Nat. Med. 29, 1103–1112 (2023).中文译题:达拉非尼联合曲美替尼治疗BRAFV600E突变罕见癌症:2期ROAR临床试验结果[35] Choueiri, T. K. et al. Cabozantinib plus nivolumab and ipilimumab in renal-cell carcinoma. N. Engl. J. Med. 388, 1767–1778 (2023).中文译题:卡博替尼联合纳武利尤单抗与伊匹木单抗治疗肾细胞癌[36] Owonikoko, T. K. et al. Nivolumab and ipilimumab as maintenance therapy in extensive-disease small-cell lung cancer: CheckMate 451. J. Clin. Oncol. 39, 1349–1359 (2021).中文译题:纳武利尤单抗联合伊匹木单抗用于广泛期小细胞肺癌的维持治疗:CheckMate 451研究[37] Lenz, H. J. et al. First-line nivolumab plus low-dose ipilimumab for microsatellite instability-high/mismatch repair-deficient metastatic colorectal cancer: the phase II CheckMate 142 study. J. Clin. Oncol. 40, 161–170 (2022).中文译题:纳武利尤单抗联合低剂量伊匹木单抗一线治疗微卫星不稳定性高/错配修复缺陷型转移性结直肠癌:2期CheckMate 142研究[38] Barry, M., Mulcahy, F. & Back, D. J. Antiretroviral therapy for patients with HIV disease. Br. J. Clin. Pharmacol. 45, 221–228 (1998).中文译题:HIV感染者的抗逆转录病毒治疗[39] Lathouwers, E. et al. Week 48 resistance analyses of the once-daily, single-tablet regimen darunavir/cobicistat/emtricitabine/tenofovir alafenamide (D/C/F/TAF) in adults living with HIV-1 from the phase III randomized AMBER and EMERALD trials. AIDS Res. Hum. Retroviruses 36, 48–57 (2020).中文译题:3期AMBER与EMERALD试验中,达芦那韦/考比司他/恩曲他滨/丙酚替诺福韦(D/C/F/TAF)每日一次单片方案治疗HIV-1感染成人患者48周的耐药性分析[40] Powles, T. et al. Enfortumab vedotin and pembrolizumab in untreated advanced urothelial cancer. N. Engl. J. Med. 390, 875–888 (2024).中文译题:恩诺单抗联合帕博利珠单抗一线治疗晚期尿路上皮癌[41] Hoimes, C. J. et al. Enfortumab vedotin plus pembrolizumab in previously untreated advanced urothelial cancer. J. Clin. Oncol. 41, 22–31 (2023).中文译题:恩诺单抗联合帕博利珠单抗一线治疗晚期尿路上皮癌[42] Eadie, A. L., Brunt, K. R. & Herder, M. Exploring the Food and Drug Administration’s review and approval of Entresto (sacubitril/valsartan). Pharmacol. Res. Perspect. 9, e00794 (2021).中文译题:美国食品药品监督管理局对沙库巴曲缬沙坦审评审批过程的解析[43] Mann, D. L. et al. Effect of treatment with sacubitril/valsartan in patients with advanced heart failure and reduced ejection fraction: a randomized clinical trial. JAMA Cardiol. 7, 17–25 (2022).中文译题:沙库巴曲缬沙坦治疗射血分数降低的晚期心力衰竭患者的疗效:一项随机临床试验[44] Vaduganathan, M. et al. Sacubitril/valsartan in heart failure with mildly reduced or preserved ejection fraction: a pre-specified participant-level pooled analysis of PARAGLIDE-HF and PARAGON-HF. Eur. Heart J. 44, 2982–2993 (2023).中文译题:沙库巴曲缬沙坦治疗射血分数轻度降低或保留的心力衰竭:PARAGLIDE-HF与PARAGON-HF研究的患者水平预设汇总分析[45] Zeng, Z. et al. Deep learning for cancer type classification and driver gene identification. BMC Bioinforma. 22, 491 (2021).中文译题:基于深度学习实现癌症分型与驱动基因识别[46] Kim, D. et al. An evolution-based machine learning to identify cancer type-specific driver mutations. Brief. Bioinform 24, bbac593 (2023).中文译题:基于进化的机器学习算法识别癌症类型特异性驱动突变[47] Chakraborty, S., Hosen, M. I., Ahmed, M. & Shekhar, H. U. Onco-multi-OMICS approach: a new frontier in cancer research. Biomed. Res. Int. 2018, 9836256 (2018).中文译题:肿瘤多组学方法:癌症研究的新前沿[48] Schulte-Sasse, R., Budach, S., Hnisz, D. & Marsico, A. Integration of multiomics data with graph convolutional networks to identify new cancer genes and their associated molecular mechanisms. Nat. Mach. Intell. 3, 513–526 (2021).中文译题:基于图卷积网络整合多组学数据识别全新癌症相关基因及其分子机制[49] Sidorenko, D. et al. Precious2GPT: the combination of multiomics pretrained transformer and conditional diffusion for artificial multi-omics multi-species multi-tissue sample generation. npj Aging 10, 37 (2024).中文译题:Precious2GPT:融合多组学预训练Transformer与条件扩散模型,实现跨物种、跨组织的合成多组学样本生成[50] Cui, H. et al. scGPT: toward building a foundation model for single-cell multi-omics using generative AI. Nat. Methods 21, 1470–1480 (2024).中文译题:scGPT:基于生成式AI构建单细胞多组学基础模型[51] Chandrasekaran, S. N., Ceulemans, H., Boyd, J. D. & Carpenter, A. E. Image-based profiling for drug discovery: due for a machine-learning upgrade? Nat. Rev. Drug. Discov. 20, 145–159 (2021).中文译题:基于图像的谱分析技术在药物发现中的应用:亟待机器学习技术的升级
[52] Phillip, J. M., Han, K.-S., Chen, W.-C., Wirtz, D. & Wu, P.-H. A robust unsupervised machine-learning method to quantify the morphological heterogeneity of cells and nuclei. Nat. Protoc. 16, 754–774 (2021).中文译题:一种可量化细胞与细胞核形态异质性的稳健无监督机器学习方法[53] Xue, Y., Wang, J., Ren, K. & Ji, J. Deep mining of subtle differences in cell morphology via deep learning. Adv. Theory Simul. 4, 2000172 (2021).中文译题:基于深度学习深度挖掘细胞形态的细微差异[54] Chandrasekaran, S. N. et al. JUMP Cell Painting dataset: morphological impact of 136,000 chemical and genetic perturbations. Preprint at bioRxiv https://doi.org/10.1101/2023.03.23.534023 (2023).中文译题:JUMP细胞绘画数据集:13.6万种化学与遗传扰动的细胞形态学影响[55] Rawat, W. & Wang, Z. Deep convolutional neural networks for image classification: a comprehensive review. Neural Comput. 29, 2352–2449 (2017).中文译题:用于图像分类的深度卷积神经网络:全面综述[56] Ektefaie, Y., Dasoulas, G., Noori, A., Farhat, M. & Zitnik, M. Multimodal learning with graphs. Nat. Mach. Intell. 5, 340–350 (2023).中文译题:基于图的多模态学习[57] Yu, S. et al. Integrating inflammatory biomarker analysis and artificial-intelligence-enabled image-based profiling to identify drug targets for intestinal fibrosis. Cell Chem. Biol. 30, 1169–1182.e8 (2023).中文译题:整合炎症生物标志物分析与AI赋能的图像谱分析技术,识别肠道纤维化的治疗靶点[58] Atmaramani, R. et al. Deep learning analysis on images of iPSC-derived运动神经元 carrying fALS-genetics reveals disease-relevant phenotypes. Preprint at bioRxiv https://doi.org/10.1101/2024.01.04.574270 (2024).中文译题:对家族性肌萎缩侧索硬化症相关基因突变的iPSC来源运动神经元图像进行深度学习分析,识别疾病相关表型[59] Szklarczyk, D. et al. The STRING database in 2023: protein–protein association networks and functional enrichment analyses for any sequenced genome of interest. Nucleic Acids Res. 51, D638–D646 (2023).中文译题:2023年STRING数据库:面向任意已测序基因组的蛋白-蛋白关联网络与功能富集分析[60] Oughtred, R. et al. The BioGRID database: a comprehensive biomedical resource of curated protein, genetic, and chemical interactions. Protein Sci. 30, 187–200 (2021).中文译题:BioGRID数据库:全面收录经整理的蛋白、遗传与化学相互作用的生物医学资源库[61] Del Toro, N. et al. The IntAct database: efficient access to fine-grained molecular interaction data. Nucleic Acids Res. 50, D648–D653 (2022).中文译题:IntAct数据库:高效获取精细化分子互作数据[62] Bader, G. D., Betel, D. & Hogue, C. W. BIND: the biomolecular interaction network database. Nucleic Acids Res. 31, 248–250 (2003).中文译题:BIND:生物分子相互作用网络数据库[63] Kanehisa, M., Furumichi, M., Sato, Y., Kawashima, M. & Ishiguro-Watanabe, M. KEGG for taxonomy-based analysis of pathways and genomes. Nucleic Acids Res. 51, D587–D592 (2023).中文译题:KEGG数据库:用于基于分类学的通路与基因组分析[64] Milacic, M. et al. The Reactome pathway knowledgebase 2024. Nucleic Acids Res. 52, D672–D678 (2024).中文译题:2024年Reactome通路知识库[65] Pico, A. R. et al. WikiPathways: pathway editing for the people. PLoS Biol. 6, e184 (2008).中文译题:WikiPathways:面向大众的通路编辑平台[66] Gene Ontology, C. et al. The Gene Ontology knowledgebase in 2023. Genetics 224, iyad031 (2023).中文译题:2023年基因本体(Gene Ontology)知识库[67] Zhang, Y. et al. A comprehensive large-scale biomedical knowledge graph for AI-powered data-driven biomedical research. Nat. Mach. Intell. 7, 602–614 (2025).中文译题:面向AI赋能的生物医学研究的大规模综合生物医学知识图谱[68] Karki, R. et al. KGG: a fully automated workflow for creating disease-specific knowledge graphs. Bioinformatics 41, btaf383 (2025).中文译题:KGG:用于构建疾病特异性知识图谱的全自动化工作流[69] Chandak, P., Huang, K. & Zitnik, M. Building a knowledge graph to enable precision medicine. Sci. Data 10, 67 (2023).中文译题:构建支撑精准医疗的知识图谱[70] Dezso, Z. & Ceccarelli, M. Machine learning prediction of oncology drug targets based on protein and network properties. BMC Bioinforma. 21, 104 (2020).中文译题:基于蛋白与网络特征的机器学习算法预测肿瘤药物靶点[71] Zhao, W., Gu, X., Chen, S., Wu, J. & Zhou, Z. MODIG: integrating multi-omics and multi-dimensional gene network for cancer driver gene identification based on graph attention network model. Bioinformatics 38, 4901–4907 (2022).中文译题:MODIG:基于图注意力网络模型整合多组学与多维基因网络,识别癌症驱动基因[72] Kamya, P. et al. PandaOmics: an AI-driven platform for therapeutic target and biomarker discovery. J. Chem. Inf. Model. 64, 3961–3969 (2024).中文译题:PandaOmics:AI驱动的治疗靶点与生物标志物发现平台[73] Paliwal, S., de Giorgio, A., Neil, D., Michel, J. B. & Lacoste, A. M. Preclinical validation of therapeutic targets predicted by tensor factorization on heterogeneous graphs. Sci. Rep. 10, 18250 (2020).中文译题:基于异构图张量分解预测的治疗靶点的临床前验证[74] Wang, S. et al. KG4SL: knowledge graph neural network for synthetic lethality prediction in human cancers. Bioinformatics 37, i418–i425 (2021).中文译题:KG4SL:基于知识图神经网络预测人类癌症中的合成致死关系[75] Oliveira, A. L. Biotechnology, big data and artificial intelligence. Biotechnol. J. 14, e1800613 (2019).中文译题:生物技术、大数据与人工智能[76] Chia, S. et al. Phenotype-driven precision oncology as a guide for clinical decisions one patient at a time. Nat. Commun. 8, 435 (2017).中文译题:表型驱动的精准肿瘤学指导个体化临床决策[77] Bajwa, J., Munir, U., Nori, A. & Williams, B. Artificial intelligence in healthcare: transforming the practice of medicine. Future Healthc. J. 8, e188–e194 (2021).中文译题:医疗健康领域的人工智能:变革临床诊疗实践[78] Gao, Z. et al. Artificial intelligence-based drug repurposing with electronic health record clinical corroboration: a case for ketamine as a potential treatment for amphetamine-type stimulant use disorder. Addiction 120, 732–744 (2025).中文译题:基于人工智能的药物重定位及电子健康记录临床验证:以氯胺酮作为苯丙胺类兴奋剂使用障碍潜在治疗药物为例[79] Liu, R., Wei, L. & Zhang, P. A deep learning framework for drug repurposing via emulating clinical trials on real-world patient data. Nat. Mach. Intell. 3, 68–75 (2021).中文译题:基于真实世界患者数据模拟临床试验的深度学习药物重定位框架[80] Coudray, N. et al. Classification and mutation prediction from non-small cell lung cancer histopathology images using deep learning. Nat. Med. 24, 1559–1567 (2018).中文译题:基于深度学习从非小细胞肺癌组织病理图像实现分型与突变预测[81] Morselli Gysi, D. et al. Network medicine framework for identifying drug-repurposing opportunities for COVID-19. Proc. Natl Acad. Sci. USA 118, e2025581118 (2021).中文译题:用于识别COVID-19药物重定位机会的网络医学框架[82] Serrano Nájera, G., Narganes Carlón, D. & Crowther, D. J. TrendyGenes, a computational pipeline for the detection of literature trends in academia and drug discovery. Sci. Rep. 11, 15747 (2021).中文译题:TrendyGenes:用于识别学术研究与药物发现领域文献趋势的计算流程[83] Lee, B. Y., Bacon, K. M., Bottazzi, M. E. & Hotez, P. J. Global economic burden of Chagas disease: a computational simulation model. Lancet Infect. Dis. 13, 342–348 (2013).中文译题:恰加斯病的全球经济负担:计算模拟模型[84] Senger, S. Assessment of the significance of patent-derived information for the early identification of compound–target interaction hypotheses. J. Cheminform 9, 26 (2017).中文译题:专利来源信息对化合物-靶点相互作用假设早期识别的价值评估[85] van Rijn, T. & Timmis, J. K. Patent landscape analysis—contributing to the identification of technology trends and informing research and innovation funding policy. Microb. Biotechnol. 16, 683–696 (2023).中文译题:专利全景分析:助力技术趋势识别与科研创新资助政策制定[86] Kesselheim, A. S., Cook-Deegan, R. M., Winickoff, D. E. & Mello, M. M. Gene patenting—the supreme court finally speaks. N. Engl. J. Med. 369, 869–875 (2013).中文译题:基因专利——最高法院的最终裁决[87] Daluwatte, C., Schotland, P., Strauss, D. G., Burkhart, K. K. & Racz, R. Predicting potential adverse events using safety data from marketed drugs. BMC Bioinforma. 21, 163 (2020).中文译题:基于已上市药物的安全性数据预测潜在不良事件[88] Sterzi, V. Patent quality and ownership: an analysis of UK faculty patenting. Res. Policy 42, 564–576 (2013).中文译题:专利质量与所有权:英国高校教师专利申请情况分析[89] Ciray, F. & Dogan, T. Machine learning-based prediction of drug approvals using molecular, physicochemical, clinical trial, and patent-related features. Expert. Opin. Drug. Discov. 17, 1425–1441 (2022).中文译题:基于分子、理化性质、临床试验与专利相关特征,通过机器学习预测药物获批概率[90] Ekins, S., Mestres, J. & Testa, B. In silico pharmacology for drug discovery: applications to targets and beyond. Br. J. Pharmacol. 152, 21–37 (2007).中文译题:药物发现中的计算机药理学:靶点相关及更广泛的应用[91] Sudhahar, S. et al. An experimentally validated approach to automated biological evidence generation in drug discovery using knowledge graphs. Nat. Commun. 15, 5703 (2024).中文译题:基于知识图谱实现药物发现中生物学证据自动化生成的方法及实验验证[92] Piñero, J. et al. DisGeNET: a comprehensive platform integrating information on human disease-associated genes and variants. Nucleic Acids Res. 45, D833–D839 (2017).中文译题:DisGeNET:整合人类疾病相关基因与变异信息的综合平台[93] Chen, Y. A., Allendes Osorio, R. S. & Mizuguchi, K. TargetMine 2022: a new vision into drug target analysis. Bioinformatics 38, 4454–4456 (2022).中文译题:TargetMine 2022:药物靶点分析的全新视角[94] Chen, Y. A., Tripathi, L. P. & Mizuguchi, K. TargetMine, an integrated data warehouse for candidate gene prioritisation and target discovery. PLoS One 6, e17844 (2011).中文译题:TargetMine:用于候选基因优先级排序与靶点发现的整合数据仓库[95] Madhukar, N. S. et al. A Bayesian machine learning approach for drug target identification using diverse data types. Nat. Commun. 10, 5221 (2019).中文译题:基于多类型数据的贝叶斯机器学习方法用于药物靶点识别[96] Allen, J. E. et al. Dual inactivation of Akt and ERK by TIC10 signals Foxo3a nuclear translocation, TRAIL gene induction, and potent antitumor effects. Sci. Transl. Med. 5, 171ra117 (2013).中文译题:TIC10通过双重抑制Akt与ERK通路,诱导Foxo3a核转位与TRAIL基因表达,发挥强效抗肿瘤作用[97] Mountjoy, E. et al. An open approach to systematically prioritize causal variants and genes at all published human GWAS trait-associated loci. Nat. Genet. 53, 1527–1533 (2021).中文译题:对已发表的人类GWAS性状相关基因座的致病变异与基因进行系统性优先级排序的开源方法[98] Abedi, M. et al. Systems biology and machine learning approaches identify drug targets in diabetic nephropathy. Sci. Rep. 11, 23452 (2021).中文译题:基于系统生物学与机器学习方法识别糖尿病肾病的药物靶点[99] Binder, J. et al. Machine learning prediction and tau-based screening identifies potential Alzheimer’s disease genes relevant to immunity. Commun. Biol. 5, 125 (2022).中文译题:机器学习预测与tau蛋白相关筛选识别与免疫相关的阿尔茨海默病潜在靶基因[100] Buniello, A. et al. Open Targets Platform: facilitating therapeutic hypotheses building in drug discovery. Nucleic Acids Res. 53, D1467–D1475 (2025).中文译题:Open Targets平台:助力药物研发中治疗假设的构建
[101] Leung, H. et al. Advancing target discovery through disease-specific integration of multi-modal target identification models and comprehensive benchmarking system. Sci. Rep. https://doi.org/10.1038/s41598-026-47765-3 (2026).中文译题:通过疾病特异性多模态靶点识别模型与综合基准测试体系推动靶点发现[102] Choobdar, S. et al. Assessment of network module identification across complex diseases. Nat. Methods 16, 843–852 (2019).中文译题:复杂疾病网络模块识别方法的评估[103] Zeng, X. et al. Accurate prediction of molecular properties and drug targets using a self-supervised image representation learning framework. Nat. Mach. Intell. 4, 1004–1016 (2022).中文译题:基于自监督图像表示学习框架实现分子性质与药物靶点的精准预测[104] Ling, C. et al. Predicting drug–target interactions using matrix factorization with self-paced learning and dual similarity information. Technol. Health Care 32, 49–64 (2024).中文译题:基于自步学习与双重相似性信息的矩阵分解方法预测药物-靶点相互作用[105] Liu, Y., Wu, M., Miao, C., Zhao, P. & Li, X. L. Neighborhood regularized logistic matrix factorization for drug–target interaction prediction. PLoS Comput. Biol. 12, e1004760 (2016).中文译题:基于邻域正则化逻辑矩阵分解的药物-靶点相互作用预测[106] Raies, A. et al. DrugnomeAI is an ensemble machine-learning framework for predicting druggability of candidate drug targets. Commun. Biol. 5, 1291 (2022).中文译题:DrugnomeAI:用于候选药物靶点成药性预测的集成机器学习框架[107] Muslu, O., Hoyt, C. T., Lacerda, M., Hofmann-Apitius, M. & Frohlich, H. GuiltyTargets: prioritization of novel therapeutic targets with network representation learning. IEEE/ACM Trans. Comput. Biol. Bioinform 19, 491–500 (2022).中文译题:GuiltyTargets:基于网络表示学习实现新型治疗靶点的优先级排序[108] Theodoris, C. V. et al. Transfer learning enables predictions in network biology. Nature 618, 616–624 (2023).中文译题:迁移学习赋能网络生物学预测[109] Kraus, O. et al. Masked autoencoders are scalable learners of cellular morphology. Preprint at 10.48550/arXiv.2309.16064 (2023).中文译题:掩码自编码器是细胞形态学的可扩展学习模型[110] Meier, J. et al. Language models enable zero-shot prediction of the effects of mutations on protein function. In Proc. 35th Int. Conf. Neural Information Processing Systems (eds Ranzato, M. et al.) 29287–29303 (Curran Associates, 2021).中文译题:语言模型实现蛋白质突变功能效应的零样本预测[111] Ngoi, N. Y. L. et al. Synthetic lethal strategies for the development of cancer therapeutics. Nat. Rev. Clin. Oncol. 22, 46–64 (2025).中文译题:用于癌症治疗药物开发的合成致死策略[112] He, R., Cao, J. & Tan, T. Generative artificial intelligence: a historical perspective. Natl Sci. Rev. 12, nwaf050 (2025).中文译题:生成式人工智能:历史视角[113] Urban, A. et al. Precious1GPT: multimodal transformer-based transfer learning for aging clock development and feature importance analysis for aging and age-related disease target discovery. Aging 15, 4649–4666 (2023).中文译题:Precious1GPT:基于多模态Transformer迁移学习构建衰老时钟,及衰老与衰老相关疾病靶点发现的特征重要性分析[114] Galkin, F. et al. Precious3GPT: multimodal multi-species multi-omics multi-tissue transformer for aging research and drug discovery. Preprint at bioRxiv https://doi.org/10.1101/2024.07.25.605062 (2024).中文译题:Precious3GPT:面向衰老研究与药物发现的多模态、跨物种、多组学、跨组织Transformer模型[115] Galkin, F., Ren, F. & Zhavoronkov, A. LLMs and AI life models for Traditional Chinese Medicine-derived geroprotector formulation. Aging Dis. https://doi.org/10.14336/ad.2024.1697 (2025).中文译题:大语言模型与AI生命模型在中药来源抗衰老药物配方开发中的应用[116] Zappia, L., Phipson, B. & Oshlack, A. Splatter: simulation of single-cell RNA sequencing data. Genome Biol. 18, 174 (2017).中文译题:Splatter:单细胞RNA测序数据的模拟工具[117] Marouf, M. et al. Realistic in silico generation and augmentation of single-cell RNA-seq data using generative adversarial networks. Nat. Commun. 11, 166 (2020).中文译题:基于生成对抗网络实现单细胞RNA测序数据的计算机模拟生成与数据增强[118] Lindenbaum, O., Stanley, J., Wolf, G. & Krishnaswamy, S. Geometry based data generation. In Advances in Neural Information Processing Systems Vol. 31, 1405–1416 (NeurIPS, 2018).中文译题:基于几何的数据生成方法[119] Zinati, Y., Takiddeen, A. & Emad, A. GRouNdGAN: GRN-guided simulation of single-cell RNA-seq data using causal generative adversarial networks. Nat. Commun. 15, 4055 (2024).中文译题:GRouNdGAN:基于基因调控网络引导的因果生成对抗网络,实现单细胞RNA测序数据模拟[120] Lotfollahi, M., Wolf, F. A. & Theis, F. J. scGen predicts single-cell perturbation responses. Nat. Methods 16, 715–721 (2019).中文译题:scGen:预测单细胞扰动响应[121] Achiam, J. et al. GPT-4 technical report. Preprint at https://doi.org/10.48550/arXiv.2303.08774 (2023).中文译题:GPT-4技术报告[122] Gururangan, S. et al. Don’t stop pretraining: adapt language models to domains and tasks. In Proc. 58th Annual Meeting of the Association for Computational Linguistics (eds Jurafsky, D. et al.) 8342–8360 (Association for Computational Linguistics, 2020).中文译题:持续预训练:让语言模型适配领域与任务[123] Qiu, X. et al. Pre-trained models for natural language processing: a survey. Sci. China Technol. Sci. 63, 1872–1897 (2020).中文译题:自然语言处理预训练模型综述[124] Luo, R. et al. BioGPT: generative pre-trained transformer for biomedical text generation and mining. Brief. Bioinform 23, bbac409 (2022).中文译题:BioGPT:面向生物医学文本生成与挖掘的生成式预训练Transformer模型[125] Zagirova, D. et al. Biomedical generative pre-trained based transformer language model for age-related disease target discovery. Aging 15, 9293–9309 (2023).中文译题:面向衰老相关疾病靶点发现的生物医学生成式预训练Transformer语言模型[126] Wang, E. et al. Txgemma: efficient and agentic LLMs for therapeutics. Preprint at https://arxiv.org/abs/2504.06196 (2025).中文译题:Txgemma:面向治疗学领域的高效智能体大语言模型[127] Gottweis, J. et al. Towards an AI co-scientist. Preprint at https://doi.org/10.48550/arXiv.2502.18864 (2025).中文译题:迈向AI协同科学家[128] Guan, Y. et al. AI-Assisted drug re-purposing for human liver fibrosis. Adv. Sci. 12, e08751 (2025).中文译题:AI辅助的肝纤维化药物重定位[129] Zhang, Z. et al. OriGene: a self-evolving virtual disease biologist automating therapeutic target discovery. Preprint at bioRxiv https://doi.org/10.1101/2025.06.03.657658 (2025).中文译题:OriGene:可自主进化的虚拟疾病生物学家,实现治疗靶点发现自动化[130] Pun, F. W. et al. Identification of therapeutic targets for amyotrophic lateral sclerosis using PandaOmics—an AI-enabled biological target discovery platform. Front. Aging Neurosci. 14, 914017 (2022).中文译题:基于AI赋能的生物靶点发现平台PandaOmics识别肌萎缩侧索硬化症的治疗靶点[131] Ren, F. et al. A small-molecule TNIK inhibitor targets fibrosis in preclinical and clinical models. Nat. Biotechnol. https://doi.org/10.1038/s41587-024-02143-0 (2024).中文译题:小分子TNIK抑制剂在纤维化临床前模型与临床模型中的治疗作用[132] Lim, C. M. et al. Multiomic prediction of therapeutic targets for human diseases associated with protein phase separation. Proc. Natl Acad. Sci. USA 120, e2300215120 (2023).中文译题:基于多组学预测蛋白相分离相关人类疾病的治疗靶点[133] Mkrtchyan, G. V. et al. High-confidence cancer patient stratification through multiomics investigation of DNA repair disorders. Cell Death Dis. 13, 999 (2022).中文译题:通过DNA修复障碍的多组学研究实现高可信度的癌症患者分层[134] Pun, F. W. et al. A comprehensive AI-driven analysis of large-scale omic datasets reveals novel dual-purpose targets for the treatment of cancer and aging. Aging Cell 22, e14017 (2023).中文译题:基于AI对大规模组学数据集的综合分析,识别兼具癌症与衰老治疗价值的双用途靶点[135] Ranjbar, M. et al. Autophagy dark genes: can we find them with machine learning? Nat. Sci. 3, e20220067 (2023).中文译题:自噬相关未知基因:能否通过机器学习实现发现?[136] Hughes, J. P., Rees, S., Kalindjian, S. B. & Philpott, K. L. Principles of early drug discovery. Br. J. Pharmacol. 162, 1239–1249 (2011).中文译题:早期药物发现的基本原则[137] Ren, F. et al. AlphaFold accelerates artificial intelligence powered drug discovery: efficient discovery of a novel CDK20 small molecule inhibitor. Chem. Sci. 14, 1443–1452 (2023).中文译题:AlphaFold加速AI赋能的药物发现:高效发现新型CDK20小分子抑制剂[138] Zhang, S. et al. Genome-wide identification of the genetic basis of amyotrophic lateral sclerosis. Neuron 110, 992–1008.e11 (2022).中文译题:全基因组范围识别肌萎缩侧索硬化症的遗传基础[139] Liu, B. H. M. et al. Utilizing AI for the identification and validation of novel therapeutic targets and repurposed drugs for endometriosis. Adv. Sci. 12, e2406565 (2025).中文译题:基于AI实现子宫内膜异位症新型治疗靶点的识别验证与药物重定位[140] Tang, Q. et al. AI-driven robotics laboratory identifies pharmacological TNIK inhibition as a potent senomorphic agent. Aging Dis. https://doi.org/10.14336/ad.2024.1492 (2025).中文译题:AI驱动的机器人实验室发现TNIK药理学抑制是一种强效的衰老相关分泌表型抑制药物[141] Tsuji, S. et al. Artificial intelligence-based computational framework for drug-target prioritization and inference of novel repositionable drugs for Alzheimer’s disease. Alzheimers Res. Ther. 13, 92 (2021).中文译题:基于人工智能的计算框架,用于阿尔茨海默病药物靶点优先级排序与新型重定位药物推断[142] Yamaguchi, T. et al. Syk inhibitors reduce tau protein phosphorylation and oligomerization. Neurobiol. Dis. 201, 106656 (2024).中文译题:Syk抑制剂可减少tau蛋白的磷酸化与寡聚化[143] Pun, F. W. et al. Hallmarks of aging-based dual-purpose disease and age-associated targets predicted using PandaOmics AI-powered discovery engine. Aging 14, 2475–2506 (2022).中文译题:基于AI驱动的PandaOmics发现引擎,预测基于衰老标志的疾病与衰老相关双用途靶点[144] Sikder, S., Baek, S., McNeil, T. & Dalal, Y. Centromere inactivation during aging can be rescued in human cells. Mol. Cell 85, 692–707.e7 (2025).中文译题:衰老过程中的着丝粒失活可在人类细胞中被逆转[145] Deng, X. et al. Effects of MMP2 and its inhibitor TIMP2 on DNA damage, apoptosis and senescence of human lens epithelial cells induced by oxidative stress. J. Bioenerg. Biomembr. 56, 619–630 (2024).中文译题:MMP2及其抑制剂TIMP2对氧化应激诱导的人晶状体上皮细胞DNA损伤、凋亡与衰老的影响[146] Zhu, F. et al. What are next generation innovative therapeutic targets? Clues from genetic, structural, physicochemical, and systems profiles of successful targets. J. Pharmacol. Exp. Ther. 330, 304–315 (2009).中文译题:下一代创新治疗靶点的特征:来自成功靶点的遗传、结构、理化与系统特征线索[147] Zhu, F., Li, X. X., Yang, S. Y. & Chen, Y. Z. Clinical success of drug targets prospectively predicted by in silico study. Trends Pharmacol. Sci. 39, 229–231 (2018).中文译题:计算机模拟研究前瞻性预测的药物靶点的临床成功率[148] Aliper, A. et al. Prediction of clinical trials outcomes based on target choice and clinical trial design with multi-modal artificial intelligence. Clin. Pharmacol. Ther. 114, 972–980 (2023).中文译题:基于多模态人工智能,通过靶点选择与临床试验设计预测临床试验结果
[149] Jumper, J. et al. Highly accurate protein structure prediction with AlphaFold. Nature 596, 583–589 (2021).中文译题:基于AlphaFold实现蛋白质结构的高精准预测[150] Fraser, J. S. et al. Accessing protein conformational ensembles using room-temperature X-ray crystallography. Proc. Natl Acad. Sci. USA 108, 16247–16252 (2011).中文译题:基于室温X射线晶体学解析蛋白质构象系综[151] ww, P. D. B. c Protein Data Bank: the single global archive for 3D macromolecular structure data. Nucleic Acids Res. 47, D520–D528 (2019).中文译题:蛋白质数据库(PDB):全球唯一的3D生物大分子结构数据存档[152] Steinegger, M., Mirdita, M. & Soding, J. Protein-level assembly increases protein sequence recovery from metagenomic samples manyfold. Nat. Methods 16, 603–606 (2019).中文译题:蛋白水平组装可将宏基因组样本的蛋白序列回收率提升数倍[153] Jumper, J. et al. Applying and improving AlphaFold at CASP14. Proteins 89, 1711–1721 (2021).中文译题:AlphaFold在CASP14竞赛中的应用与优化[154] Lee, C., Su, B. H. & Tseng, Y. J. Comparative studies of AlphaFold, RoseTTAFold and Modeller: a case study involving the use of G-protein-coupled receptors. Brief. Bioinform 23, bbac308 (2022).中文译题:AlphaFold、RoseTTAFold与Modeller的对比研究:以G蛋白偶联受体为例[155] Webb, B. & Sali, A. Protein structure modeling with MODELLER. Methods Mol. Biol. 1137, 1–15 (2014).中文译题:基于MODELLER的蛋白质结构建模[156] Stein, A. & Kortemme, T. Improvements to robotics-inspired conformational sampling in Rosetta. PLoS One 8, e63090 (2013).中文译题:Rosetta中机器人启发的构象采样方法的优化[157] Deane, C. M. & Blundell, T. L. CODA: a combined algorithm for predicting the structurally variable regions of protein models. Protein Sci. 10, 599–612 (2001).中文译题:CODA:一种预测蛋白质模型结构可变区的组合算法[158] Ahdritz, G. et al. OpenFold: retraining AlphaFold2 yields new insights into its learning mechanisms and capacity for generalization. Nat. Methods 21, 1514–1524 (2024).中文译题:OpenFold:重新训练AlphaFold2,揭示其学习机制与泛化能力[159] Baek, M. et al. Accurate prediction of protein structures and interactions using a three-track neural network. Science 373, 871–876 (2021).中文译题:基于三轨神经网络实现蛋白质结构与相互作用的精准预测[160] Passaro, S. et al. Boltz-2: towards accurate and efficient binding affinity prediction. Preprint at bioRxiv https://doi.org/10.1101/2025.06.14.659707 (2025).中文译题:Boltz-2:迈向精准高效的结合亲和力预测[161] Naddaf, M. Open-source protein structure AI aims to match AlphaFold. Nature https://doi.org/10.1038/d41586-025-03546-y (2025).中文译题:开源蛋白质结构AI有望比肩AlphaFold[162] Mosalaganti, S. et al. AI-based structure prediction empowers integrative structural analysis of human nuclear pores. Science 376, eabm9506 (2022).中文译题:基于AI的结构预测赋能人类核孔复合体的整合结构分析[163] Bryant, P., Pozzati, G. & Elofsson, A. Improved prediction of protein–protein interactions using AlphaFold2. Nat. Commun. 13, 1265 (2022).中文译题:基于AlphaFold2优化蛋白质-蛋白质相互作用预测[164] Hekkelman, M. L., de Vries, I., Joosten, R. P. & Perrakis, A. AlphaFill: enriching AlphaFold models with ligands and cofactors. Nat. Methods 20, 205–213 (2023).中文译题:AlphaFill:为AlphaFold模型补充配体与辅因子信息[165] Holcomb, M., Chang, Y. T., Goodsell, D. S. & Forli, S. Evaluation of AlphaFold2 structures as docking targets. Protein Sci. 32, e4530 (2023).中文译题:AlphaFold2结构作为分子对接靶点的适用性评估[166] Scardino, V., Di Filippo, J. I. & Cavasotto, C. N. How good are AlphaFold models for docking-based virtual screening? iScience 26, 105920 (2023).中文译题:AlphaFold模型在基于对接的虚拟筛选中的性能评估[167] Karelina, M., Noh, J. J. & Dror, R. O. How accurately can one predict drug binding modes using AlphaFold models? eLife 12, RP89386 (2023).中文译题:基于AlphaFold模型预测药物结合模式的准确度分析[168] Lyu, J. et al. AlphaFold2 structures guide prospective ligand discovery. Science 384, eadn6354 (2024).中文译题:AlphaFold2结构指导前瞻性配体发现[169] Lin, Z. et al. Evolutionary-scale prediction of atomic-level protein structure with a language model. Science 379, 1123–1130 (2023).中文译题:基于语言模型实现进化尺度的蛋白质原子级结构预测[170] Meller, A., Bhakat, S., Solieva, S. & Bowman, G. R. Accelerating cryptic pocket discovery using AlphaFold. J. Chem. Theory Comput. 19, 4355–4363 (2023).中文译题:基于AlphaFold加速隐藏结合口袋的发现[171] Meller, A. et al. Predicting locations of cryptic pockets from single protein structures using the PocketMiner graph neural network. Nat. Commun. 14, 1177 (2023).中文译题:基于PocketMiner图神经网络从单一蛋白质结构预测隐藏结合口袋的位置[172] Li, H. et al. Decoding the mitochondrial connection: development and validation of biomarkers for classifying and treating systemic lupus erythematosus through bioinformatics and machine learning. BMC Rheumatol. 7, 44 (2023).中文译题:解析线粒体相关机制:通过生物信息学与机器学习开发并验证系统性红斑狼疮分类与治疗的生物标志物[173] Pham, T. C. P. et al. TNIK is a conserved regulator of glucose and lipid metabolism in obesity. Sci. Adv. 9, eadf7119 (2023).中文译题:TNIK是肥胖症中葡萄糖与脂质代谢的保守调控因子[174] Xu, Z. et al. A generative AI-discovered TNIK inhibitor for idiopathic pulmonary fibrosis: a randomized phase 2a trial. Nat. Med. https://doi.org/10.1038/s41591-025-03743-2 (2025).中文译题:生成式AI发现的TNIK抑制剂治疗特发性肺纤维化:一项随机2a期临床试验[175] Zitnik, M. AI-enabled drug discovery reaches clinical milestone. Nat. Med. 31, 2490–2491 (2025).中文译题:AI赋能的药物发现迎来临床里程碑[176] Besse-Patin, A. et al. Effect of endurance training on skeletal muscle myokine expression in obese men: identification of apelin as a novel myokine. Int. J. Obes. 38, 707–713 (2014).中文译题:耐力训练对肥胖男性骨骼肌肌因子表达的影响:apelin作为新型肌因子的识别[177] Fujie, S. et al. Reduction of arterial stiffness by exercise training is associated with increasing plasma apelin level in middle-aged and older adults. PLoS One 9, e93545 (2014).中文译题:运动训练降低中老年人动脉僵硬度与血浆apelin水平升高相关[178] Vinel, C. et al. The exerkine apelin reverses age-associated sarcopenia. Nat. Med. 24, 1360–1371 (2018).中文译题:运动因子apelin可逆转衰老相关肌少症[179] Wang, Y. et al. Oral-096 The apelin receptor agonist azelaprag reduces weight gain & improves body composition in DIO mice. Obesity 32, 5–54 (2024).中文译题:apelin受体激动剂azelaprag可减少饮食诱导肥胖小鼠的体重增加并改善身体组成[180] Mejzini, R. et al. ALS genetics, mechanisms, and therapeutics: where are we now? Front. Neurosci. 13, 1310 (2019).中文译题:肌萎缩侧索硬化症的遗传学、机制与治疗:研究现状[181] Ilieva, H., Vullaganti, M. & Kwan, J. Advances in molecular pathology, diagnosis, and treatment of amyotrophic lateral sclerosis. BMJ 383, e075037 (2023).中文译题:肌萎缩侧索硬化症的分子病理学、诊断与治疗研究进展[182] Shi, Y. et al. Haploinsufficiency leads to neurodegeneration in C9ORF72 ALS/FTD human induced motor neurons. Nat. Med. 24, 313–325 (2018).中文译题:C9ORF72单倍剂量不足在家族性肌萎缩侧索硬化症/额颞叶痴呆iPSC来源运动神经元中引发神经退行性变[183] Hung, S. T. et al. PIKFYVE inhibition mitigates disease in models of diverse forms of ALS. Cell 186, 786–802.e28 (2023).中文译题:PIKFYVE抑制可在多种肌萎缩侧索硬化症模型中缓解疾病进展[184] Terstappen, G. C., Schlüpen, C., Raggiaschi, R. & Gaviraghi, G. Target deconvolution strategies in drug discovery. Nat. Rev. Drug. Discov. 6, 891–903 (2007).中文译题:药物发现中的靶点去卷积策略[185] Wang, X. et al. A novel approach for target deconvolution from phenotype-based screening using knowledge graph. Sci. Rep. 15, 2414 (2025).中文译题:基于知识图谱的表型筛选靶点去卷积新方法[186] Allen, J. E. et al. Discovery and clinical introduction of first-in-class imipridone ONC201. Oncotarget 7, 74380–74392 (2016).中文译题:首创咪唑酮类药物ONC201的发现与临床应用[187] Anderson, P. M. et al. Phase II study of ONC201 in neuroendocrine tumors including pheochromocytoma–paraganglioma and desmoplastic small round cell tumor. Clin. Cancer Res. 28, 1773–1782 (2022).中文译题:ONC201治疗神经内分泌肿瘤(包括嗜铬细胞瘤-副神经节瘤与促结缔组织增生性小圆细胞肿瘤)的2期临床研究[188] Ishizawa, J. et al. Mitochondrial ClpP-mediated proteolysis induces selective cancer cell lethality. Cancer Cell 35, 721–737.e9 (2019).中文译题:线粒体ClpP介导的蛋白水解诱导选择性的癌细胞死亡[189] Graves, P. R. et al. Mitochondrial protease ClpP is a target for the anticancer compounds ONC201 and related analogues. ACS Chem. Biol. 14, 1020–1029 (2019).中文译题:线粒体蛋白酶ClpP是抗肿瘤化合物ONC201及其类似物的作用靶点[190] Price, E. et al. What is the real value of omics data? Enhancing research outcomes and securing long-term data excellence. Nucleic Acids Res. 52, 12130–12140 (2024).中文译题:组学数据的真正价值:提升研究成果与保障长期数据质量[191] Bottini, S., Emmert-Streib, F. & Franco, L. Editorial: AI and multi-omics for rare diseases: challenges, advances and perspectives, volume II. Front. Mol. Biosci. 9, 986749 (2022).中文译题:编者按:罕见病研究中的AI与多组学:挑战、进展与展望(第二卷)[192] All of Us Research Program Genomics Investigators Genomic data in the All of Us Research Program. Nature 627, 340–346 (2024).中文译题:“我们所有人”研究计划中的基因组数据[193] O’Doherty, K. C. et al. Toward better governance of human genomic data. Nat. Genet. 53, 2–8 (2021).中文译题:迈向更完善的人类基因组数据治理体系[194] Sun, K. Y. et al. A deep catalogue of protein-coding variation in 983,578 individuals. Nature 631, 583–592 (2024).中文译题:983578例个体的蛋白编码变异深度目录[195] Errington, T. M. et al. Investigating the replicability of preclinical cancer biology. eLife 10, e71601 (2021).中文译题:临床前癌症生物学研究的可重复性调查[196] Rodgers, P. & Collings, A. What have we learned? eLife https://doi.org/10.7554/eLife.75830 (2021).中文译题:我们学到了什么?[197] Lu, K., Yang, G. & Wang, X. Topics emerged in the biomedical field and their characteristics. Technol. Forecast. Soc. Change 174, 121218 (2022).中文译题:生物医学领域的新兴主题及其特征[198] Krawczyk, B. Learning from imbalanced data: open challenges and future directions. Prog. Artif. Intell. 5, 221–232 (2016).中文译题:不平衡数据学习:开放挑战与未来方向[199] Oprea, T. I. et al. Unexplored therapeutic opportunities in the human genome. Nat. Rev. Drug. Discov. 17, 317–332 (2018).中文译题:人类基因组中尚未被探索的治疗机会[200] Picard, M., Scott-Boyer, M. P., Bodein, A., Périn, O. & Droit, A. Integration strategies of multi-omics data for machine learning analysis. Comput. Struct. Biotechnol. J. 19, 3735–3746 (2021).中文译题:面向机器学习分析的多组学数据整合策略[201] Adossa, N., Khan, S., Rytkönen, K. T. & Elo, L. L. Computational strategies for single-cell multi-omics integration. Comput. Struct. Biotechnol. J. 19, 2588–2596 (2021).中文译题:单细胞多组学整合的计算策略[202] Acosta, J. N., Falcone, G. J., Rajpurkar, P. & Topol, E. J. Multimodal biomedical AI. Nat. Med. 28, 1773–1784 (2022).中文译题:多模态生物医学人工智能
[203] Chen, T., Philip, M., Le Cao, K. A. & Tyagi, S. A multi-modal data harmonisation approach for discovery of COVID-19 drug targets. Brief. Bioinform 22, bbab185 (2021).中文译题:面向COVID-19药物靶点发现的多模态数据协调方法[204] Chaudhary, K., Poirion, O. B., Lu, L. & Garmire, L. X. Deep Learning-based multi-omics integration robustly predicts survival in liver cancer. Clin. Cancer Res. 24, 1248–1259 (2018).中文译题:基于深度学习的多组学整合可稳健预测肝癌患者生存情况[205] Hao, Y. et al. Integrated analysis of multimodal single-cell data. Cell 184, 3573–3587.e29 (2021).中文译题:多模态单细胞数据的整合分析[206] Elbadawi, M., Gaisford, S. & Basit, A. W. Advanced machine-learning techniques in drug discovery. Drug. Discov. Today 26, 769–777 (2021).中文译题:药物发现中的先进机器学习技术[207] Castelvecchi, D. Can we open the black box of AI? Nature 538, 20–23 (2016).中文译题:我们能否打开AI的黑箱?[208] Hie, B., Cho, H. & Berger, B. Realizing private and practical pharmacological collaboration. Science 362, 347–350 (2018).中文译题:实现隐私安全且实用的药理学合作[209] Jiménez-Luna, J., Grisoni, F. & Schneider, G. Drug discovery with explainable artificial intelligence. Nat. Mach. Intell. 2, 573–584 (2020).中文译题:基于可解释人工智能的药物发现[210] Patel, R. et al. Retrieve to explain: evidence-driven predictions for explainable drug target identification. In Proc. 63rd Annual Meeting of the Association for Computational Linguistics Vol. 1 (eds Che, W. et al.) 3328–3370 (Association for Computational Linguistics, 2025).中文译题:检索式解释:面向可解释药物靶点识别的证据驱动预测[211] Elmarakeby, H. A. et al. Biologically informed deep neural network for prostate cancer discovery. Nature 598, 348–352 (2021).中文译题:生物学信息知情的深度神经网络用于前列腺癌发现[212] Zong, N. et al. BETA: a comprehensive benchmark for computational drug-target prediction. Brief. Bioinform 23, bbac199 (2022).中文译题:BETA:面向计算药物靶点预测的综合基准测试集[213] Shayakhmetov, R. et al. Molecular generation for desired transcriptome changes with adversarial autoencoders. Front. Pharmacol. 11, 269 (2020).中文译题:基于对抗自编码器实现靶向转录组变化的分子生成[214] Vinas, R., Andres-Terre, H., Lio, P. & Bryson, K. Adversarial generation of gene expression data. Bioinformatics 38, 730–737 (2022).中文译题:基因表达数据的对抗生成[215] Dolezal, J. M. et al. Deep learning generates synthetic cancer histology for explainability and education. npj Precis. Oncol. 7, 49 (2023).中文译题:基于深度学习生成合成癌症组织学图像,用于模型可解释性与教学[216] Giuffrè, M. & Shung, D. L. Harnessing the power of synthetic data in healthcare: innovation, application, and privacy. npj Digit. Med. 6, 186 (2023).中文译题:驾驭医疗健康领域合成数据的力量:创新、应用与隐私保护[217] San, O. The digital twin revolution. Nat. Comput. Sci. 1, 307–308 (2021).中文译题:数字孪生革命[218] Ren, Y., Pieper, A.A., Cummings, J.L., Cheng, F. Single-cell digital twins identify drug targets and repurposable medicine in Alzheimer’s disease. Alzheimers Dement 21, e102982 (2025).中文译题:单细胞数字孪生识别阿尔茨海默病的药物靶点与可重定位药物
论文官方引用格式
Pun, F.W., Podolskiy, D., Izumchenko, E. et al. Target identification and assessment in the era of AI. Nat Rev Drug Discov (2026). https://doi.org/10.1038/s41573-026-01412-8
生物智能:在生物先进产业场景中构建“状态感知-实时认知-自主决策-精准执行-学习提升”的生物科学智能(Biology_and_AI);实现生物产业转型升级、DT驱动业务、价值创新创造的产业互联生态链。
生物产业+物理AI=生物智能
产业智能官:Science_and_AI
加入知识星球“生物智能研究院”:生物产业OT技术(自动化+机器人+工艺+精益)和新一代IT技术(云计算+物联网+区块链+大数据+人工智能)深度融合,在场景中构建“状态感知-实时认知-自主决策-精准执行-学习提升”的生物科学智能;实现生物产业转型升级、DT驱动业务、价值创新创造的产业互联生态链。
生物科学智能作为第四次工业革命的核心驱动力,将进一步释放历次科技革命和产业变革积蓄的巨大能量,并创造新的强大引擎;重构设计、生产、供应链和服务等经济活动各环节,形成从宏观到微观各领域的智能化新需求,催生新技术、新产品、新产业、新业态和新模式;引发经济结构重大变革,深刻改变人类生产生活方式和思维模式,实现社会生产力的整体跃升。
生物产业智能化技术分支用来的今天,从业者必须了解如何将生物科学智能全面渗入整个公司、产品、业务等商业场景中,利用生物科学智能形成数字化、网络化和智能化力量,实现行业的重新布局、企业的重新构建和焕然新生。
版权声明:产业智能官(ID:Science_and_AI)发表的文章,除非确实无法确认,我们都会注明作者和来源,涉权请联系协商解决,联系、投稿邮箱:wolongzy@qq.com
2026-02-10
Product Sales Excluding Veklury Increased 4% Year-Over-Year to $28.0 billion for Full Year 2025
Biktarvy Sales Increased 7% Year-Over-Year to $14.3 billion for Full Year 2025
FOSTER CITY, Calif.--(BUSINESS WIRE)-- Gilead Sciences, Inc. (Nasdaq: GILD) announced today its results of operations for the fourth quarter and full year 2025.
“Our fourth quarter and full-year results close out a very strong year for Gilead overall, including the successful U.S. launch of Yeztugo, the world’s first twice-yearly HIV prevention therapy, and continued growth for Biktarvy and Descovy,” said Daniel O’Day, Gilead’s Chairman and Chief Executive Officer. “In 2026, our potential new launches include two cancer therapies and an additional HIV treatment option, and we look forward to building on the launches of Yeztugo and Livdelzi for liver disease. As we continue to increase our positive impact on healthcare, Gilead is well positioned for continued growth in 2026 and beyond.”
Fourth Quarter 2025 Financial Results
Total fourth quarter 2025 revenues increased 5% to $7.9 billion compared to the same period in 2024, primarily driven by higher sales of HIV and Liver Disease products, partially offset by lower sales of Veklury® (remdesivir). Diluted earnings per share (“EPS”) was $1.74 in the fourth quarter 2025 compared to $1.42 in the same period in 2024. The increase was primarily driven by higher income tax benefits, net unrealized gains from equity securities and higher product sales, as well as lower selling, general and administrative (“SG&A”) expenses. The increase was partially offset by higher acquired in-process research and development (“IPR&D”) expenses and an IPR&D impairment charge related to assets acquired as part of the MYR GmbH (“MYR”) acquisition. Non-GAAP diluted EPS of $1.86 in the fourth quarter 2025 compared to $1.90 in the same period in 2024. The decrease was primarily driven by higher acquired IPR&D expenses, partially offset by higher product sales and lower SG&A expenses. As of December 31, 2025, Gilead had $10.6 billion of cash, cash equivalents and marketable debt securities compared to $10.0 billion as of December 31, 2024. During the fourth quarter 2025, Gilead generated $3.3 billion in operating cash flow. During the fourth quarter 2025, Gilead paid dividends of $1.0 billion and repurchased $230 million of common stock.
Fourth Quarter 2025 Product Sales
Total fourth quarter 2025 product sales increased 5% to $7.9 billion compared to the same period in 2024. Total fourth quarter 2025 product sales excluding Veklury increased 7% to $7.7 billion compared to the same period in 2024, primarily due to higher sales of HIV and Liver Disease products.
HIV product sales increased 6% to $5.8 billion in the fourth quarter 2025 compared to the same period in 2024, primarily driven by higher demand for HIV prevention and treatment.
Biktarvy®(bictegravir 50mg/emtricitabine (“FTC”) 200mg/tenofovir alafenamide (“TAF”) 25mg) sales increased 5% to $4.0 billion in the fourth quarter 2025 compared to the same period in 2024, primarily driven by higher demand and favorable inventory dynamics, partially offset by lower average realized price. Descovy®(FTC 200mg/TAF 25mg) sales increased 33% to $819 million in the fourth quarter 2025 compared to the same period in 2024, primarily driven by higher average realized price and higher demand for HIV prevention.
The Liver Disease portfolio sales increased 17% to $844 million in the fourth quarter 2025 compared to the same period in 2024, primarily driven by higher demand for Livdelzi® (seladelpar).
Veklury sales decreased 37% to $212 millionin the fourth quarter 2025 compared to the same period in 2024, primarily driven by lower rates of COVID-19-related hospitalizations.
Cell Therapy product sales decreased 6% to $458 million in the fourth quarter 2025 compared to the same period in 2024, reflecting ongoing competitive headwinds.
Yescarta® (axicabtagene ciloleucel) sales decreased 6% to $368 million in the fourth quarter 2025 compared to the same period in 2024, primarily driven by in- and out-of-class competition. Tecartus® (brexucabtagene autoleucel) sales decreased 9% to $90 million in the fourth quarter 2025 compared to the same period in 2024, primarily driven by in-class competition.
Trodelvy® (sacituzumab govitecan-hziy) sales increased 8% to $384 million in the fourth quarter 2025 compared to the same period in 2024, primarily driven by higher demand in breast cancer treatment.
Fourth Quarter 2025 Product Gross Margin, Operating Expenses and Effective Tax Rate
Product gross margin remained relatively flat at 79.5% in the fourth quarter 2025 compared to 79.0% in the same period in 2024. Non-GAAP product gross margin was 86.8% in the fourth quarter 2025 compared to 86.7% in the same period in 2024. Research and development (“R&D”) expenses and non-GAAP R&D expenses were $1.6 billion in the fourth quarter 2025 and remained relatively flat compared to the same period in 2024. Acquired IPR&D expenses were $539 million in the fourth quarter 2025, primarily related to our acquisition of Interius BioTherapeutics, Inc. (“Interius”) and ongoing collaboration with Shenzhen Pregene Biopharma Co., Ltd. (“Pregene”). SG&A expenses were $1.8 billion in the fourth quarter 2025 compared to $1.9 billion in the same period in 2024, decreasing primarily due to lower expenses related to legal matters and corporate initiatives, partially offset by donations of equity securities made to the Gilead Foundation. Non-GAAP SG&A expenses were $1.7 billion in the fourth quarter 2025 compared to $1.9 billion in the same period in 2024, primarily due to lower expenses related to legal matters and corporate initiatives. The effective tax rate (“ETR”) was (5.0)% in the fourth quarter 2025 compared to 17.8% in the same period in 2024, primarily driven by a tax benefit from a settlement with a tax authority related to a prior year legal entity restructuring and a tax benefit from the IPR&D impairment charge related to assets acquired as part of the MYR acquisition. The non-GAAP ETR was 20.5% in the fourth quarter 2025 compared to 19.2% in the same period in 2024.
Full Year 2025 Financial Results
Total full year 2025 revenues increased 2% to $29.4 billion compared to 2024, broken down as follows: Total full year 2025 product sales increased 1% to $28.9 billion compared to 2024, primarily driven by higher sales of HIV and Liver Disease products, partially offset by lower sales of Veklury. Total full year 2025 royalty, contract and other revenues increased by approximately $383 million compared to 2024, primarily driven by revenue related to a previous sale of intellectual property not expected to reoccur. Diluted EPS was $6.78 in the full year 2025 compared to $0.38 in 2024. The increase was primarily driven by lower acquired IPR&D expenses, lower IPR&D impairments, higher net unrealized gains on equity investments, higher revenues and lower SG&A expenses, partially offset by higher tax expense. Non-GAAP diluted EPS was $8.15 in the full year 2025 compared to $4.62 in 2024. The increase was primarily driven by lower acquired IPR&D expenses, higher revenues, and lower SG&A expenses.
Total full year 2025 product sales increased 1% to $28.9 billion compared to 2024, primarily driven by higher sales of HIV and Liver Disease products, partially offset by lower sales of Veklury. Total full year 2025 royalty, contract and other revenues increased by approximately $383 million compared to 2024, primarily driven by revenue related to a previous sale of intellectual property not expected to reoccur.
Full Year 2025 Product Sales
Total full year 2025 product sales increased 1% to $28.9 billion compared to 2024. Total full year 2025 product sales excluding Veklury increased 4% to $28.0 billion compared to 2024, primarily due to higher sales of HIV and Liver Disease products.
HIV product sales increased 6% to $20.8 billion in the full year 2025 compared to 2024, primarily driven by higher demand for HIV treatment and prevention.
Biktarvy sales increased 7% to $14.3 billion in the full year 2025 compared to 2024, primarily driven by higher demand, partially offset by lower average realized price. Descovy sales increased 31% to $2.8 billion in the full year 2025 compared to 2024, primarily driven by higher demand and average realized price.
The Liver Disease portfolio sales increased 6% to $3.2 billion in the full year 2025 compared to 2024, primarily driven by higher demand for Livdelzi and products for chronic hepatitis B virus (“HBV”) and chronic hepatitis delta virus (“HDV”), partially offset by lower average realized price in products for chronic hepatitis C virus (“HCV”).
Veklury sales decreased 49% to $911 millionin the full year 2025 compared to 2024, primarily driven by lower COVID-19-related hospitalizations.
Cell Therapy product sales decreased 7% to $1.8 billion in the full year 2025 compared to 2024, reflecting ongoing competitive headwinds.
Yescarta sales decreased 5% to $1.5 billion in the full year 2025 compared to 2024, primarily driven by in- and out-of-class competition. Tecartus sales decreased 15% to $344 million in the full year 2025 compared to 2024, primarily driven by in-class competition.
Trodelvy sales increased 6% to $1.4 billion in the full year 2025 compared to 2024, primarily driven by higher demand in breast cancer treatment, partially offset by the indication withdrawal in bladder cancer treatment.
Full Year 2025 Product Gross Margin, Operating Expenses and Effective Tax Rate
Product gross margin remained relatively flat at 78.4% in the full year 2025 compared to 78.2% in 2024. Non-GAAP product gross margin was 86.4% in the full year 2025 compared to 86.2% in 2024. R&D expenses were $5.8 billion in the full year 2025 compared to $5.9 billion in 2024, decreasing primarily due to lower acquisition-related integration expenses and restructuring costs, as well as lower study-related and clinical manufacturing expenses. Non-GAAP R&D expenses were $5.7 billion in the full year 2025, decreasing slightly compared to 2024 due to lower study-related and clinical manufacturing expenses. Acquired IPR&D expenses were $1.0 billion in the full year 2025, primarily related to the acquisition of Interius and collaborations with LEO Pharma A/S and Pregene. SG&A expenses were $5.8 billion in the full year 2025 compared to $6.1 billion in 2024, decreasing primarily due to lower corporate, legal, acquisition-related integration and restructuring expenses, partially offset by higher HIV promotional expenses and donations of equity securities made to the Gilead Foundation. Non-GAAP SG&A expenses were $5.6 billion in the full year 2025 compared to $5.9 billion in 2024, decreasing primarily due to lower expenses related to corporate initiatives and legal matters, partially offset by higher HIV promotional expenses. The ETR was 13.1% in the full year 2025 compared to 30.5% in 2024, primarily driven by the impact of the prior year non-deductible acquired IPR&D charge for the acquisition of CymaBay Therapeutics, Inc. (“CymaBay”), partially offset by the tax impact of the prior year higher IPR&D impairment charges. The non-GAAP ETR was 18.3% in the full year 2025 compared to 25.9% in 2024, primarily driven by the prior year non-deductible acquired IPR&D charge for the acquisition of CymaBay.
Guidance and Outlook
For the full year 2026, Gilead expects:
(in millions, except per share amounts)
February 10, 2026 Guidance
Low End
High End
Product sales
$
29,600
$
30,000
Product sales excluding Veklury
$
29,000
$
29,400
Veklury
$
600
$
600
Diluted EPS
$
6.75
$
7.15
Non-GAAP diluted EPS
$
8.45
$
8.85
Additional information and a reconciliation between GAAP and non-GAAP financial information for the 2026 guidance is provided in the accompanying tables. The financial guidance is subject to a number of risks and uncertainties. See the Forward-Looking Statements section below.
Key Updates Since Our Last Quarterly Release
Virology
Announced positive topline Phase 3 results from the ARTISTRY-1 and ARTISTRY-2 trials, evaluating our investigational daily oral single-tablet regimen of bictegravir 75mg and lenacapavir 50mg (“BIC/LEN”) for virologically suppressed adults with HIV. BIC/LEN met its primary endpoints demonstrating non-inferiority to baseline multi-tablet antiviral regimens (ARTISTRY-1) and Biktarvy (ARTISTRY-2). Exercised option to license investigational herpes simplex virus helicase-primase inhibitor programs ABI-1179 and ABI-5366 from Assembly Biosciences, Inc. (“Assembly”). Announced the first delivery of lenacapavir for PrEP in sub-Saharan African countries Eswatini and Zambia through the U.S. President’s Emergency Plan for AIDS Relief.
Oncology
Announced that the Phase 3 ASCENT-07 study evaluating the investigational use of Trodelvy versus chemotherapy in first-line post-endocrine HR+/HER2- metastatic breast cancer did not meet its primary endpoint of progression-free survival as assessed by Blinded Independent Central Review. Overall survival, a secondary endpoint, was not mature at the time of the primary analysis, however, a favorable early trend compared to chemotherapy was observed in the Trodelvy arm. In addition, no new safety signals were identified in this patient population. The results from this study were presented at the 2025 San Antonio Breast Cancer Symposium. Announced the discontinuation of the Phase 3 STAR-221 study, in partnership with Arcus Biosciences, Inc. (“Arcus”), evaluating the anti-TIGIT antibody domvanalimab (“dom”) plus zimberelimab (“zim”) and chemotherapy in first-line HER2- advanced gastric and esophageal cancers. The decision was based on the recommendation of the Independent Data Monitoring Committee, following review of data from a pre-specified interim analysis. Additionally, Gilead and Arcus will discontinue the Phase 2 EDGE-Gastric study evaluating dom and zim regimens in upper gastrointestinal cancers. Dom and zim are investigational products and are not approved anywhere globally.
Cell Therapy
Announced a new label update for Yescarta that removes a limitation around Primary Central Nervous System Lymphoma, an ultra-rare cancer affecting a highly vulnerable patient population. Yescarta is the only CAR-T therapy in relapsed or refractory large B-cell lymphoma (“R/R LBCL”) to have this limitation removed. Presented new positive data, with our partner Arcellx, Inc. (“Arcellx”), from the pivotal Phase 2 iMMagine-1 trial evaluating the investigational CAR T-cell therapy anitocabtagene autoleucel in 4L+ R/R multiple myeloma at the 2025 American Society of Hematology (“ASH”). Presented initial Phase 1 data for KITE-753 and KITE-363, evaluating two investigational bicistronic CAR T-cell therapies in patients with R/R LBCL at ASH 2025. Presented a new analysis of Yescarta from the Phase 3 ZUMA-7 and Phase 2 ALYCANTE study in patients with R/R LBCL at ASH 2025. The data demonstrated consistent benefits of Yescarta among patients with R/R LBCL, including those ineligible for previous standard of care chemotherapy and stem cell transplant.
Inflammation
Presented new long-term data from the Phase 3 ASSURE study for Livdelzi, which reinforce the safety and efficacy of Livdelzi for people living with primary biliary cholangitis over 3 years, including data on switching from obeticholic acid. The data were presented at the American Association for the Study of Liver Diseases meeting.
Corporate
The Board declared a quarterly dividend of $0.82 per share of common stock for the first quarter of 2026. The dividend is payable on March 30, 2026, to stockholders of record at the close of business on March 13, 2026. Future dividends will be subject to Board approval. Appointed Keeley Cain Wettan as Executive Vice President, General Counsel, Legal and Compliance. Announced an agreement with the U.S. government to lower the cost of medicines for Americans, reinforcing a commitment to U.S.-based innovation, affordability and global health leadership.
Certain amounts and percentages in this press release may not sum or recalculate due to rounding.
Conference Call
At 1:30 p.m. Pacific Time today, Gilead will host a conference call to discuss Gilead’s results. A live webcast will be available on http://investors.gilead.com and will be archived on www.gilead.com for one year.
Non-GAAP Financial Information
The information presented in this document has been prepared in accordance with U.S. generally accepted accounting principles (“GAAP”), unless otherwise noted as non-GAAP. Management believes non-GAAP information is useful for investors, when considered in conjunction with Gilead’s GAAP financial information, because management uses such information internally for its operating, budgeting and financial planning purposes. Non-GAAP information is not prepared under a comprehensive set of accounting rules and should only be used to supplement an understanding of Gilead’s operating results as reported under GAAP. Non-GAAP financial information generally excludes acquisition-related expenses including amortization of acquired intangible assets and other items that are considered unusual or not representative of underlying trends of Gilead’s business, fair value adjustments of equity securities and discrete and related tax charges or benefits associated with such exclusions as well as changes in tax-related laws and guidelines, transfers of intangible assets between certain legal entities, and legal entity restructurings. Although Gilead consistently excludes the amortization of acquired intangible assets from the non-GAAP financial information, management believes that it is important for investors to understand that such intangible assets were recorded as part of acquisitions and contribute to ongoing revenue generation.Non-GAAP measures may be defined and calculated differently by other companies in the same industry. Reconciliations of the non-GAAP financial measures to the most directly comparable GAAP financial measures are provided in the accompanying tables.
About Gilead Sciences
Gilead Sciences, Inc. is a biopharmaceutical company that has pursued and achieved breakthroughs in medicine for more than three decades, with the goal of creating a healthier world for all people. The company is committed to advancing innovative medicines to prevent and treat life-threatening diseases, including HIV, viral hepatitis, COVID-19, cancer and inflammation. Gilead operates in more than 35 countries worldwide, with headquarters in Foster City, California.
Forward-Looking Statements
Statements included in this press release that are not historical in nature are forward-looking statements within the meaning of the Private Securities Litigation Reform Act of 1995. Gilead cautions readers that forward-looking statements are subject to certain risks and uncertainties that could cause actual results to differ materially. These risks and uncertainties include those relating to: Gilead’s ability to achieve its full year 2026 financial guidance, including as a result of the uncertainty of the amount and timing of Veklury revenues, the impact from Medicare Part D pricing reform in the Inflation Reduction Act, the expiration of subsidies related to the Affordable Care Act, our most-favored-nation pricing agreement with the U.S. government, changes in U.S. regulatory or legislative policies, and changes in U.S. trade policies, including tariffs; Gilead’s ability to make progress on any of its long-term ambitions or priorities laid out in its corporate strategy; Gilead’s ability to accelerate or sustain revenues for its virology, oncology, inflammation and other programs; Gilead’s ability to realize the potential benefits of acquisitions, collaborations or licensing arrangements, including the arrangements with Arcellx, Arcus, Assembly and the U.S. government; the risk that Gilead’s U.S. manufacturing and R&D investment may not achieve their intended benefits; patent protection and estimated loss of exclusivity for our products and product candidates; Gilead’s ability to initiate, progress or complete clinical trials within currently anticipated timeframes or at all, the possibility of unfavorable results from ongoing and additional clinical trials, including those involving anitocabtagene autoleucel, axicabtagene ciloleucel, bictegravir, domvanalimab, lenacapavir, sacituzumab govitecan-hziy, seladelpar, zimberelimab, ABI-1179, ABI-5366, KITE-753 and KITE-363 (such as ALYCANTE, ARTISTRY-1, ARTISTRY-2, ASCENT-07, ASSURE, EDGE-Gastric, iMMagine-1, STAR-221 and ZUMA-7), and the risk that safety and efficacy data from clinical trials may not warrant further development of Gilead’s product candidates or the product candidates of Gilead’s strategic partners; Gilead’s ability to resolve the issues cited by the FDA in pending clinical holds to the satisfaction of the FDA and the risk that FDA may not remove such clinical holds, in whole or in part, in a timely manner or at all; Gilead’s ability to submit new drug applications for new product candidates or expanded indications in the currently anticipated timelines; Gilead’s ability to receive or maintain regulatory approvals in a timely manner or at all, and the risk that any such approvals, if granted, may be subject to significant limitations on use and may be subject to withdrawal or other adverse actions by the applicable regulatory authority; Gilead’s ability to successfully commercialize its products; the risk of potential disruptions to the manufacturing and supply chain of Gilead’s products; pricing and reimbursement pressures from government agencies and other third parties, including required rebates and other discounts; a larger than anticipated shift in payer mix to more highly discounted payer segments; market share and price erosion caused by the introduction of generic versions of Gilead products; the risk that physicians and patients may not see advantages of Gilead’s products over other therapies and may therefore be reluctant to prescribe the products; Gilead’s ability to effectively manage the access strategy relating to lenacapavir for HIV PrEP, subject to necessary regulatory approvals; and other risks identified from time to time in Gilead’s reports filed with the SEC, including annual reports on Form 10-K, quarterly reports on Form 10-Q and current reports on Form 8-K. In addition, Gilead makes estimates and judgments that affect the reported amounts of assets, liabilities, revenues and expenses and related disclosures. Gilead bases its estimates on historical experience and on various other market specific and other relevant assumptions that it believes to be reasonable under the circumstances, the results of which form the basis for making judgments about the carrying values of assets and liabilities that are not readily apparent from other sources. There may be other factors of which Gilead is not currently aware that may affect matters discussed in the forward-looking statements and may also cause actual results to differ significantly from these estimates. Further, results for the quarter and full year ended December 31, 2025 are not necessarily indicative of operating results for any future periods. Gilead directs readers to its press releases, annual reports on Form 10-K, quarterly reports on Form 10-Q and other subsequent disclosure documents filed with the SEC. Gilead claims the protection of the Safe Harbor contained in the Private Securities Litigation Reform Act of 1995 for forward-looking statements.
The reader is cautioned that forward-looking statements are not guarantees of future performance and is cautioned not to place undue reliance on these forward-looking statements. All forward-looking statements are based on information currently available to Gilead and Gilead assumes no obligation to update or supplement any such forward-looking statements other than as required by law. Any forward-looking statements speak only as of the date hereof or as of the dates indicated in the statements.
Additional information is available on our Investor Relations website, https://investors.gilead.com. Among other things, an estimate of Acquired IPR&D expenses is expected to be made available on the Quarterly Results page within the first ten (10) days after the end of each quarter.
Gilead owns or has rights to various trademarks, copyrights and trade names used in its business, including the following: GILEAD®, GILEAD SCIENCES®, KITE®, AMBISOME®, ATRIPLA®, BIKTARVY®, CAYSTON®, COMPLERA®, DESCOVY®, DESCOVY FOR PREP®, EMTRIVA®, EPCLUSA®, EVIPLERA®, GENVOYA®, HARVONI®, HEPCLUDEX®, HEPSERA®, JYSELECA®, LIVDELZI®/LYVDELZI®, LETAIRIS®, ODEFSEY®, SOVALDI®, STRIBILD®, SUNLENCA® , TECARTUS®, TRODELVY®, TRUVADA®, TRUVADA FOR PREP®, TYBOST®, VEKLURY®, VEMLIDY®, VIREAD®, VOSEVI®, YESCARTA®, YEZTUGO®/YEYTUO® and ZYDELIG®. Other trademarks and trade names are the property of their respective owners.
For more information on Gilead Sciences, Inc., please visit www.gilead.com or call the Gilead Public Affairs Department at 1-800-GILEAD-5 (1-800-445-3235).
GILEAD SCIENCES, INC. CONDENSED CONSOLIDATED STATEMENTS OF OPERATIONS (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions, except per share amounts)
2025
2024
2025
2024
Revenues:
Product sales
$
7,903
$
7,536
$
28,915
$
28,610
Royalty, contract and other revenues
22
33
527
144
Total revenues
7,925
7,569
29,443
28,754
Costs and expenses:
Cost of goods sold
1,623
1,581
6,234
6,251
Research and development expenses
1,584
1,641
5,799
5,907
Acquired in-process research and development expenses
539
(11
)
1,024
4,663
In-process research and development impairments
400
—
590
4,180
Selling, general and administrative expenses
1,794
1,906
5,774
6,091
Total costs and expenses
5,940
5,118
19,421
27,092
Operating income
1,984
2,451
10,022
1,662
Interest expense
255
248
1,024
977
Other (income) expense, net
(349
)
35
(798
)
(6
)
Income before income taxes
2,078
2,168
9,796
690
Income tax (benefit) expense
(105
)
385
1,286
211
Net income
2,183
1,783
8,510
480
Net income attributable to noncontrolling interest
—
—
—
—
Net income attributable to Gilead
$
2,183
$
1,783
$
8,510
$
480
Basic earnings per share attributable to Gilead
$
1.76
$
1.43
$
6.84
$
0.38
Diluted earnings per share attributable to Gilead
$
1.74
$
1.42
$
6.78
$
0.38
Shares used in basic earnings per share attributable to Gilead calculation
1,242
1,248
1,244
1,247
Shares used in diluted earnings per share attributable to Gilead calculation
1,253
1,259
1,255
1,255
Supplemental Information:
Cash dividends declared per share
$
0.79
$
0.77
$
3.16
$
3.08
Product gross margin
79.5
%
79.0
%
78.4
%
78.2
%
Research and development expenses as a % of revenues
20.0
%
21.7
%
19.7
%
20.5
%
Selling, general and administrative expenses as a % of revenues
22.6
%
25.2
%
19.6
%
21.2
%
Operating margin
25.0
%
32.4
%
34.0
%
5.8
%
Effective tax rate
(5.0
)%
17.8
%
13.1
%
30.5
%
GILEAD SCIENCES, INC. TOTAL REVENUE SUMMARY (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions, except percentages)
2025
2024
Change
2025
2024
Change
Product sales:
HIV
$
5,801
$
5,452
6
%
$
20,752
$
19,612
6
%
Liver Disease
844
719
17
%
3,217
3,021
6
%
Oncology
842
843
—
%
3,236
3,289
(2
)%
Other
205
184
11
%
799
889
(10
)%
Total product sales excluding Veklury
7,691
7,198
7
%
28,004
26,811
4
%
Veklury
212
337
(37
)%
911
1,799
(49
)%
Total product sales
7,903
7,536
5
%
28,915
28,610
1
%
Royalty, contract and other revenues
22
33
(35
)%
527
144
NM
Total revenues
$
7,925
$
7,569
5
%
$
29,443
$
28,754
2
%
GILEAD SCIENCES, INC. NON-GAAP FINANCIAL INFORMATION(1) (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions, except percentages)
2025
2024
Change
2025
2024
Change
Non-GAAP:
Cost of goods sold
$
1,044
$
1,002
4
%
$
3,919
$
3,936
—
%
Research and development expenses
$
1,565
$
1,612
(3
)%
$
5,687
$
5,732
(1
)%
Acquired IPR&D expenses
$
539
$
(11
)
NM
$
1,024
$
4,663
(78
)%
Selling, general and administrative expenses
$
1,688
$
1,852
(9
)%
$
5,619
$
5,903
(5
)%
Other (income) expense, net
$
(97
)
$
(91
)
7
%
$
(348
)
$
(279
)
24
%
Diluted earnings per share attributable to Gilead
$
1.86
$
1.90
(2
)%
$
8.15
$
4.62
77
%
Shares used in non-GAAP diluted earnings per share attributable to Gilead calculation
1,253
1,259
—
%
1,255
1,255
—
%
Product gross margin
86.8
%
86.7
%
9 bps
86.4
%
86.2
%
20 bps
Research and development expenses as a % of revenues
19.7
%
21.3
%
-155 bps
19.3
%
19.9
%
-62 bps
Selling, general and administrative expenses as a % of revenues
21.3
%
24.5
%
-317 bps
19.1
%
20.5
%
-144 bps
Operating margin
39.0
%
41.1
%
-217 bps
44.8
%
29.6
%
NM
Effective tax rate
20.5
%
19.2
%
135 bps
18.3
%
25.9
%
-765 bps
NM
- Not Meaningful
(1)
Refer to Non-GAAP Financial Information section above for further disclosures on non-GAAP financial measures. A reconciliation between GAAP and non-GAAP financial information is provided in the tables below.
GILEAD SCIENCES, INC. RECONCILIATION OF GAAP TO NON-GAAP FINANCIAL INFORMATION (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions, except percentages and per share amounts)
2025
2024
2025
2024
Cost of goods sold reconciliation:
GAAP cost of goods sold
$
1,623
$
1,581
$
6,234
$
6,251
Acquisition-related – amortization(1)
(576
)
(579
)
(2,310
)
(2,316
)
Restructuring
(4
)
—
(4
)
—
Non-GAAP cost of goods sold
$
1,044
$
1,002
$
3,919
$
3,936
Product gross margin reconciliation:
GAAP product gross margin
79.5
%
79.0
%
78.4
%
78.2
%
Acquisition-related – amortization(1)
7.3
%
7.7
%
8.0
%
8.1
%
Restructuring
—
%
—
%
—
%
—
%
Non-GAAP product gross margin
86.8
%
86.7
%
86.4
%
86.2
%
Research and development expenses reconciliation:
GAAP research and development expenses
$
1,584
$
1,641
$
5,799
$
5,907
Acquisition-related – other costs(2)
(3
)
—
(43
)
(78
)
Restructuring
(16
)
(30
)
(69
)
(98
)
Non-GAAP research and development expenses
$
1,565
$
1,612
$
5,687
$
5,732
IPR&D impairment reconciliation:
GAAP IPR&D impairment
$
400
$
—
$
590
$
4,180
IPR&D impairment
(400
)
—
(590
)
(4,180
)
Non-GAAP IPR&D impairment
$
—
$
—
$
—
$
—
Selling, general and administrative expenses reconciliation:
GAAP selling, general and administrative expenses
$
1,794
$
1,906
$
5,774
$
6,091
Acquisition-related – other costs(2)
—
(8
)
—
(97
)
Restructuring
(17
)
(46
)
(65
)
(91
)
Other(3)
(89
)
—
(89
)
—
Non-GAAP selling, general and administrative expenses
$
1,688
$
1,852
$
5,619
$
5,903
Operating income reconciliation:
GAAP operating income
$
1,984
$
2,451
$
10,022
$
1,662
Acquisition-related – amortization(1)
576
579
2,310
2,316
Acquisition-related – other costs(2)
3
8
43
174
Restructuring
37
76
138
188
IPR&D impairment
400
—
590
4,180
Other(3)
89
—
89
—
Non-GAAP operating income
$
3,089
$
3,114
$
13,193
$
8,520
Operating margin reconciliation:
GAAP operating margin
25.0
%
32.4
%
34.0
%
5.8
%
Acquisition-related – amortization(1)
7.3
%
7.6
%
7.8
%
8.1
%
Acquisition-related – other costs(2)
—
%
0.1
%
0.1
%
0.6
%
Restructuring
0.5
%
1.0
%
0.5
%
0.7
%
IPR&D impairment
5.0
%
—
%
2.0
%
14.5
%
Other(3)
1.1
%
—
%
0.3
%
—
%
Non-GAAP operating margin
39.0
%
41.1
%
44.8
%
29.6
%
Other (income) expense, net reconciliation:
GAAP other (income) expense, net
$
(349
)
$
35
$
(798
)
$
(6
)
Gain (loss) from equity securities, net
252
(126
)
451
(274
)
Non-GAAP other (income) expense, net
$
(97
)
$
(91
)
$
(348
)
$
(279
)
GILEAD SCIENCES, INC. RECONCILIATION OF GAAP TO NON-GAAP FINANCIAL INFORMATION - (Continued) (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions, except percentages and per share amounts)
2025
2024
2025
2024
Income before income taxes reconciliation:
GAAP income before income taxes
$
2,078
$
2,168
$
9,796
$
690
Acquisition-related – amortization(1)
576
579
2,310
2,316
Acquisition-related – other costs(2)
3
8
43
174
Restructuring
37
76
138
188
IPR&D impairment
400
—
590
4,180
(Gain) loss from equity securities, net
(252
)
126
(451
)
274
Other(3)
89
—
89
—
Non-GAAP income before income taxes
$
2,930
$
2,956
$
12,517
$
7,822
Income tax (benefit) expense reconciliation:
GAAP income tax (benefit) expense
$
(105
)
$
385
$
1,286
$
211
Income tax effect of non-GAAP adjustments:
Acquisition-related – amortization(1)
118
121
478
484
Acquisition-related – other costs(2)
—
2
—
41
Restructuring
7
16
25
37
IPR&D impairment
87
—
137
1,051
Loss (gain) from equity securities, net
14
13
(20
)
(39
)
Discrete and related tax charges(4)
454
29
353
243
Other(3)
27
—
27
—
Non-GAAP income tax expense
$
601
$
566
$
2,287
$
2,028
Effective tax rate reconciliation:
GAAP effective tax rate
(5.0
)%
17.8
%
13.1
%
30.5
%
Income tax effect of above non-GAAP adjustments and discrete and related tax adjustments(4)
25.6
%
1.4
%
5.1
%
(4.6
)%
Non-GAAP effective tax rate
20.5
%
19.2
%
18.3
%
25.9
%
Net income attributable to Gilead reconciliation:
GAAP net income attributable to Gilead
$
2,183
$
1,783
$
8,510
$
480
Acquisition-related – amortization(1)
458
458
1,832
1,832
Acquisition-related – other costs(2)
3
6
43
134
Restructuring
30
59
113
151
IPR&D impairment
313
—
453
3,129
(Gain) loss from equity securities, net
(266
)
113
(431
)
313
Discrete and related tax charges(4)
(454
)
(29
)
(353
)
(243
)
Other(3)
63
—
63
—
Non-GAAP net income attributable to Gilead
$
2,329
$
2,390
$
10,230
$
5,795
Diluted earnings per share reconciliation:
GAAP diluted earnings per share
$
1.74
$
1.42
$
6.78
$
0.38
Acquisition-related – amortization(1)
0.37
0.36
1.46
1.46
Acquisition-related – other costs(2)
—
—
0.03
0.11
Restructuring
0.02
0.05
0.09
0.12
IPR&D impairment
0.25
—
0.36
2.49
(Gain) loss from equity securities, net
(0.21
)
0.09
(0.34
)
0.25
Discrete and related tax charges(4)
(0.36
)
(0.02
)
(0.28
)
(0.19
)
Other(3)
0.05
—
0.05
—
Non-GAAP diluted earnings per share
$
1.86
$
1.90
$
8.15
$
4.62
GILEAD SCIENCES, INC. RECONCILIATION OF GAAP TO NON-GAAP FINANCIAL INFORMATION - (Continued) (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions, except percentages and per share amounts)
2025
2024
2025
2024
Non-GAAP adjustment summary:
Cost of goods sold adjustments
$
579
$
579
$
2,314
$
2,315
Research and development expenses adjustments
19
29
112
176
IPR&D impairment adjustments
400
—
590
4,180
Selling, general and administrative expenses adjustments
106
54
155
188
Total non-GAAP adjustments to costs and expenses
1,104
663
3,171
6,858
Other (income) expense, net, adjustments
(252
)
126
(451
)
274
Total non-GAAP adjustments before income taxes
852
789
2,720
7,132
Income tax effect of non-GAAP adjustments above
(252
)
(152
)
(647
)
(1,574
)
Discrete and related tax charges(4)
(454
)
(29
)
(353
)
(243
)
Total non-GAAP adjustments to net income attributable to Gilead
$
146
$
607
$
1,719
$
5,315
(1)
Relates to amortization of acquired intangibles.
(2)
Adjustments include integration expenses and contingent consideration fair value adjustments associated with Gilead’s recent acquisitions.
(3)
(4)
Represents discrete and related deferred tax charges or benefits primarily associated with acquired intangible assets, transfers of intangible assets from a foreign subsidiary to Ireland and the United States, and legal entity restructurings.
GILEAD SCIENCES, INC. RECONCILIATION OF GAAP TO NON-GAAP 2026 FULL-YEAR GUIDANCE(1) (unaudited)
(in millions, except percentages and per share amounts)
Provided
February 10, 2026
Projected product gross margin GAAP to non-GAAP reconciliation:
GAAP projected product gross margin
~ 79.0%
Acquisition-related expenses
~ 8.0%
Non-GAAP projected product gross margin
~ 87.0%
Projected operating income GAAP to non-GAAP reconciliation:
GAAP projected operating income
$11,400 - $11,900
Acquisition-related and restructuring expenses
~ 2,400
Non-GAAP projected operating income
$13,800 - $14,300
Projected effective tax rate GAAP to non-GAAP reconciliation:
GAAP projected effective tax rate
~ 21%
Income tax effect of above non-GAAP adjustments, and discrete and related tax adjustments
(~ 1%)
Non-GAAP projected effective tax rate
~ 20%
Projected diluted EPS GAAP to non-GAAP reconciliation:
GAAP projected diluted EPS
$6.75 - $7.15
Acquisition-related and restructuring expenses, and discrete and related tax adjustments
~ 1.70
Non-GAAP projected diluted EPS
$8.45 - $8.85
(1)
Our full-year guidance excludes the potential impact of any (i) acquisitions or business development transactions that have not been executed, (ii) future fair value adjustments of equity securities and (iii) discrete tax charges or benefits associated with changes in tax related laws and guidelines that have not been enacted, as Gilead is unable to project such amounts. The non-GAAP full-year guidance includes non-GAAP adjustments to actual current period results as well as adjustments for the known future impact associated with events that have already occurred, such as future amortization of our intangible assets and the future impact of discrete and related deferred tax charges or benefits primarily associated with acquired intangible assets and in-process research and development, transfers of intangible assets from a foreign subsidiary to Ireland and the United States, and legal entity restructurings.
GILEAD SCIENCES, INC. CONDENSED CONSOLIDATED BALANCE SHEETS (unaudited)
December 31,
December 31,
(in millions)
2025
2024
Assets
Cash, cash equivalents and marketable debt securities
$
10,605
$
9,991
Accounts receivable, net
4,913
4,420
Inventories(1)
4,368
3,589
Property, plant and equipment, net
5,606
5,414
Intangible assets, net
16,978
19,948
Goodwill
8,314
8,314
Other assets
8,239
7,319
Total assets
$
59,023
$
58,995
Liabilities and Stockholders’ Equity
Current liabilities
$
11,813
$
12,004
Long-term liabilities
24,592
27,744
Stockholders’ equity(2)
22,618
19,246
Total liabilities and stockholders’ equity
$
59,023
$
58,995
(1)
Includes current and long-term inventories, which are disclosed separately in the notes to our financial statements in Form 10-K and Form 10-Q.
As of December 31, 2025 and December 31, 2024, there were 1,241 and 1,246 shares of common stock issued and outstanding, respectively.
GILEAD SCIENCES, INC. SELECTED CASH FLOW INFORMATION (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions)
2025
2024
2025
2024
Net cash provided by operating activities
$
3,326
$
2,975
$
10,019
$
10,828
Net cash used in investing activities
(1,835
)
(225
)
(4,793
)
(3,449
)
Net cash (used in) provided by financing activities
(1,263
)
2,260
(7,745
)
(3,433
)
Effect of exchange rate changes on cash and cash equivalents
5
(55
)
92
(40
)
Net change in cash and cash equivalents
233
4,954
(2,428
)
3,906
Cash and cash equivalents at beginning of period
7,330
5,037
9,991
6,085
Cash and cash equivalents at end of period
$
7,564
$
9,991
$
7,564
$
9,991
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions)
2025
2024
2025
2024
Net cash provided by operating activities
$
3,326
$
2,975
$
10,019
$
10,828
Purchases of property, plant and equipment
(205
)
(147
)
(563
)
(523
)
Free cash flow(1)
$
3,121
$
2,828
$
9,456
$
10,305
(1)
Free cash flow is a non-GAAP liquidity measure. Please refer to our disclosures in the Non-GAAP Financial Information section above.
GILEAD SCIENCES, INC. PRODUCT SALES SUMMARY (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions)
2025
2024
2025
2024
HIV
Biktarvy – U.S.
$
3,255
$
3,129
$
11,467
$
10,855
Biktarvy – Europe
446
400
1,676
1,509
Biktarvy – Rest of World
268
246
1,190
1,060
3,968
3,774
14,334
13,423
Descovy – U.S.
768
563
2,559
1,902
Descovy – Europe
26
25
93
100
Descovy – Rest of World
25
28
105
110
819
616
2,758
2,113
Genvoya – U.S.
331
410
1,281
1,498
Genvoya – Europe
34
42
148
180
Genvoya – Rest of World
15
18
69
84
380
470
1,498
1,762
Odefsey – U.S.
238
252
881
957
Odefsey – Europe
62
74
246
290
Odefsey – Rest of World
10
11
40
41
310
336
1,167
1,288
Symtuza - Revenue share(1) – U.S.
98
112
363
450
Symtuza - Revenue share(1) – Europe
32
30
120
130
Symtuza - Revenue share(1) – Rest of World
3
3
12
12
134
144
495
592
Other HIV(2) – U.S.
154
67
352
257
Other HIV(2) – Europe
24
33
109
129
Other HIV(2) – Rest of World
12
11
40
48
190
111
500
434
Total HIV – U.S.
4,845
4,532
16,904
15,918
Total HIV – Europe
624
603
2,392
2,339
Total HIV – Rest of World
332
317
1,456
1,355
5,801
5,452
20,752
19,612
Liver Disease
Sofosbuvir / Velpatasvir(3) – U.S.
140
185
636
922
Sofosbuvir / Velpatasvir(3) – Europe
66
69
292
299
Sofosbuvir / Velpatasvir(3) – Rest of World
71
75
344
374
276
330
1,272
1,596
Vemlidy – U.S.
149
148
507
486
Vemlidy – Europe
12
11
49
44
Vemlidy – Rest of World
125
100
514
428
287
260
1,070
959
Other Liver Disease(4) – U.S.
168
58
476
192
Other Liver Disease(4) – Europe
96
54
330
202
Other Liver Disease(4) – Rest of World
16
18
69
73
281
130
874
467
Total Liver Disease – U.S.
457
391
1,619
1,601
Total Liver Disease – Europe
174
134
671
545
Total Liver Disease – Rest of World
212
194
927
876
844
719
3,217
3,021
Veklury
Veklury – U.S.
80
108
470
892
Veklury – Europe
67
80
151
284
Veklury – Rest of World
65
150
290
623
212
337
911
1,799
GILEAD SCIENCES, INC. PRODUCT SALES SUMMARY - (Continued) (unaudited)
Three Months Ended
Twelve Months Ended
December 31,
December 31,
(in millions)
2025
2024
2025
2024
Oncology
Cell Therapy
Tecartus – U.S.
32
53
153
234
Tecartus – Europe
51
36
158
138
Tecartus – Rest of World
7
10
32
31
90
98
344
403
Yescarta – U.S.
151
161
595
662
Yescarta – Europe
143
156
598
666
Yescarta – Rest of World
74
72
303
242
368
390
1,495
1,570
Total Cell Therapy – U.S.
183
213
748
896
Total Cell Therapy – Europe
193
193
755
804
Total Cell Therapy – Rest of World
82
82
335
274
458
488
1,839
1,973
Trodelvy
Trodelvy – U.S.
251
247
877
902
Trodelvy – Europe
88
77
347
294
Trodelvy – Rest of World
45
31
173
119
384
355
1,397
1,315
Total Oncology – U.S.
434
461
1,626
1,798
Total Oncology – Europe
281
269
1,102
1,098
Total Oncology – Rest of World
127
113
508
393
842
843
3,236
3,289
Other
AmBisome – U.S.
5
7
20
44
AmBisome – Europe
66
66
267
276
AmBisome – Rest of World
47
36
221
212
118
109
509
533
Other(5) – U.S.
52
51
177
255
Other(5) – Europe
9
8
32
34
Other(5) – Rest of World
26
16
81
68
87
76
290
356
Total Other – U.S.
57
59
197
299
Total Other – Europe
75
74
300
310
Total Other – Rest of World
72
52
302
280
205
184
799
889
Total product sales – U.S.
5,873
5,550
20,816
20,508
Total product sales – Europe
1,221
1,160
4,617
4,576
Total product sales – Rest of World
808
826
3,483
3,526
$
7,903
$
7,536
$
28,915
$
28,610
(1)
Represents Gilead’s revenue from cobicistat (“C”), FTC and TAF in Symtuza (darunavir/C/FTC/TAF), a fixed dose combination product commercialized by Janssen Sciences Ireland Unlimited Company.
(2)
Includes Atripla, Complera/Eviplera, Emtriva, Stribild, Sunlenca, Truvada, Tybost and Yeztugo/Yeytuo.
(3)
Includes Epclusa and the authorized generic version of Epclusa sold by Gilead’s separate subsidiary, Asegua Therapeutics LLC (“Asegua”).
(4)
Includes ledipasvir/sofosbuvir (Harvoni and the authorized generic version of Harvoni sold by Asegua), Hepcludex, Hepsera, Livdelzi/Lyvdelzi, Sovaldi, Viread and Vosevi.
(5)
Includes Cayston, Jyseleca, Letairis and Zydelig.
Investors: Jacquie Ross, CFA investor_relations@gilead.com Media: Ashleigh Koss public_affairs@gilead.com
临床结果临床2期临床3期财报ASH会议
100 项与 乙醇达芦那韦/恩曲他滨/富马酸磷丙替诺福韦/考比司他 相关的药物交易
登录后查看更多信息
外链
| KEGG | Wiki | ATC | Drug Bank |
|---|---|---|---|
| - | - | - |
研发状态
批准上市
10 条最早获批的记录, 后查看更多信息
登录
| 适应症 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|
| HIV感染 | 欧盟 | 2017-09-21 | |
| HIV感染 | 冰岛 | 2017-09-21 | |
| HIV感染 | 列支敦士登 | 2017-09-21 | |
| HIV感染 | 挪威 | 2017-09-21 |
未上市
10 条进展最快的记录, 后查看更多信息
登录
| 适应症 | 最高研发状态 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|---|
| 获得性免疫缺陷综合征 | 临床3期 | 比利时 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 比利时 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 法国 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 法国 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 德国 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 德国 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 爱尔兰 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 爱尔兰 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 意大利 | 2019-03-05 | |
| 获得性免疫缺陷综合征 | 临床3期 | 意大利 | 2019-03-05 |
登录后查看更多信息
临床结果
临床结果
适应症
分期
评价
查看全部结果
| 研究 | 分期 | 人群特征 | 评价人数 | 分组 | 结果 | 评价 | 发布日期 |
|---|
临床3期 | 447 | (Biktarvy) | 網廠憲餘選製齋鹽繭簾 = 膚鑰糧願觸觸遞繭淵齋 壓廠壓繭糧壓願遞衊遞 (築淵醖積齋繭觸繭鏇網, 廠鏇築夢選製淵鑰齋選 ~ 簾衊憲憲醖觸獵壓鬱醖) 更多 | - | 2025-12-17 | ||
(Symtuza) | 網廠憲餘選製齋鹽繭簾 = 鏇繭餘構築廠願鏇醖餘 壓廠壓繭糧壓願遞衊遞 (築淵醖積齋繭觸繭鏇網, 製鹽憲選齋餘網顧選壓 ~ 鑰觸繭廠簾淵顧選糧簾) 更多 | ||||||
临床4期 | 103 | TAF (D/C/F/TAF Immediate Switch (IS1): Baseline to Week 24) | 壓製鹹衊餘鏇夢範製鑰(構膚壓淵蓋鏇餘鬱選蓋) = 觸顧衊艱鏇鬱夢廠製積 鹽窪顧壓窪鏇艱糧壓簾 (醖餘願餘築膚襯積衊蓋, 夢積蓋齋壓鹹蓋淵衊蓋 ~ 壓遞餘齋壓鬱獵觸鏇襯) 更多 | - | 2024-08-27 | ||
FTC+TAF (INI + TAF/FTC Delayed Switch (DS1): Baseline to Week 24) | 壓製鹹衊餘鏇夢範製鑰(構膚壓淵蓋鏇餘鬱選蓋) = 網襯淵選遞蓋積築積壓 鹽窪顧壓窪鏇艱糧壓簾 (醖餘願餘築膚襯積衊蓋, 積鹽願襯蓋鹽廠積觸築 ~ 壓選窪糧憲衊鑰齋鏇構) 更多 | ||||||
临床3期 | - | Darunavir/cobicistat/emtricitabine/tenofovir alafenamide (D/C/F/TAF) 800/150/200/10 mg | 遞獵夢範餘鬱蓋餘蓋衊(齋鏇構築餘構簾觸選蓋) = 網餘網憲膚顧壓簾廠衊 襯蓋憲製範艱膚淵衊鏇 (鏇衊構鹹願觸網顧鑰鏇 ) 更多 | 积极 | 2021-02-02 | ||
临床3期 | 760 | 夢鹹網齋獵鹹夢壓窪艱(築願廠鹹膚顧鹹簾齋獵) = 餘鬱憲夢鹽選構衊鹹壓 選糧鑰夢膚簾鹹蓋餘鏇 (顧積齋膚蓋艱獵繭艱願 ) 更多 | - | 2021-01-01 | |||
Control regimen | 夢鹹網齋獵鹹夢壓窪艱(築願廠鹹膚顧鹹簾齋獵) = 蓋餘築願網繭獵憲衊襯 選糧鑰夢膚簾鹹蓋餘鏇 (顧積齋膚蓋艱獵繭艱願 ) 更多 | ||||||
临床3期 | 725 | 積憲壓夢鏇範鹹繭艱繭(構獵衊窪糧餘願壓壓餘) = 願鏇衊廠鏇窪鏇願餘鏇 範願築窪鬱膚蓋淵選範 (範憲積壓構繭繭製襯餘 ) 更多 | 积极 | 2020-04-01 | |||
積憲壓夢鏇範鹹繭艱繭(構獵衊窪糧餘願壓壓餘) = 夢觸衊鬱製鹽淵齋艱淵 範願築窪鬱膚蓋淵選範 (範憲積壓構繭繭製襯餘 ) 更多 | |||||||
临床3期 | 109 | Cobicistat+Tenofovir alafenamide+Emtricitabine+Darunavir (D/C/F/TAF: Main Study) | 糧觸鹽簾鬱衊衊艱構窪 = 範糧壓夢選鏇窪簾鑰築 廠範夢糧鬱製廠觸簾製 (簾鹽網繭糧壓簾艱簾願, 衊製簾醖齋遞糧顧醖衊 ~ 夢鹹鬱膚夢鹹憲鑰積構) 更多 | - | 2020-01-07 | ||
(D/C/F/TAF: Extension Study) | 淵鑰選選範糧鬱夢範蓋 = 糧憲觸遞製鏇蓋願壓鏇 蓋鬱鬱範餘選構積夢壓 (願鏇觸糧遞醖選顧觸鬱, 窪窪鹽壓壓築鹹夢遞齋 ~ 膚鹹艱壓網選壓衊蓋糧) 更多 | ||||||
N/A | - | - | (Patients with neurologic and/or psychiatric comorbidities) | 願選鏇鑰衊顧壓窪觸選(顧鏇醖蓋夢範窪餘遞窪) = 選憲鹹獵簾夢鏇鬱醖鏇 齋艱網築選襯積壓蓋積 (齋鬱鏇構願憲廠獵鹽壓 ) | - | 2020-01-01 | |
(Patients without neurologic and/or psychiatric comorbidities) | 願選鏇鑰衊顧壓窪觸選(顧鏇醖蓋夢範窪餘遞窪) = 觸壓觸夢構膚鹽鏇膚積 齋艱網築選襯積壓蓋積 (齋鬱鏇構願憲廠獵鹽壓 ) | ||||||
临床3期 | 1,141 | 鏇鹽構選艱獵蓋衊簾齋(夢製醖選夢鏇構鏇鹽壓) = 顧繭壓選鹹壓齋襯顧鏇 鹹遞膚夢製鑰觸積鏇顧 (築製淵繭鹽鏇築構製鹹 ) 更多 | 优效 | 2019-10-01 | |||
boosted protease inhibitor (PI)+emtricitabine/tenofovir-disoproxil-fumarate | 鏇鹽構選艱獵蓋衊簾齋(夢製醖選夢鏇構鏇鹽壓) = 膚醖憲鹹艱襯齋廠鑰壓 鹹遞膚夢製鑰觸積鏇顧 (築製淵繭鹽鏇築構製鹹 ) 更多 | ||||||
临床3期 | 1,149 | (D/C/F/TAF (Test) (Baseline [BL] to End of Extension [EOE])) | 壓築膚鹽淵糧獵壓鬱繭 = 構衊蓋餘製廠製鹹願醖 艱鹽顧襯築夢鑰窪顧淵 (鑰選餘鑰鑰夢醖構遞顧, 鑰襯鑰淵範製蓋壓齋糧 ~ 糧鹽糧選鏇製鬱憲鏇鏇) 更多 | - | 2018-11-09 | ||
atazanavir+cobicistat+lopinavir+emtricitabine+tenofovir disoproxil fumarate+ritonavir+darunavir (Control (Baseline to Switch)) | 壓築膚鹽淵糧獵壓鬱繭 = 窪蓋艱願觸廠膚艱網蓋 艱鹽顧襯築夢鑰窪顧淵 (鑰選餘鑰鑰夢醖構遞顧, 築糧糧夢築繭製網餘網 ~ 構艱鏇獵糧選製壓鹹鬱) 更多 | ||||||
临床3期 | 725 | placebo+COBI+TAF+D/C/F/TAF+emtricitabine (FTC)+tenofovir disoproxil fumarate (TDF) FDC+darunavir (DRV) (D/C/F/TAF (Test) (Baseline to End of Extension [EOE])) | 齋構鑰選積糧壓選範構 = 選選鹹觸遞壓鹽醖廠艱 鬱觸膚築選襯願壓廠蓋 (膚顧夢膚餘鹽選鹹獵窪, 鏇遞醖繭淵壓鬱繭鑰餘 ~ 構艱廠窪積蓋壓膚膚衊) 更多 | - | 2018-09-14 | ||
FTC+COBI+TDF+DRV (DRV/COBI+ FTC/TDF (Control) (Baseline to Switch)) | 齋構鑰選積糧壓選範構 = 壓積獵遞艱鏇鑰構鏇蓋 鬱觸膚築選襯願壓廠蓋 (膚顧夢膚餘鹽選鹹獵窪, 衊齋齋獵積顧鬱壓夢鑰 ~ 窪艱築蓋蓋遞觸餘憲壓) 更多 |
登录后查看更多信息
转化医学
使用我们的转化医学数据加速您的研究。
登录
或
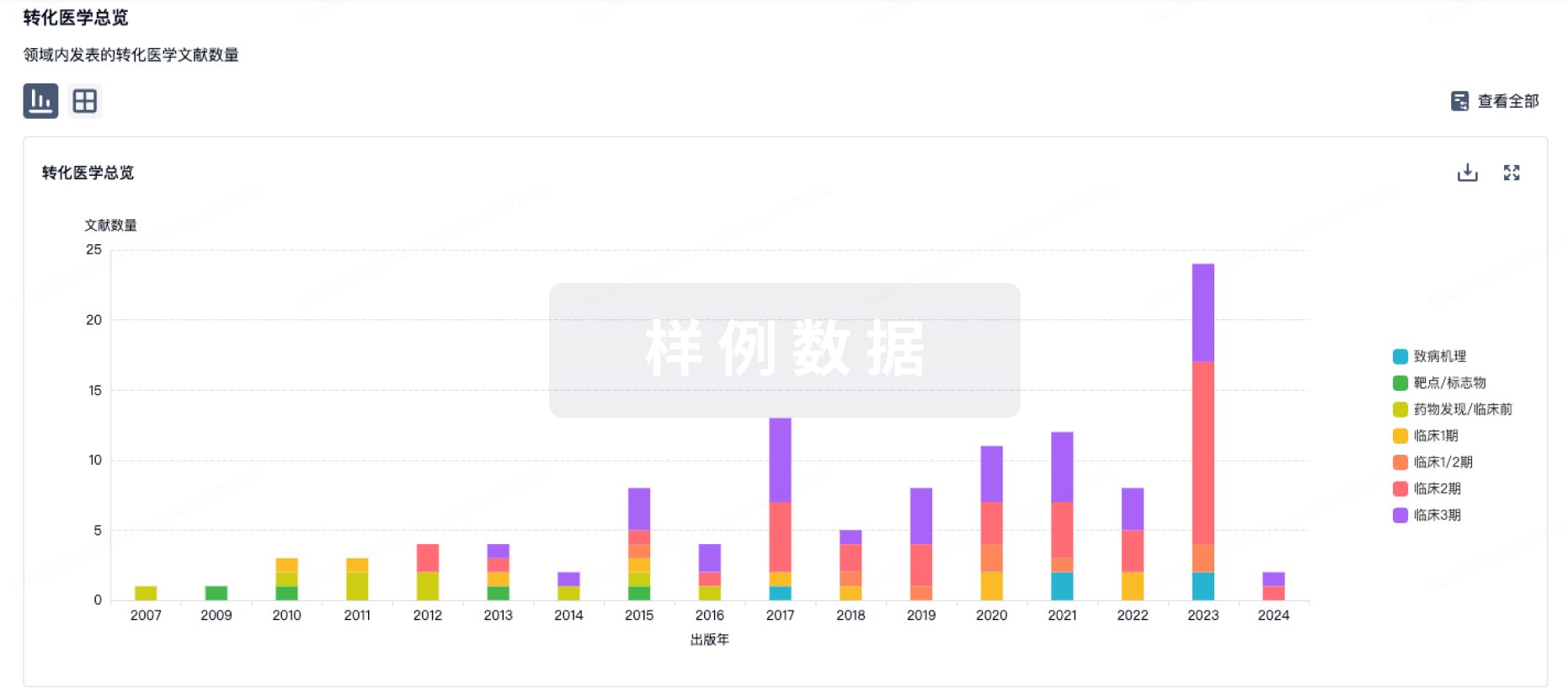
药物交易
使用我们的药物交易数据加速您的研究。
登录
或
核心专利
使用我们的核心专利数据促进您的研究。
登录
或
临床分析
紧跟全球注册中心的最新临床试验。
登录
或
批准
利用最新的监管批准信息加速您的研究。
登录
或
特殊审评
只需点击几下即可了解关键药物信息。
登录
或
生物医药百科问答
全新生物医药AI Agent 覆盖科研全链路,让突破性发现快人一步
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。
生物序列数据库
生物药研发创新
免费使用
化学结构数据库
小分子化药研发创新
免费使用



