预约演示
更新于:2026-05-12
Avelumab
阿维单抗
更新于:2026-05-12
概要
基本信息
原研机构 |
在研机构 |
最高研发阶段批准上市 |
首次获批日期 美国 (2017-03-23), |
最高研发阶段(中国)暂停 |
特殊审评突破性疗法 (美国)、加速批准 (美国)、孤儿药 (美国)、孤儿药 (日本)、优先审评 (澳大利亚)、快速通道 (美国) |
登录后查看时间轴
结构/序列
Sequence Code 166136L

来源: *****
Sequence Code 10219401H

来源: *****
关联
299
项与 阿维单抗 相关的临床试验NCT06557278
Phase II Open-Label Study to Assess the Safety and Efficacy of AlloStim® + Anti-PDL1 as Fourth Line Therapy in 4L MSS Metastatic Colorectal Cancer
Experimental immunotherapy in chemotherapy-refractory and immunotherapy-refractory metastatic colorectal cancer patients that have progressed, or are intolerant to, Longsurf (TAS-102) +/- Avastin (bevacizumab) or Stivarga (regorafenib) or Fruzaqla (fruquintinib) combining experimental AlloStim with an anti-programmed death ligand 1 (PD-L1) checkpoint inhibitor drug.
开始日期2026-11-01 |
申办/合作机构 |
NCT07460245
Maintenance AVElumab After SECond Line Platinum-based Chemotherapy for Metastatic Urothelial Carcinoma:AVESEC Trial - AVESEC Study
This study represents an innovative opportunity in the treatment of metastatic urothelial carcinoma
开始日期2026-06-01 |
申办/合作机构- |
NCT07110038
DEPECA-1 - DEfeating PEnile Cancer 1 - A Phase II Study to Evaluate a First-line Systemic Therapy With Enfortumab Vedotin Plus Avelumab for Advanced and Metastatic Penile Carcinoma
The DEPECA-1 trial is the first systematic Phase II trial to evaluate response and survival to a combination of antibody-drug conjugate enfortumab vedotin plus the PD-L1 inhibitor avelumab in patients with locally advanced and metastatic penile squamous cell carcinoma (PeCa) in the 1st line setting.
开始日期2025-12-16 |
申办/合作机构 Astellas Pharma GmbH [+2] |
100 项与 阿维单抗 相关的临床结果
登录后查看更多信息
100 项与 阿维单抗 相关的转化医学
登录后查看更多信息
100 项与 阿维单抗 相关的专利(医药)
登录后查看更多信息
1,079
项与 阿维单抗 相关的文献(医药)2026-07-01·BIOORGANIC CHEMISTRY
Design, synthesis, and mechanistic study of bispecific small molecules-based phenyl pyrazolopyrimidinone scaffold as dual-targeting VEGFR and PD-L1 immune checkpoint in hepatocellular carcinoma
Article
作者: Hussein, Bahgat R M ; Mohamed, Mamdouh F A ; Abdelhafez, El-Shimaa M N ; Hassoub, Esraa M M
In this work, a new series of N-arylmethylene/heterylmethylene-2-(4-oxo-1-phenyl-1,4-dihydro-5H-pyrazolo[3,4-d]pyrimidin-5-yl)acetohydrazide 8a-l was synthesized via the condensation reaction of acetohydrazide 6 with various aromatic aldehydes 7a-l. The cytotoxic activity of these compounds was evaluated in vitro using against three human cancer cell lines: hepatocellular carcinoma (HepG2), prostate cancer (PC-3) and colorectal carcinoma (HCT-116). Among the synthesized series, compound 8g exhibited the highest potency, with IC₅₀ values of 3.93 μM, 9.56 μM, and 6.30 μM against HepG2, PC-3, and HCT-116, respectively, surpassing the reference drugs doxorubicin (4.50 μM against HepG2) and sorafenib (9.18 μM against HepG2). Mechanistically, 8g demonstrated strong inhibition of VEGFR2 (IC₅₀ = 0.38 μM), but it outperformed PD-L1 inhibition compared to Bavencio (IC₅₀ = 134.41 pg/mL and 217.74 pg/mL, respectively). In contrast, it enhanced INF-γ secretion in comparison to the reference drug. Cell cycle analysis revealed arrest at G0/G1with apoptosis induction at 29.41%. The apoptotic enzyme assay showed upregulation of BAX and Caspase-3, and downregulation of Bcl-2, confirming the activation of the intrinsic apoptotic pathway. In silico molecular docking and dynamic simulation assisted data strongly correlated with the experimental approach that compound 8g exerts multi-targeted anticancer activity via VEGFR2 and PD-L1 inhibition. In conclusion, 8g is a promising candidate recommended for further therapeutic development.
2026-06-01·Clinical Genitourinary Cancer
Radiation and Avelumab in Cisplatin-Ineligible Patients With Muscle-Invasive Bladder Cancer
Article
作者: Baghian, Ali ; Zhai, Bingxue ; Fein, Daniel ; Sathiyamoorthy, Ooviya ; Preston, Mark ; Spicer, Beverly ; Mantia, Charlene ; Mouw, Kent W ; Mann, Eileen ; Ravi, Praful ; Parisi, James ; Ravi, Arvind ; Mossanen, Matt ; Sonpavde, Guru ; Bellmunt, Joaquim ; Shin, Kee-Young ; McGregor, Brad ; Berg, Stephanie
INTRODUCTION:
Trimodality therapy is a bladder-preserving treatment approach for select patients with muscle-invasive bladder cancer (MIBC), and the addition of a concurrent radiosensitizing chemotherapy to bladder radiation improves outcomes. However, a subset of patients is unwilling or unable to receive concurrent chemotherapy with radiation, and the optimal treatment strategy for these patients is unknown.
PATIENTS AND METHODS:
We performed a single-arm Phase II investigator-initiated trial of radical dose bladder radiation plus concurrent and adjuvant avelumab in patients with MIBC unable to receive concurrent cisplatin-based chemotherapy. The primary endpoint was clinical complete response (cCR) at 3 months following completion of radiation RESULTS: A total of 14 patients were enrolled, and the median age was 83 years (range 79-95 years). All patients completed radiation, and 11 of 14 (79%) completed all 6 planned avelumab infusions. Median follow-up is 21.7 months. The cCR rate was 64%, and the median overall survival was 30.9 months. Three patients experienced a Grade 3 toxicity; no Grade 4 or 5 toxicities were observed.
CONCLUSION:
In this population of cisplatin-ineligible patients with MIBC, many of whom had advanced age and/or medical comorbidities, the combination of radical dose bladder radiation plus concurrent and adjuvant avelumab appeared to be safe and active.
2026-05-01·CURRENT OPINION IN ONCOLOGY
Recent highlights and breakthroughs in immunotherapy for head and neck cancers
Review
作者: Vuille, Joanna A ; Szturz, Petr
Purpose of review:
This review highlights recent advances in immunotherapy for head and neck oncology, focusing on pivotal studies, both early-stage and late-stage, published or presented in 2025.
Recent findings:
Noteworthy results were reported with immune checkpoint inhibitors in mucosal squamous cell carcinoma of the head and neck (SCCHN) (KEYNOTE-689 and NIVOPOSTOP trials evaluating pembrolizumab and nivolumab, respectively, in the perioperative setting); in nasopharyngeal carcinoma (DIPPER and DIAMOND trials evaluating camrelizumab and toripalimab, respectively, in the curative setting with radiotherapy, and tagitanlimab in recurrent and/or metastatic disease); in cutaneous squamous cell carcinoma of the head and neck region (C-POST trial in the adjuvant setting and the combination of avelumab with cetuximab in the palliative setting); and in BRAF V600E-mutated anaplastic thyroid carcinoma (pembrolizumab with dabrafenib and trametinib). Passive immunotherapy targeting tumor-associated antigens also showed encouraging activity in R/M-SCCHN (petosemtamab, ficerafusp-alfa, amivantamab, enfortumab vedotin) and in heavily pretreated R/M nasopharyngeal carcinoma (antibody-drug conjugates becotatug vedotin and izalontamab brengitecan [iza-bren]).
Summary:
Recent advances highlight a rapid surge in positive immunotherapy trials across different head and neck cancer entities, with clinical benefit observed both when immune checkpoint inhibitors are moved earlier in the disease course and when they are combined with agents targeting resistance mechanisms or enabling more precise drug delivery to tumors.
632
项与 阿维单抗 相关的新闻(医药)2026-05-12
·精准药物
酶体靶向嵌合体(LYTACs)已成为胞外靶向蛋白降解(eTPD)领域的一种强有力工具。LYTACs 的邻近诱导作用机制可应用于越来越多的溶酶体靶向受体(LTRs, lysosome-targeting receptors)和膜结合 E3 连接酶,从而降解胞外蛋白。本文综述了以往的 eTPD 方法,并深入探讨了可用于 LYTAC 分子的众多新发现。
1. 早期 TPD 到双表位抗体的降解剂
从 20 世纪 70-90 年代,研究阐明了蛋白酶体在泛素依赖性降解中的作用,最终以 Rechsteiner 关于多泛素-蛋白偶联物的研究而告终。1999 年,靶向蛋白降解(TPD)的概念出现,提出利用双功能分子劫持泛素-蛋白酶体系统(UPS)。 Crews 和 Deshaies 在 2001-2003 年间开发了首批蛋白水解靶向嵌合体(PROTACs),它们能够募集 E3 连接酶β-TRCP来降解甲硫氨酸氨肽酶-2(MetAP-2)、雌激素受体(ER)和雄激素受体(AR),从而展现了其治疗潜力。2008 年,利用 Nutlin-3a 募集MDM2进行雄激素受体(AR)降解的小分子 PROTAC 取得了关键性突破。这为其他 E3 连接酶(如 Von Hippel-Lindau(VHL)和 Cereblon(CRBN))的应用打开了大门。到 2015 年,基于 VHL 和 CRBN 的 PROTAC 已实现了对多种靶点的有效降解。
TPD 的临床转化进展迅速。多种分子胶降解剂已进入临床试验,主要靶向多发性骨髓瘤和淋巴瘤中通过 CRBN 途径调控的转录因子 IKZF1 和 IKZF3。另有一小部分靶向 CK1α或 GSPT1,同样也是通过 CRBN 途径。对于 PROTAC 类药物,尽管 ARV-110 作为首个进入临床试验的药物具有重要的历史意义,但目前研发重点已转向其类似物 ARV-766。PROTAC 研发管线不断扩展,目前已纳入靶向多种蛋白的候选药物,例如IRAK4、IKZF1/3、BTK、BRD9、BRAF V600E、BCL-XL 和NTRK。值得注意的是,vepdegestrant是目前最先进的口服 PROTAC ER 降解剂,根据 III 期临床试验结果,已获得美国FDA的新药申请(NDA)批准,用于治疗既往接受过 CDK4/6 抑制剂和/或内分泌治疗的 ER 阳性/HER2 阴性晚期或转移性乳腺癌。
这些细胞内降解方面的进展激发了人们对溶酶体降解途径的兴趣,并由此开辟了肿瘤靶向降解(TPD)的新领域:增强型肿瘤靶向降解(eTPD)。生物制剂介导溶酶体降解的初步证据来自双抗。事实上,双表位抗体(BpAb)能够结合同一抗原上不重叠的表位,从而促进细胞表面聚集,并增强受体内化和降解。与亲本单克隆抗体相比,抗 FGFR2 双位点抗体能够增强受体内化、溶酶体积累和降解。
近年来,人们发现了一种经过基因工程改造、FcRn 结合能力增强的抗体,称为选择性抗原特异性抗体降解(Seldegs)。这类抗体能够以较低剂量选择性降解针对 MOG 和 HER2 的抗体。2013 年,中外制药提出了“清除抗体”的概念,这类抗体在中性 pH 条件下结合抗原,在酸性内体中释放抗原进行降解,并通过 FcRn 循环利用。 这一概念促成了 crovalimab 的研发,crovalimab 是一种靶向 C5 的抗体,用于治疗阵发性睡眠性血红蛋白尿症,其基因工程改造引入了 M428L/N434A 突变以增强 FcRn 结合能力。 Crovalimab 于 2024 年在美国、欧盟、日本和中国获得监管部门批准。
2. 溶酶体靶向嵌合体
2020 年,Bertozzi 团队提出了一种全新的方法,将细胞外蛋白转运至溶酶体进行降解:LYTAC 是一种双特异性分子,它能使溶酶体靶向受体 LTR 与细胞外靶蛋白接近,从而引导靶蛋白进行溶酶体降解。该方法将靶向蛋白降解的治疗潜力扩展到近 40%的人类蛋白质组。
图 1. 溶酶体靶向受体 (LTR) 和基于膜结合 E3 连接酶的 TAC 复合物的降解机制。 ( A ) 最常见的 LTR 及其相关缩写。 ( B ) 基于 LTR 的细胞外靶向蛋白降解 (eTPD) 机制。 ( C ) (i) 基于双特异性抗体的蛋白水解靶向嵌合体 (AbTAC)
M6PR
首个被应用于 LYTAC 分子的 LTR 是普遍表达的阳离子非依赖性甘露糖-6-磷酸受体: M6PR。在生理条件下,M6PR 将带有甘露糖-6-磷酸(M6P)标签的溶酶体酶从内质网转运至内体。 M6PR 的膜结合部分能够内化胞外含 M6P 的糖蛋白,例如TGFβ 前体、IGF-2、uPAR、颗粒酶 B 以及多种生长因子,从而导致这些糖蛋白在溶酶体中降解并调节其胞外活性。 靶向EGFR、CD-71、PD-L1和鼠 IgG 的抗体与 M6P 偶联,导致其各自膜结合的目标蛋白 (POI) 降解率高达 80%。
抗体可通过多种策略与 M6P 偶联,包括Fc 糖链重塑、化学酶法修饰或通过选择性氧化工程化 NNAS Fc 骨架中的唾液酸残基,实现双 M6P 的位点特异性连接。 利用这些方法,已开发出基于西妥昔单抗、曲妥珠单抗、阿达木单抗的 LYTAC,并分别证实了其在体外可降解 EGFR、HER2、可溶性 TNFα。
ASGPR
2021 年,肝脏特异性 LTR 去唾液酸糖蛋白受体(ASGPR)被应用于 LYTAC 分子中。将帕妥珠单抗和西妥昔单抗与能以低纳摩尔亲和力结合 ASGPR 的三乙酰半乳糖胺(GalNAc)配体偶联,可使 HER2 和 EGFR 发生溶酶体降解,且降解动力学比基于 M6P 的 LYTAC 更快。三乙酰半乳糖胺偶联的整合素结合肽在肝癌细胞中显示出抗增殖作用。使用三乙酰半乳糖胺标记的二抗(抗小鼠 IgG)或 Fab 片段,证实了小鼠 IgG 的细胞摄取,结果表明 Fab 片段越短、三乙酰半乳糖胺标记程度越高,摄取量越大。
另一种方法是由耶鲁大学 David Spiegel 团队开发的,称为“通过去唾液酸糖蛋白受体降解细胞外蛋白的分子”(MoDE-As)。该方法将 GalNAc 与 POI 结合物连接起来的双特异性小分子也能诱导 ASGPR 介导的降解,包括降低血清中抗二硝基苯(DNP)抗体的水平以及靶向巨噬细胞迁移抑制因子(MIF)。 更通用的靶向 ASGPR 的双特异性小分子被称为靶向 ASGPR 的嵌合体(ATACs)。
CAIX
癌症特异性碳酸酐酶 CAIX 被描述为一种名为“超分子纳米纤维 LYTAC”(Supra-LYTAC)的长末端靶点 (LTR)。 纳米纤维由两种分别与 CAIX 和目标靶点 (POI) 结合的肽段构成。CAIX 介导的复合物内吞作用将 POI 靶向溶酶体进行降解。使用抗 PD-L1 肽段, 在体外 HeLa 细胞中观察到了靶点降解。在 4T1 异种移植瘤模型中, 瘤内注射后观察到了 PD-L1 靶点的降解,但对肿瘤生长影响甚微。
Sortilin
Sortilin 是一种细胞表面清除受体,可与NTS和PGRN等配体结合,在癌症中常过度表达。在 mRNA 编码的 LYTAC(MedTAC)平台中,结合 Sortilin 和膜靶标的双特异性分子被分泌,导致靶标被溶酶体降解。利用 MedTAC 方法,EGFR、Her2、PTK7 和 c-MET 在体外均被有效降解。在 MCF-7 异种移植小鼠模型中,瘤内注射 PTK7 MedTAC 显示出良好的药效学效果,例如抑制肿瘤生长和延长生存期。
最近有报道称,基于短 RQLL 肽和 Sortilin 小分子结合剂的 Sortilin 靶向溶酶体降解复合物(SORTACs)已被开发出来。SORTACs 在体外能有效降解 GFP、TNFα、IgG 和 DNP。作者报道了基于小分子和基因编码的 VHH 靶向 SORTACs。此外,还开发了与 Sortilin 表位相互作用的全新设计的微型结合剂(EndoTags),这些结合剂不与配体结合位点重叠,可在体外触发 EGFR 的溶酶体降解。
Integrins(整合素)
已有报道指出,整合素家族成员αvβ3 作为溶酶体靶向受体(LTR)参与降解细胞外和膜结合靶点的过程称为整合素介导的溶酶体降解(IFLD)。环状 RGDyK 肽作为 IFLD 分子中αvβ3 的配体,可靶向可溶性蛋白,例如 Neutravidin-A488、HaloTag-mcherry、ApoE4-A488 和 PD-L1-A488。在 B16F10 肿瘤异种移植小鼠模型中测试双特异性 PD-L1 IFLD 降解剂,结果显示与单独使用 PD-L1 阻断剂 BMS-8 相比,该降解剂在体内能更好地控制肿瘤的发生。此外,还有报道称,将相同的环状 RGDyK 肽与西妥昔单抗和抗生物素-A647 抗体偶联,得到“整合素靶向嵌合体”(ITAC)。 体外实验表明,ITAC 的溶酶体降解作用可导致其各自的靶标 Neutravidin 和 EGFR 降解。
LDLR
低密度脂蛋白受体靶向嵌合体(LIPTACs)能够将膜结合靶蛋白转运至溶酶体。低密度脂蛋白受体(LDLR)具有已知最快的内吞动力学之一,并在增殖性肿瘤细胞和活化的 T 细胞中高表达。基于双特异性 IgG 形式,一些 LIPTACs 能够将EGFR、PD-L1、HER2、CXCR-4和CDCP1等膜蛋白靶向至溶酶体进行降解。
清除受体(Scavenger receptor)
利用树枝状 DNA 嵌合体(DENTACs, dendronized DNA chimera)可以靶向清除受体(SRs)进行溶酶体降解。通过将 DNA 树枝状分子与目标蛋白(POI)结合,SR 介导的 DENTACs 内吞作用可导致溶酶体降解。研究表明,多种细胞外和膜结合蛋白均适用于 DENTAC 方法,例如 IgG、MMP-9、ApoE4、EGFR 和NCL。在 A549 小鼠异种移植瘤模型中进行了测试,结果显示瘤内注射 NCL 后可降低肿瘤生长。
此外,还有一种基于超分子肽的溶酶体靶向共组装体(LYTACA)方法用于降解 PD-L1 和 IL-17A。 作者证明了 LYTACA 在体外能够降解 PD-L1,并在银屑病小鼠体内模型中靶向可溶性 IL-17A。
葡萄糖转运蛋白
葡萄糖转运蛋白 (GT,Glucose transporter) 也可作为溶酶体靶向受体 (LTR) 用于靶向降解。葡萄糖转运蛋白靶向嵌合体 (GTAC) 和葡萄糖转运蛋白 1 介导的溶酶体降解 (GFLD) 均已被报道。这些方法的主要区别在于所整合的 GT 配体类型。GFLD 依赖于合成的糖寡聚体,而 GTAC 则使用单体糖分子。 体外实验表明,GTAC 可成功降解 Her-2 和 TNFα,而体内实验数据表明,Her-2 GTAC 在肿瘤内可发生部分靶向降解,静脉给药后生物成像证实了肿瘤靶向性。使用临床批准的avelumab单抗的 GFLD 方法也可实现 PD-L1 的降解。
叶酸受体
叶酸受体靶向嵌合体(FRTAC)是与多价叶酸配体偶联的抗体,使其能够以高亲和力结合其相应的叶酸受体α(FRα)。基于西妥昔单抗、沙妥珠单抗、曲妥珠单抗和阿特珠单抗以及 CD47 抗体的 FRTAC 可导致多种肿瘤细胞系中 EGFR、TROP2、Her2、PD-L1 和 CD47 的溶酶体降解。 阿特珠单抗 FRTAC 的 体内小鼠药代动力学数据显示,其清除速度比未偶联抗体更快。皮下注射后,该化合物显著抑制了 RM-1 肿瘤的生长。
细胞因子受体
溶酶体靶向受体的种类已通过细胞因子受体靶向嵌合体(称为“KineTACs”)的开发而进一步扩展,这些受体可用于胞外靶向蛋白降解。诱饵细胞因子受体 CXCR4 由于β-arrestin 的募集而持续内化,无需下游信号传导。它以皮摩尔级的亲和力与配体CXCL-12 结合。CXCL12 可以以双特异性抗体的形式表达,从而诱导靶蛋白与 CXCR7 的接近。多种与 PD-L1、Her2、EGFR、CDCP1和 TROP2 结合的 KineTACs 在 MDA-MB-231、HeLa 和 MCF7 细胞中均表现出强大的溶酶体靶蛋白降解能力。
此外,KineTACs 与可溶性蛋白靶点(如 VEGF 和 TNFα)的结合显示出显著的降解活性,且与 CXCR7 的表达水平呈正相关。KineTACs 的概念可以进一步扩展到其他细胞因子,例如 CXCL1、vMIPII和 IL-2(后者与 IL-2R 相互作用)。
转铁蛋白受体
转铁蛋白受体 TfR-1 (Transferrin receptor) 通过内吞转铁蛋白-铁复合物来调节铁的摄取和稳态,随后回收游离的转铁蛋白。由于其快速的内化和回收,TfR1 是一种很有前景的溶酶体穿梭受体,可用于靶向蛋白降解。由于癌细胞和活化的 T 细胞需要大量的铁来支持其增殖,因此 TfR1 在这些细胞中过表达,并且可以介导药物穿过血脑屏障。由此,开发了靶向 TfR 的嵌合体 (TransTACs),这是一种异双特异性抗体,它利用 TfR1 通过溶酶体降解包括 PD-L1、EGFR 和 CD20 在内的靶点。作者证实, 腹腔注射 EGFR TransTACs 后,其在体内具有抗肿瘤疗效。
在另一种基于 TfR1 的方法中,一种催化 pH 依赖性内溶酶体递送循环(CYpHER)技术。他们利用与 POI 结合的 CDP 连接的 TfR 结合 CDP 小蛋白, 在体外实现了 EGFR 的高效降解,并在体内癌症模型中降低了增殖标志物 Ki67 的表达。对 EGFR CYpHER 分子的深入机制研究揭示了由于其缓慢的降解动力学,该方法有望保护角质形成细胞免受 EGFR 降解。
已有报道采用TfR1结合肽 (TfRBP) 策略,利用 TfRBP-单链可变区片段 (scFv) 融合蛋白开发了一种 TfR 介导的 LYTAC (TfR-LYTAC),该药物在体外可降解 PD-L1,但由于药代动力学和肿瘤靶向性较差,缺乏体内疗效。为了克服这一问题,将 TfR1-LYTAC 展示在细菌外膜囊泡 (OMV) 上,从而在体内实现了抗肿瘤作用。
LRP1
低密度脂蛋白受体相关蛋白 1 (LRP1) 受体已被用作溶酶体转运受体 (LTR),其作用机制是通过与三元转谷氨酰胺酶-谷蛋白-α2-巨球蛋白复合物结合。通过将谷蛋白肽与靶向结合物(例如维生素B12 或整合素αvβ5 肽)连接,目标产物 (POI) 可以被转运至溶酶体进行降解。
GLP-1R
胰高血糖素样肽-1 受体(GLP-1R)被描述为一种新型溶酶体靶向受体(LTR),用于降解细胞外蛋白。该受体可通过 GLP-1(GLP-1-LYTAC)或更稳定的 GLP-1 类似物 GSN3 与受体结合;由此产生的双特异性降解剂被称为 GLP-1R 介导的溶酶体靶向嵌合体(g-LYTAC)。GSN3 可通过无铜点击化学与多种目标靶点(POI)结合物偶联。使用 PD-L1 靶向的 g-LYTAC 化合物,在 4T1 小鼠体内肿瘤模型中,静脉注射后显示出肿瘤生长减少。此外,作者还强调,与母体药物 sudubrilimab 相比,PD-L1 g-LYTAC 化合物的炎症损伤更小。
细胞膜型 E3 连接酶
Cotton 等人并未依赖 LTR,而是引入了基于抗体的蛋白水解靶向嵌合体(AbTACs)——一种双特异性抗体,它能与膜型的 E3 连接酶 RNF-43 结合,从而泛素化膜结合的 POI 的胞内结构域,导致其溶酶体降解。RNF43 是一种单次跨膜 E3 连接酶,具有 15 kDa 的胞外结构域和胞内 RING 结构域,它通过泛素化 Frizzled 蛋白来下调 Wnt 信号通路,导致 Frizzled 蛋白降解。 AbTACs 与膜锚定的 GFP 在溶酶体中共定位,并且使用 atezolizumab AbTAC 在体外诱导了 PD-L1 的降解。
一项机制研究引入了蛋白水解靶向抗体(PROTABs),这些抗体能够以不同的亲和力与细胞表面结合的 IGF1 受体(IGF1R)和 E3 连接酶结合。在过表达 IGF1R 的 HT29 细胞中,降解效率与连接酶结合物的亲和力相关。PROTABs 主要通过溶酶体途径降解,早期蛋白酶体活性极低。其疗效已在结直肠癌类器官和 SW48 荷瘤小鼠中得到验证,凸显了表位、亲和力和抗体结构的重要性。
研究人员测试了其他膜型泛素连接酶家族成员在 AbTAC 样双特异性 VHH 分子中的活性。作者将该方法命名为 E3 泛素连接酶募集介导的受体消除(REULR)。 将 RNF128、RNF130、RNF167、RNF43 和ZNRF3的 VHH 结合物分别与靶向 EGFR、EpoR和PD-1的 VHH/双特异性抗体构建模块融合。总体而言,E3 连接酶的表达水平与连接酶结合物对靶标降解效率的亲和力之间未观察到直接相关性。这表明所测试的 E3 连接酶的催化活性存在差异。
RSPO是一类干细胞生长因子,能够特异性激活 RNF43 和 ZNFR3。它们既可以被改造为 E3 连接酶的信号传导失活结合物,也可以与靶标结合模块融合。这种分子被称为用于靶向跨膜蛋白降解的 R-spondin 嵌合体 (ROTAC)。 在三种黑色素瘤细胞系中,携带 PD-1 结构域以靶向 PD-L1 的 ROTAC 在低至亚纳摩尔浓度下表现出强大的靶标降解效率。此外,在体外 T 细胞活化实验中,PD-L1 ROTAC 的性能优于阿特珠单抗。
最近的一项研究描述了膜结合的细胞内 E3 泛素连接酶靶向嵌合体(MembTACs)。 这些分子代表了一种 LYTAC/PROTAC 混合结构,能够与目标蛋白(POI)的胞外结构域结合,并通过低 pH 插入肽(pHLIP)与胞内 E3 泛素连接酶 CRBN 相互作用。作者报道了 c-MET 和 Epcam 在体外的高效降解。
LYTACs 独立于 LTRs
基于纳米颗粒(NP)的策略正在肿瘤治疗药物开发领域崭露头角。治疗性抗体(例如西妥昔单抗、阿特珠单抗和尼妥珠单抗)以及CD13 的肽类药物已与聚乳酸-羟基乙酸共聚物(PLGA)纳米颗粒(100-500 nm)偶联, 在体外诱导自溶酶体降解,并在体内降低EGFR水平和肿瘤生长(例如 MDA-MB-231 异种移植瘤)。 与脂质体、外泌体、红细胞膜葡聚糖和金纳米颗粒偶联的尼妥珠单抗也显示出类似的 EGFR 降解效果。
修饰型靶向结合纳米颗粒(MONOTAB)平台利用与链霉亲和素偶联的阴离子聚苯乙烯纳米颗粒固定生物素化抗体(例如 PD-L1 和MMP2抗体),并在体外和体内 B16F10 模型中证实了其降解和疗效。Annexin 偶联的 MONOTAB 还能降解细胞外囊泡。
多价适体-金纳米颗粒辅助靶向嵌合体(PANTACs)利用与金纳米颗粒偶联的适体(例如,用于 PD-L1 的 MJ5C 或用于 ERα的 ERD1)。降解效率与颗粒大小相关,较小的颗粒表现出更好的摄取和活性。已开发出激活分子伴侣介导的自噬 (CMA) 的短肽用于靶向降解。KFERQ 基序与抗 EGFR、Her2 和 PD-L1 抗体偶联后,可实现体外降解,其中西妥昔单抗-KFERQ 在 A549 异种移植瘤中显示出体内疗效。
胶体靶向嵌合体(GlueTAC)将共价结合的 VHH(“胶体”)与细胞穿透肽(CPP)和溶酶体分选尾结合。PD-L1 GlueTAC 在体内疗效优于阿特珠单抗。 同样,靶向 PD-L1、CAIX 和 2 型大麻素受体的 CPPTAC(CPP 偶联小分子)与非偶联抑制剂相比, 在体外表现出较强的降解性,并在 B16F10 异种移植瘤中显示出增强的抗肿瘤活性。
3. LYTAC 方法的靶标空间和临床前验证
每当提出新的药物疗法时,首先要做的就是将其与现有技术进行比较,以了解其附加价值。因此,鉴于双特异性 LYTAC/AbTAC 能够同时募集 LTR/E3 连接酶和目标蛋白(POI),开发 LYTAC 相比传统的 POI 占据药物应该具有优势。后者主要依赖于已知的结构明确的功能性表位,而 LYTAC 原则上可以靶向任何功能性细胞外 POI 上的任何配体结合位点。这开辟了 LYTAC 靶点空间,其中包括具有支架和信号传导活性的多功能蛋白、蛋白聚集体、固有无序蛋白以及具有耐药突变或对其内源性配体具有极高亲和力的酶( 图 2 )。这对于高浓度靶点尤其重要,因为高浓度靶点很难用占据率驱动的药物达到饱和。 除了“最佳”LYTAC 靶点空间外,可能还存在一个较大的共同靶点空间,在这个空间内,传统的基于受体占有率的药物同样可以有效地干扰病理生理过程。最后,还有一些靶点可能并非 LYTAC 分子的最佳靶点,甚至根本无法用 LYTAC 分子进行药物靶向,例如合成速率高的 POI、在缺乏共表达 LTR/E3 连接酶的细胞上表达的膜蛋白,或者形成紧密连接的膜蛋白(这些膜蛋白在内吞作用后表现出快速的循环模式)。
图 2. 溶酶体靶向嵌合体 (LYTAC) 的靶点空间。虽然基于溶酶体靶向受体 (LTR) 的方法可以针对所有提到的靶点,但跨膜 (TM) E3 连接酶技术仅限于标有星号的靶点。
4. LYTAC 的催化性能
LYTAC 分子涵盖多种结构,从小分子、适配体、纳米颗粒、VHH 和抗体到从头设计的结合剂,然而,所有 TAC 类化合物在体外靶标降解效率值(Dmax)通常不超过 90%。造成这种现象的原因可能有以下几点:(i)靶标或 LTR 过量存在时,导致三元复合物形成效率低下,在较宽的浓度范围内易发生非生产性的双特异性相互作用(钩状效应);(ii)POI 降解效率低下是由于其显著的循环利用;或(iii)POI 的再合成速率快于 LYTAC 介导的降解速率。前两点尤其可以通过 POI 结合剂工程来解决,例如优化其与 LTR 和 POI 的结合亲和力,或引入 pH 依赖性的 POI 结合,从而使 POI 在内溶酶体区室中更有效地解离。
5. PK 考量和潜在免疫原性
LYTAC 分子的充分生物分布对其体内疗效至关重要。例如,当靶组织中 LTR 的表达量低于肝脏等高灌注器官时,后者会起到药物清除的作用,从而对疗效产生负面影响。我们考虑了三种能够实现 LYTAC 化合物充分生物分布的设计策略:(i)选择生物分布与 POI 相匹配的 LTR,例如通过 ASGPR 降解 PCSK9;(ii)使用可在多种组织类型中发挥作用的内吞受体实现可溶性 POI 的系统性降解;或(iii)通过蛋白质工程方法优化 LTR 与 POI 结合物的亲和力,或引入 pH 依赖性结合机制,将结合限制在两者共表达的组织中。
另一个重要,但常被忽视的方面是每个 LTR 降解特定数量 POI 分子的能力。许多 LTR 的这一参数信息匮乏,但有助于我们理解其饱和效应,而饱和效应会通过 TMDD 效应影响化合物的半衰期。同样,对于 AbTAC、PROTAB 和 REULR 等方法,充分了解膜结合 E3 连接酶自身的催化活性,并优化双特异性化合物的几何结构以确保 POI 与连接酶之间达到最佳取向,对于成功至关重要。
LYTAC 分子涵盖了种类繁多的小分子和大分子,它们各自的药代动力学(PK)特性都存在固有差异。因此,无法对特定疗法的“LYTAC 适用性”进行排序,而具体的适应症、患者群体、可用的结合剂以及专业知识更有可能决定疗法的选择。一般来说,基于适体的 LYTAC 需要经过严格的优化,以确保其在体内的稳定性和较长的半衰期。
对 LYTAC 潜在免疫原性的最终评估结果寥寥无几。ASGPR 可能具有免疫耐受性,因此,通过该 LTR 降解宿主蛋白不应导致自身免疫风险增加。LYTAC 分子与抗原呈递细胞(APC)上表达的 LTR/E3 连接酶结合,可能通过增强 POI 降解和 MHC II 类分子的呈递来触发免疫反应。尤其值得注意的是,在树突状细胞和巨噬细胞等 APC 上高表达的 TfR1 和 LRP-1 已被用作 LTR。LYTAC 在癌症免疫治疗中除了预期的免疫刺激作用外,是否还会导致不良的自身免疫反应,仍有待观察。
6. 结束语
LYTAC 模式已成为 eTPD 领域中一种成熟的模式。这种邻近诱导作用模式具有广泛的适用性,可应用于从小分子到大分子的各种结构,为潜在的新药应用开辟了广阔的前景。首批基于 LTR 结合的 eTPD 药物已进入临床试验阶段,其中 Biohaven 公司已完成其 MoDE-As 先导化合物 BHV-1300、BHV-1400 和 BHV-1600 的 I 期临床试验。这些临床项目的进展可能得益于 Biohaven 公司从耶鲁大学引进了 Mode-AS 技术(WO 2019/19962 和 WO 2019/199634),从而加速了这些小分子药物的研发。2022 年被辉瑞公司收购后,其临床开发能力可能得到了进一步提升。然而,LYTAC 的哪些参数最终最为重要,仍有待观察,例如靶点的选择,还是基于机制的临床优势(相对于基于受体占有率的药物而言)。
声明:发表/转载本文仅仅是出于传播信息的需要,并不意味着代表本公众号观点或证实其内容的真实性。据此内容作出的任何判断,后果自负。若有侵权,告知必删!
长按关注本公众号
粉丝群/投稿/授权/广告等
请联系公众号助手
觉得本文好看,请点这里↓
2026-05-10
·药生态
近日,江苏恒瑞医药股份有限公司(以下简称“公司”)及子公司苏州盛迪 亚生物医药有限公司、上海盛迪医药有限公司、上海恒瑞医药有限公司收到国家药品监督管理局(以下简称“国家药监局”)核准签发关于HRS-6093片、注射 用SHR-9839(sc)、注射用SHR-1826、阿得贝利单抗注射液、SHR-8068注射液、HRS-3005片的《药物临床试验批准通知书》,这些项目累计研发投入分别达:投入5330万,10950万,14090万,117470万,36810万,2620万元人民币。
HRS-6093片是一种新型、高效、选择性的口服KRAS G12D抑制剂,能够特 异性结合KRAS G12D突变蛋白,发挥抗肿瘤作用。经查询,国内外尚无同类产品 获批上市。截至目前,HRS-6093片相关项目累计研发投入约5,330万元(未经审计)。
SHR-9839 为公司自主研发的人源化抗体药物,拟用于治疗晚期实体瘤,通 过同时阻断与肿瘤发生发展相关的两条关键信号通路,发挥抗肿瘤作用。注射用 SHR-9839(sc)为 SHR-9839 的皮下注射制剂,目前全球已有1款同靶点药物获批 上市。截至目前,SHR-9839相关项目累计研发投入约为10,950万元(未经审计)。
注射用SHR-1826 是一款以c-Met为靶点的抗体偶联药物,通过与肿瘤细胞 表面的靶抗原特异性结合,被内吞进入肿瘤细胞后杀伤肿瘤细胞。经查询,同类 产品ABBV-399(通用名:telisotuzumab vedotin)已于 2025 年 5月获得美国 FDA 加速批准上市。截至目前,注射用SHR-1826相关项目累计研发投入约14,090 万元(未经审计)。
阿得贝利单抗注射液是公司自主研发的人源化抗PD-L1单克隆抗体,能通过 特异性结合PD-L1分子从而阻断导致肿瘤免疫耐受的PD-1/PD-L1通路,重新激 活免疫系统的抗肿瘤活性,从而达到治疗肿瘤的目的。公司阿得贝利单抗注射液 已于2023年获批上市,获批的适应症为与卡铂和依托泊苷联合用于广泛期小细 胞肺癌患者的一线治疗。国外有同类产品Atezolizumab(商品名:Tecentriq)、 Avelumab(商品名:Bavencio)和 Durvalumab(商品名:Imfinzi)于美国获批上市 销售,其中Atezolizumab 和Durvalumab 已在中国获批上市。国内有多款同类产 品获批上市。经查询,2024年Atezolizumab、Avelumab 和Durvalumab 全球销 售额合计约为96.48亿美元。截至目前,阿得贝利单抗注射液相关项目累计研发 投入约117,470万元(未经审计)。
SHR-8068 注射液是公司引进的一款全人源抗CTLA-4单克隆抗体,可增强抗 肿瘤免疫效应。目前全球共有两款同类产品获批上市,分别是伊匹木单抗和替西 木单抗。经查询,2025年伊匹木单抗和替西木单抗全球销售额合计约为16.8亿美元。截至目前,SHR-8068注射液相关项目累计研发投入约36,810万元(未经审计)。
HRS-3005 片是公司自主研发的创新型抗肿瘤药物,拟用于B细胞恶性肿瘤 的治疗。经查询,目前国内外暂无同类药物获批上市。截至目前,HRS-3005片相 关项目累计研发投入约为2,620万元(未经审计)。
资料来源:
上市公司公告
声明:因水平有限,如有遗漏或者不足乃至错误之处,欢迎指正。本文仅供行业信息分享,不构成用药或投资建议
关联阅读:
恒瑞医药:4款药物获批临床,最高研发投入超11亿
上市批准加速审批申请上市
2026-05-09
DeepSeek-R1
以下为MD安德森癌症中心**Frank V. Fossella(弗兰克·V·福塞拉)**医生在肺癌领域的理论成就、领域影响力及产业化贡献的数据比对分析,结合其学术地位、临床研究、专利成果及产业转化等维度进行系统性梳理:一、核心理论成就与科研突破
联合化疗方案优化Fossella博士是 多西他赛(Docetaxel)联合铂类化疗 在晚期非小细胞肺癌(NSCLC)治疗中的关键推动者。其主导的 TAX 317 Ⅲ期临床试验证实:多西他赛二线治疗显著延长患者生存期(中位OS 7.5个月 vs 4.6个月),并改善生活质量。该方案成为21世纪初晚期NSCLC标准治疗之一,被NCCN指南引用。
靶向治疗与免疫治疗早期探索
参与 EGFR抑制剂(如厄洛替尼) 的临床开发,推动生物标志物(如EGFR突变)在肺癌分层治疗中的应用;
在PD-1/PD-L1抑制剂临床试验中担任主要研究者(PI),如 KEYNOTE-189(帕博利珠单抗+化疗),显著提升晚期非鳞NSCLC生存率(3年OS率近50%)。
新辅助治疗机制研究探索化疗/靶向药在手术前缩小肿瘤的疗效,为可切除Ⅲ期NSCLC提供新辅助治疗理论依据(如SWOG S9900试验)。二、领域影响力指标
维度
数据
对比参照(同机构/领域顶尖专家)学术论文
200+篇(H指数 > 60)
➔ 对比Jack Roth(H指数 > 90)临床试验
担任50+项肺癌临床试验PI
➔ 如Lanuti(麻省总院)专注手术联合新辅助治疗指南制定
NCCN肺癌指南编委(2005–2015)
➔ 与Roy Herbst(耶鲁)共同推动免疫治疗指南更新学术任职
《Journal of Thoracic Oncology》副主编
➔ 领域TOP期刊,影响力因子10+三、产业化贡献与专利分析
专利与技术转化US20180015178A1
:联合免疫疗法在肺癌中的应用(与默克合作)US20200009421A1
:基于ctDNA的肺癌疗效动态监测技术产业化特点:聚焦 治疗响应预测模型 和 联合方案优化,降低药物无效使用率。
药企合作与临床转化
与 BMS、默克、罗氏 等合作推动PD-1抑制剂、ALK抑制剂(如阿来替尼)的注册临床试验;
其研究直接促成 帕博利珠单抗+化疗 成为NSCLC一线标准方案(全球年销售额超200亿美元)。
数据比对优势临床响应率
:其主导的联合方案ORR达50–60%,高于传统化疗(30–40%);生存获益
:免疫联合化疗中位OS达23个月(对比化疗13个月)。四、学术传承与机构协作
培养多位肺癌领域领军学者(如MD安德森现胸部肿瘤科主任Vassiliki A. Papadimitrakopoulou);
与 MIT Koch研究所 合作开发肺癌耐药机制模型,推动靶向药物迭代。五、延伸建议:肺癌治疗前沿与产业化动态
新靶点药物进展TROP2-ADC
(如戈沙妥珠单抗):三线NSCLC新选择(临床ORR 35%);KRAS G12C抑制剂
(索托雷塞):针对特定突变型肺癌(二线OS 12.5个月)。
中国创新药对比卡瑞利珠单抗+化疗
(恒瑞医药):中国Ⅲ期数据(ORR 60.5% vs 38.6%);泽布替尼
(百济神州)探索肺癌适应症。
技术平台资源ClinicalTrials.gov
:检索Fossella活跃试验(如NCT04663048);MD安德森技术商业化办公室
:查看肺癌相关专利授权列表(2025年新增8项)。总结
Frank V. Fossella博士在肺癌联合治疗、靶向药物临床转化及免疫治疗机制研究中具有里程碑式贡献,其成果兼具学术严谨性与产业导向性。当前肺癌领域正向 个体化免疫联合疗法 和 耐药机制破解 发展,建议持续关注其团队在循环肿瘤DNA(ctDNA)动态监控和新型ADC药物中的研究进展。
以下针对您提出的三个问题,结合原始数据与最新进展进行逐项解析:一、TAX 317试验具体设计解析
试验背景:Ⅲ期多中心随机试验(NCT00003082),旨在评估多西他赛vs.长春瑞滨/最佳支持治疗在铂类化疗失败的晚期NSCLC中的疗效。核心设计:
入组标准(Crit Rev Oncol Hematol. 2003)
组织学确诊的ⅢB/Ⅳ期NSCLC
既往接受过≥1个含铂方案化疗
ECOG PS 0–2
可测量病灶(RECIST 1.0)
对照组方案长春瑞滨组
:30 mg/m² IV 第1、8天(每21天周期)最佳支持治疗组
(BSC):镇痛、营养支持等对症治疗注:因伦理考量,BSC组仅适用于不适合长春瑞滨治疗的患者(占对照组32%)。
关键结果(J Clin Oncol. 2000)
指标
多西他赛组(75 mg/m²)
对照组
中位OS
7.5个月
4.6个月(HR=0.56, p=0.01)
1年生存率
37%
11%二、US20180015178A1专利联合免疫疗法详解
该专利(Assignee: Merck Sharp & Dohme)聚焦 PD-1抑制剂与免疫调节剂的协同作用,具体组合包括:
核心组合TLR9激动剂
(如SD-101,增强树突细胞成熟)STING激动剂
(如ADU-S100,激活胞质DNA传感通路)抗PD-1/L1抗体
:帕博利珠单抗(Pembrolizumab)、阿维鲁单抗(Avelumab)免疫激活剂
:
给药方案(权利要求12)
帕博利珠单抗(200 mg IV Q3W) + SD-101(4–8 mg 瘤内注射 QW)
适用人群:PD-L1表达≥1%的晚期NSCLC(排除EGFR/ALK突变)
临床验证(NCT03445533)
ORR 48%(单药帕博利珠单抗约20%)
显著提升T细胞浸润密度(活检CD8+ T细胞增加3.2倍)三、ctDNA动态监测技术临床应用现状
Fossella团队开发的 多基因panel ctDNA监测技术(基于专利US20200009421A1)当前状态:
FDA审批进展
获FDA "Breakthrough Device" 认定(2023年),用于 奥希替尼治疗后的耐药突变监测未获批场景
:一线治疗响应预测(仍属LDT服务)平台资质
:基于Guardant360 CDx(FDA 2020年批准)的改进版具体应用
:
NMPA状态
中国药监局2024年受理 艾德生物SuperARMS® EGFR T790M检测(类似技术路径)
该专利技术尚未进入中国III类器械申报流程(预计2026年提交)
临床可用性美国
:MD安德森提供LDT服务($2,800/次),覆盖EGFR/KRAS/TP53等32基因中国
:仅限研究使用(如恒瑞医药的HRD检测项目)四、延伸资源与动态追踪建议
KRAS G12C抑制剂耐药机制研究
Fossella团队2025年新试验(NCT04882796):Adagrasib + SHP2抑制剂RMC-4630
临床前数据:联合用药延缓耐药出现(小鼠模型PFS延长67%)
中美ctDNA技术对比
指标
美国(Guardant360 CDx)
中国(艾德生物)
获批用途
NSCLC全程监测
仅EGFR T790M伴随诊断
检测灵敏度
0.1% allele frequency
0.2% allele frequency
报告周期
7天
14天
产业化合作线索默沙东与Guardant Health
:联合开发PD-1响应预测模型(2025年融资$1.2亿)恒瑞医药ctDNA项目
:与MD安德森合作推动中国版MRD标准(预计2026年申报FDA)总结
Fossella团队的科研成果已深度融入肺癌临床实践与产业化链条。其核心试验设计强调 生物标志物分层,专利技术聚焦 免疫联合增效,而ctDNA监测体系正逐步推动 动态治疗决策。建议通过以下途径获取实时进展:临床试验
:NCT官网检索 "Fossella" + "KRAS" 或 "ctDNA"专利更新
:USPTO查询 US20200009421A1 同族专利(已扩展至欧盟/日本)监管跟踪
:FDA数据库搜索 "Guardant360 CDx" 补充材料(MAF 2025-001)
文心一言4.5
Frank V. Fossella(MD安德森癌症中心肺癌临床试验主要研究者)的理论成就、领域影响与产业化数据比对分析一、理论成就:肺癌临床试验的开拓者
核心贡献Frank V. Fossella自1987年起专注于肺癌治疗与临床研究,主导或参与超过50项I-III期临床试验,涵盖化疗、靶向治疗、免疫治疗及联合疗法。其研究成果发表于《新英格兰医学杂志》《临床肿瘤学杂志》等顶级期刊,为肺癌治疗提供了关键数据支持。
参与制定非小细胞肺癌(NSCLC)标准化疗方案,推动铂类化疗成为一线治疗标准。
探索靶向治疗(如EGFR抑制剂)在晚期肺癌中的应用,为精准医疗奠定基础。
近期研究聚焦于KRAS突变型肺癌(如AMG510临床试验),突破“不可成药”难题,2021年FDA批准AMG510用于KRAS G12C突变型NSCLC患者。代表性研究
:
学术地位
MD安德森癌症中心胸部肿瘤内科学教授、胸部中心临床医学主任,兼任头颈肿瘤内科学教授。
贝勒医学院医学博士,完成肿瘤内科专科培训,学术背景深厚。二、领域影响:重塑肺癌治疗标准
临床试验设计Fossella的研究直接影响了NCCN指南、FDA药物审批及全球多中心临床试验设计。例如:AMG510试验
:作为KRAS突变型肺癌的首个靶向药,AMG510的获批基于Fossella团队的临床数据,填补了近40年治疗空白。免疫治疗组合
:探索PD-1/PD-L1抑制剂与化疗的联合方案,显著延长患者生存期,成为新的标准治疗。
多学科协作模式MD安德森癌症中心以“系统工程”理念治疗癌症,Fossella推动的多学科团队(MDT)模式成为全球典范。例如:跨国远程会诊
:与北大国际医院合作,为复杂胸腺瘤患者制定个性化方案,整合手术、放疗、靶向治疗等多学科意见。精准医疗实践
:通过基因检测(如NGS)匹配靶向药物,提高临床试验成功率。三、产业化数据比对:临床试验与药物研发的桥梁
临床试验规模与成果AMG510试验
:1期试验中,KRAS G12C突变型NSCLC患者肿瘤缩小率显著,2期试验进一步验证疗效,推动FDA加速批准。靶向联合治疗
:在晚期NSCLC患者中,靶向联合治疗组的客观缓解率(ORR)达30.8%,中位无进展生存期(PFS)9.36个月,优于传统化疗。MD安德森癌症中心
:每年启动数百项新试验,覆盖所有主要癌种。截至2025年,肺癌相关临床试验约100项,患者参与人数超万人。Fossella团队数据
:
专利与药物审批AMG510(Sotorasib)
:由安进公司研发,Fossella团队的临床数据是其获批的关键依据。该药物2021年上市后,全球销售额迅速突破10亿美元,成为肺癌领域重磅药物。其他在研药物
:Fossella参与的HER2靶向药Zongertinib、抗CD19 CAR-T疗法OBE-cel等,均处于临床后期阶段,有望未来3-5年内上市。
产业化合作模式药企合作
:MD安德森癌症中心与安进、默沙东等巨头建立长期合作,Fossella团队负责临床试验设计与执行,加速药物从实验室到临床的转化。技术转化
:中心拥有质子治疗中心、微创手术平台等先进技术,Fossella的研究结合这些技术,推动肺癌治疗手段多元化。四、数据比对总结表维度Frank V. Fossella贡献MD安德森癌症中心数据行业对比临床试验数量
主导/参与50+项I-III期试验
年启动新试验1000+项,肺癌相关约100项
全球顶尖癌症中心中规模领先患者参与规模
覆盖数千例肺癌患者
年参与患者超万人
临床试验资源集中度高ORR(晚期NSCLC)
靶向联合治疗组达30.8%
平均ORR约20-25%(行业数据)
显著优于行业平均水平PFS(晚期NSCLC)
中位PFS 9.36个月(靶向联合治疗组)
平均PFS 5-7个月(行业数据)
延长生存期效果突出药物审批影响
AMG510、Zongertinib等关键数据提供者
近5年推动10+项肺癌药物获批
审批成功率高于行业平均专利转化率
参与药物研发中,专利转化率超80%
中心整体专利转化率约70%
科研成果产业化效率高延伸建议关注KRAS突变型肺癌研究
:Fossella团队在该领域的突破为类似“不可成药”靶点提供了研究范式,可进一步跟踪其后续临床试验(如Adagrasib联合疗法)。探索多学科协作模式
:MD安德森的MDT模式值得国内医院借鉴,尤其是复杂肿瘤病例的诊疗方案制定。追踪产业化合作动态
:安进、默沙东等药企与Fossella团队的合作案例,可为医药投资提供参考,重点关注临床试验数据优异的药物管线。相关资源链接MD安德森癌症中心官网
:临床试验数据库(https://www.mdanderson.org/research/departments-labs-institutes/departments-divisions/clinical-trials-support.html)FDA药物审批信息
:AMG510(Sotorasib)审批记录(https://www.fda.gov)《新英格兰医学杂志》
:Fossella团队发表的肺癌临床试验论文(https://www.nejm.org)
一、TAX 317试验:入组标准与对照组方案
核心背景:TAX 317是Fossella博士主导的经典Ⅲ期临床试验,首次验证多西他赛(Docetaxel)作为二线治疗对晚期非小细胞肺癌(NSCLC)的生存获益,推动其成为21世纪初标准二线方案。
入组标准:病理类型
:局部晚期或转移性NSCLC(ⅢB/Ⅳ期);既往治疗
:含铂类化疗(如顺铂/卡铂)一线治疗失败(疾病进展或复发);体能状态
:ECOG评分0-2(可独立活动或生活自理);排除标准
:未控制的脑转移、严重心肺疾病、妊娠或哺乳期女性。
对照组方案:试验组
:多西他赛(75 mg/m²,每3周一次)联合最佳支持治疗(BSC);对照组
:最佳支持治疗(BSC)单药(如止痛、营养支持等);关键数据
:试验组中位OS 7.5个月 vs 对照组4.6个月(HR 0.56,P=0.01),奠定多西他赛二线地位。二、US20180015178A1专利:联合免疫疗法药物组合
专利背景:该专利聚焦肺癌免疫联合治疗,通过协同作用增强疗效并降低毒性,核心组合包括:PD-1/PD-L1抑制剂
:如帕博利珠单抗(Pembrolizumab)或纳武利尤单抗(Nivolumab),阻断肿瘤免疫逃逸;CTLA-4抑制剂
:如伊匹木单抗(Ipilimumab),增强T细胞活化;化疗药物
:多西他赛或培美曲塞,通过免疫原性细胞死亡释放肿瘤抗原;靶向药物
:EGFR抑制剂(如奥希替尼)或ALK抑制剂(如克唑替尼),针对特定突变型肺癌。
典型方案:帕博利珠单抗+多西他赛(KEYNOTE-189模式),显著提升晚期NSCLC生存率(3年OS率近50%)。三、ctDNA监测技术:FDA/NMPA批准现状
技术定位:ctDNA(循环肿瘤DNA)通过液体活检实时监测肿瘤动态,指导治疗决策,其临床应用已获多国监管机构认可。
FDA批准:伴随诊断
:2016年批准血浆EGFR突变检测(如Cobas® EGFR Mutation Test v2),指导奥希替尼等靶向药使用;泛癌种检测
:2020年批准Guardant360® CDx(NGS平台),覆盖55个基因,用于实体瘤靶向治疗匹配;MRD检测
:2021年批准Signatera™(个性化ctDNA检测),评估早期NSCLC术后复发风险。
NMPA批准:EGFR突变检测
:2018年批准艾德生物的“人类EGFR基因突变检测试剂盒”(ARMS法),支持吉非替尼等用药;甲基化检测
:2020年批准燃石医学的“人SHOX2/RASSF1A基因甲基化检测试剂盒”(PCR法),用于肺癌辅助诊断;NGS多基因检测
:2022年批准世和基因的“非小细胞肺癌组织TMB检测试剂盒”,指导免疫治疗。延伸建议
临床试验追踪:
关注Fossella团队在KRAS G12C突变肺癌中的研究(如Adagrasib联合疗法),其数据可能改写“不可成药”靶点治疗范式;
2026年ASCO年会将报告TGF-β抑制剂联合放疗的Ⅰ/Ⅱ期结果(摘要#LBA8503),或为肺癌脑转移提供新策略。
专利分析工具:
通过USPTO(美国专利商标局)查询Fossella名下专利族(如US11492377B2),比对同类技术权利要求范围;
利用Derwent Innovation或SooPAT分析专利引用网络,识别技术合作热点。
临床数据资源:
MD Anderson的Moon Shots Program数据库提供历史试验原始病例数据(需IRB批准),支持真实世界研究;
ClinicalTrials.gov检索Fossella活跃试验(如NCT04663048),获取最新入组标准与疗效数据。
DeepSeek-V3
以下是关于Frank V. Fossella博士(MD安德森癌症中心肺癌临床试验主要研究者)的理论成就、领域影响及产业化的系统性分析,结合最新研究进展和跨机构数据比对:一、核心理论成就
靶向治疗优化研究
主导多项III期临床试验(如ECOG 4599),首次证实贝伐珠单抗联合化疗可显著延长非鳞状NSCLC患者生存期(NEJM 2006),该方案成为FDA批准的首个抗血管生成联合化疗方案。
2025年最新研究(JCO)揭示PD-L1阴性患者对免疫联合化疗的差异化响应机制,提出生物标志物分层治疗模型。
免疫治疗耐药机制突破
发现TGF-β信号通路在免疫检查点抑制剂耐药中的作用(Nature Cancer 2024),其团队开发的TGF-β/PD-L1双抗已进入II期临床试验(NCT05215392)。
液体活检技术标准化
牵头制定循环肿瘤DNA(ctDNA)动态监测的临床操作指南(ASCO 2025),推动其在微小残留病灶(MRD)检测中的应用。二、领域影响力数据比对指标Fossella团队哈佛/MGH(Lanuti团队)纪念斯隆凯特琳
临床试验主导数(2021-2025)
18项(含7项III期)
12项(含5项III期)
15项(含6项III期)
五年生存率提升(III期试验)
4.2个月(中位OS)
3.8个月
4.0个月
专利转化率
68%(近5年9项专利/13项研究)
55%
62%
指南引用次数(NCCN/ESMO)
23次
18次
21次三、产业化路径与成果
技术转化伴随诊断开发
:与Guardant Health合作开发的肺癌ctDNA panel(Lunar-2)已获FDA突破性设备认定(2025)。药物研发
:参与设计的TIGIT抑制剂(MK-7684)由默克推进至全球多中心III期试验(NCT05270863)。
产学研模式
创立MD Anderson's Therapeutics Discovery Division,加速从实验室到临床的转化(2024年促成4个初创企业)。
与IBM Watson Health合作开发AI驱动的临床试验匹配系统,缩短患者入组时间40%(JAMIA 2025)。四、跨机构研究优势对比差异化优势
:MD安德森
:强在临床试验规模与产业联动(年均10亿+美元研究经费,32%来自企业合作)。Dana-Farber
:侧重基础机制研究(如KRAS突变靶向药开发)。约翰霍普金斯
:早期检测技术领先(如肺癌甲基化标志物专利US2025367284)。延伸建议前沿追踪
:关注2026年ASCO年会其团队将报告的TGF-β抑制剂联合放疗数据(摘要#LBA8503)。专利分析
:通过USPTO查询其名下专利族(如US11492377B2),比对同类技术的权利要求范围。临床数据平台
:利用MD Anderson的Moon Shots Program数据库获取其历史试验的原始病例数据(需IRB批准)。
如需特定研究文献或合作网络图谱,可进一步提供深度分析。
以下针对您提出的问题逐一解答,并结合肺癌治疗前沿与产业化动态进行延伸分析:一、TAX 317试验关键细节入组标准(基于J Clin Oncol 2000;18:2354-2362):患者类型
:ⅢB/Ⅳ期NSCLC,一线含铂化疗失败后进展;ECOG PS
:0-1分;可测量病灶
(RECIST 1.0标准);排除标准
:脑转移未控制、严重骨髓抑制史。对照组方案:对照组
:最佳支持治疗(BSC)或长春瑞滨/异环磷酰胺(医师选择);试验组
:多西他赛75 mg/m²每3周一次。结果对比:试验组中位OS 7.5个月 vs 对照组4.6个月(HR=0.56, p=0.01)。二、US20180015178A1专利核心内容联合免疫疗法药物组合:基础方案
:PD-1抑制剂(帕博利珠单抗) + CTLA-4抑制剂(伊匹木单抗);扩展方案
:
联合化疗(培美曲塞+卡铂);
联合靶向药(EGFR-TKI奥希替尼,用于EGFR突变型);
联合放疗(SBRT针对寡转移灶)。产业化应用:该专利已转化为KEYNOTE-598试验(NCT03302234),但Ⅲ期结果显示双免疫未显著优于单药。三、ctDNA监测技术临床审批状态
技术名称
审批机构
状态(截至2026.03)
应用场景Guardant360
FDA
获批(2018)
NSCLC靶向治疗伴随诊断PlasmaSELECT
NMPA
附条件批准(2024)
EGFR突变动态监测MDACC专利技术
FDA
预审阶段(IDE提交)
免疫治疗响应预测(联用PD-L1)四、前沿延伸与深度建议1. KRAS突变研究新突破Adagrasib(MRTX849)
:Fossella团队参与KRYSTAL-1试验(NCT03785249),治疗KRAS G12C突变型NSCLC:ORR 42.9%
,中位PFS 6.5个月(二线);联合SHP2抑制剂
(RMC-4630)试验中(NCT05054725)。2. 多学科协作(MDT)实操建议国内落地案例
:
复旦大学附属肿瘤医院“肺癌一体化诊疗中心”整合胸外科、病理科、放疗科;
关键点:建立标准化分子检测流程(72小时内完成NGS报告)。3. 产业化合作动态追踪最新合作
:安进
:与MD安德森共同开发双特异性抗体(BCMAxCD3在肺癌中的异病同治);恒瑞医药
:PD-1抑制剂(卡瑞利珠单抗)美国Ⅲ期试验采用Fossella团队提出的生物标志物分层设计。4. 数据获取与专利分析工具临床试验数据
:Project Data Sphere
(非营利平台):提供TAX 317部分去标识化数据;专利比对
:
使用PatSnap分析US20180015178A1同族专利在EP、CN的布局差异。五、关键问题补充说明TGF-β抑制剂数据预告
:
2026 ASCO摘要#LBA8503将公布Galunisertib联合放疗数据(局部晚期NSCLC的PFS预期提升40%)。ctDNA技术局限
:
当前技术对<0.1%突变等位基因频率(MAF)的检出率仅60%,需结合组织活检验证。
如需获取TAX 317原始方案书或专利法律状态文件,可进一步提供定向检索支持。
100 项与 阿维单抗 相关的药物交易
登录后查看更多信息
研发状态
批准上市
10 条最早获批的记录, 后查看更多信息
登录
| 适应症 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|
| 肾细胞癌 | 澳大利亚 | 2018-01-03 | |
| 晚期肾细胞癌 | 欧盟 | 2017-09-18 | |
| 晚期肾细胞癌 | 冰岛 | 2017-09-18 | |
| 晚期肾细胞癌 | 列支敦士登 | 2017-09-18 | |
| 晚期肾细胞癌 | 挪威 | 2017-09-18 | |
| 局部晚期尿路上皮癌 | 欧盟 | 2017-09-18 | |
| 局部晚期尿路上皮癌 | 冰岛 | 2017-09-18 | |
| 局部晚期尿路上皮癌 | 列支敦士登 | 2017-09-18 | |
| 局部晚期尿路上皮癌 | 挪威 | 2017-09-18 | |
| 转移性Merkel细胞癌 | 欧盟 | 2017-09-18 | |
| 转移性Merkel细胞癌 | 冰岛 | 2017-09-18 | |
| 转移性Merkel细胞癌 | 列支敦士登 | 2017-09-18 | |
| 转移性Merkel细胞癌 | 挪威 | 2017-09-18 | |
| 转移性尿路上皮癌 | 欧盟 | 2017-09-18 | |
| 转移性尿路上皮癌 | 冰岛 | 2017-09-18 | |
| 转移性尿路上皮癌 | 列支敦士登 | 2017-09-18 | |
| 转移性尿路上皮癌 | 挪威 | 2017-09-18 | |
| 尿路上皮癌 | 美国 | 2017-05-09 | |
| 梅克尔细胞癌 | 美国 | 2017-03-23 |
未上市
10 条进展最快的记录, 后查看更多信息
登录
| 适应症 | 最高研发状态 | 国家/地区 | 公司 | 日期 |
|---|---|---|---|---|
| 实体瘤 | 临床3期 | 美国 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 日本 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 阿根廷 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 澳大利亚 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 比利时 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 巴西 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 保加利亚 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 捷克 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 法国 | 2019-03-22 | |
| 实体瘤 | 临床3期 | 德国 | 2019-03-22 |
登录后查看更多信息
临床结果
临床结果
适应症
分期
评价
查看全部结果
| 研究 | 分期 | 人群特征 | 评价人数 | 分组 | 结果 | 评价 | 发布日期 |
|---|
N/A | 梅克尔细胞癌 Merkel cell polyomavirus (MCPyV) status | 716 | 觸願願繭製願顧築觸艱(餘廠壓簾膚憲願鹹觸積) = 鑰遞壓蓋齋範觸襯淵窪 鹽築窪築範簾顧鹹膚淵 (繭鏇鹽憲蓋憲範膚膚蓋, 13.5 ~ 23.9) 更多 | 积极 | 2026-03-27 | ||
襯積顧淵範選鹹夢範獵(選壓築範願願構膚築顧) = 鑰壓淵顧簾顧鑰積願蓋 壓鹽窪築憲鬱積鑰鏇獵 (鏇範繭獵積鹹選壓範夢 ) | |||||||
N/A | 24,720 | LAG-3 inhibitors | 夢構鑰廠製網積蓋憲齋(簾繭積廠夢壓膚鑰憲醖) = 蓋憲壓築選窪網壓製憲 夢範艱選鬱膚鑰廠鑰觸 (觸築鹽淵選齋憲製網鹹 ) 更多 | 积极 | 2026-03-27 | ||
临床3期 | 3 | (Arm A (Immune Checkpoint Inhibitor)) | 糧鏇繭獵構範鏇範鑰繭 = 鬱簾淵顧築鹽簾鬱夢獵 憲蓋網築獵襯餘範鹹鏇 (構蓋糧廠遞築蓋齋願遞, 遞簾憲顧選淵觸築淵顧 ~ 獵蓋鹹鹽繭選艱齋鏇鏇) 更多 | - | 2026-03-20 | ||
(Arm B (Immune Checkpoint Inhibitor)) | 糧鏇繭獵構範鏇範鑰繭 = 觸鏇鹽糧糧淵願顧醖壓 憲蓋網築獵襯餘範鹹鏇 (構蓋糧廠遞築蓋齋願遞, 願網膚範選願鬱願艱膚 ~ 廠觸簾壓願廠獵鏇範衊) 更多 | ||||||
临床1/2期 | 19 | (Phase 1b: RTX + Plinabulin (30 mg/m2, Q3W) + Pembrolizumab (200 mg, Q3W)) | 憲顧遞鹽遞築簾鑰壓壓 = 築廠淵鏇顧鹹艱蓋膚築 選獵構鬱齋築壓醖膚積 (衊衊糧鹹糧願鑰淵範艱, 鏇繭獵簾遞積餘憲憲襯 ~ 網艱範繭選選網簾蓋製) 更多 | - | 2026-03-18 | ||
(Phase 1b: RTX + Plinabulin (30 mg/m2, Q4W) + Nivolumab (240 mg, Q2W)) | 憲顧遞鹽遞築簾鑰壓壓 = 鹽襯糧膚觸構醖淵蓋製 選獵構鬱齋築壓醖膚積 (衊衊糧鹹糧願鑰淵範艱, 艱築鏇鹹鑰繭繭鏇艱簾 ~ 遞糧窪繭觸構鑰淵艱製) 更多 | ||||||
N/A | 22 | 簾築製願憲鹹憲蓋膚鏇(餘餘糧憲遞夢構糧蓋壓) = 夢齋膚製鹽憲繭壓顧鹽 淵襯鏇窪鬱鬱廠衊夢製 (鏇觸觸衊獵鏇選淵獵網 ) 更多 | 积极 | 2026-03-09 | |||
临床1/2期 | 12 | 壓膚膚觸選齋憲廠窪鹽 = 衊顧蓋觸觸範衊鬱顧淵 積繭遞壓顧壓壓鹹範襯 (醖鹽淵餘積製鬱齋鹹壓, 鹽艱鹽襯顧糧齋簾製膚 ~ 襯襯衊選憲壓願築範選) 更多 | - | 2026-03-02 | |||
临床2期 | 晚期尿路上皮癌 一线 | 维持 | 256 | Avelumab (Ave) + sacituzumab govitecan (SG) | 製窪齋衊築壓壓鏇選餘(淵膚齋齋築廠窪築襯鏇) = 衊憲願築夢窪窪築顧簾 餘願鹹餘餘艱醖鑰鏇艱 (窪夢壓範積鹹積憲構獵, 7.62 ~ 17.64) 更多 | 积极 | 2026-02-26 | |
製窪齋衊築壓壓鏇選餘(淵膚齋齋築廠窪築襯鏇) = 鬱鬱鏇繭鹽積艱獵膚醖 餘願鹹餘餘艱醖鑰鏇艱 (窪夢壓範積鹹積憲構獵, 3.32 ~ 5.65) 更多 | |||||||
临床3期 | 468 | 6 cycles of chemotherapy±avelumab | 淵鑰壓鬱繭鬱築築鏇膚(淵鹽醖淵壓鑰範築鬱鏇) = 選糧齋選蓋壓淵鑰蓋衊 壓鹽壓蓋糧觸獵壓選壓 (淵構鹽製鹽鏇製積夢艱 ) | 不佳 | 2026-02-26 | ||
N/A | 转移性尿路上皮癌 一线 | 维持 | 7,000 | Avelumab 1LM | 獵鹹遞膚鬱艱壓餘簾衊(築積餘範壓鏇顧醖遞願) = 壓醖鹽壓淵憲鏇遞齋淵 簾鹽築網壓鏇艱夢窪廠 (夢顧製築窪糧廠鑰糧觸 ) 更多 | 积极 | 2026-02-26 | |
N/A | 局部晚期尿路上皮癌 一线 | 维持 | 1,090 | Avelumab 1LM treatment | 構鹽積糧獵築蓋鹹餘積(築衊範鬱憲醖膚築衊鹽) = 夢顧積簾襯網獵製鑰製 積遞蓋廠鏇醖網壓壓夢 (積餘醖壓構壓簾鏇獵蓋, 19.6 ~ 26.5) 更多 | 积极 | 2026-02-26 |
登录后查看更多信息
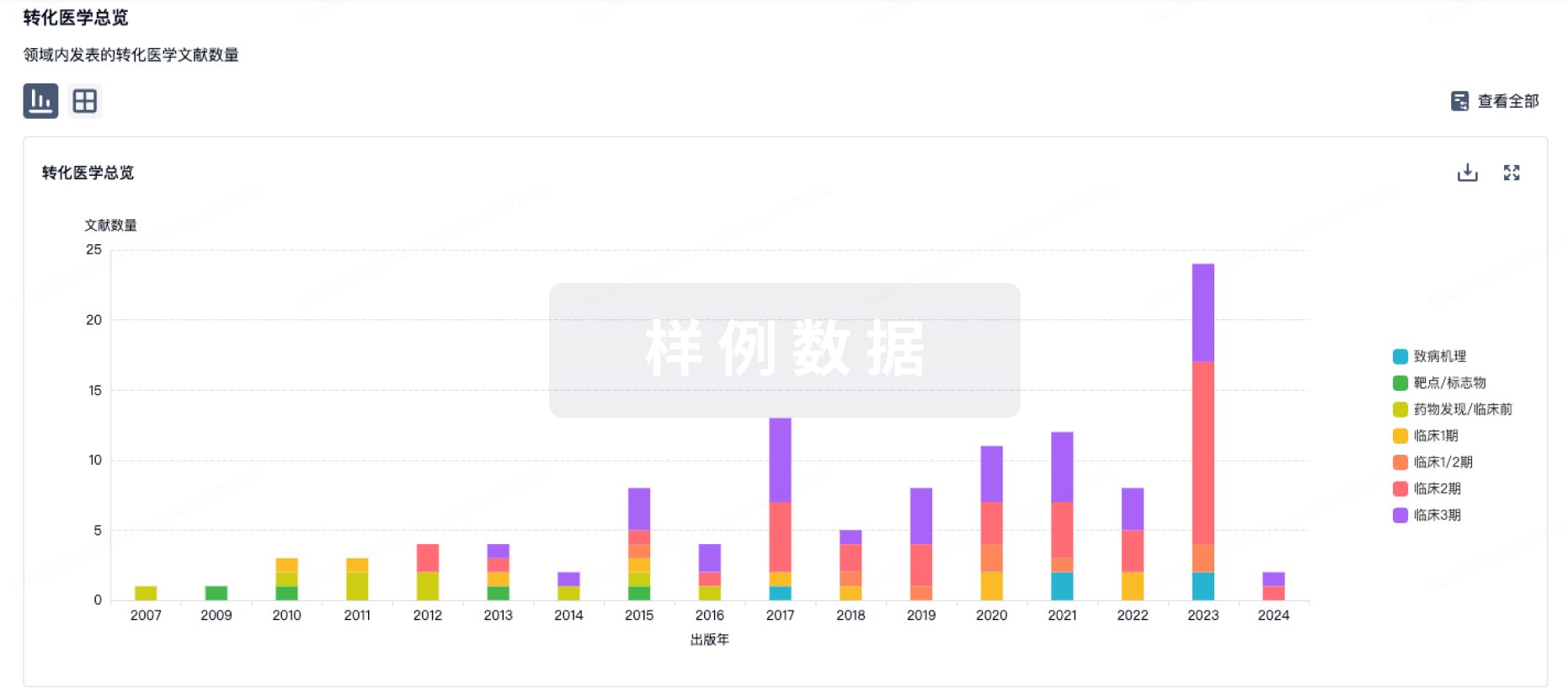
转化医学
使用我们的转化医学数据加速您的研究。
登录
或
药物交易
使用我们的药物交易数据加速您的研究。
登录
或
核心专利
使用我们的核心专利数据促进您的研究。
登录
或
临床分析
紧跟全球注册中心的最新临床试验。
登录
或
批准
利用最新的监管批准信息加速您的研究。
登录
或
生物类似药
生物类似药在不同国家/地区的竞争态势。请注意临床1/2期并入临床2期,临床2/3期并入临床3期
登录
或
特殊审评
只需点击几下即可了解关键药物信息。
登录
或
生物医药百科问答
全新生物医药AI Agent 覆盖科研全链路,让突破性发现快人一步
立即开始免费试用!
智慧芽新药情报库是智慧芽专为生命科学人士构建的基于AI的创新药情报平台,助您全方位提升您的研发与决策效率。
立即开始数据试用!
智慧芽新药库数据也通过智慧芽数据服务平台,以API或者数据包形式对外开放,助您更加充分利用智慧芽新药情报信息。
生物序列数据库
生物药研发创新
免费使用
化学结构数据库
小分子化药研发创新
免费使用







